peptides
spectra
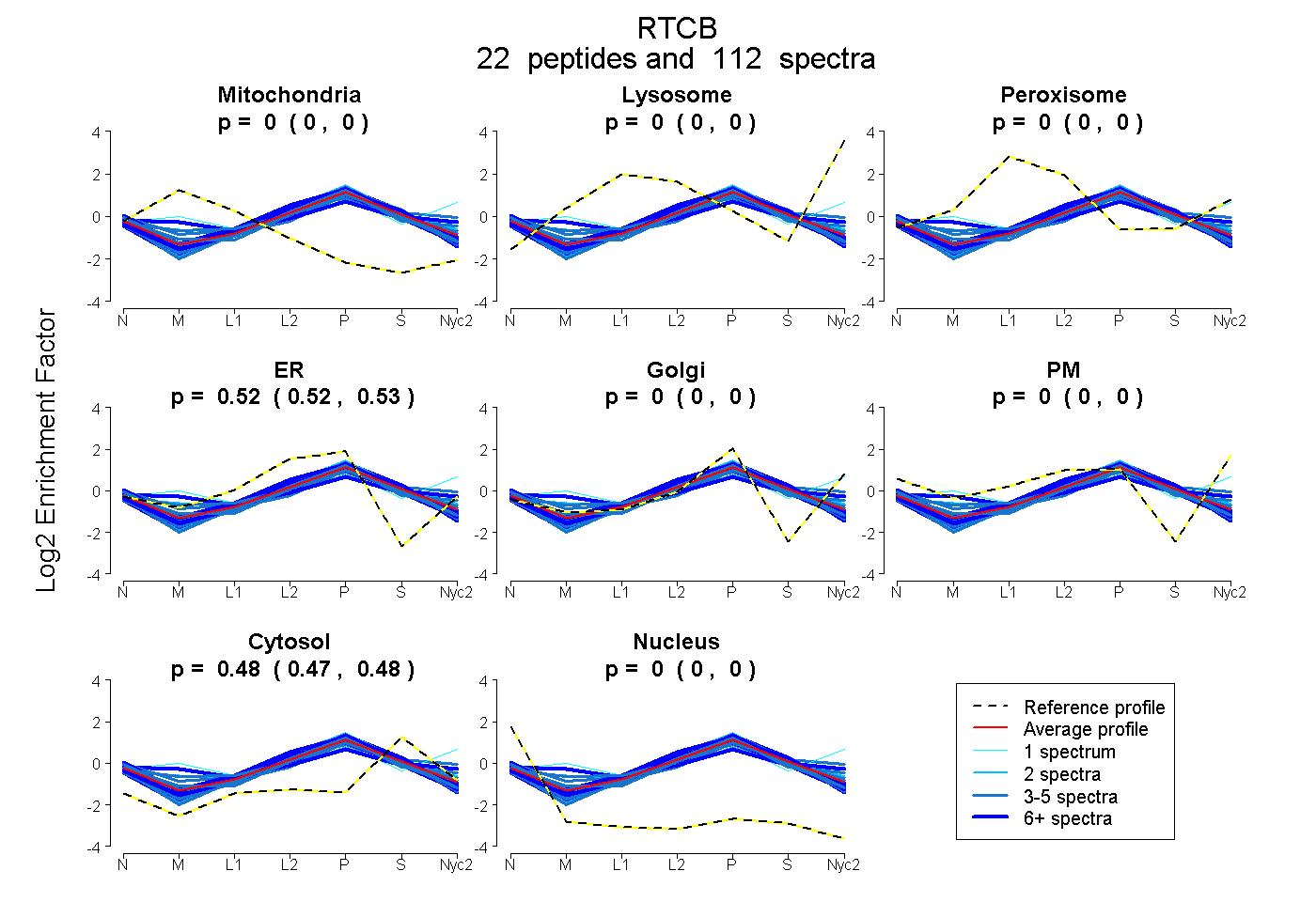
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.523 | 0.526
0.000 | 0.000
0.000 | 0.000
0.474 | 0.477
0.000 | 0.000
peptides
spectra
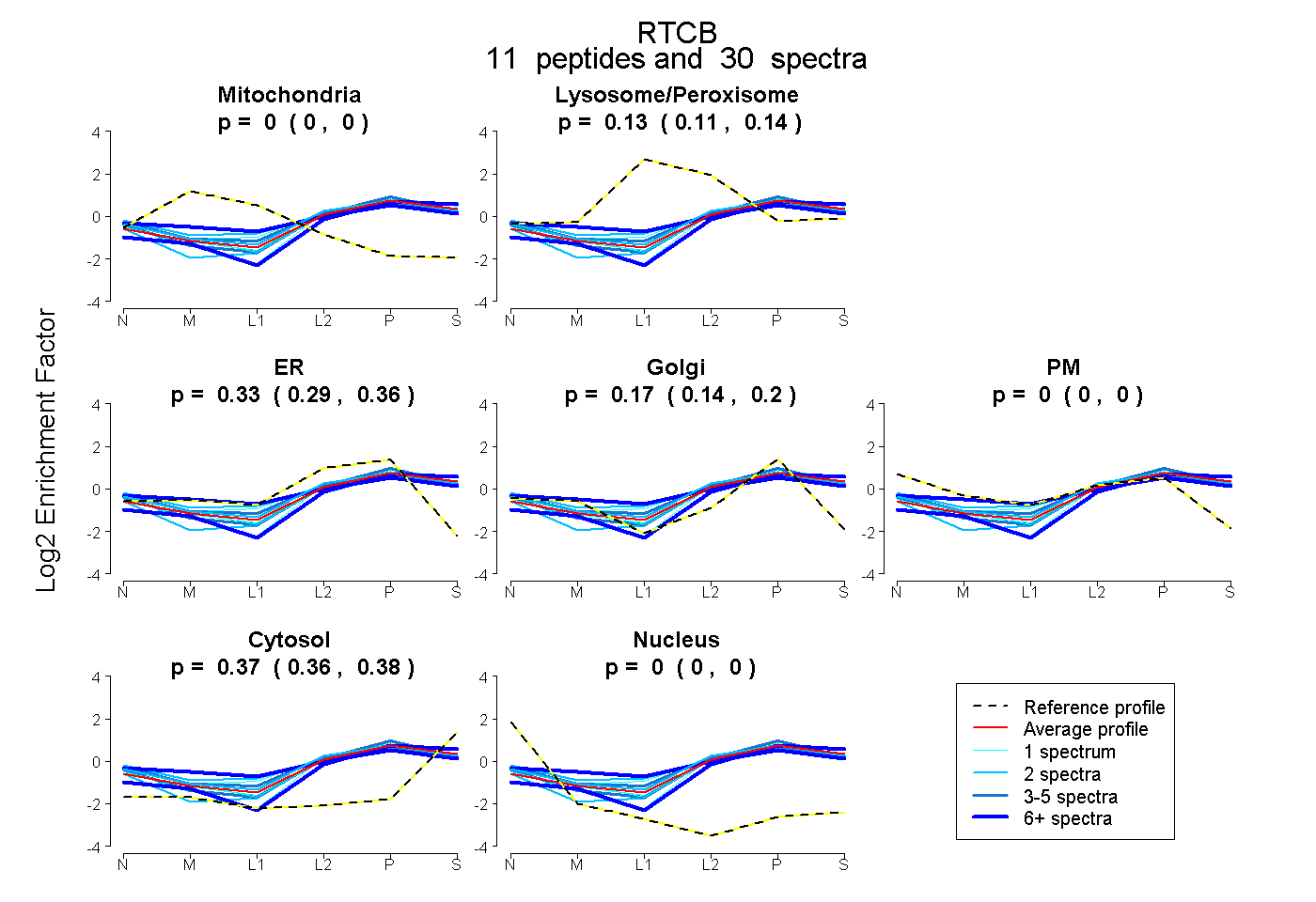
0.000 | 0.000
0.105 | 0.141
0.290 | 0.360
0.143 | 0.197
0.000 | 0.000
0.362 | 0.383
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
112 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.524 0.523 | 0.526 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.476 0.474 | 0.477 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
30 spectra |
 |
0.000 0.000 | 0.000 |
0.125 0.105 | 0.141 |
0.329 0.290 | 0.360 |
0.173 0.143 | 0.197 |
0.000 0.000 | 0.000 |
0.373 0.362 | 0.383 |
0.000 0.000 | 0.000 |
| 8 spectra, QIGNVAALPGIVHR | 0.000 | 0.337 | 0.000 | 0.405 | 0.026 | 0.232 | 0.000 | |||
| 2 spectra, GGGVGGFLPAMK | 0.000 | 0.319 | 0.000 | 0.405 | 0.036 | 0.239 | 0.000 | |||
| 3 spectra, LRPIAVIK | 0.000 | 0.048 | 0.436 | 0.155 | 0.000 | 0.361 | 0.000 | |||
| 2 spectra, VEQHVVDGK | 0.000 | 0.171 | 0.293 | 0.218 | 0.000 | 0.318 | 0.000 | |||
| 1 spectrum, NLDFQDVLDK | 0.000 | 0.081 | 0.414 | 0.125 | 0.000 | 0.380 | 0.000 | |||
| 2 spectra, LMFEELR | 0.000 | 0.021 | 0.513 | 0.000 | 0.000 | 0.466 | 0.000 | |||
| 6 spectra, SSMTFLTR | 0.000 | 0.000 | 0.366 | 0.155 | 0.000 | 0.479 | 0.000 | |||
| 3 spectra, NYNDELQFLDK | 0.000 | 0.241 | 0.144 | 0.322 | 0.005 | 0.287 | 0.000 | |||
| 1 spectrum, MGIDHK | 0.000 | 0.031 | 0.507 | 0.000 | 0.000 | 0.463 | 0.000 | |||
| 1 spectrum, GLGHQVATDALVAMEK | 0.000 | 0.181 | 0.409 | 0.000 | 0.000 | 0.410 | 0.000 | |||
| 1 spectrum, LGDMGIAIR | 0.000 | 0.000 | 0.480 | 0.062 | 0.000 | 0.458 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
107 spectra |
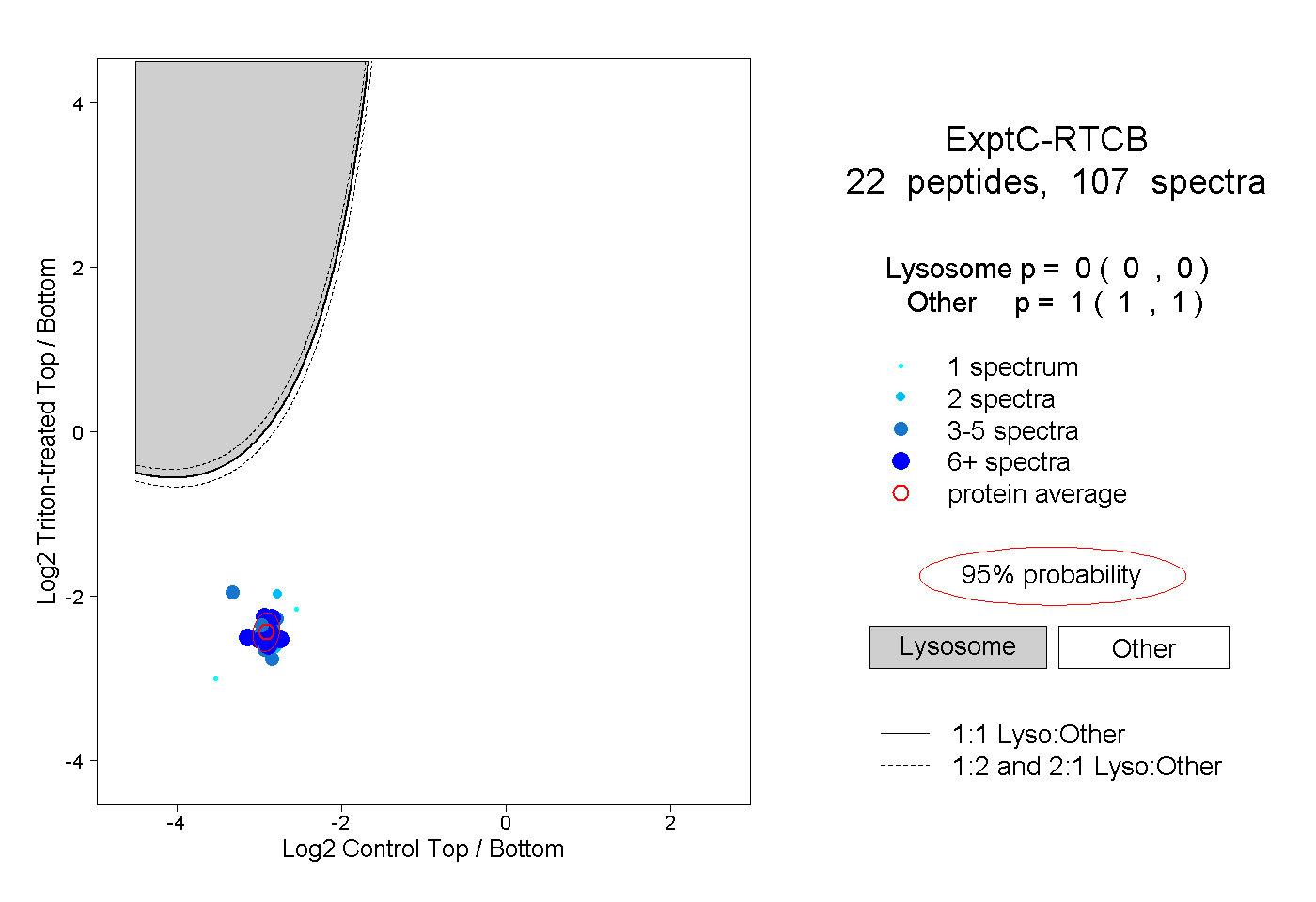 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
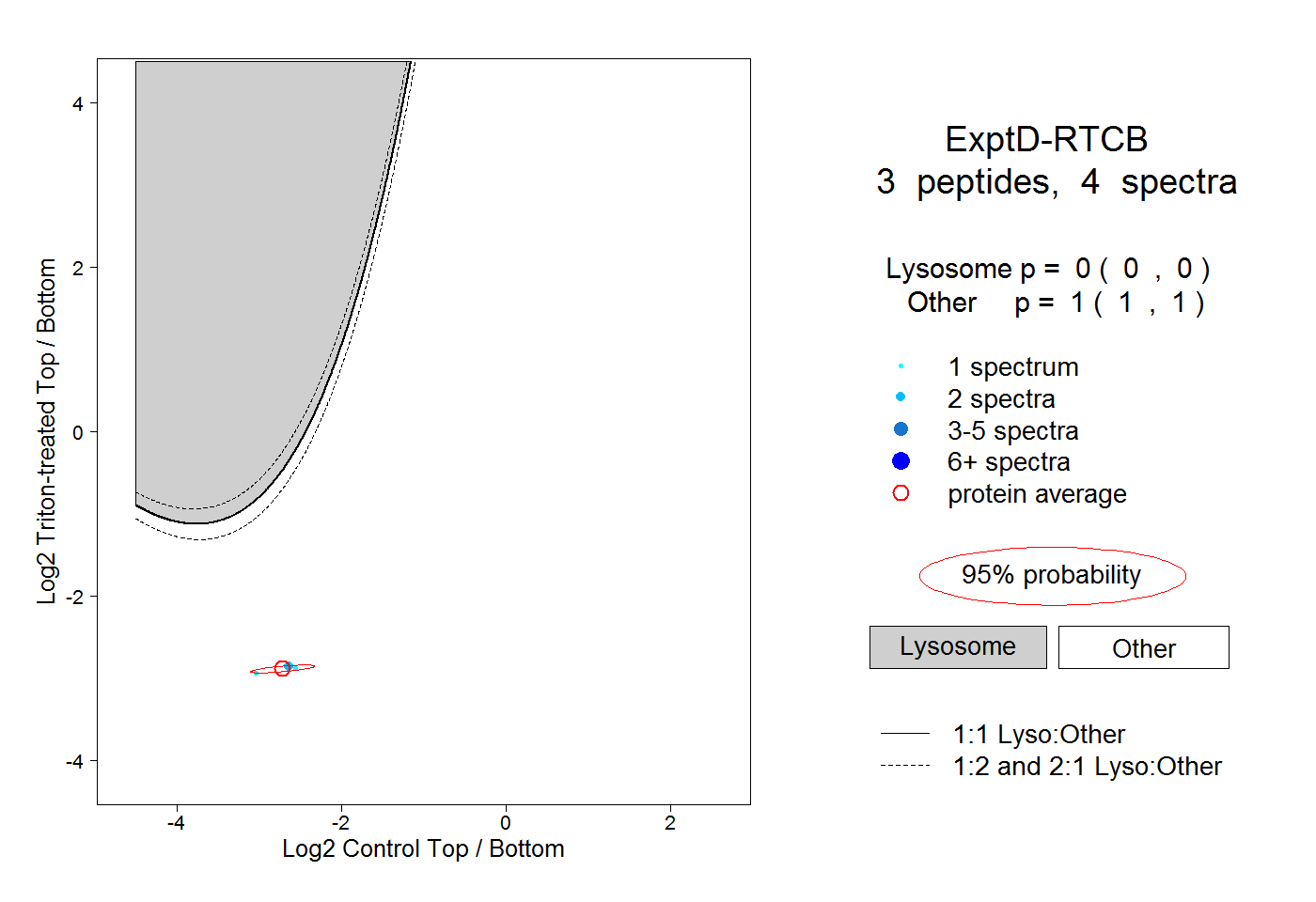 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |