peptides
spectra
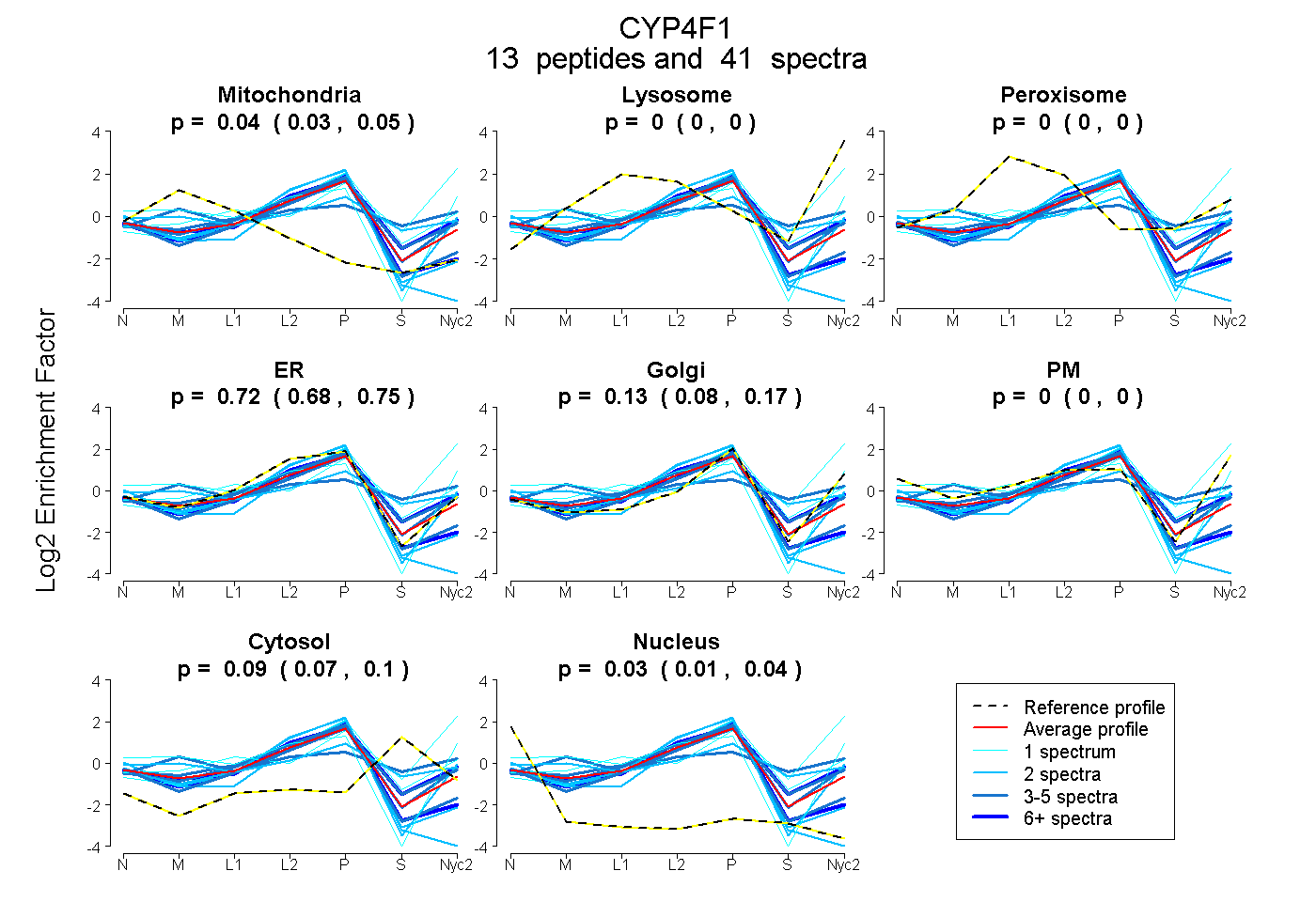
0.026 | 0.046
0.000 | 0.000
0.000 | 0.000
0.683 | 0.749
0.084 | 0.167
0.000 | 0.000
0.073 | 0.103
0.013 | 0.036
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
41 spectra |
 |
0.037 0.026 | 0.046 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.720 0.683 | 0.749 |
0.128 0.084 | 0.167 |
0.000 0.000 | 0.000 |
0.089 0.073 | 0.103 |
0.026 0.013 | 0.036 |
| 2 spectra, VEPLSAGAQ | 0.113 | 0.000 | 0.184 | 0.092 | 0.424 | 0.000 | 0.188 | 0.000 | ||
| 4 spectra, NCIGQTFAMSEMK | 0.089 | 0.000 | 0.000 | 0.833 | 0.000 | 0.000 | 0.000 | 0.079 | ||
| 6 spectra, ACNLVHEFTDAVIR | 0.000 | 0.000 | 0.000 | 0.836 | 0.000 | 0.000 | 0.000 | 0.164 | ||
| 1 spectrum, LLPDDK | 0.000 | 0.048 | 0.000 | 0.474 | 0.332 | 0.000 | 0.147 | 0.000 | ||
| 3 spectra, HQQPLLFMDLLYNLTPDGMR | 0.115 | 0.053 | 0.241 | 0.000 | 0.389 | 0.000 | 0.202 | 0.000 | ||
| 1 spectrum, SSEYIAAILELSALVAK | 0.087 | 0.000 | 0.000 | 0.291 | 0.000 | 0.622 | 0.000 | 0.000 | ||
| 7 spectra, LISEGSSR | 0.000 | 0.000 | 0.009 | 0.665 | 0.172 | 0.000 | 0.154 | 0.000 | ||
| 5 spectra, NWLMGHVGMVTPTEQGLK | 0.000 | 0.000 | 0.006 | 0.712 | 0.201 | 0.000 | 0.082 | 0.000 | ||
| 5 spectra, TLPDQGLDEFLK | 0.000 | 0.000 | 0.000 | 0.581 | 0.217 | 0.000 | 0.202 | 0.000 | ||
| 1 spectrum, SILNASAAVALK | 0.000 | 0.426 | 0.000 | 0.000 | 0.486 | 0.000 | 0.089 | 0.000 | ||
| 2 spectra, QEVQELLR | 0.000 | 0.000 | 0.000 | 0.769 | 0.231 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, CCTQDILLPDGR | 0.000 | 0.000 | 0.000 | 0.874 | 0.000 | 0.000 | 0.000 | 0.126 | ||
| 2 spectra, CVFSFDSNCQEK | 0.000 | 0.000 | 0.000 | 0.714 | 0.000 | 0.000 | 0.000 | 0.286 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
24 spectra |
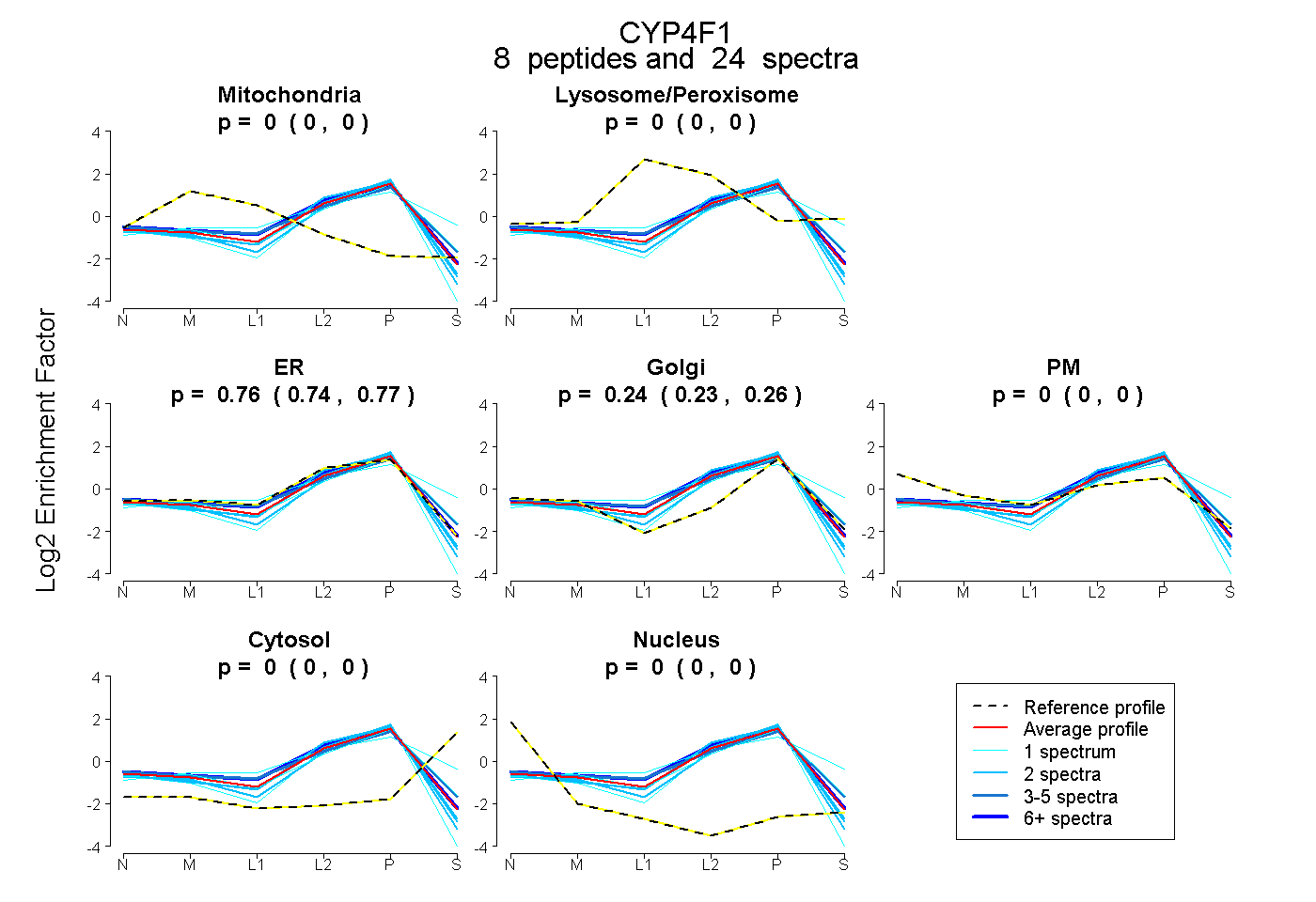 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.757 0.738 | 0.770 |
0.243 0.227 | 0.259 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
126 spectra |
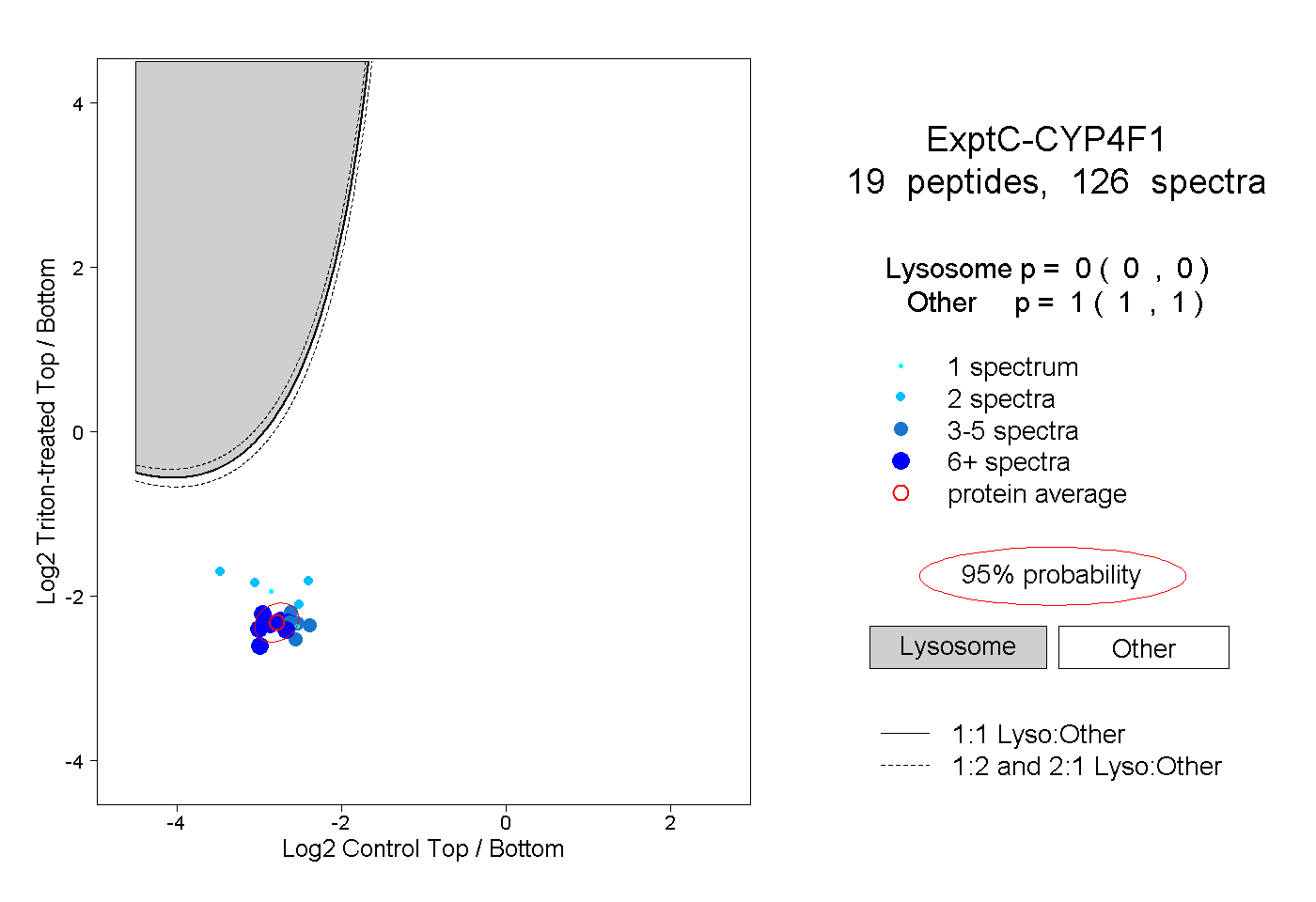 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
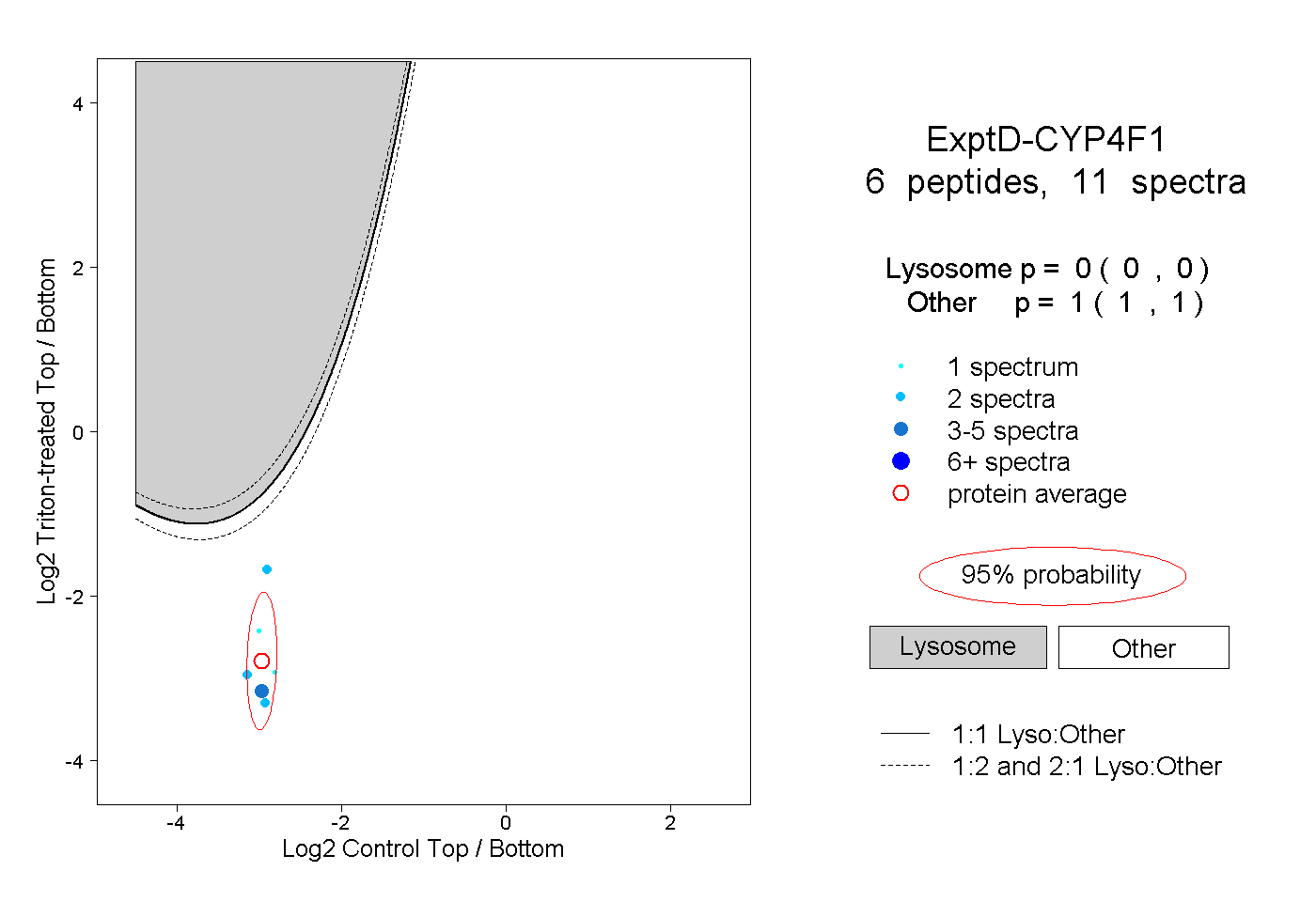 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |