peptides
spectra
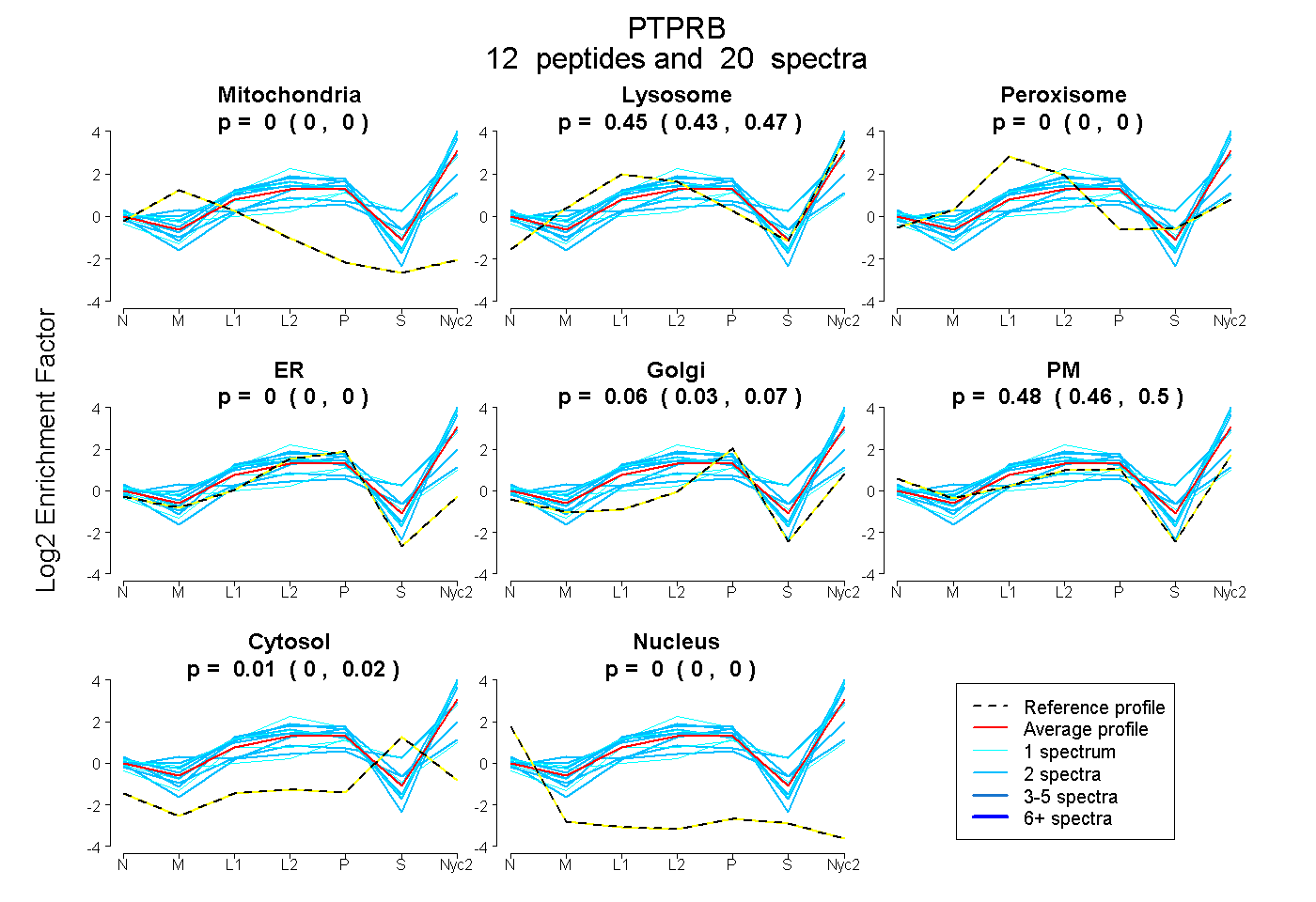
0.000 | 0.000
0.433 | 0.470
0.000 | 0.000
0.000 | 0.000
0.028 | 0.074
0.455 | 0.504
0.000 | 0.023
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
20 spectra |
 |
0.000 0.000 | 0.000 |
0.454 0.433 | 0.470 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.055 0.028 | 0.074 |
0.481 0.455 | 0.504 |
0.010 0.000 | 0.023 |
0.000 0.000 | 0.000 |
| 2 spectra, DLQAGTIYNFR | 0.000 | 0.526 | 0.000 | 0.000 | 0.000 | 0.474 | 0.000 | 0.000 | ||
| 1 spectrum, TVPSSVSGVTVNNSGR | 0.000 | 0.009 | 0.153 | 0.000 | 0.290 | 0.393 | 0.155 | 0.000 | ||
| 1 spectrum, IVNGLRPGR | 0.000 | 0.584 | 0.000 | 0.000 | 0.000 | 0.416 | 0.000 | 0.000 | ||
| 2 spectra, FQGLIPGR | 0.000 | 0.547 | 0.000 | 0.000 | 0.000 | 0.453 | 0.000 | 0.000 | ||
| 2 spectra, DSVDIYGAVHDLR | 0.009 | 0.346 | 0.000 | 0.000 | 0.000 | 0.454 | 0.191 | 0.000 | ||
| 1 spectrum, VTSGGSLTSLNVK | 0.000 | 0.544 | 0.000 | 0.000 | 0.082 | 0.142 | 0.231 | 0.000 | ||
| 2 spectra, TVPAAVTNLR | 0.000 | 0.534 | 0.000 | 0.000 | 0.000 | 0.466 | 0.000 | 0.000 | ||
| 2 spectra, GPGNVEQFR | 0.000 | 0.500 | 0.000 | 0.000 | 0.000 | 0.250 | 0.250 | 0.000 | ||
| 2 spectra, DLVPGR | 0.000 | 0.590 | 0.000 | 0.000 | 0.000 | 0.410 | 0.000 | 0.000 | ||
| 1 spectrum, VSSLSASIQWR | 0.000 | 0.567 | 0.000 | 0.000 | 0.000 | 0.433 | 0.000 | 0.000 | ||
| 2 spectra, ATEIQFK | 0.000 | 0.177 | 0.000 | 0.359 | 0.069 | 0.201 | 0.194 | 0.000 | ||
| 2 spectra, SGQYEASEQGTGR | 0.000 | 0.428 | 0.000 | 0.000 | 0.000 | 0.572 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
40 spectra |
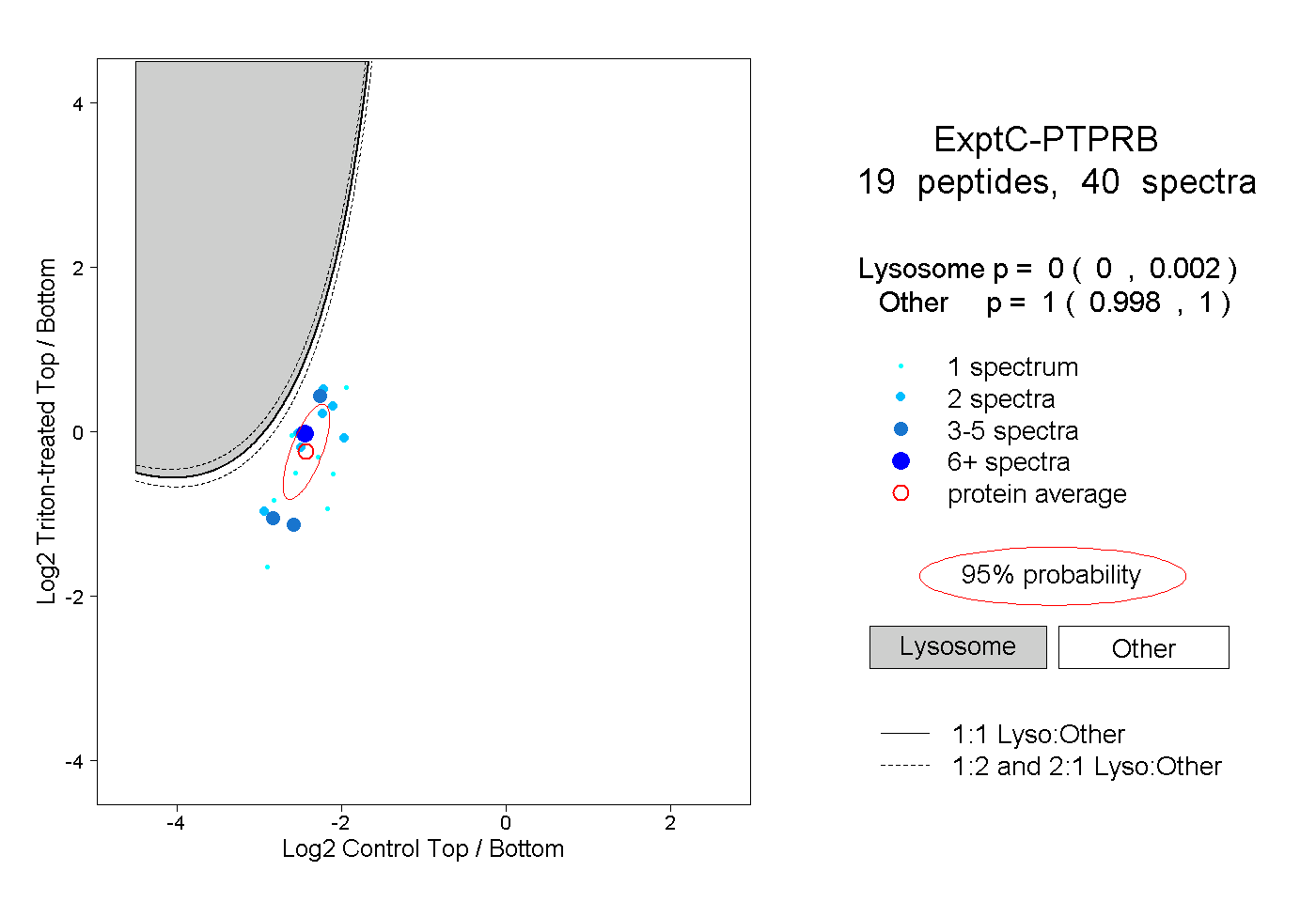 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
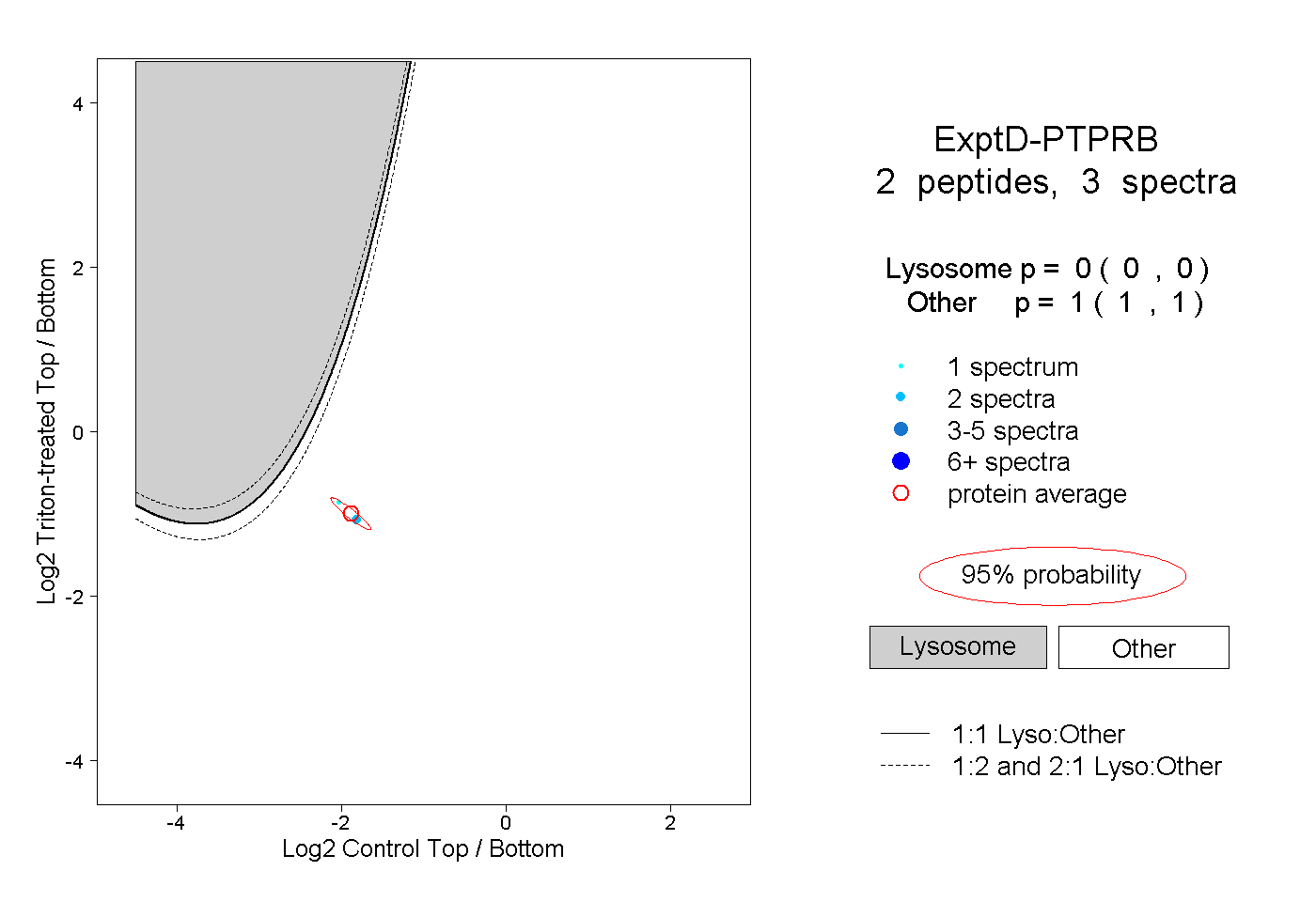 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |