peptides
spectra
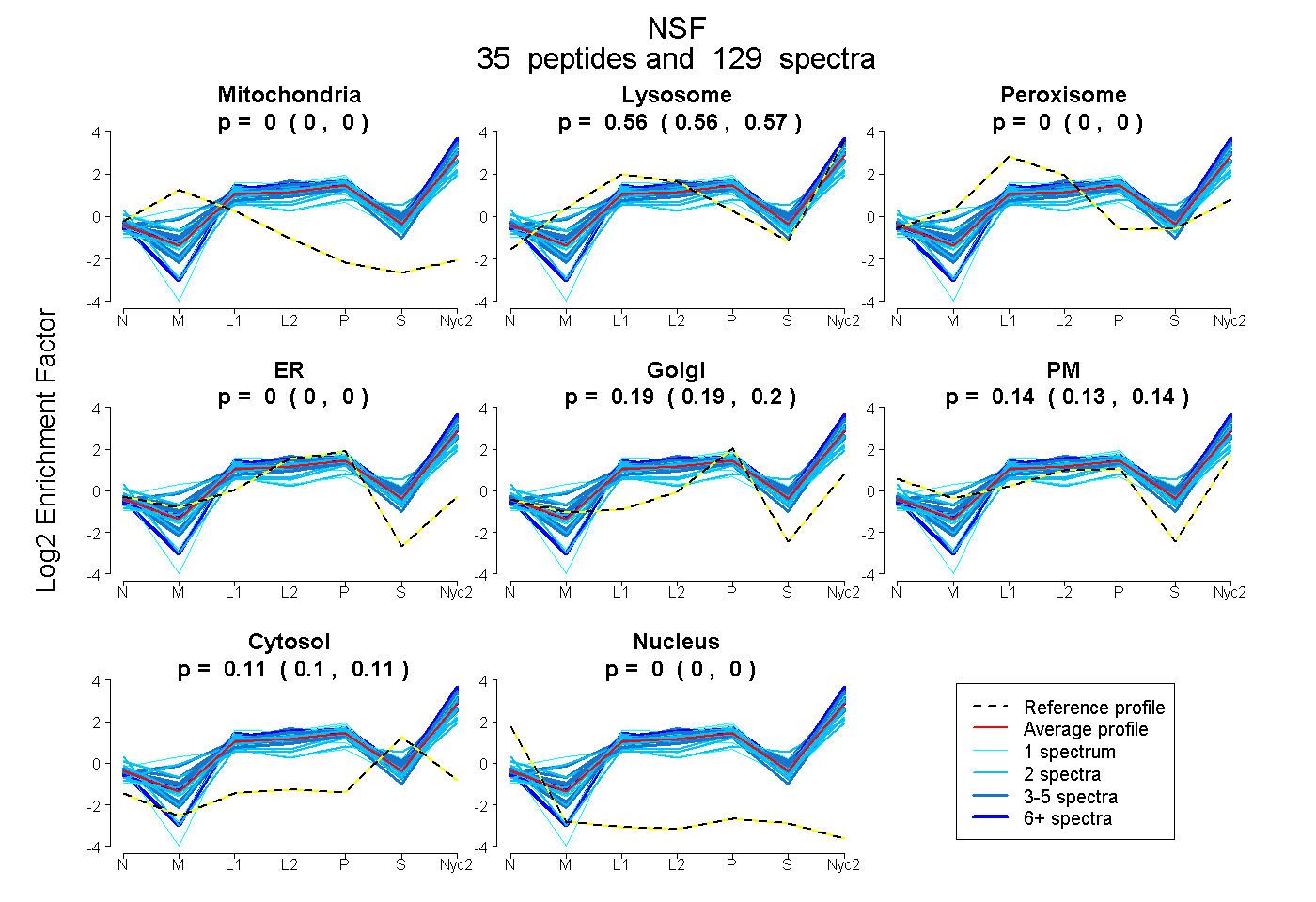
0.000 | 0.000
0.561 | 0.566
0.000 | 0.000
0.000 | 0.000
0.189 | 0.196
0.132 | 0.141
0.105 | 0.108
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
129 spectra |
 |
0.000 0.000 | 0.000 |
0.564 0.561 | 0.566 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.193 0.189 | 0.196 |
0.137 0.132 | 0.141 |
0.106 0.105 | 0.108 |
0.000 0.000 | 0.000 |
| 4 spectra, LFADAEEEQR | 0.000 | 0.586 | 0.000 | 0.000 | 0.172 | 0.144 | 0.098 | 0.000 | ||
| 2 spectra, GILLYGPPGCGK | 0.000 | 0.441 | 0.166 | 0.000 | 0.326 | 0.000 | 0.068 | 0.000 | ||
| 3 spectra, DIEAMDPSILK | 0.000 | 0.604 | 0.000 | 0.000 | 0.259 | 0.045 | 0.093 | 0.000 | ||
| 2 spectra, YVGESEANIR | 0.000 | 0.480 | 0.000 | 0.000 | 0.134 | 0.300 | 0.085 | 0.000 | ||
| 7 spectra, NIDSNPYDTDK | 0.000 | 0.746 | 0.000 | 0.000 | 0.234 | 0.000 | 0.020 | 0.000 | ||
| 1 spectrum, LQILHIHTAR | 0.000 | 0.465 | 0.000 | 0.000 | 0.267 | 0.157 | 0.112 | 0.000 | ||
| 4 spectra, YIFTLR | 0.000 | 0.685 | 0.000 | 0.000 | 0.197 | 0.099 | 0.019 | 0.000 | ||
| 3 spectra, LFGLLVK | 0.000 | 0.628 | 0.000 | 0.000 | 0.047 | 0.322 | 0.004 | 0.000 | ||
| 1 spectrum, GEPASGK | 0.026 | 0.404 | 0.000 | 0.000 | 0.005 | 0.405 | 0.161 | 0.000 | ||
| 2 spectra, TTIAQQVK | 0.000 | 0.632 | 0.000 | 0.000 | 0.238 | 0.000 | 0.131 | 0.000 | ||
| 3 spectra, VLDDGELLVQQTK | 0.000 | 0.532 | 0.000 | 0.000 | 0.178 | 0.135 | 0.156 | 0.000 | ||
| 1 spectrum, MIGFSETAK | 0.000 | 0.709 | 0.000 | 0.000 | 0.242 | 0.000 | 0.049 | 0.000 | ||
| 2 spectra, WGDPVTR | 0.000 | 0.683 | 0.000 | 0.000 | 0.289 | 0.028 | 0.000 | 0.000 | ||
| 1 spectrum, MEIGLPDEK | 0.000 | 0.570 | 0.000 | 0.000 | 0.216 | 0.000 | 0.214 | 0.000 | ||
| 2 spectra, EFSDIFR | 0.000 | 0.659 | 0.000 | 0.000 | 0.243 | 0.007 | 0.091 | 0.000 | ||
| 5 spectra, NFSGAELEGLVR | 0.000 | 0.480 | 0.000 | 0.000 | 0.099 | 0.222 | 0.199 | 0.000 | ||
| 3 spectra, LLDYVPIGPR | 0.000 | 0.626 | 0.000 | 0.000 | 0.224 | 0.150 | 0.000 | 0.000 | ||
| 1 spectrum, DYQSGQHVMVR | 0.000 | 0.505 | 0.024 | 0.000 | 0.298 | 0.120 | 0.052 | 0.000 | ||
| 2 spectra, VFPPEIVEQMGCK | 0.000 | 0.320 | 0.085 | 0.072 | 0.063 | 0.270 | 0.189 | 0.000 | ||
| 2 spectra, ELAVETK | 0.000 | 0.461 | 0.000 | 0.000 | 0.080 | 0.089 | 0.370 | 0.000 | ||
| 1 spectrum, AENSSLNLIGK | 0.000 | 0.626 | 0.000 | 0.000 | 0.288 | 0.066 | 0.020 | 0.000 | ||
| 1 spectrum, CQAMK | 0.000 | 0.571 | 0.000 | 0.000 | 0.224 | 0.158 | 0.048 | 0.000 | ||
| 3 spectra, IAEESNFPFIK | 0.000 | 0.585 | 0.000 | 0.000 | 0.112 | 0.293 | 0.009 | 0.000 | ||
| 1 spectrum, QSIINPDWNFEK | 0.000 | 0.614 | 0.000 | 0.000 | 0.352 | 0.027 | 0.007 | 0.000 | ||
| 33 spectra, AAQSTAMNR | 0.000 | 0.551 | 0.000 | 0.000 | 0.294 | 0.000 | 0.155 | 0.000 | ||
| 4 spectra, ICSPDK | 0.000 | 0.542 | 0.000 | 0.047 | 0.120 | 0.193 | 0.098 | 0.000 | ||
| 2 spectra, TPLVSVLLEGPPHSGK | 0.000 | 0.715 | 0.000 | 0.000 | 0.241 | 0.000 | 0.044 | 0.000 | ||
| 2 spectra, VEVDMEK | 0.000 | 0.191 | 0.000 | 0.000 | 0.081 | 0.463 | 0.264 | 0.000 | ||
| 4 spectra, IFDDAYK | 0.000 | 0.656 | 0.000 | 0.000 | 0.185 | 0.004 | 0.154 | 0.000 | ||
| 14 spectra, LLIIGTTSR | 0.000 | 0.697 | 0.000 | 0.000 | 0.183 | 0.091 | 0.029 | 0.000 | ||
| 1 spectrum, GHQLLSADVDIK | 0.000 | 0.489 | 0.000 | 0.000 | 0.172 | 0.168 | 0.171 | 0.000 | ||
| 2 spectra, VWIGIK | 0.000 | 0.360 | 0.000 | 0.000 | 0.098 | 0.414 | 0.128 | 0.000 | ||
| 1 spectrum, TSPNHK | 0.000 | 0.352 | 0.003 | 0.000 | 0.000 | 0.479 | 0.166 | 0.000 | ||
| 6 spectra, APPQGR | 0.000 | 0.576 | 0.000 | 0.000 | 0.085 | 0.189 | 0.149 | 0.000 | ||
| 3 spectra, AESLQVTR | 0.000 | 0.494 | 0.000 | 0.000 | 0.286 | 0.083 | 0.136 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
31 spectra |
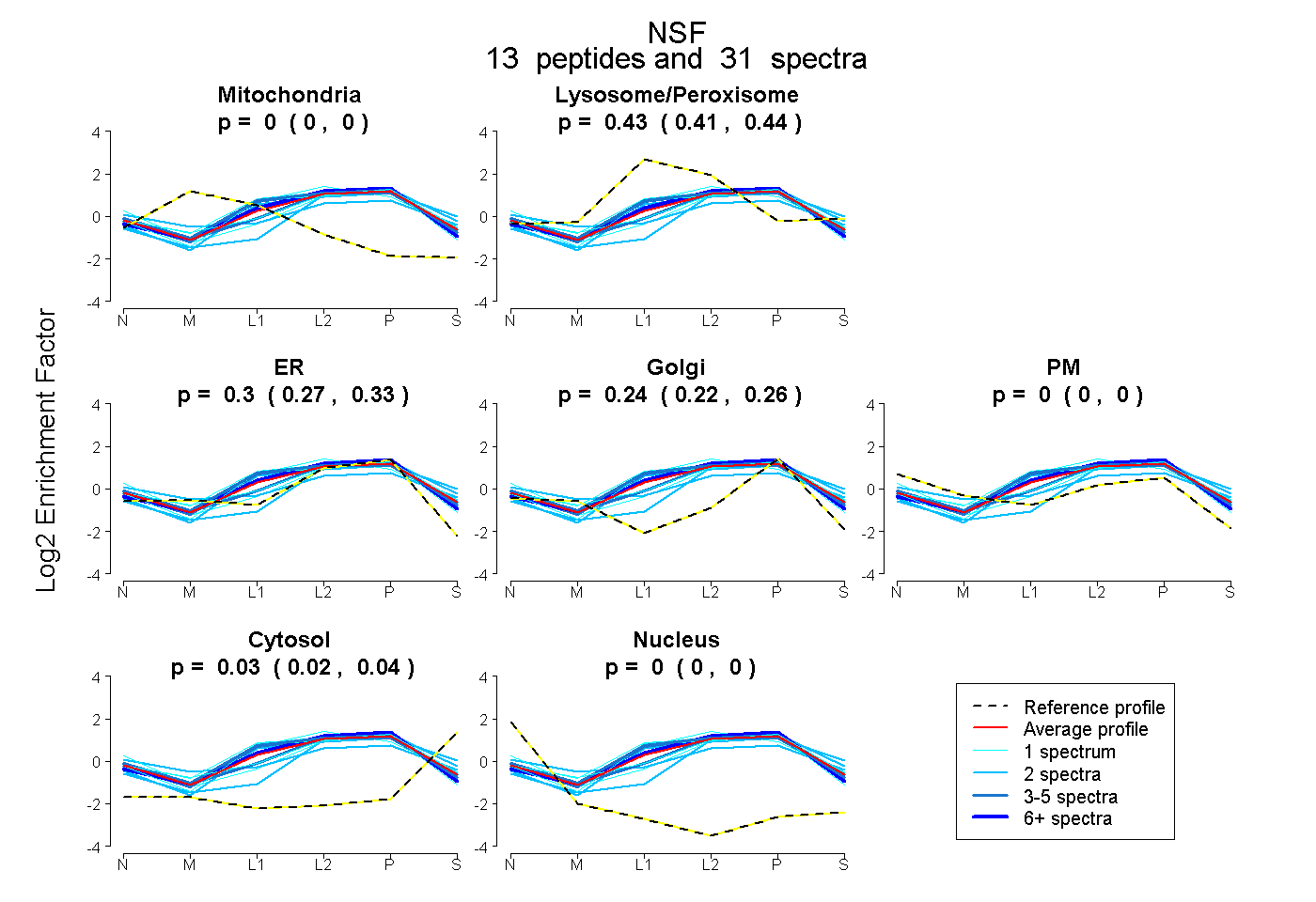 |
0.000 0.000 | 0.000 |
0.426 0.408 | 0.441 |
0.305 0.275 | 0.332 |
0.241 0.215 | 0.260 |
0.000 0.000 | 0.000 |
0.028 0.019 | 0.037 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
200 spectra |
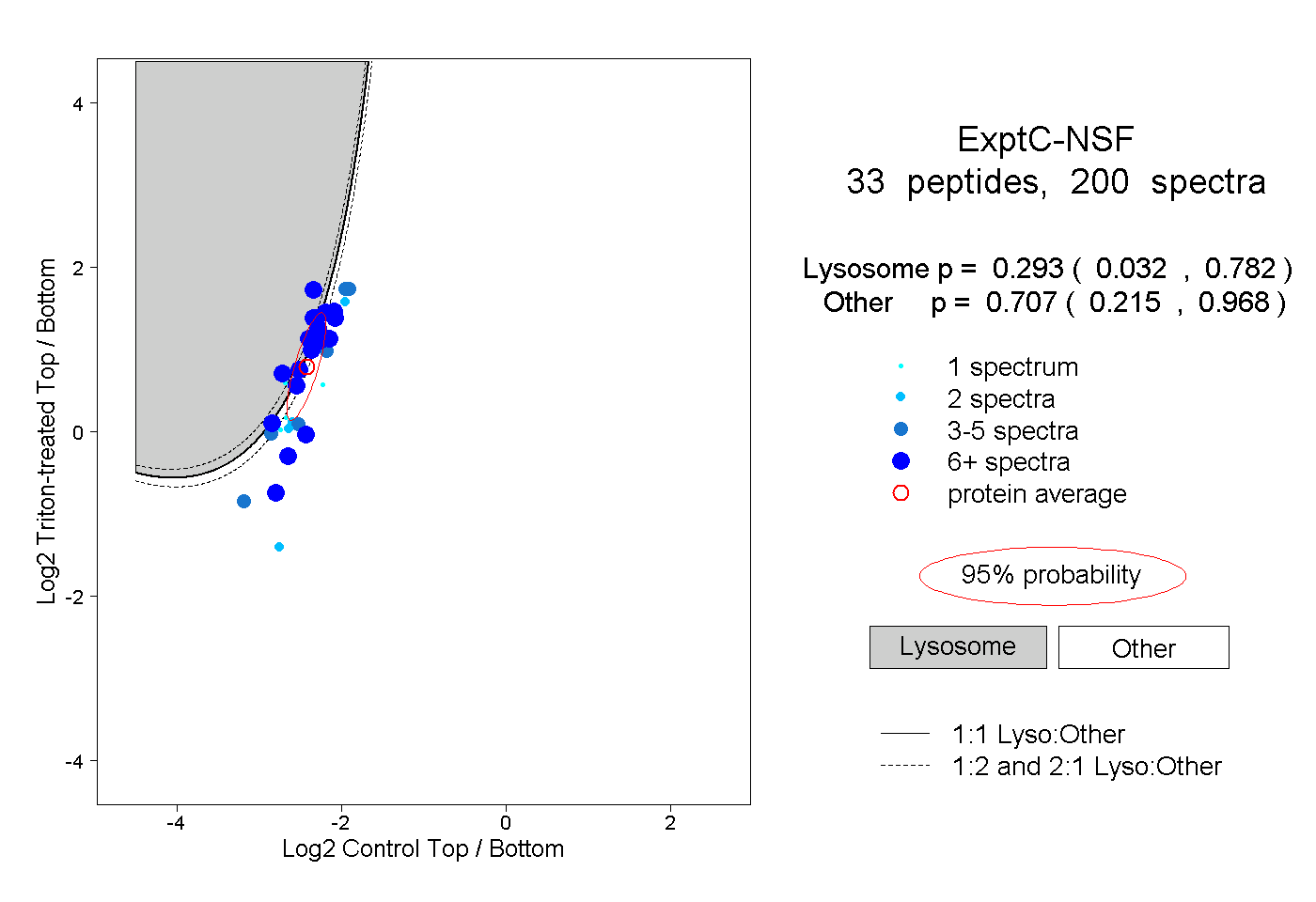 |
0.293 0.032 | 0.782 |
0.707 0.215 | 0.968 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
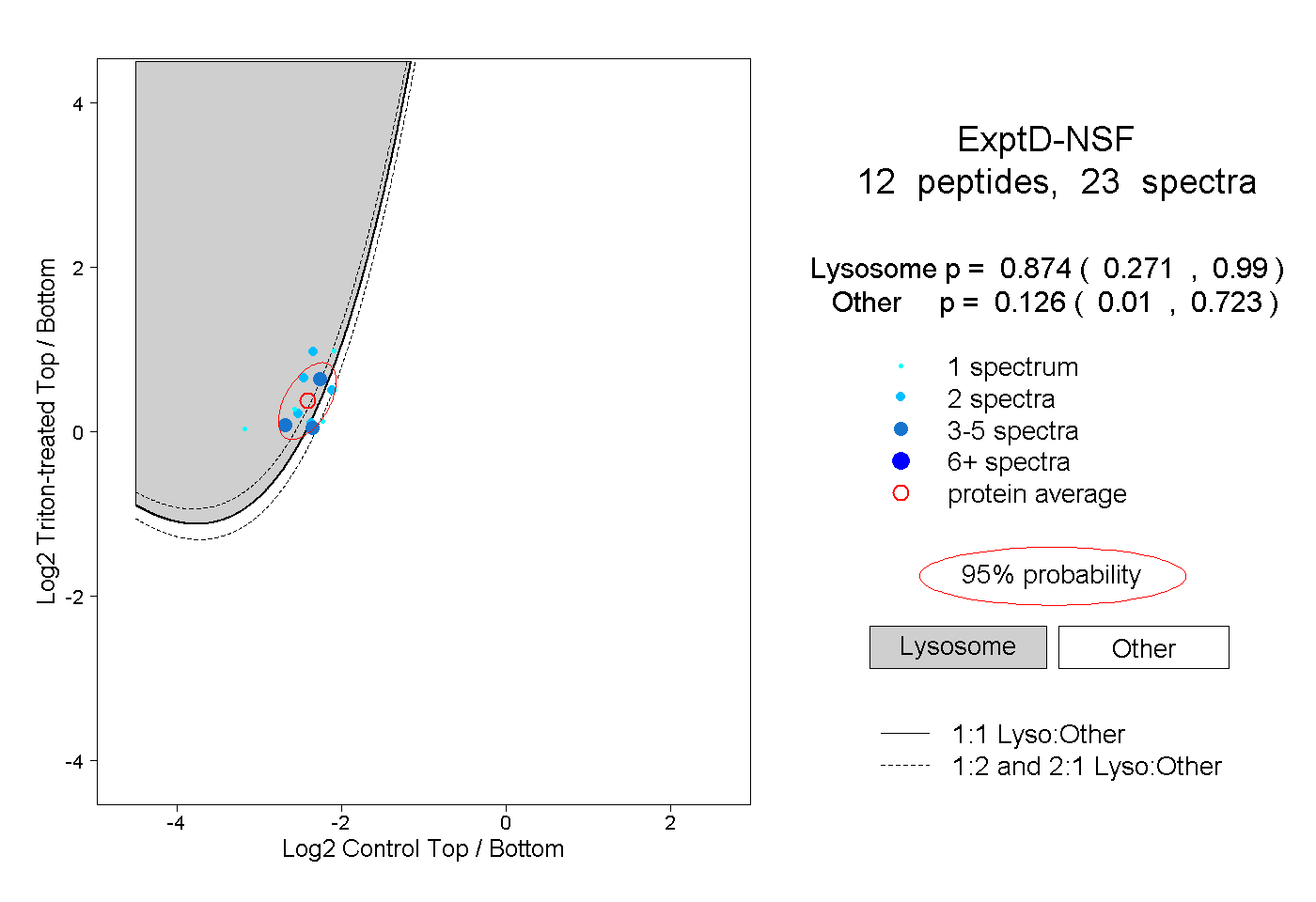 |
0.874 0.271 | 0.990 |
0.126 0.010 | 0.723 |