peptides
spectra
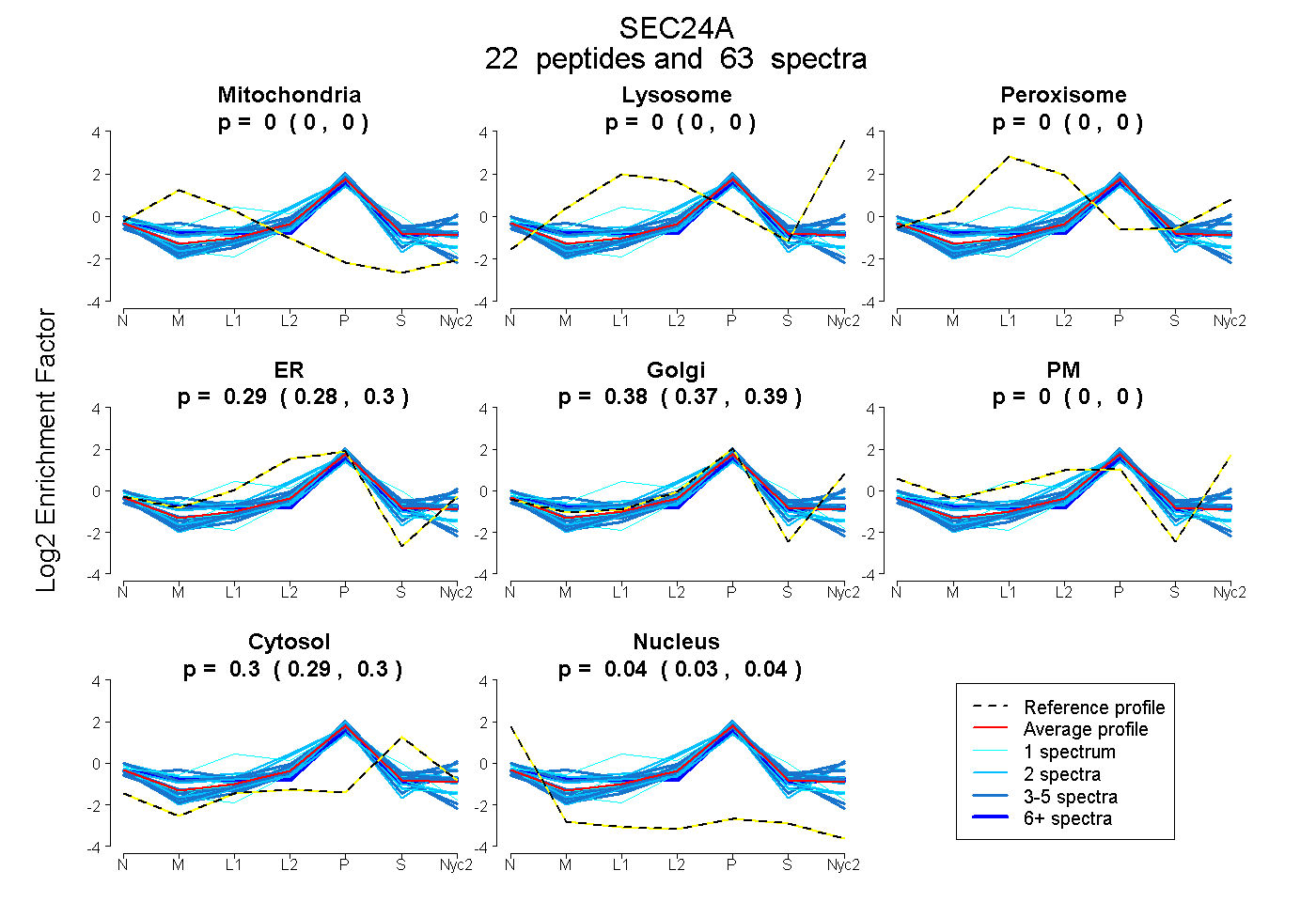
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.276 | 0.296
0.366 | 0.390
0.000 | 0.000
0.293 | 0.300
0.034 | 0.040
peptides
spectra
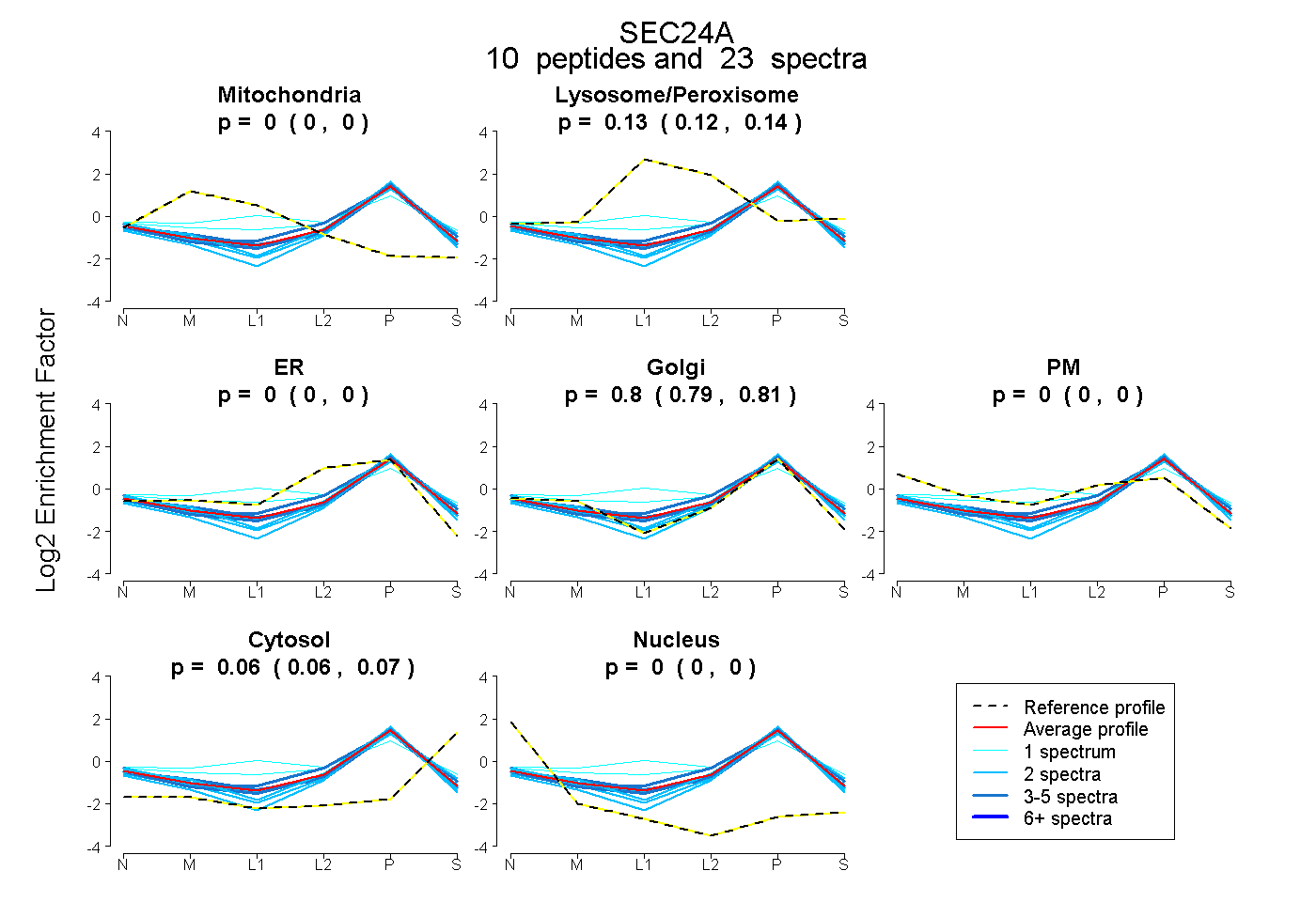
0.000 | 0.000
0.122 | 0.143
0.000 | 0.000
0.795 | 0.811
0.000 | 0.000
0.057 | 0.069
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
63 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.287 0.276 | 0.296 |
0.379 0.366 | 0.390 |
0.000 0.000 | 0.000 |
0.297 0.293 | 0.300 |
0.038 0.034 | 0.040 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.134 0.122 | 0.143 |
0.000 0.000 | 0.000 |
0.803 0.795 | 0.811 |
0.000 0.000 | 0.000 |
0.063 0.057 | 0.069 |
0.000 0.000 | 0.000 |
| 3 spectra, LISPTGGR | 0.000 | 0.118 | 0.000 | 0.818 | 0.000 | 0.064 | 0.000 | |||
| 4 spectra, VVNLLQER | 0.000 | 0.102 | 0.000 | 0.821 | 0.000 | 0.077 | 0.000 | |||
| 2 spectra, VDNLSDEGALNINDR | 0.000 | 0.116 | 0.006 | 0.855 | 0.000 | 0.023 | 0.000 | |||
| 4 spectra, LNCNPELFR | 0.000 | 0.195 | 0.000 | 0.742 | 0.000 | 0.063 | 0.000 | |||
| 2 spectra, VYGEPHK | 0.000 | 0.065 | 0.030 | 0.816 | 0.000 | 0.088 | 0.000 | |||
| 1 spectrum, CNLCYR | 0.000 | 0.397 | 0.000 | 0.549 | 0.000 | 0.054 | 0.000 | |||
| 1 spectrum, ELVQDLLK | 0.000 | 0.265 | 0.000 | 0.735 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, SVTASLSDAR | 0.000 | 0.000 | 0.000 | 0.903 | 0.000 | 0.097 | 0.000 | |||
| 2 spectra, TIPQPPILQLSVEK | 0.000 | 0.144 | 0.000 | 0.741 | 0.000 | 0.115 | 0.000 | |||
| 2 spectra, SFQTGTNVR | 0.000 | 0.016 | 0.022 | 0.908 | 0.000 | 0.053 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
62 spectra |
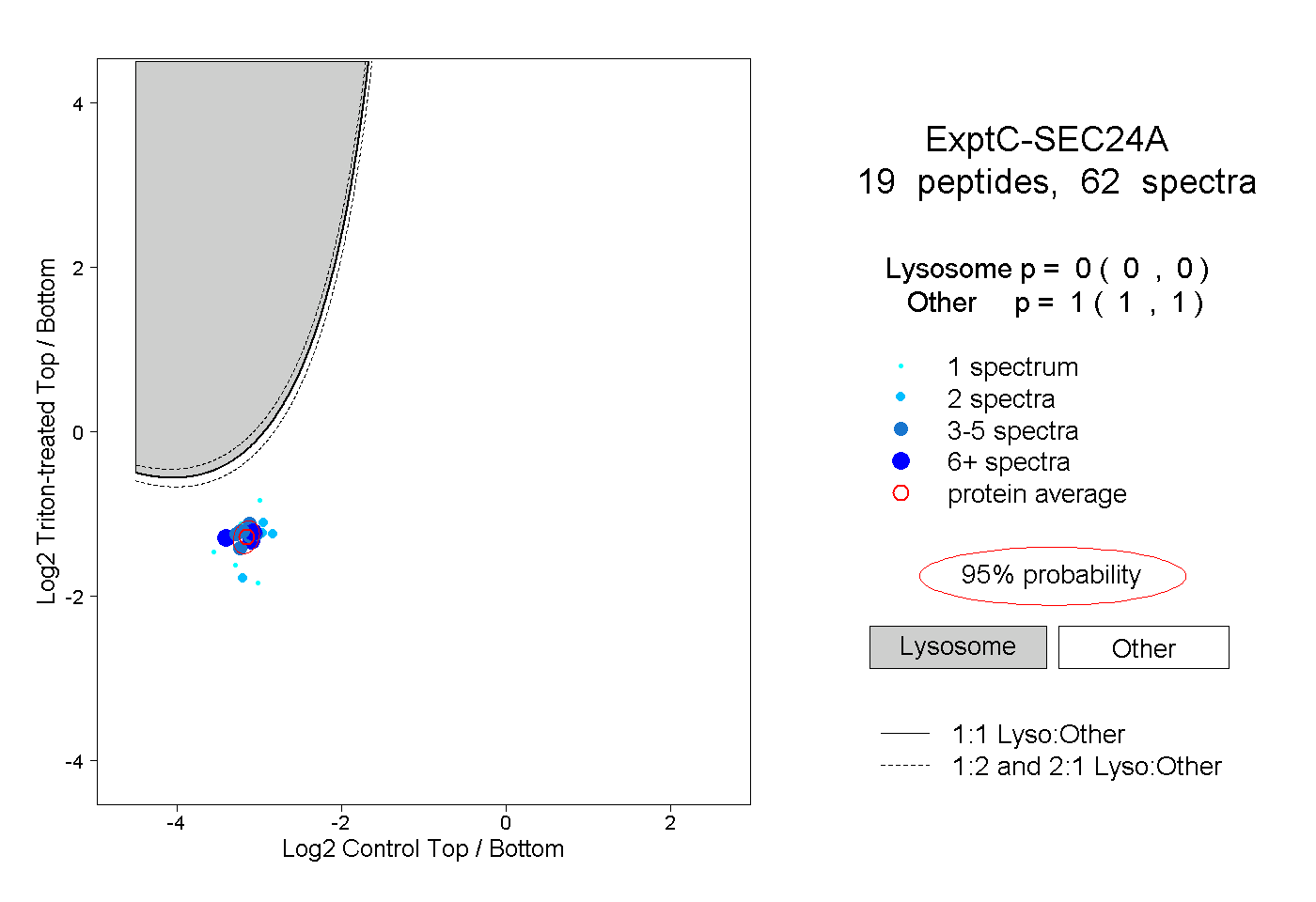 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
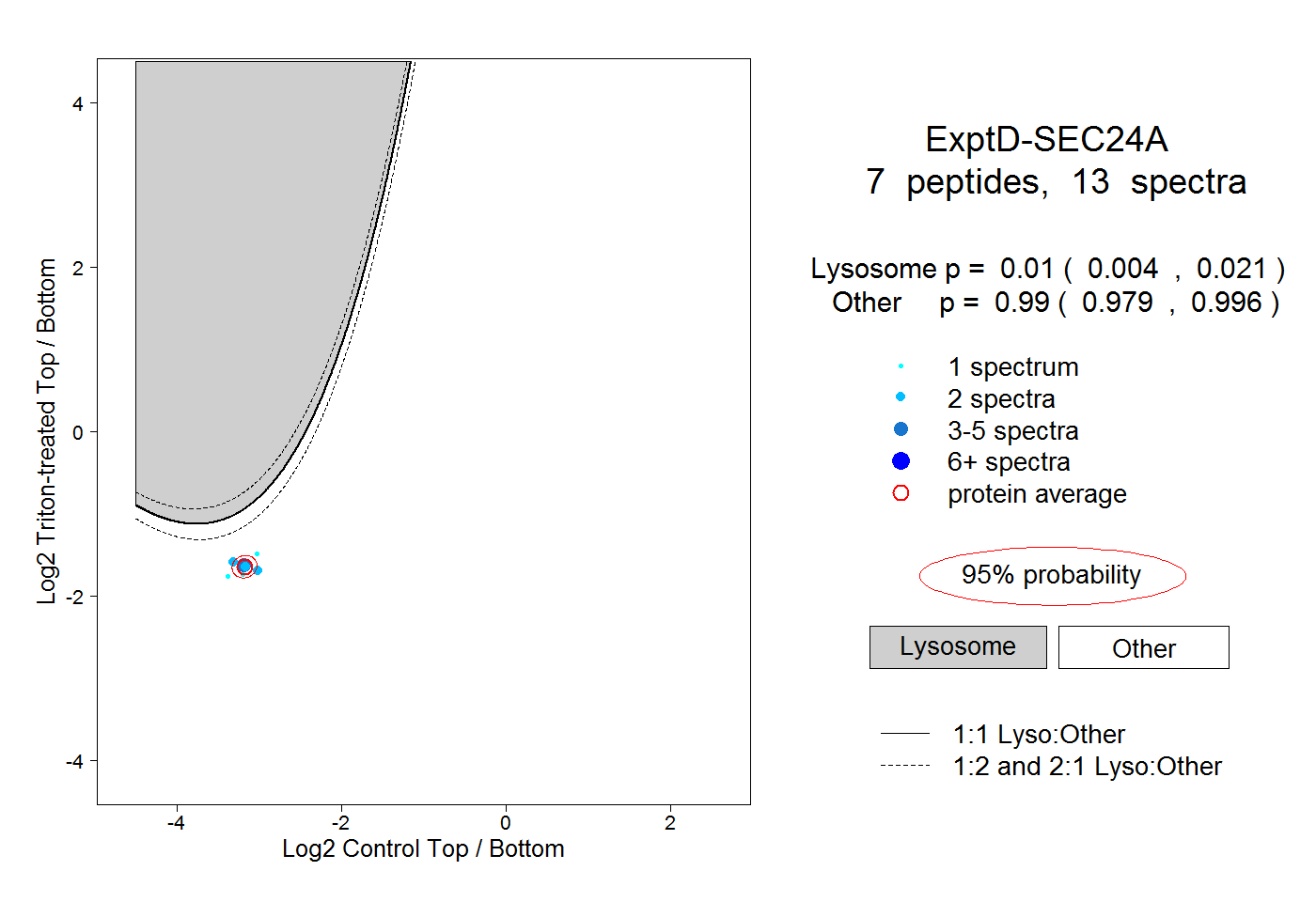 |
0.010 0.004 | 0.021 |
0.990 0.979 | 0.996 |