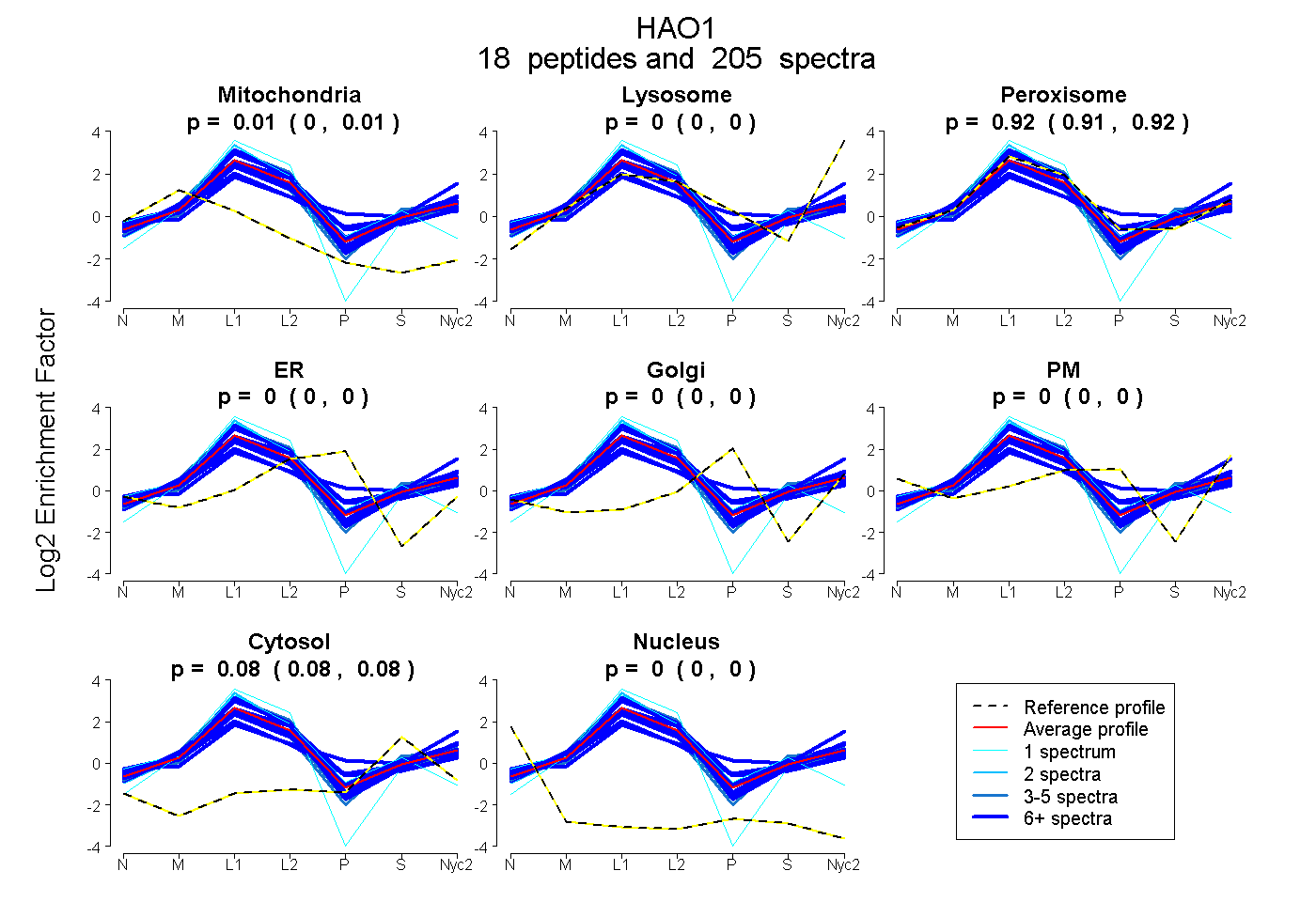
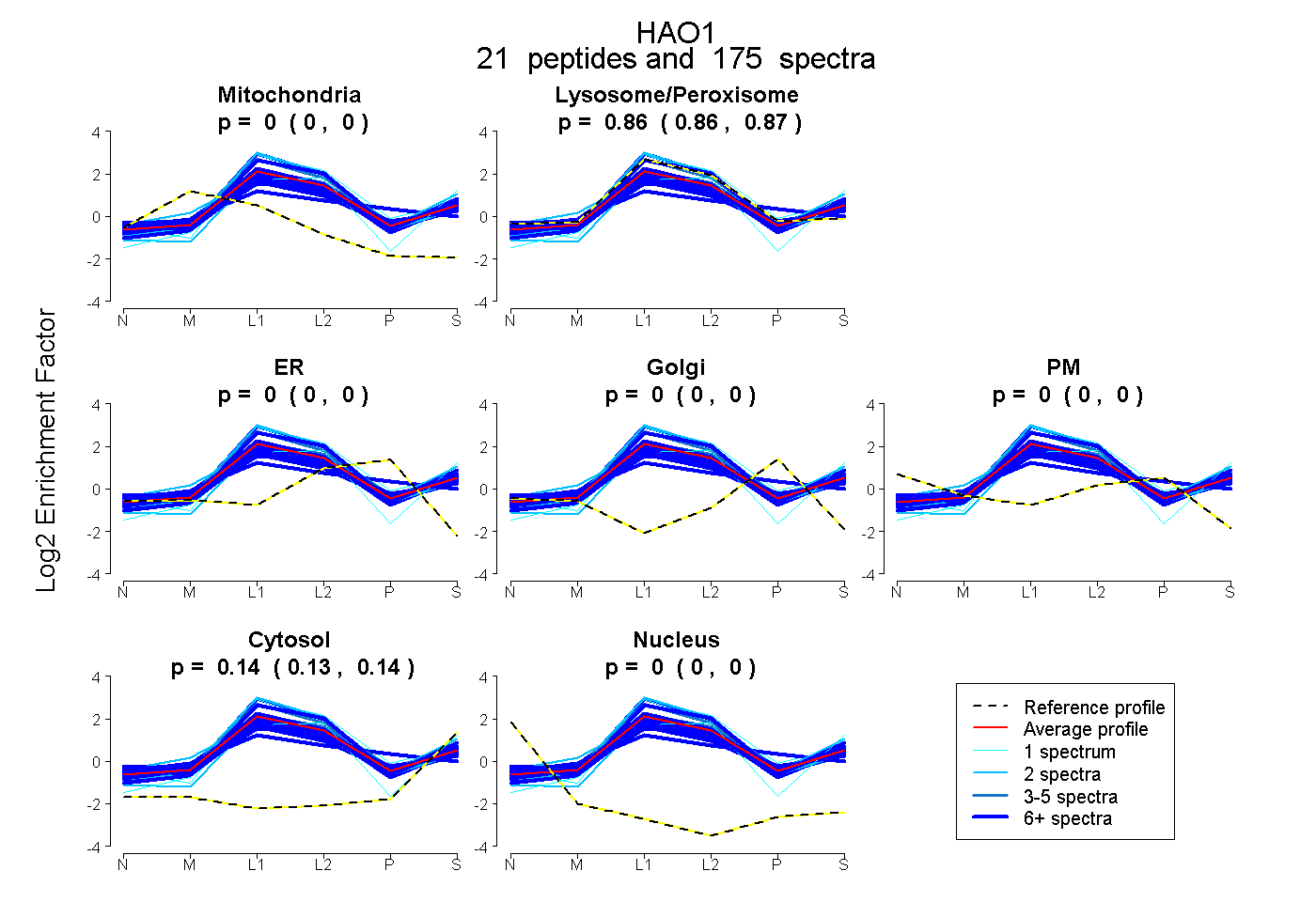
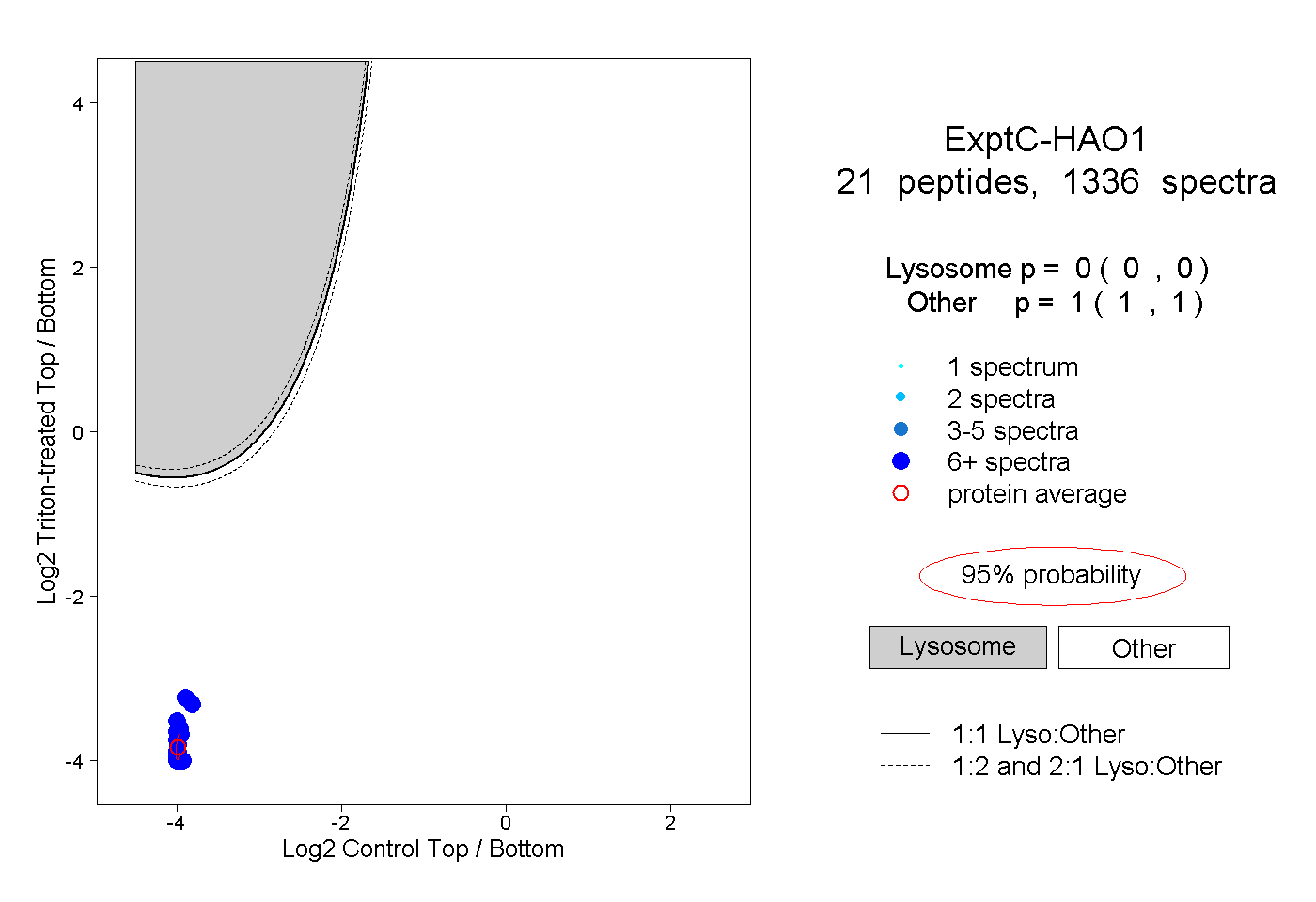
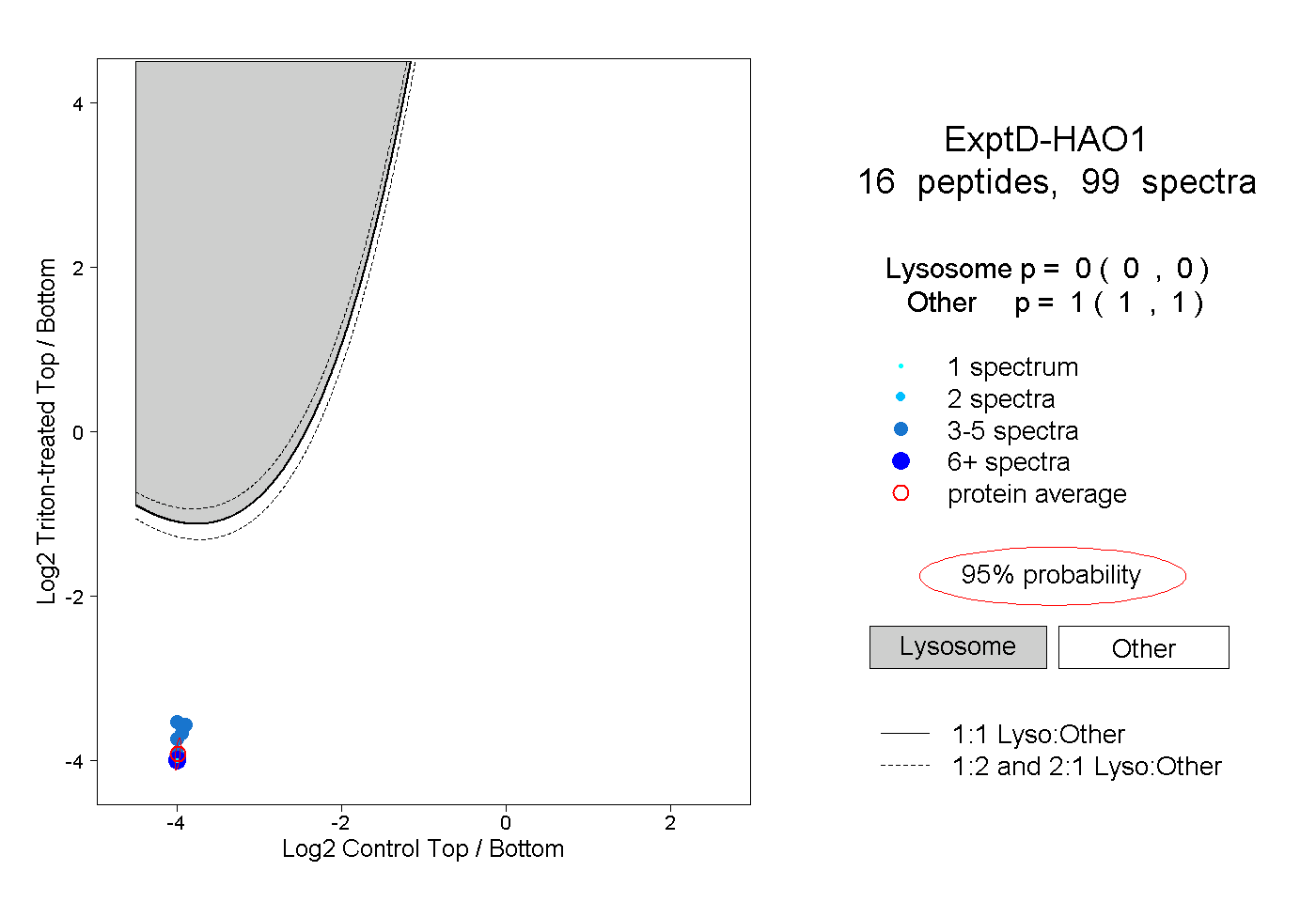
| 20 spectra, AVFVGRPIIWGLAFQGEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 63 spectra, SGANDQETLADNIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 99 spectra, AEQMGYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, QLDGVPATIDALPEIVEAVEGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 66 spectra, WMQLYIYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 31 spectra, NVADIDLSTSVLGQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 34 spectra, VSMPICVGATAMQCMAHVDGELATVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 45 spectra, NPLAVSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 50 spectra, GTDVLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 36 spectra, GVQDVLEILK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 29 spectra, LVCISDYEQHAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, NFETNDLAFSPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 111 spectra, VEVFLDGGVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 103 spectra, ALALGAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 275 spectra, GDDAQEAVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 87 spectra, LTSLPIVVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, HGVDGILVSNHGAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, AIFVTVDTPYLGNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 102 spectra, SVYDYYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 76 spectra, LAMALSGCQNVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 46 spectra, LPPQLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |