peptides
spectra
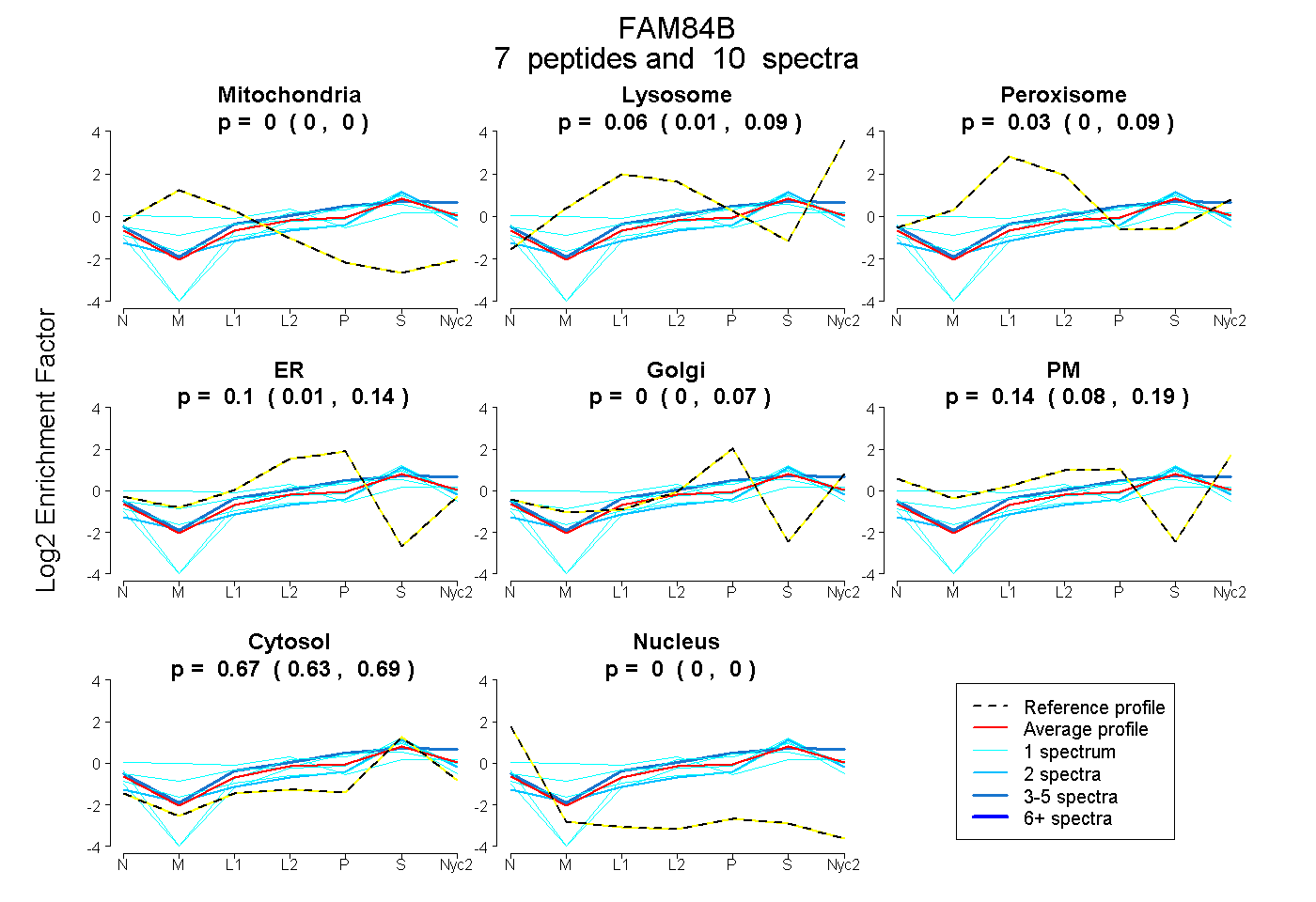
0.000 | 0.000
0.014 | 0.089
0.000 | 0.085
0.013 | 0.135
0.000 | 0.066
0.076 | 0.194
0.631 | 0.689
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
10 spectra |
 |
0.000 0.000 | 0.000 |
0.060 0.014 | 0.089 |
0.030 0.000 | 0.085 |
0.096 0.013 | 0.135 |
0.000 0.000 | 0.066 |
0.145 0.076 | 0.194 |
0.669 0.631 | 0.689 |
0.000 0.000 | 0.000 |
| 2 spectra, LQIQLSAQR | 0.000 | 0.109 | 0.000 | 0.000 | 0.111 | 0.000 | 0.781 | 0.000 | ||
| 3 spectra, NALAHVGAK | 0.000 | 0.166 | 0.004 | 0.032 | 0.088 | 0.163 | 0.547 | 0.000 | ||
| 1 spectrum, AAVLQELATHLHPAEPDEGDSDAAR | 0.000 | 0.000 | 0.000 | 0.097 | 0.058 | 0.000 | 0.845 | 0.000 | ||
| 1 spectrum, NSESFAAWCR | 0.000 | 0.000 | 0.128 | 0.027 | 0.107 | 0.000 | 0.737 | 0.000 | ||
| 1 spectrum, YKPLSPSAVVR | 0.000 | 0.000 | 0.246 | 0.000 | 0.297 | 0.000 | 0.456 | 0.000 | ||
| 1 spectrum, SFAPGSAALSTYTPENLLNK | 0.000 | 0.000 | 0.000 | 0.215 | 0.000 | 0.059 | 0.726 | 0.000 | ||
| 1 spectrum, LEVSNSFLTDASQGR | 0.098 | 0.000 | 0.284 | 0.000 | 0.000 | 0.248 | 0.370 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
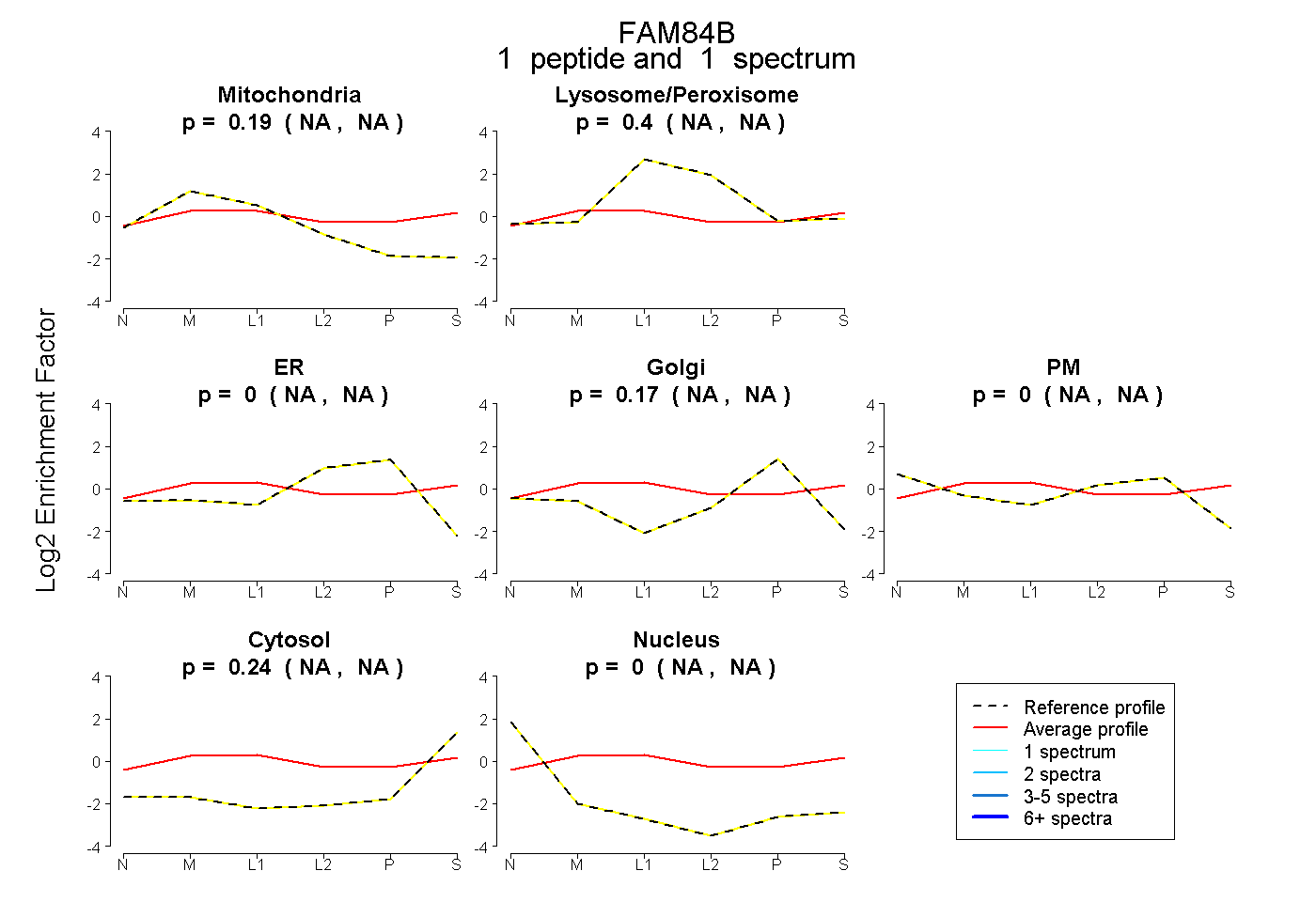 |
0.188 NA | NA |
0.400 NA | NA |
0.000 NA | NA |
0.175 NA | NA |
0.000 NA | NA |
0.237 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
10 spectra |
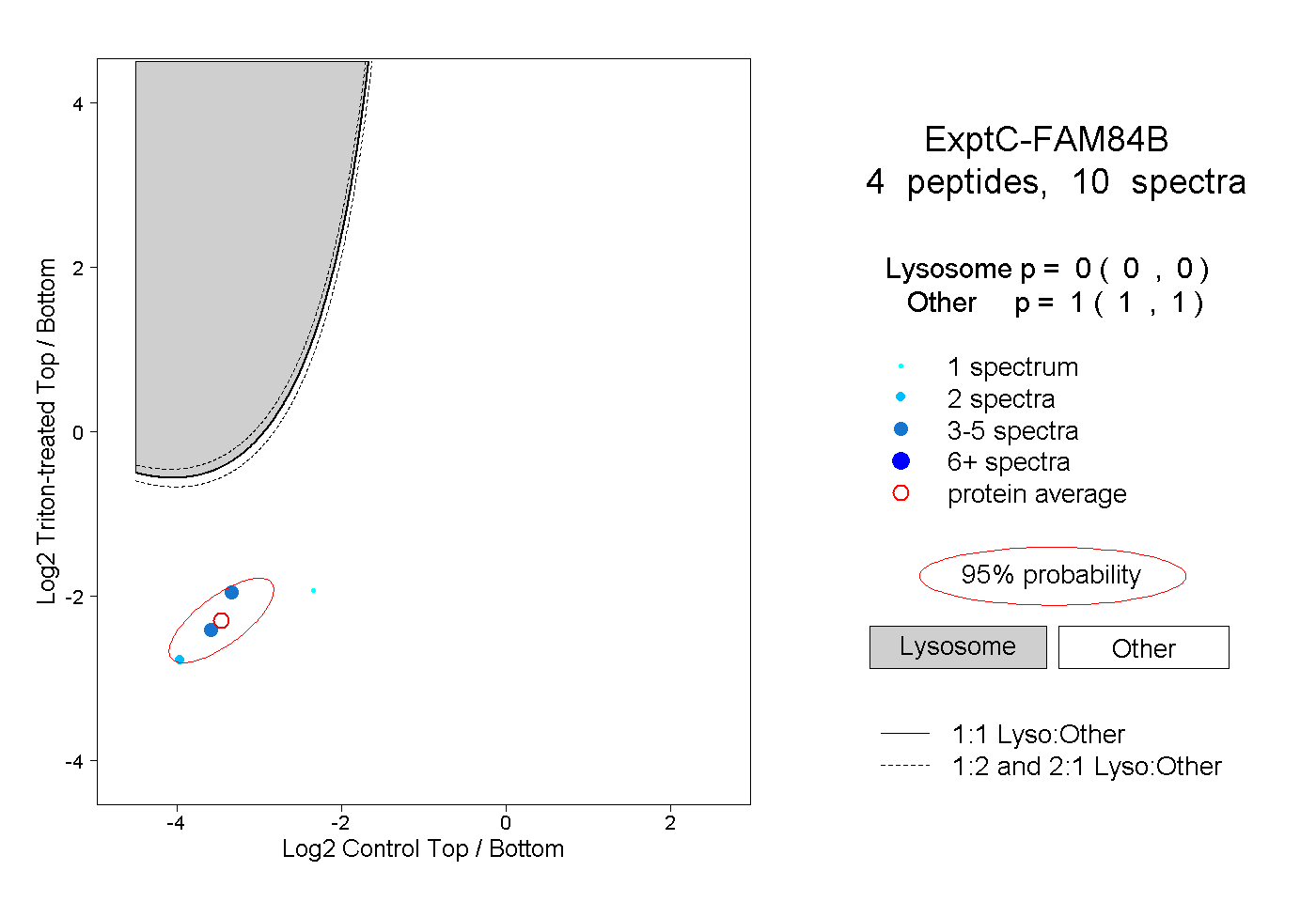 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |