peptides
spectra
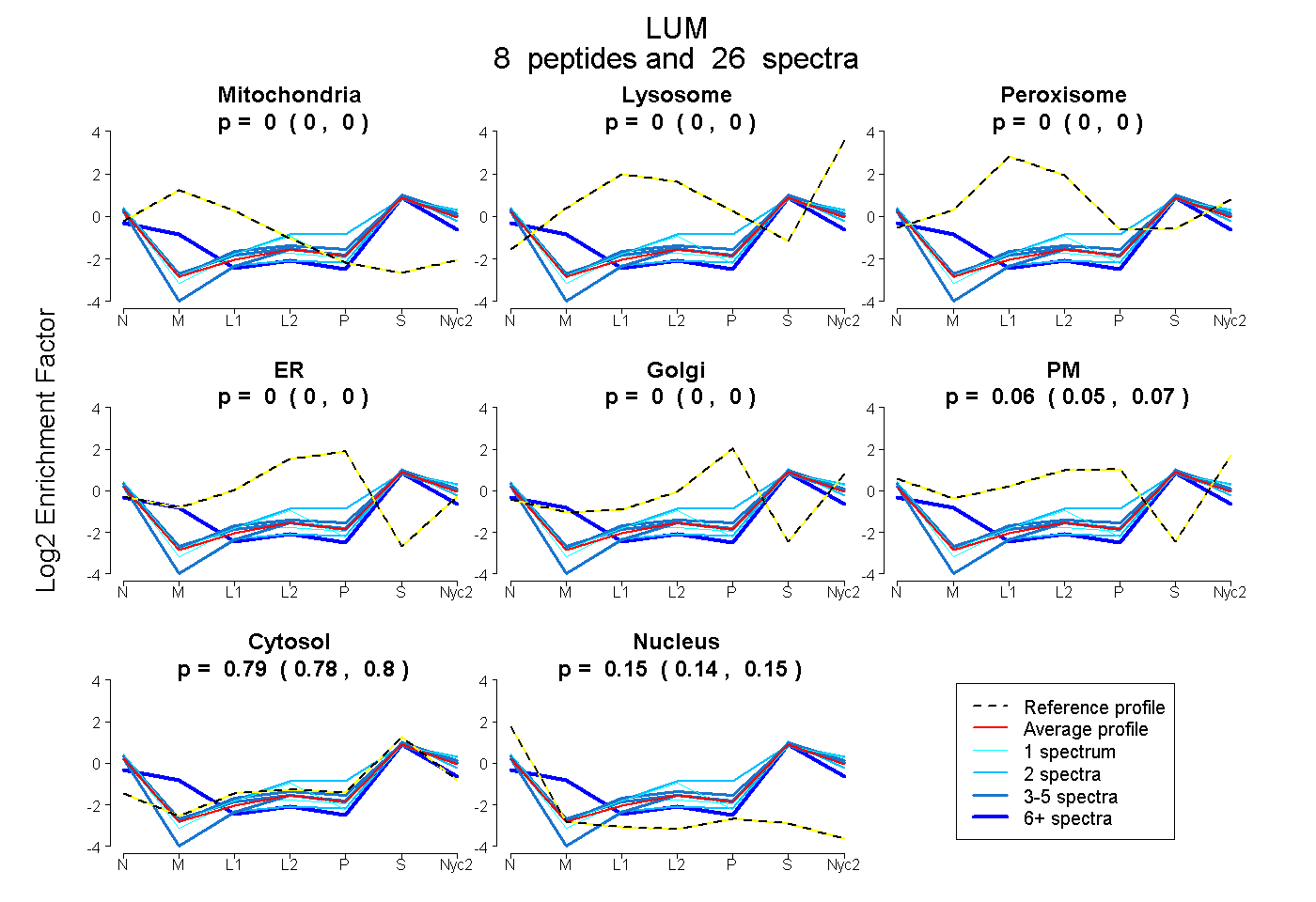
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.050 | 0.069
0.784 | 0.798
0.142 | 0.153
peptides
spectra
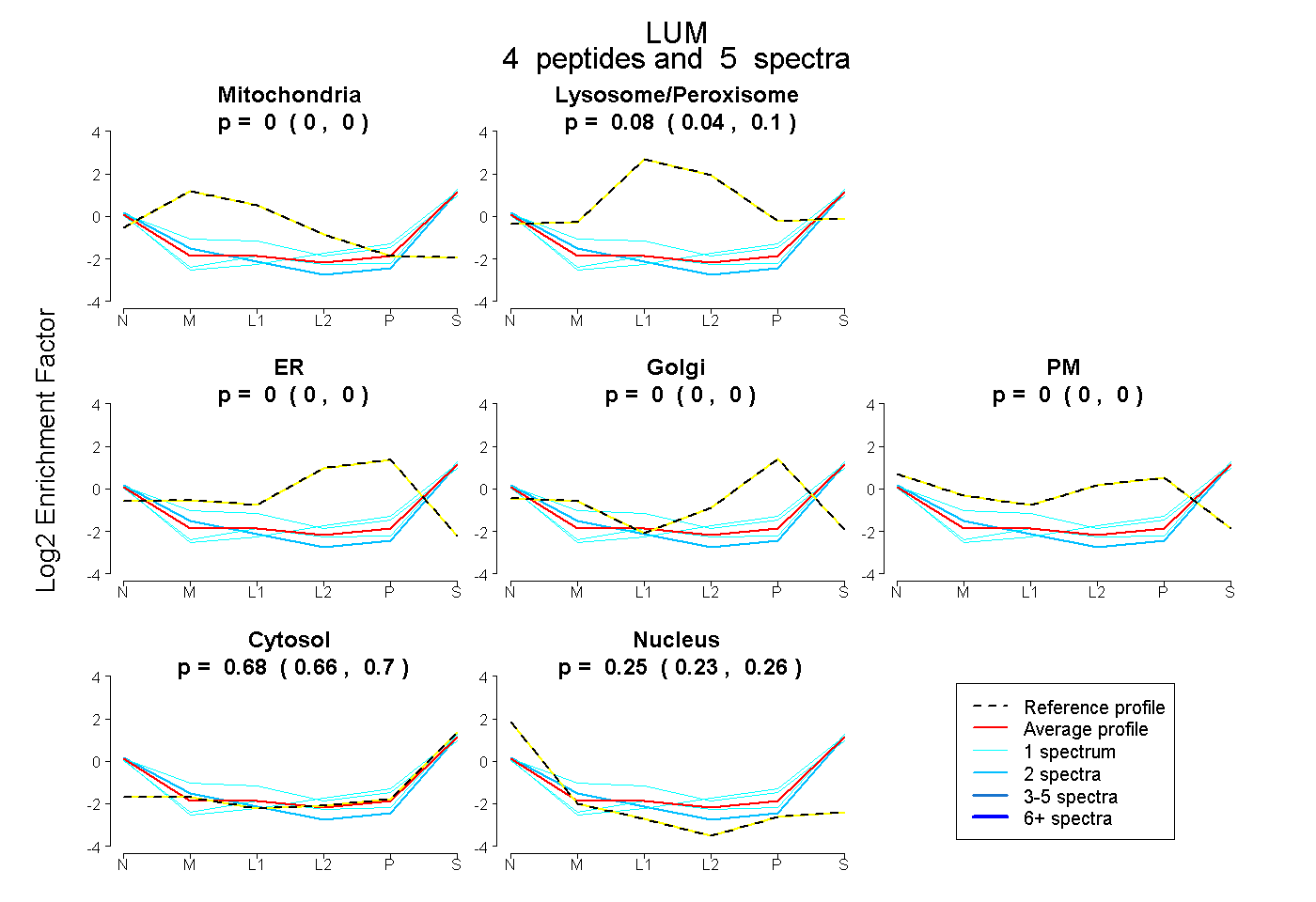
0.000 | 0.000
0.044 | 0.102
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.656 | 0.698
0.231 | 0.259
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
26 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.060 0.050 | 0.069 |
0.792 0.784 | 0.798 |
0.149 0.142 | 0.153 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
5 spectra |
 |
0.000 0.000 | 0.000 |
0.076 0.044 | 0.102 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.679 0.656 | 0.698 |
0.246 0.231 | 0.259 |
| 1 spectrum, SLQDLQLANNK | 0.000 | 0.212 | 0.000 | 0.000 | 0.000 | 0.563 | 0.225 | |||
| 2 spectra, FTGLQYLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.700 | 0.300 | |||
| 1 spectrum, ITNIPDEYFNR | 0.000 | 0.036 | 0.000 | 0.000 | 0.000 | 0.722 | 0.242 | |||
| 1 spectrum, NNQIDHIDEK | 0.000 | 0.030 | 0.000 | 0.000 | 0.064 | 0.723 | 0.183 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
23 spectra |
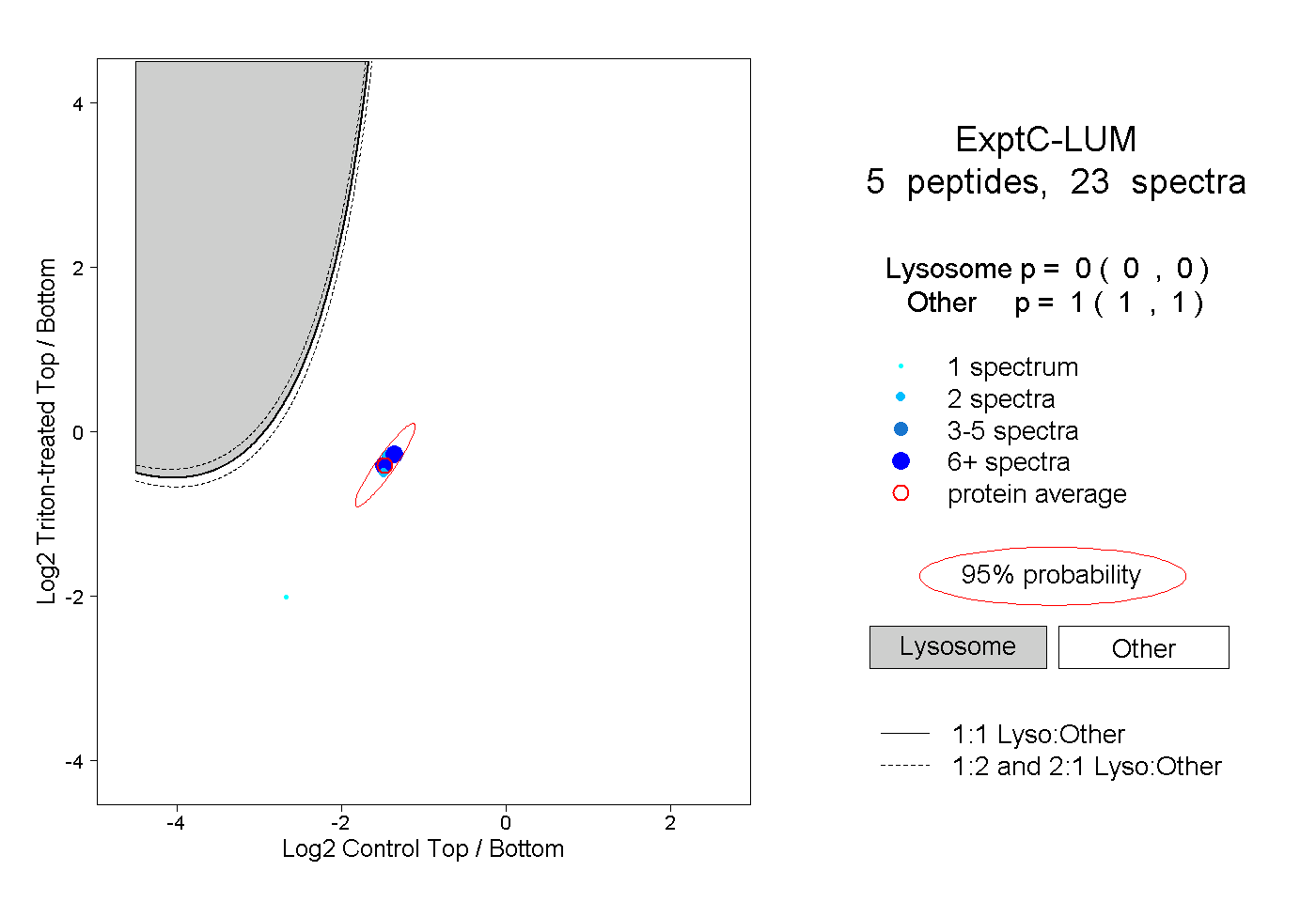 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
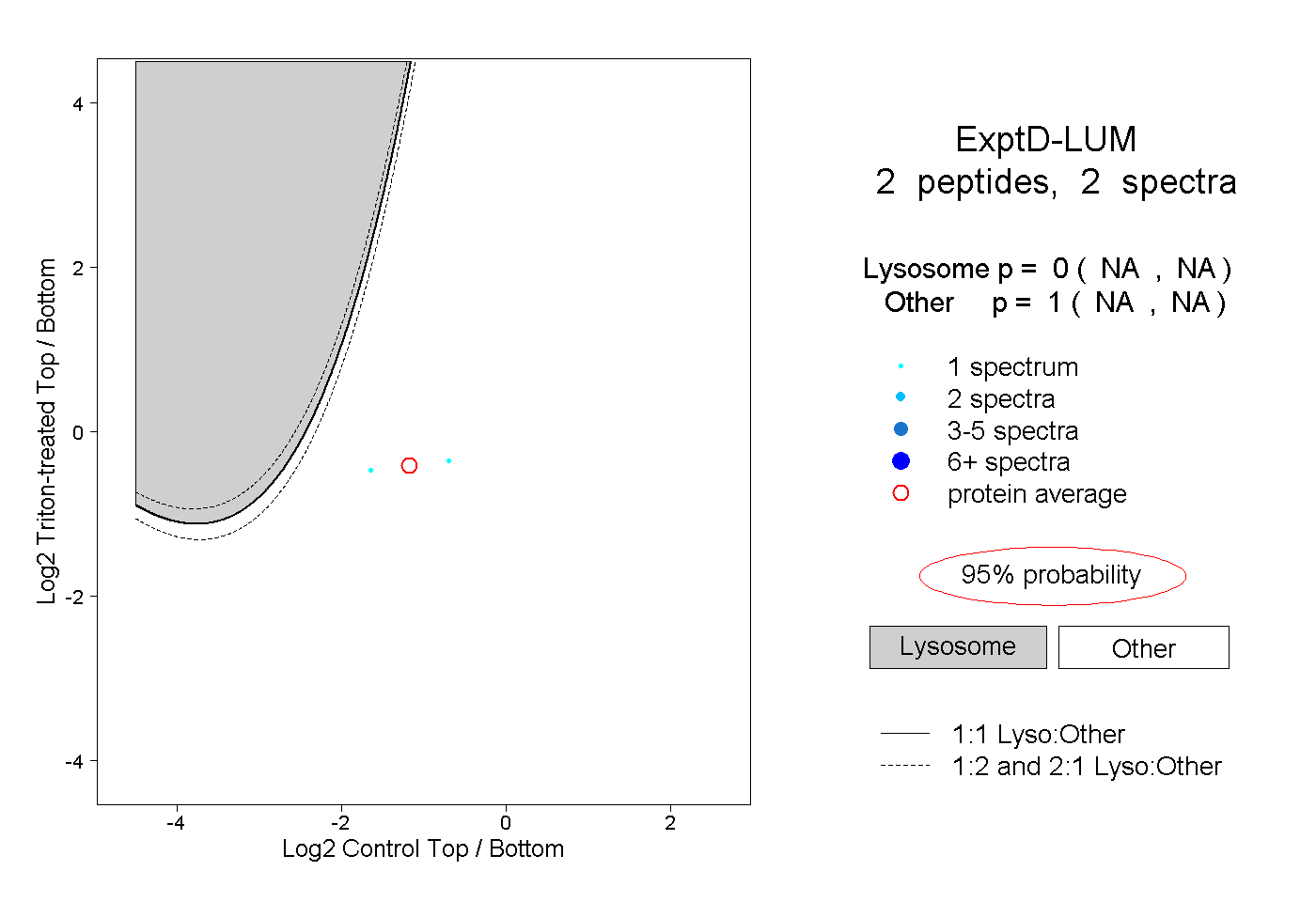 |
0.000 NA | NA |
1.000 NA | NA |