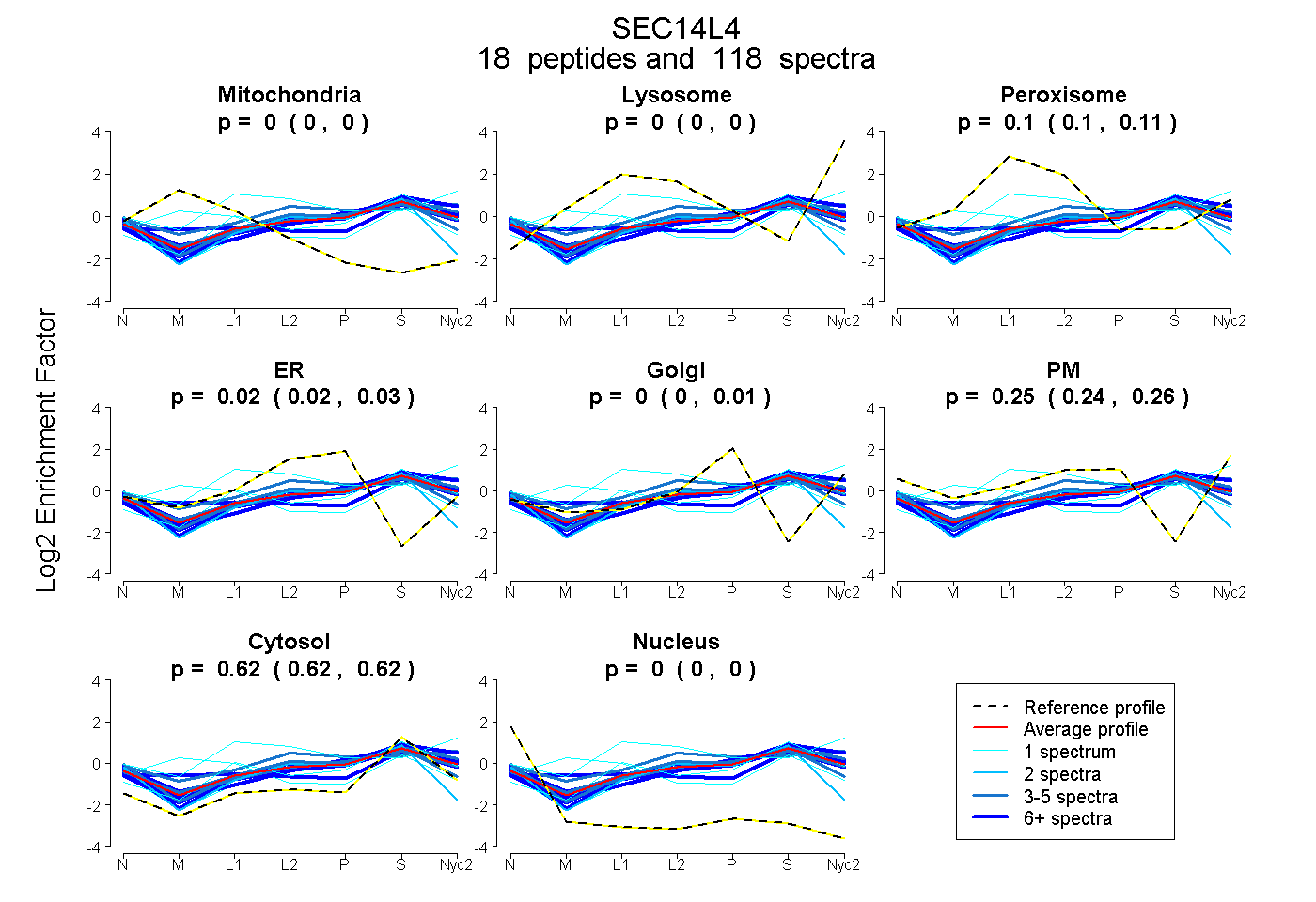
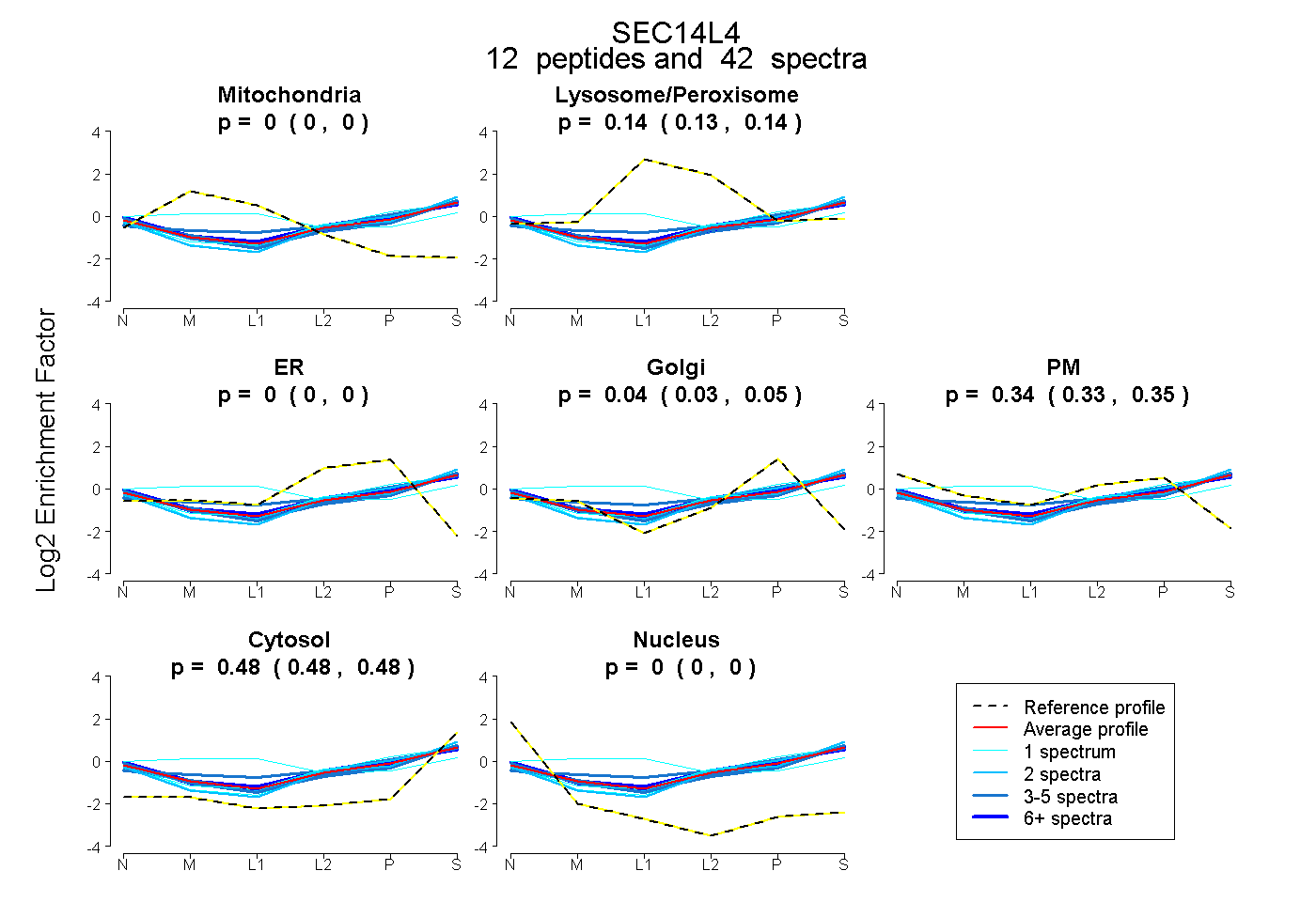
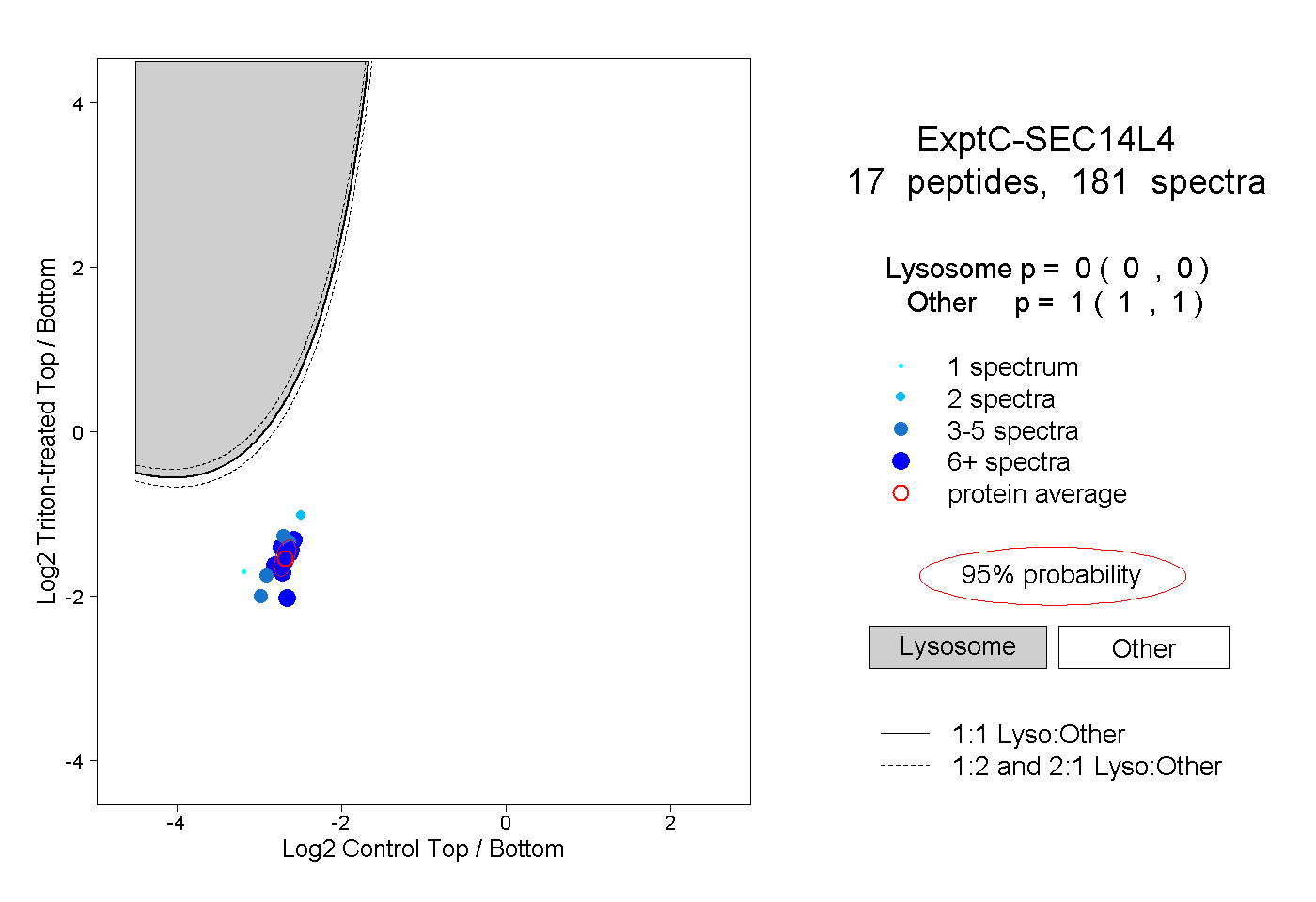
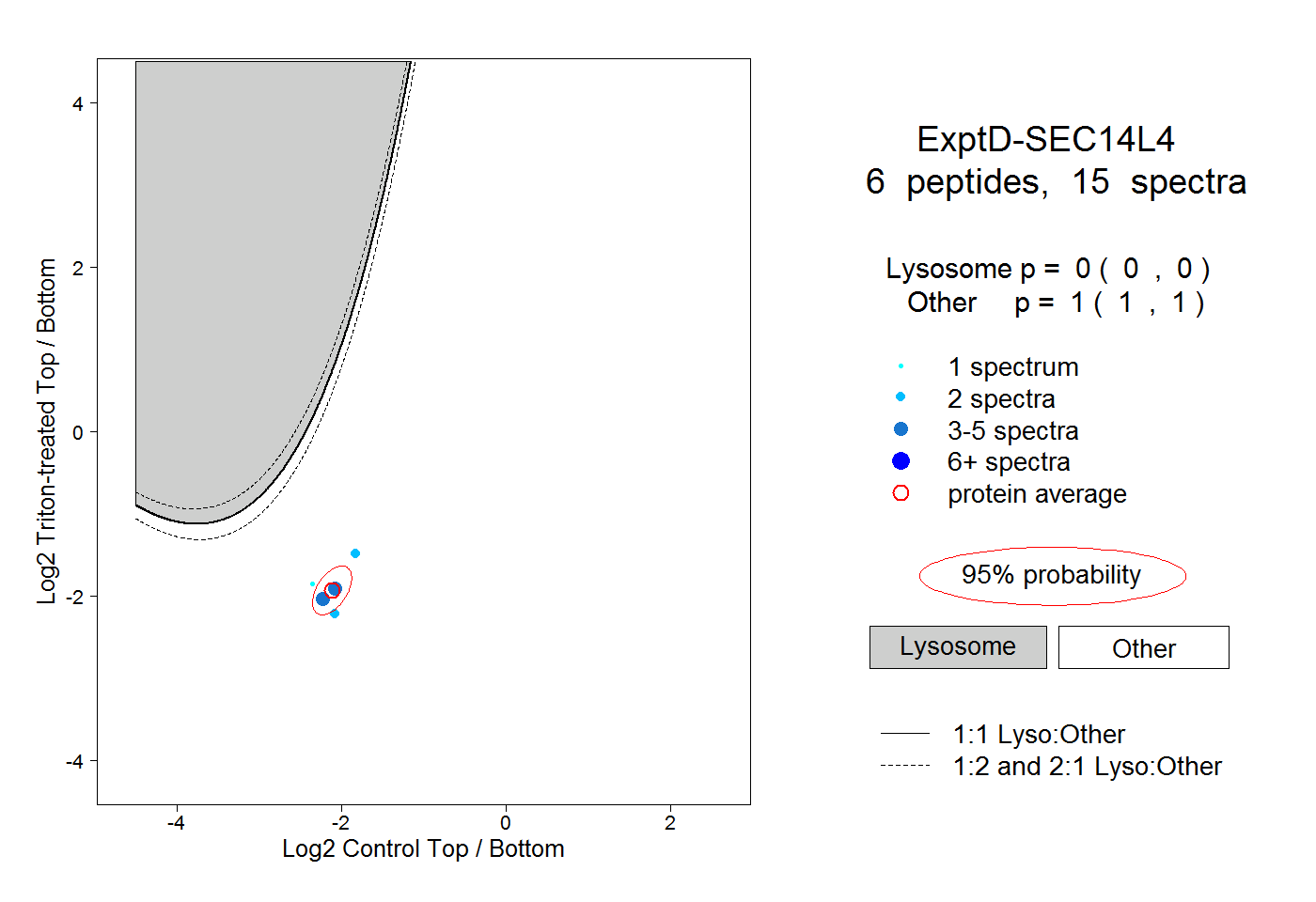
| 1 spectrum, SGQVGDLSPQQQEALTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GSSHQVENEILFPGCVLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EILQDVLPTLPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VGYTAEVLLPDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, IVILGGNWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 21 spectra, ADDFFLLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NQQDLDHILTWQPPEVIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, AGEMTEVLPNQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 30 spectra, GLFMSASK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, VCEMLLHECELQSQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, SEDMLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, SFIGEVTQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, TGVYVLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, YNSHMVPEDGSLTCLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, LFPVAFNLVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, MVMVFDMEGLSLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, INYGGDVPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |