peptides
spectra
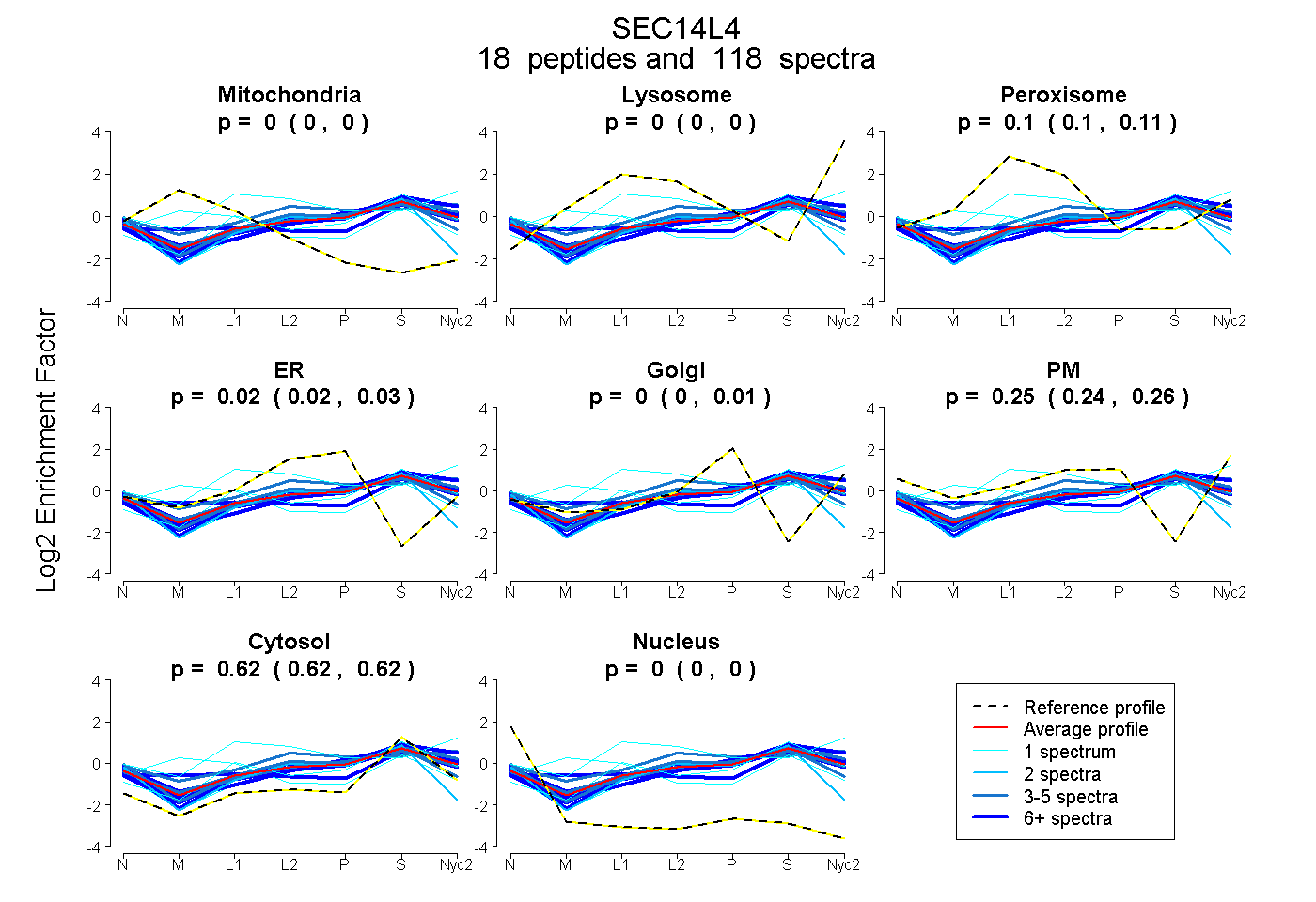
0.000 | 0.000
0.000 | 0.000
0.099 | 0.106
0.015 | 0.031
0.000 | 0.006
0.244 | 0.260
0.616 | 0.621
0.000 | 0.000
peptides
spectra
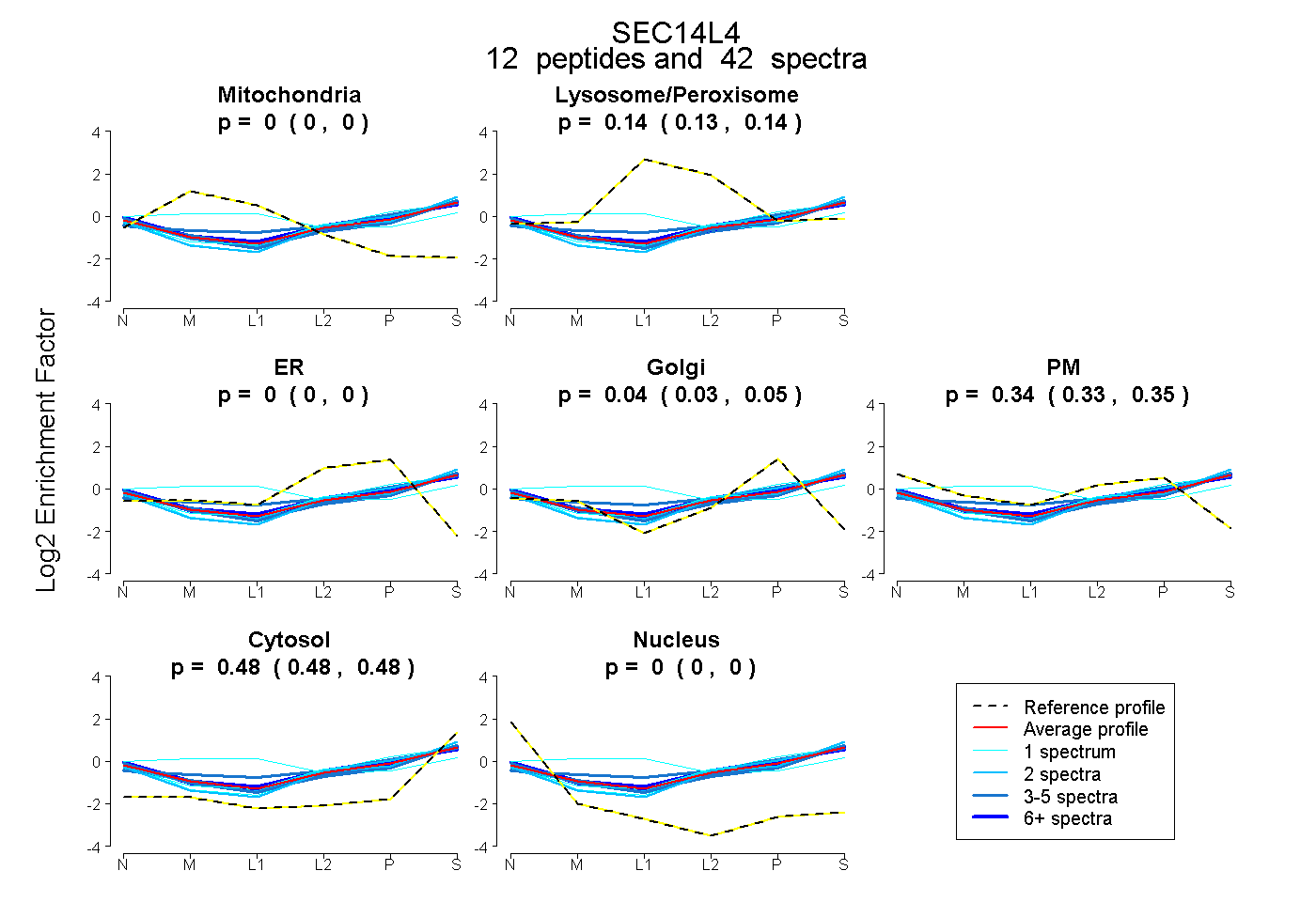
0.000 | 0.000
0.130 | 0.141
0.000 | 0.000
0.027 | 0.047
0.331 | 0.354
0.479 | 0.485
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
118 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.103 0.099 | 0.106 |
0.025 0.015 | 0.031 |
0.000 0.000 | 0.006 |
0.254 0.244 | 0.260 |
0.619 0.616 | 0.621 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
42 spectra |
 |
0.000 0.000 | 0.000 |
0.136 0.130 | 0.141 |
0.000 0.000 | 0.000 |
0.038 0.027 | 0.047 |
0.344 0.331 | 0.354 |
0.482 0.479 | 0.485 |
0.000 0.000 | 0.000 |
| 1 spectrum, VCEMLLHECELQSQK | 0.000 | 0.176 | 0.000 | 0.053 | 0.251 | 0.520 | 0.000 | |||
| 1 spectrum, SGQVGDLSPQQQEALTR | 0.165 | 0.289 | 0.000 | 0.000 | 0.250 | 0.296 | 0.000 | |||
| 1 spectrum, EILQDVLPTLPK | 0.000 | 0.105 | 0.008 | 0.121 | 0.261 | 0.506 | 0.000 | |||
| 2 spectra, VGYTAEVLLPDK | 0.000 | 0.081 | 0.021 | 0.000 | 0.329 | 0.569 | 0.000 | |||
| 2 spectra, SFIGEVTQK | 0.000 | 0.146 | 0.000 | 0.117 | 0.270 | 0.467 | 0.000 | |||
| 2 spectra, IVILGGNWK | 0.000 | 0.091 | 0.000 | 0.000 | 0.399 | 0.510 | 0.000 | |||
| 14 spectra, ADDFFLLR | 0.000 | 0.144 | 0.000 | 0.051 | 0.368 | 0.438 | 0.000 | |||
| 5 spectra, TGVYVLR | 0.000 | 0.086 | 0.000 | 0.000 | 0.389 | 0.525 | 0.000 | |||
| 3 spectra, NQQDLDHILTWQPPEVIR | 0.000 | 0.300 | 0.000 | 0.259 | 0.047 | 0.393 | 0.000 | |||
| 3 spectra, AGEMTEVLPNQR | 0.000 | 0.127 | 0.000 | 0.058 | 0.278 | 0.537 | 0.000 | |||
| 7 spectra, LFPVAFNLVK | 0.000 | 0.099 | 0.000 | 0.000 | 0.414 | 0.487 | 0.000 | |||
| 1 spectrum, INYGGDVPK | 0.000 | 0.085 | 0.000 | 0.122 | 0.335 | 0.458 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
181 spectra |
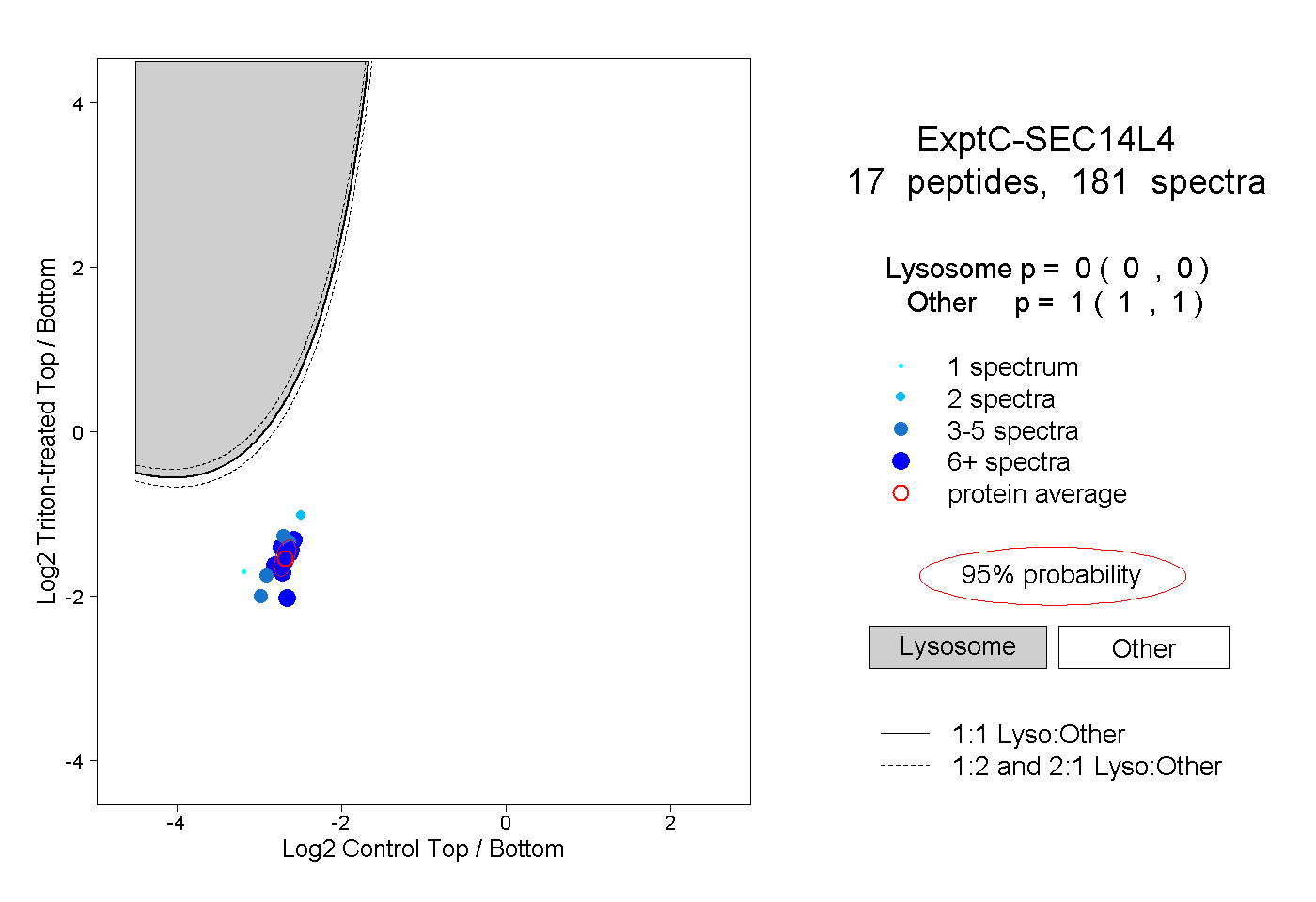 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
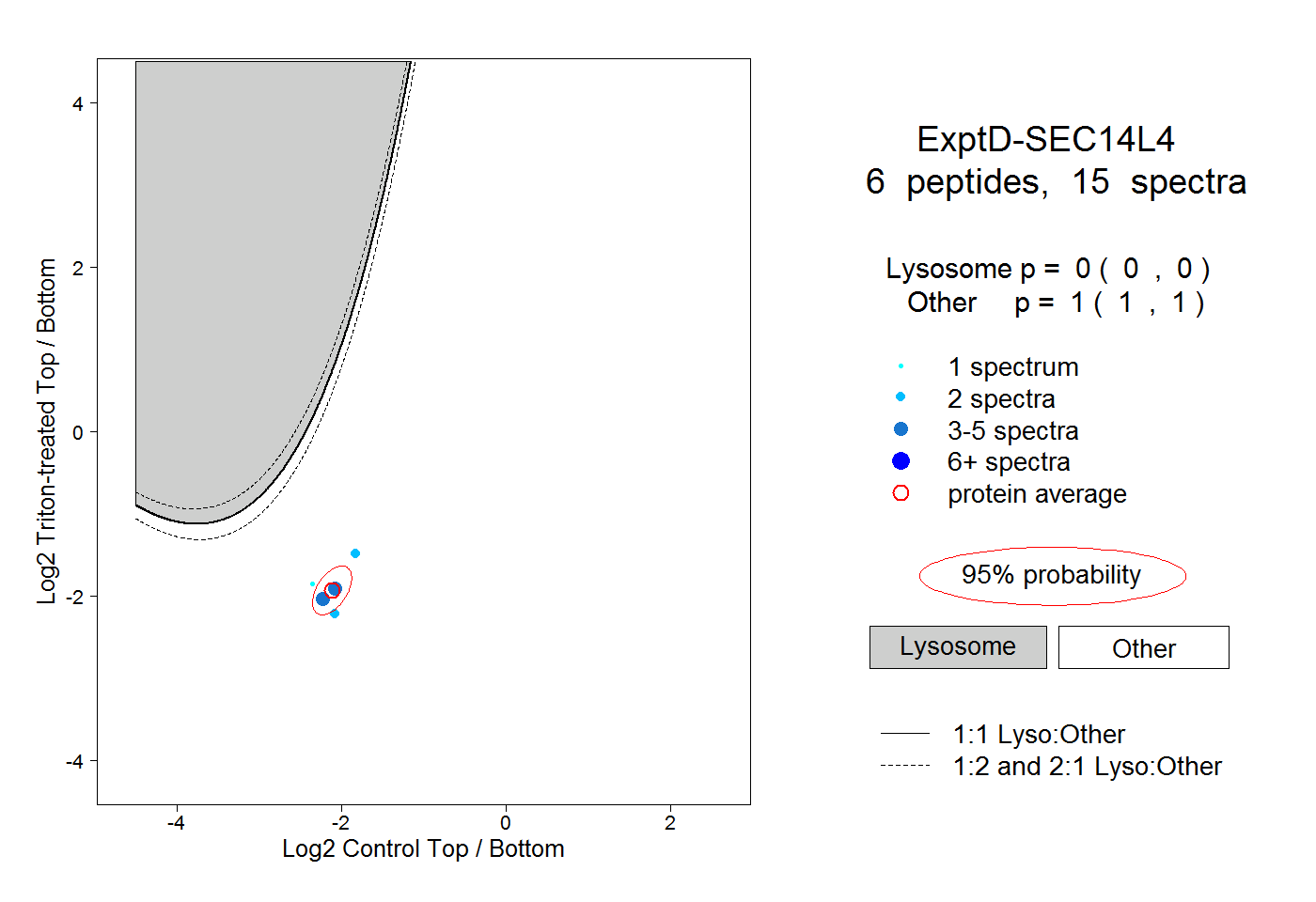 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |