peptides
spectra
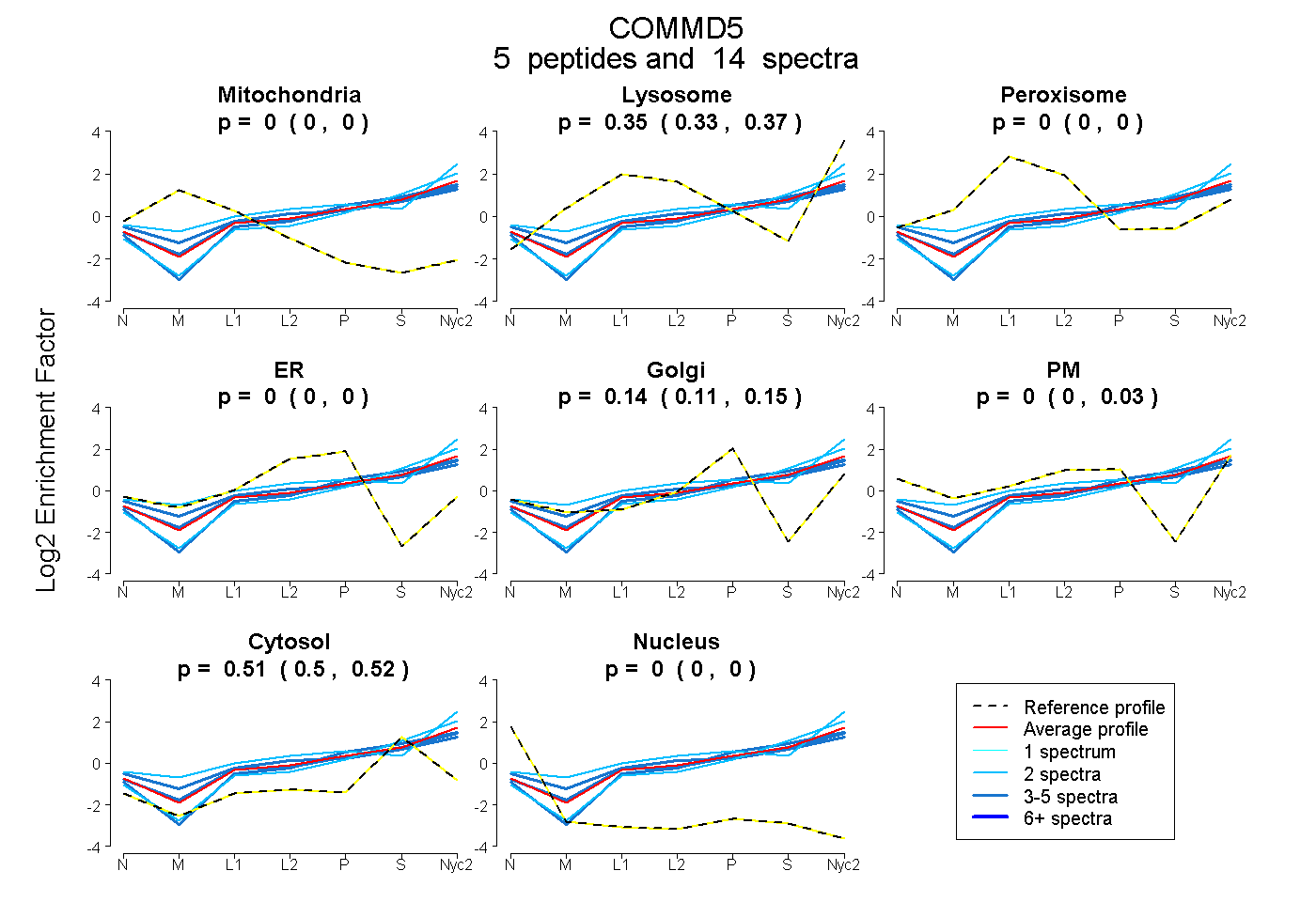
0.000 | 0.000
0.327 | 0.365
0.000 | 0.000
0.000 | 0.000
0.114 | 0.150
0.000 | 0.028
0.496 | 0.524
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
0.350 0.327 | 0.365 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.140 0.114 | 0.150 |
0.000 0.000 | 0.028 |
0.510 0.496 | 0.524 |
0.000 0.000 | 0.000 |
| 2 spectra, VDVAISTSAQSR | 0.000 | 0.320 | 0.000 | 0.000 | 0.065 | 0.000 | 0.614 | 0.000 | ||
| 4 spectra, LVVGALHGK | 0.000 | 0.242 | 0.000 | 0.000 | 0.169 | 0.000 | 0.589 | 0.000 | ||
| 3 spectra, EMAELEK | 0.000 | 0.332 | 0.000 | 0.000 | 0.140 | 0.000 | 0.529 | 0.000 | ||
| 2 spectra, SLQPSVLMQLK | 0.000 | 0.457 | 0.000 | 0.000 | 0.016 | 0.200 | 0.327 | 0.000 | ||
| 3 spectra, EAVEQLGASANLSEER | 0.000 | 0.285 | 0.000 | 0.000 | 0.000 | 0.215 | 0.499 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
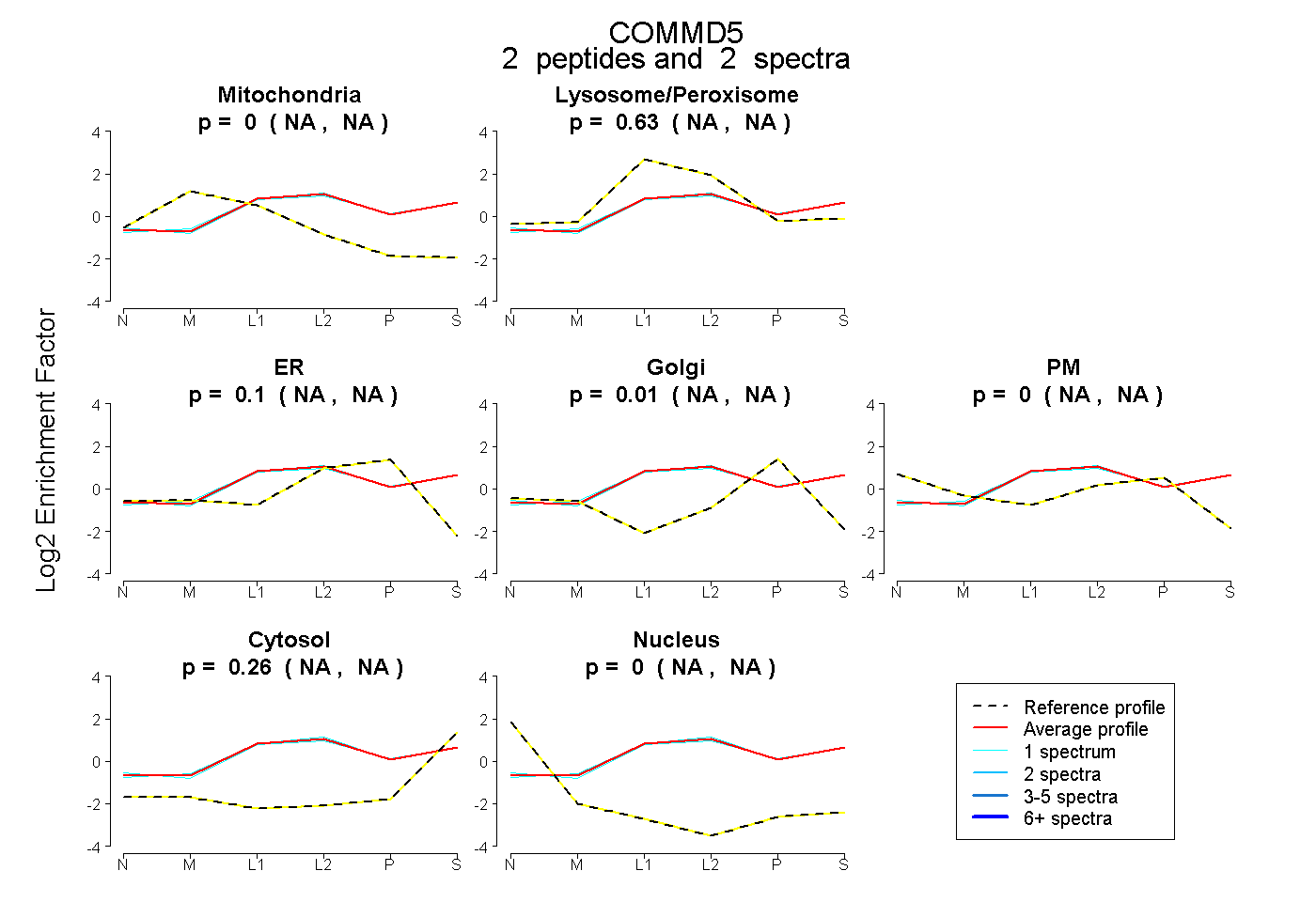 |
0.000 NA | NA |
0.630 NA | NA |
0.097 NA | NA |
0.015 NA | NA |
0.000 NA | NA |
0.259 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
21 spectra |
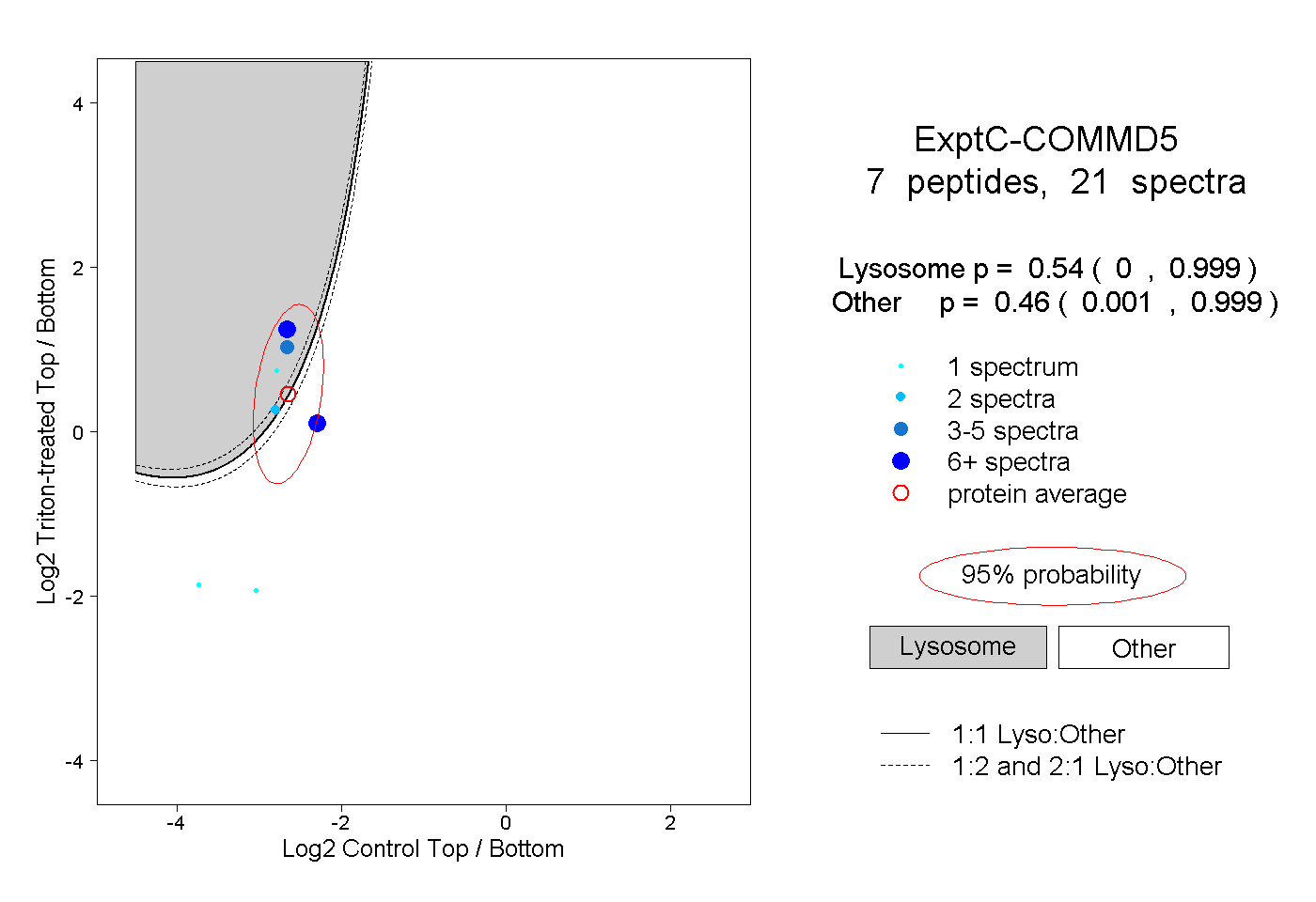 |
0.540 0.000 | 0.999 |
0.460 0.001 | 0.999 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
2 spectra |
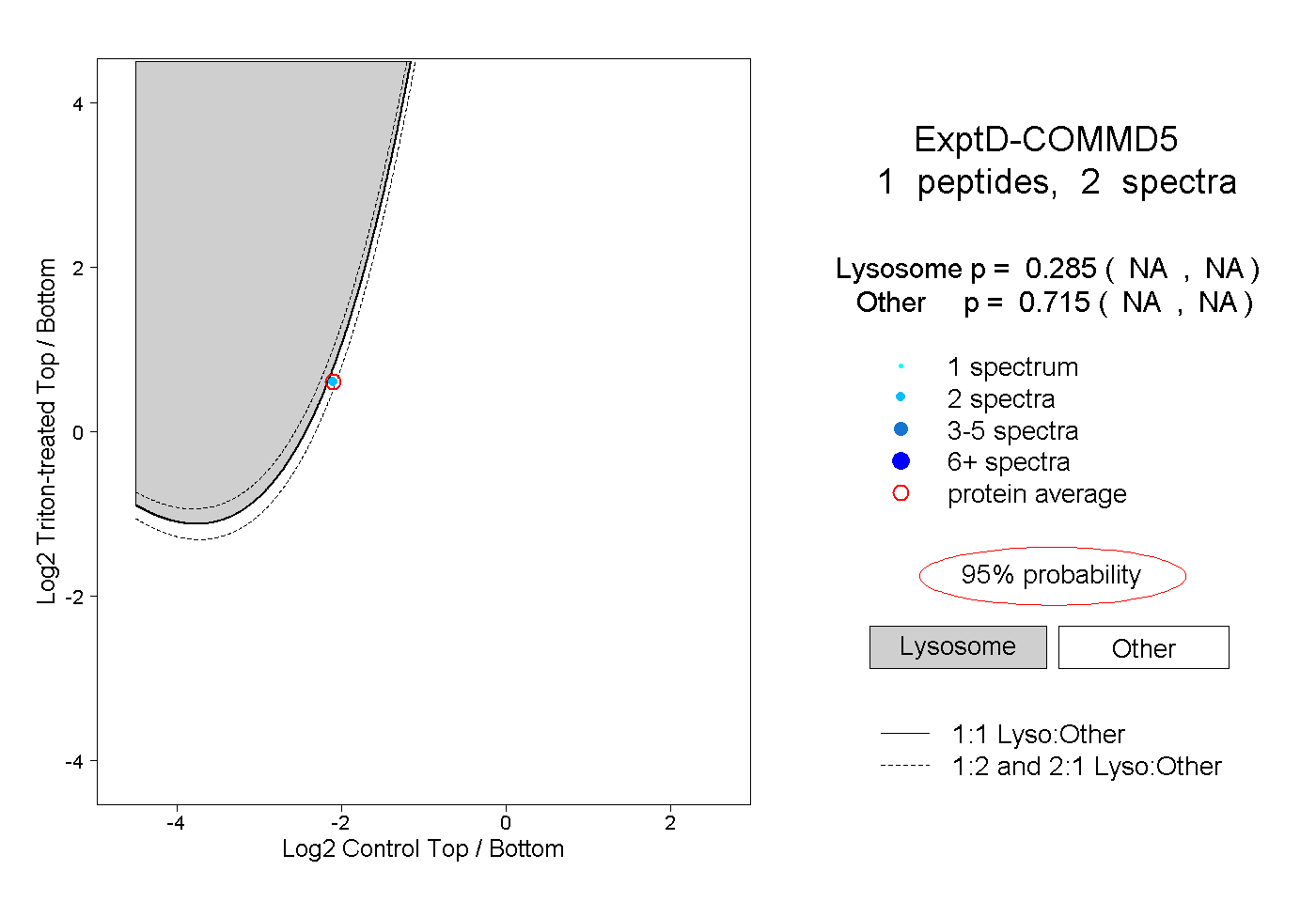 |
0.285 NA | NA |
0.715 NA | NA |