peptides
spectra
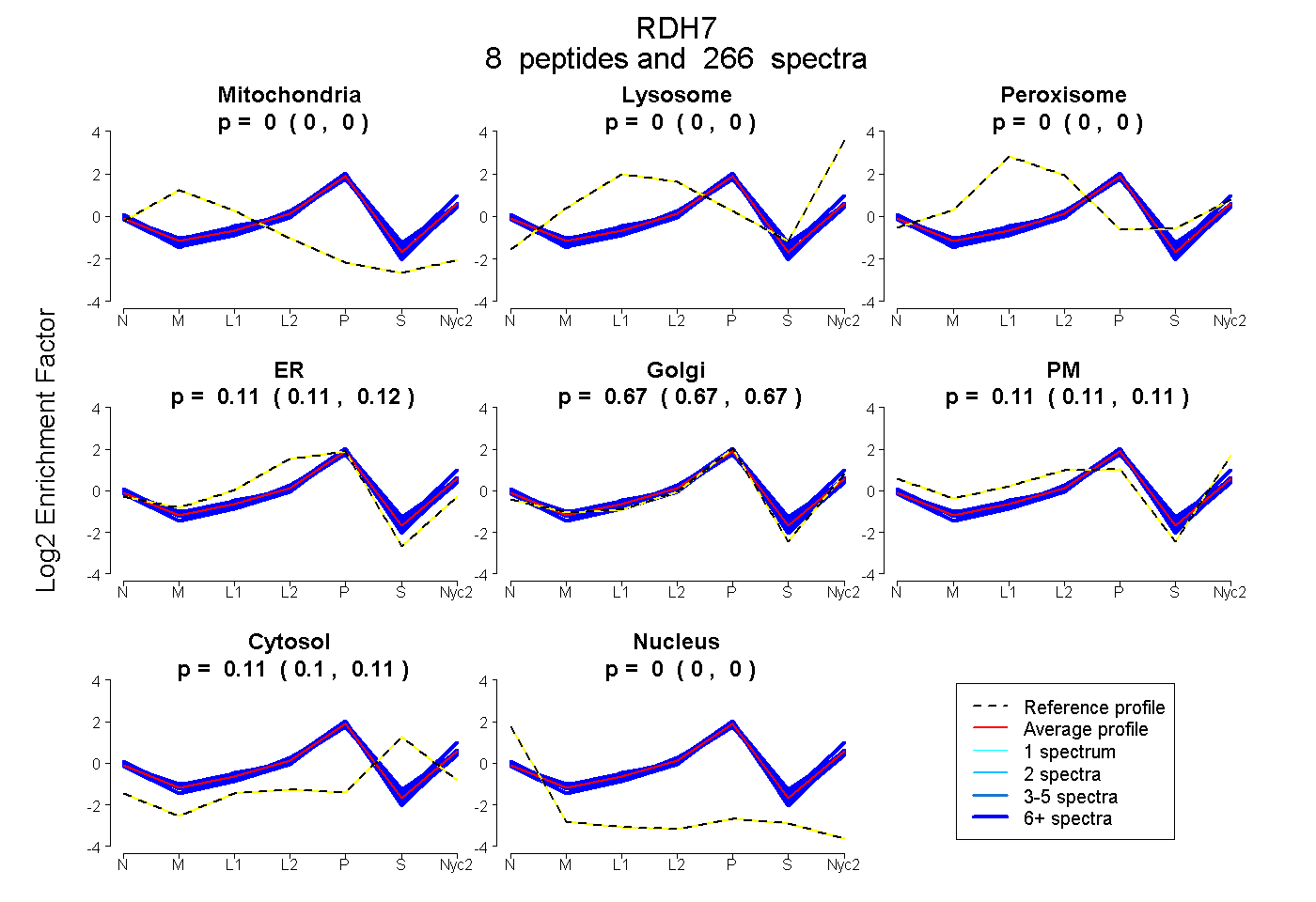
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.110 | 0.115
0.666 | 0.672
0.109 | 0.114
0.104 | 0.107
0.000 | 0.000
peptides
spectra
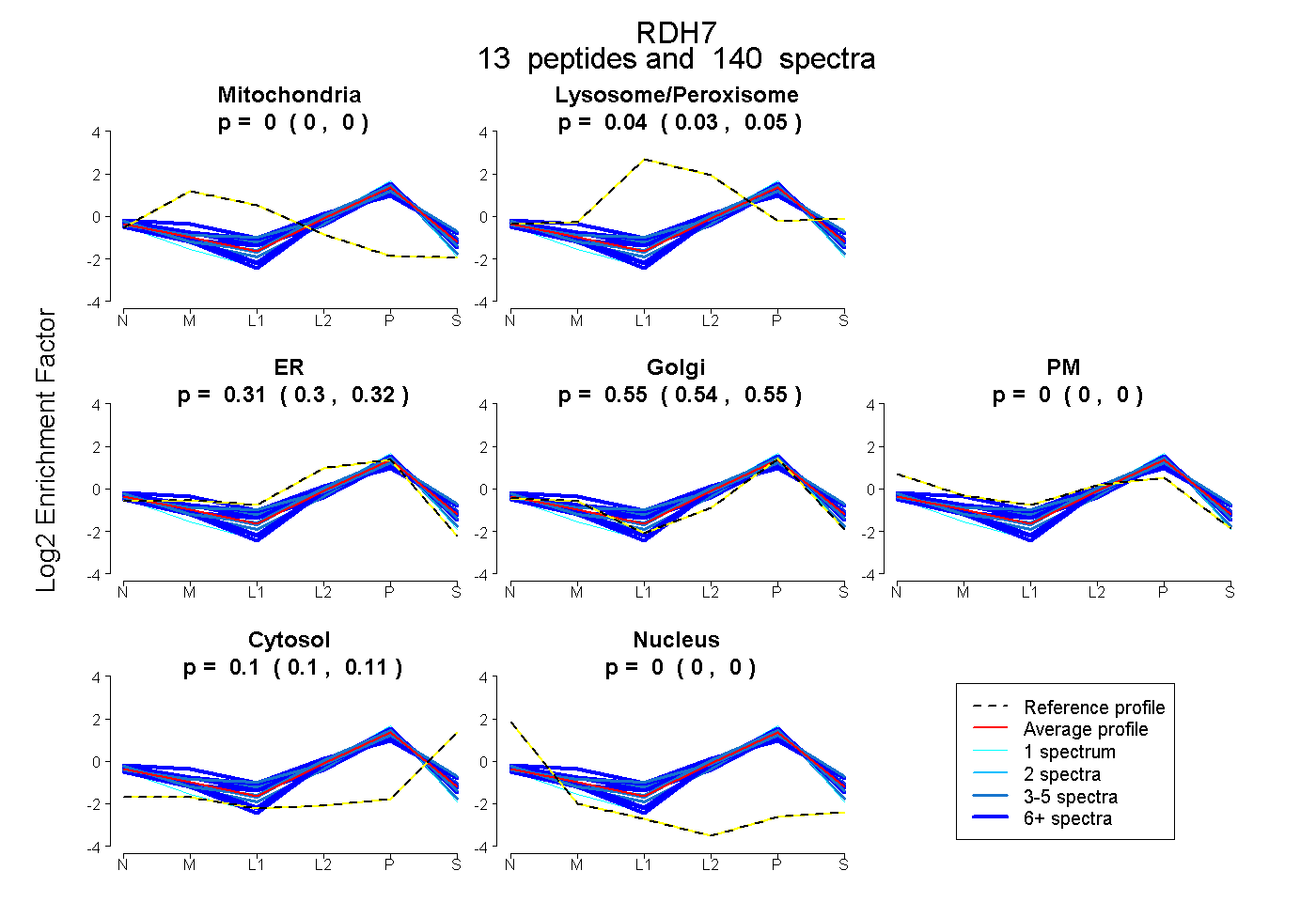
0.000 | 0.000
0.032 | 0.046
0.298 | 0.322
0.537 | 0.555
0.000 | 0.000
0.098 | 0.106
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
266 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.113 0.110 | 0.115 |
0.669 0.666 | 0.672 |
0.112 0.109 | 0.114 |
0.106 0.104 | 0.107 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
140 spectra |
 |
0.000 0.000 | 0.000 |
0.040 0.032 | 0.046 |
0.311 0.298 | 0.322 |
0.547 0.537 | 0.555 |
0.000 0.000 | 0.000 |
0.102 0.098 | 0.106 |
0.000 0.000 | 0.000 |
| 7 spectra, YGVEAFSDSLR | 0.000 | 0.000 | 0.232 | 0.650 | 0.000 | 0.118 | 0.000 | |||
| 7 spectra, TESIVAATQWVK | 0.000 | 0.247 | 0.000 | 0.585 | 0.111 | 0.056 | 0.000 | |||
| 8 spectra, ELTYFGVK | 0.000 | 0.165 | 0.000 | 0.773 | 0.004 | 0.059 | 0.000 | |||
| 4 spectra, EIYGEK | 0.000 | 0.173 | 0.101 | 0.695 | 0.000 | 0.030 | 0.000 | |||
| 9 spectra, LETVILDVTK | 0.000 | 0.065 | 0.349 | 0.504 | 0.000 | 0.082 | 0.000 | |||
| 4 spectra, MSLLGGGYCISK | 0.000 | 0.000 | 0.464 | 0.400 | 0.000 | 0.136 | 0.000 | |||
| 1 spectrum, LWDQATEEVK | 0.000 | 0.000 | 0.190 | 0.810 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, TNVTNMER | 0.000 | 0.000 | 0.270 | 0.635 | 0.000 | 0.095 | 0.000 | |||
| 3 spectra, YSAGWDAK | 0.000 | 0.000 | 0.438 | 0.445 | 0.030 | 0.088 | 0.000 | |||
| 6 spectra, VAIIEPGGFK | 0.000 | 0.237 | 0.000 | 0.689 | 0.000 | 0.074 | 0.000 | |||
| 74 spectra, VVNIASTMGR | 0.000 | 0.000 | 0.186 | 0.757 | 0.000 | 0.058 | 0.000 | |||
| 5 spectra, YSPGWDAK | 0.000 | 0.251 | 0.000 | 0.663 | 0.000 | 0.085 | 0.000 | |||
| 3 spectra, LSDNLK | 0.000 | 0.000 | 0.226 | 0.747 | 0.000 | 0.006 | 0.021 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
380 spectra |
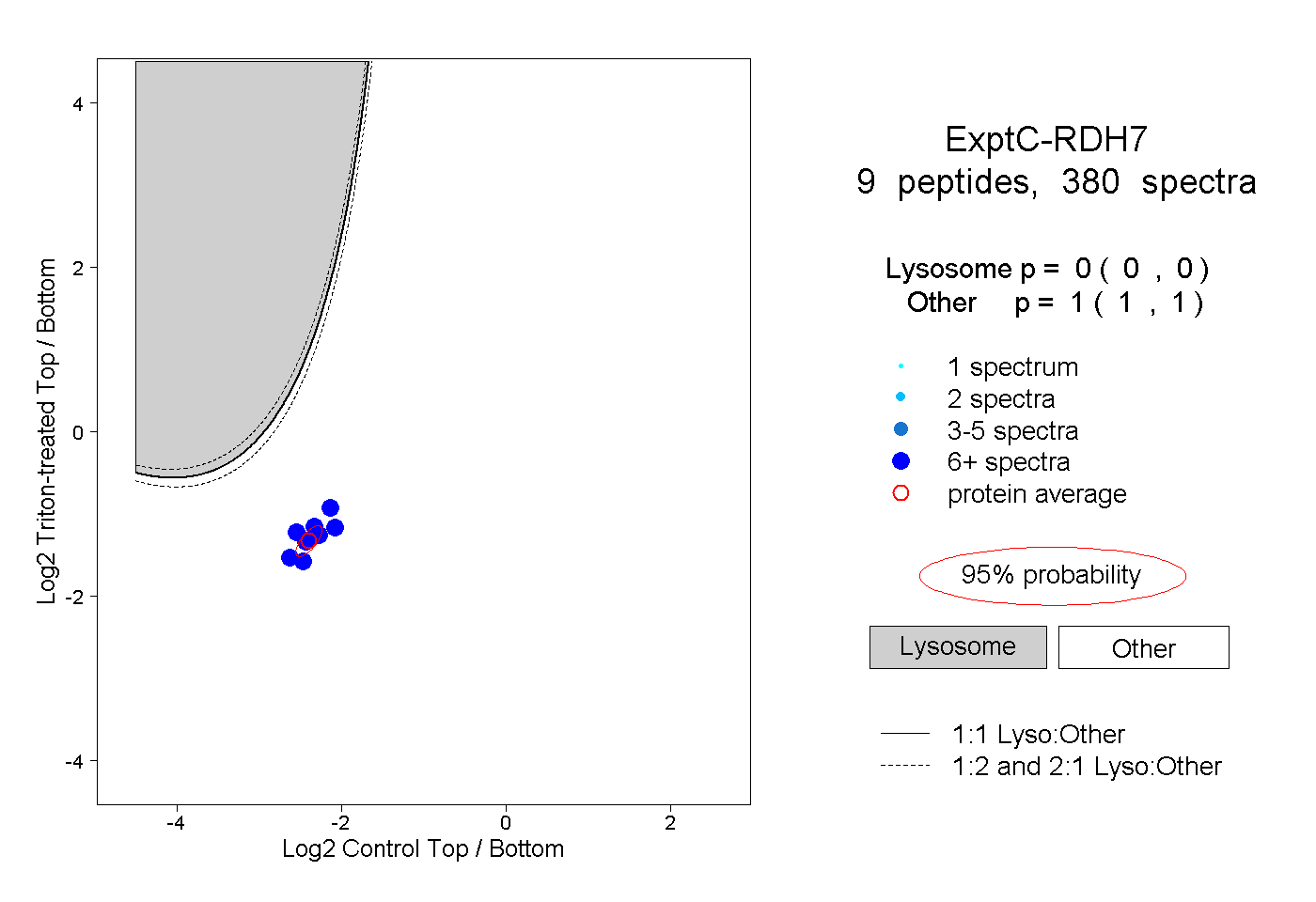 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
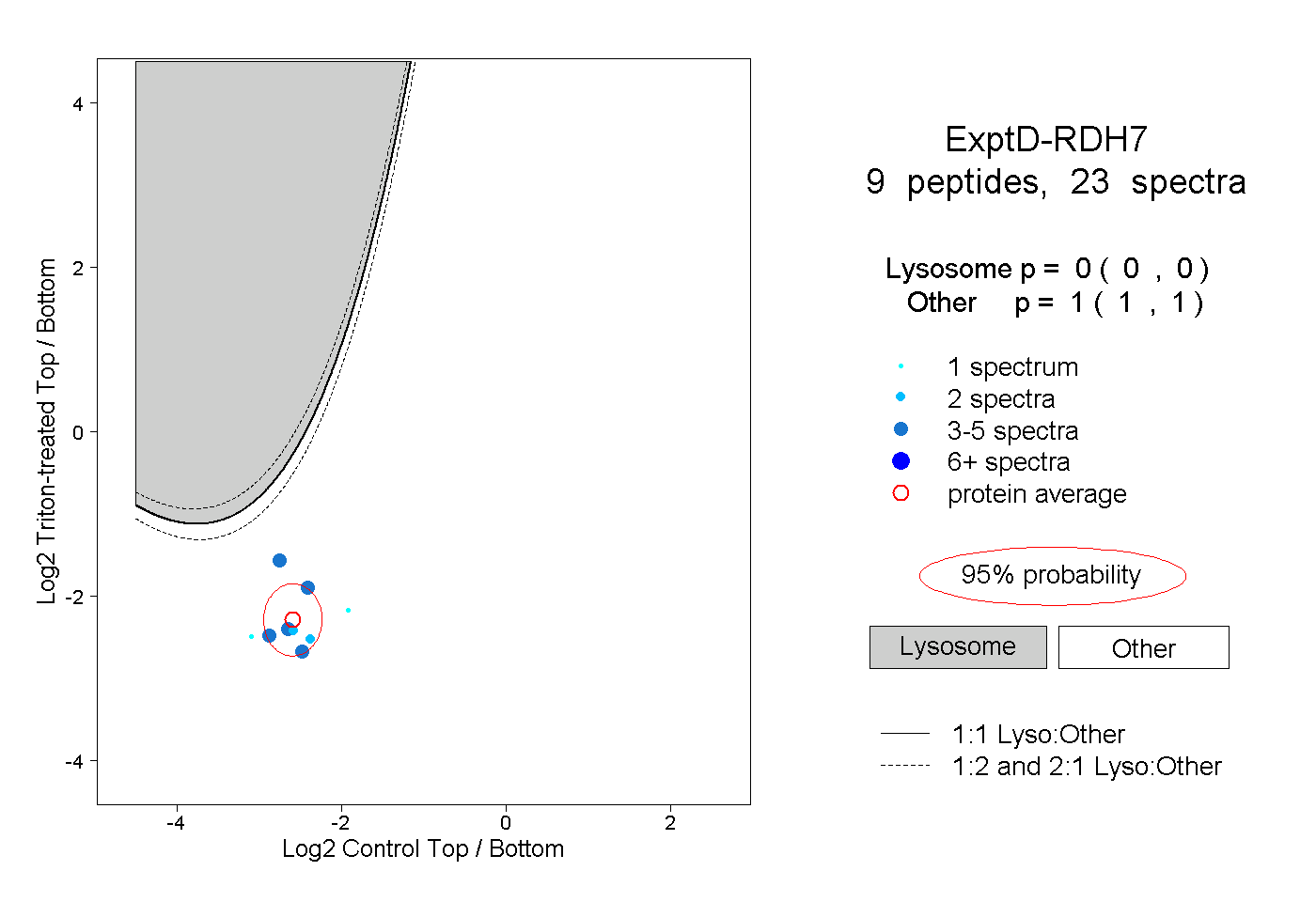 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |