peptides
spectra
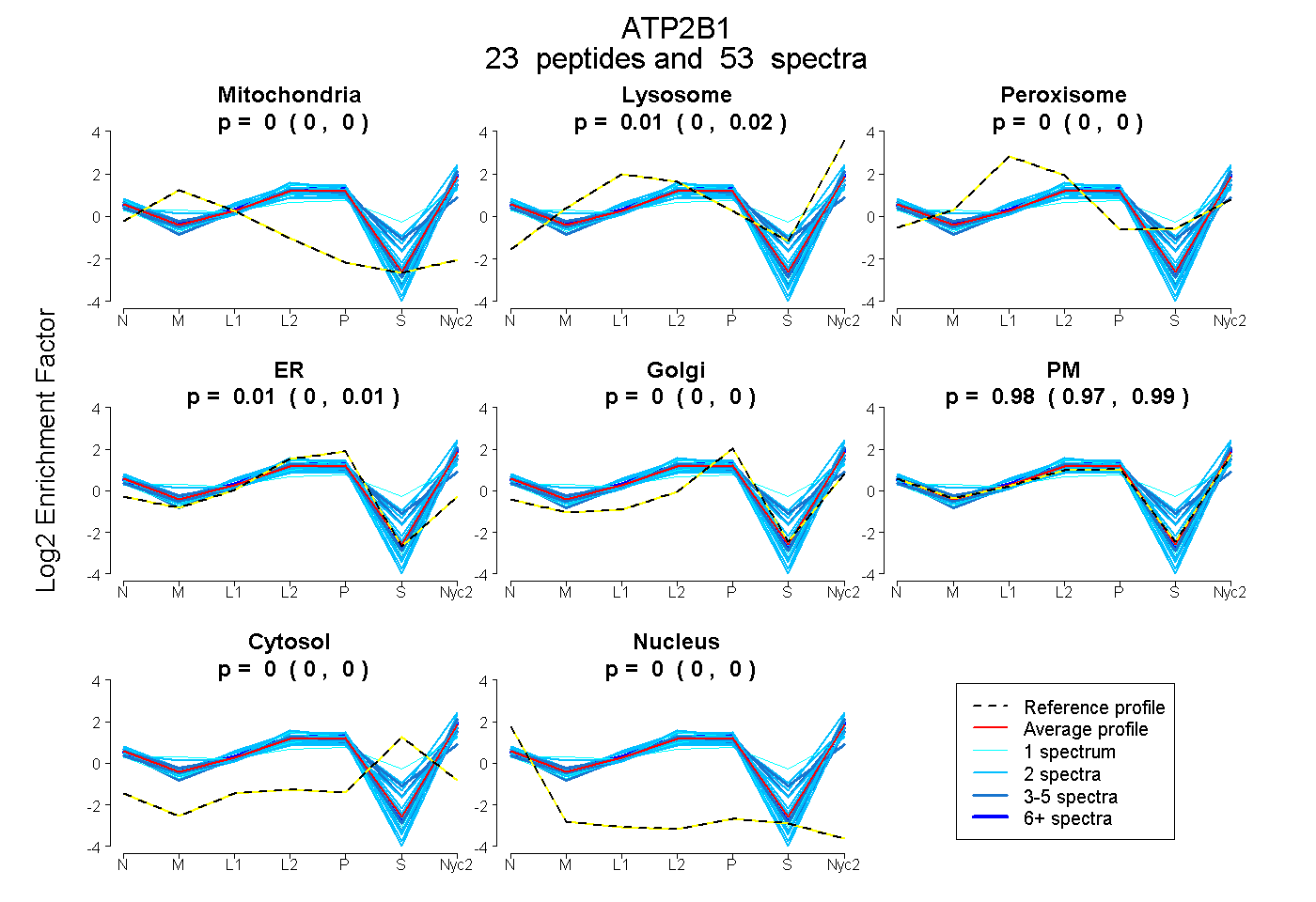
0.000 | 0.000
0.004 | 0.015
0.000 | 0.000
0.002 | 0.014
0.000 | 0.000
0.973 | 0.989
0.000 | 0.000
0.000 | 0.000
peptides
spectra
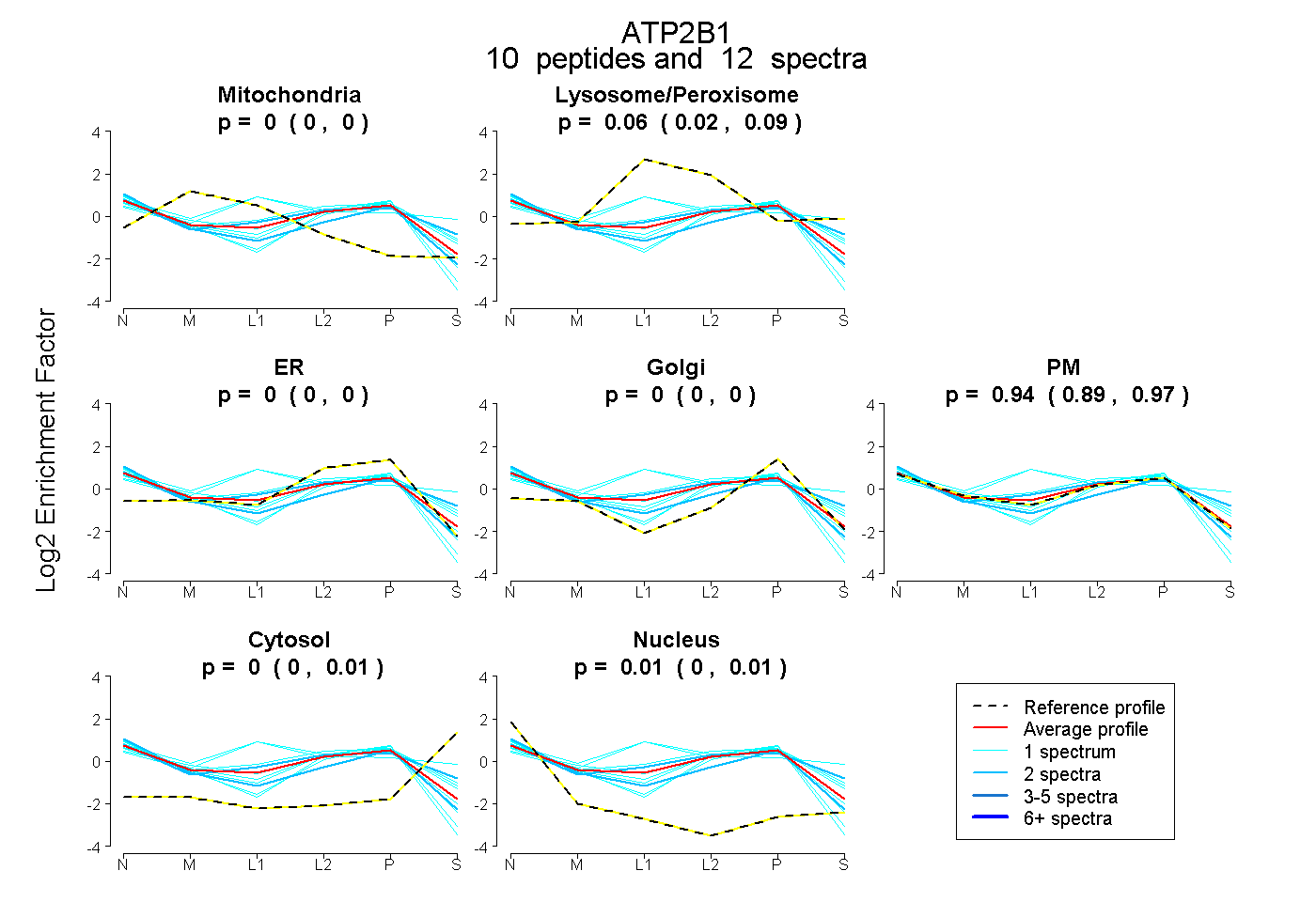
0.000 | 0.000
0.020 | 0.086
0.000 | 0.000
0.000 | 0.000
0.894 | 0.970
0.000 | 0.011
0.000 | 0.012
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
53 spectra |
 |
0.000 0.000 | 0.000 |
0.010 0.004 | 0.015 |
0.000 0.000 | 0.000 |
0.008 0.002 | 0.014 |
0.000 0.000 | 0.000 |
0.982 0.973 | 0.989 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
12 spectra |
 |
0.000 0.000 | 0.000 |
0.056 0.020 | 0.086 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.939 0.894 | 0.970 |
0.000 0.000 | 0.011 |
0.005 0.000 | 0.012 |
| 1 spectrum, EANHDGDFGITLAELR | 0.000 | 0.218 | 0.000 | 0.037 | 0.713 | 0.031 | 0.000 | |||
| 2 spectra, TICLAFR | 0.000 | 0.000 | 0.000 | 0.056 | 0.841 | 0.000 | 0.103 | |||
| 1 spectrum, IQTQIR | 0.000 | 0.000 | 0.105 | 0.000 | 0.888 | 0.000 | 0.007 | |||
| 1 spectrum, VVNAFR | 0.000 | 0.000 | 0.276 | 0.000 | 0.656 | 0.000 | 0.068 | |||
| 1 spectrum, NEIPEEALYK | 0.000 | 0.369 | 0.000 | 0.000 | 0.595 | 0.000 | 0.036 | |||
| 1 spectrum, ALMELR | 0.000 | 0.145 | 0.000 | 0.113 | 0.694 | 0.048 | 0.000 | |||
| 1 spectrum, GIIDSTVSEQR | 0.000 | 0.000 | 0.469 | 0.000 | 0.350 | 0.000 | 0.181 | |||
| 1 spectrum, NKPLISR | 0.080 | 0.272 | 0.000 | 0.000 | 0.648 | 0.000 | 0.000 | |||
| 1 spectrum, QVVAVTGDGTNDGPALK | 0.000 | 0.020 | 0.000 | 0.000 | 0.706 | 0.273 | 0.000 | |||
| 2 spectra, VYTFNSVR | 0.000 | 0.190 | 0.000 | 0.000 | 0.721 | 0.089 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
125 spectra |
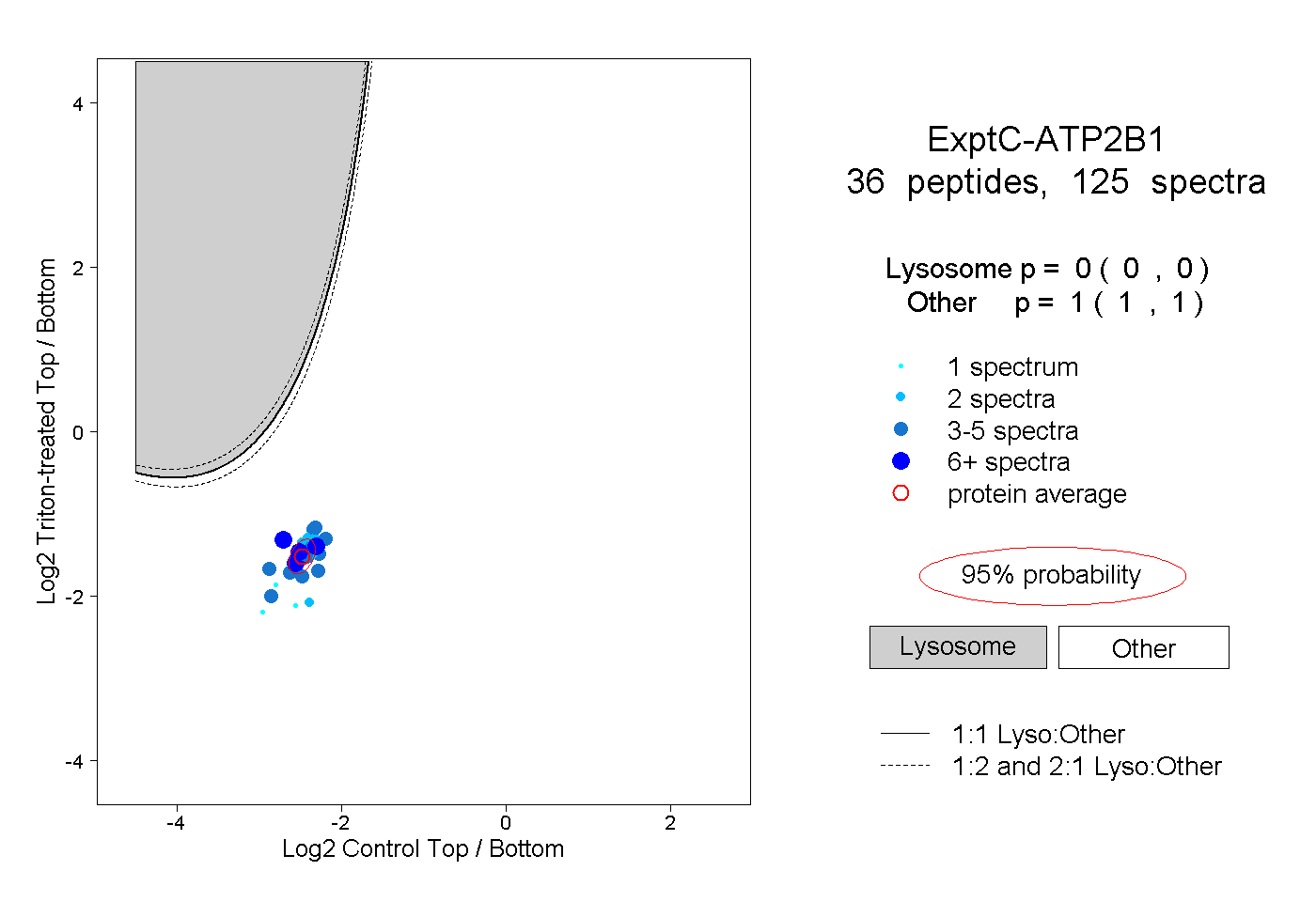 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
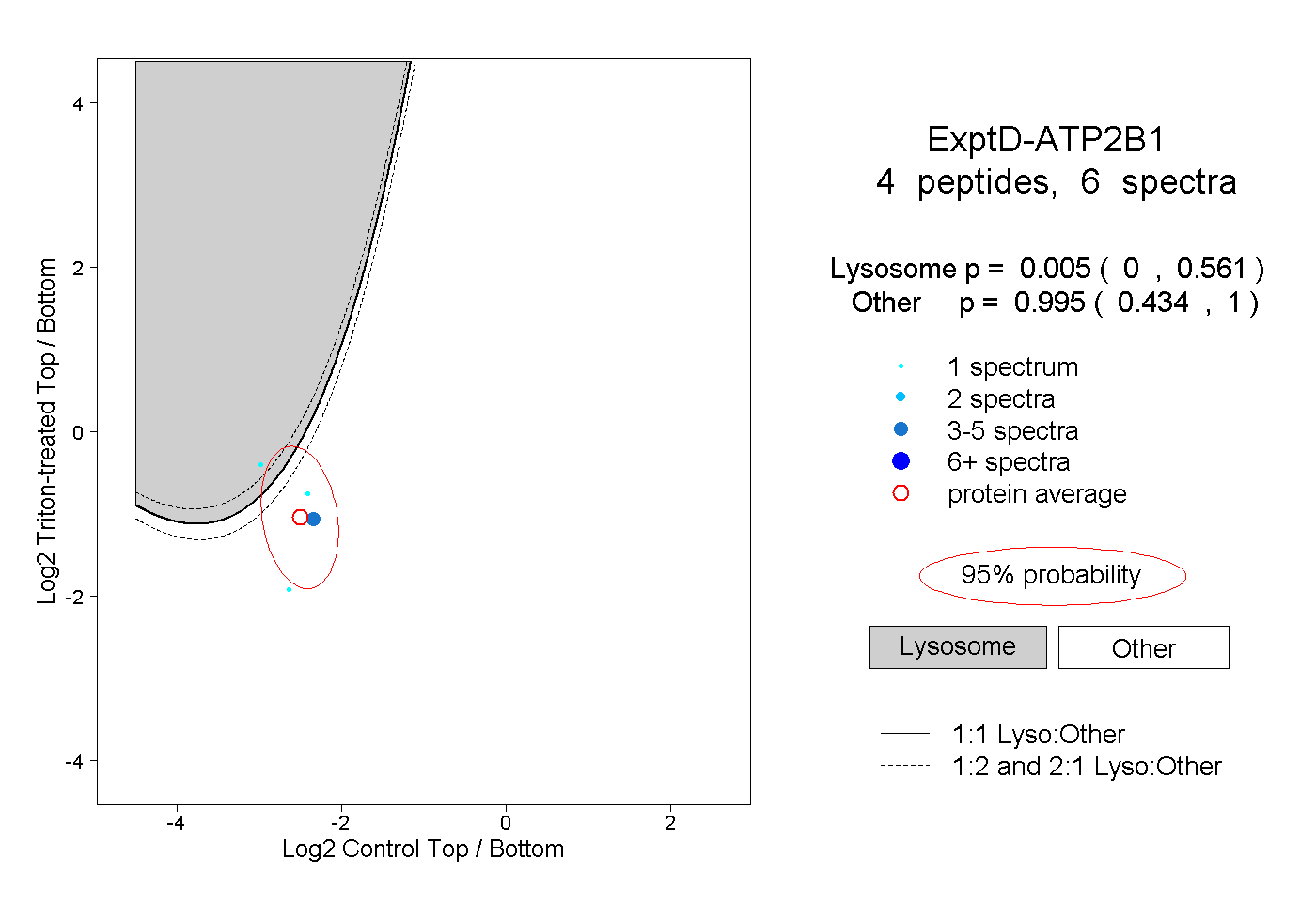 |
0.005 0.000 | 0.561 |
0.995 0.434 | 1.000 |