peptides
spectra
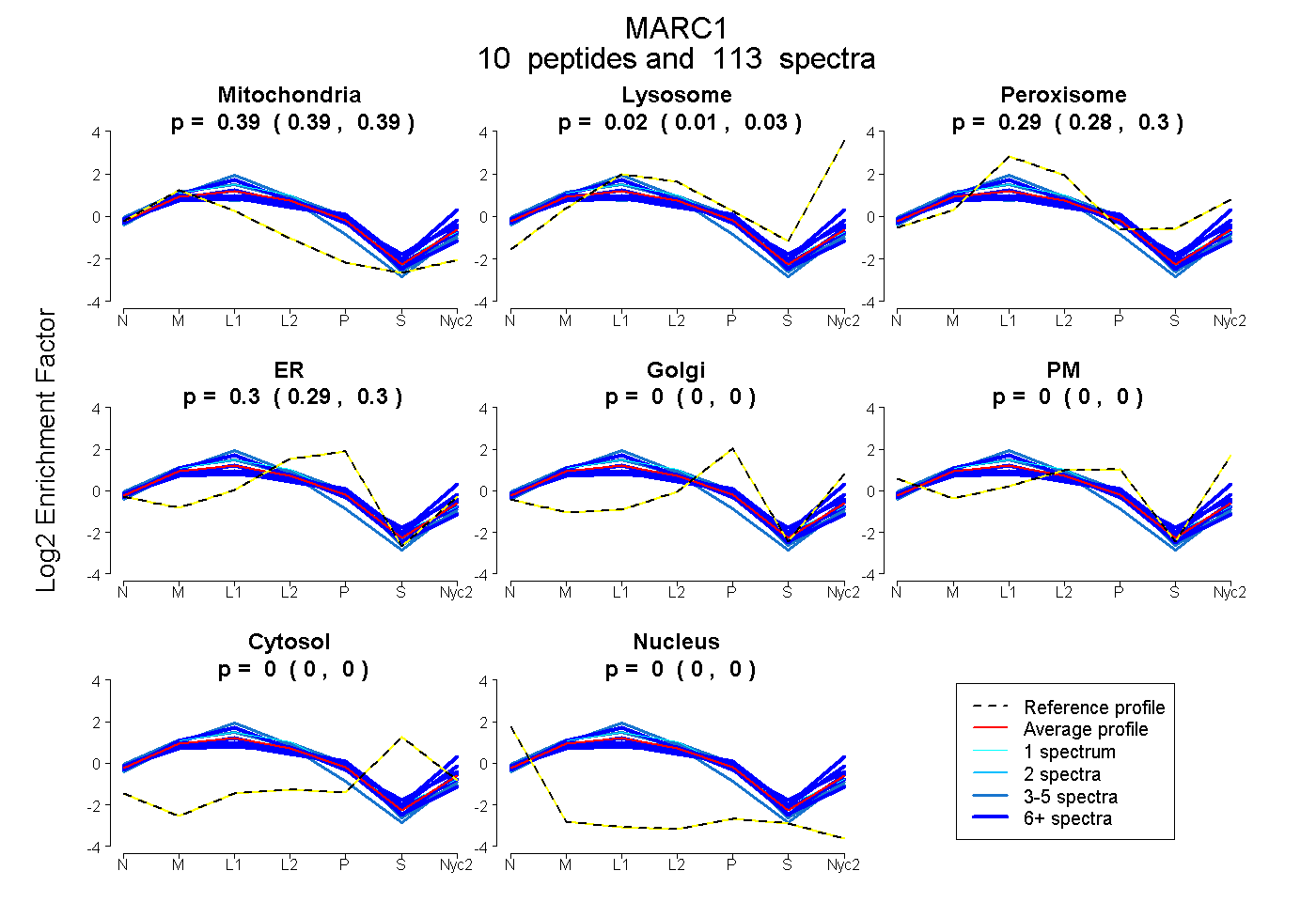
0.388 | 0.393
0.014 | 0.028
0.283 | 0.299
0.291 | 0.299
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
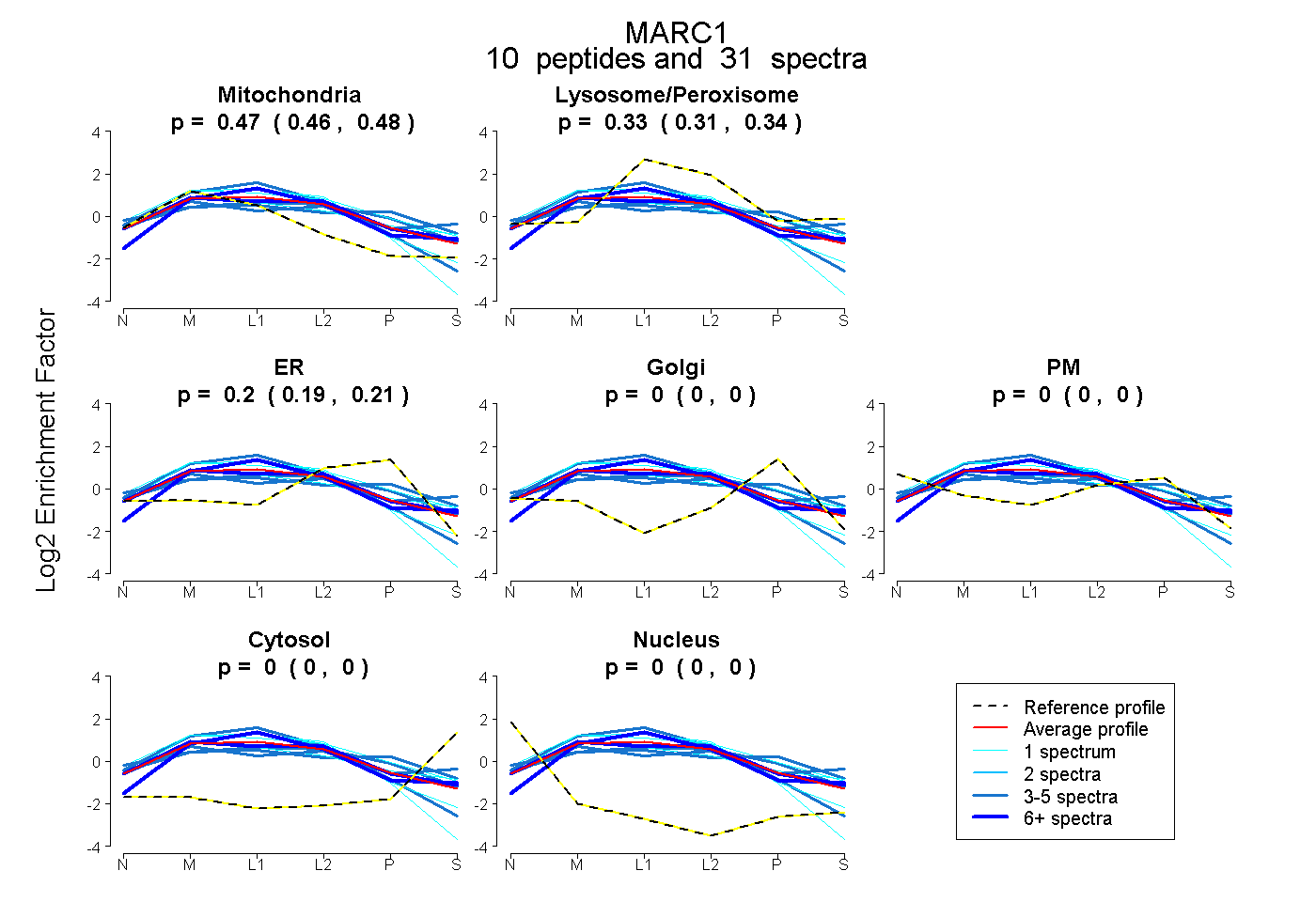
0.463 | 0.481
0.312 | 0.339
0.186 | 0.212
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
113 spectra |
 |
0.391 0.388 | 0.393 |
0.022 0.014 | 0.028 |
0.292 0.283 | 0.299 |
0.296 0.291 | 0.299 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
31 spectra |
 |
0.473 0.463 | 0.481 |
0.326 0.312 | 0.339 |
0.201 0.186 | 0.212 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, TWALALLGFSATR | 0.437 | 0.366 | 0.000 | 0.190 | 0.000 | 0.007 | 0.000 | |||
| 3 spectra, LVHFEPHMHPR | 0.231 | 0.410 | 0.000 | 0.331 | 0.028 | 0.000 | 0.000 | |||
| 1 spectrum, GVSVTEAECTAMGLR | 0.599 | 0.259 | 0.141 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, FWLVVNEEGNMVTAR | 0.322 | 0.362 | 0.178 | 0.138 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LQQVGTVAQLWIYPIK | 0.324 | 0.478 | 0.182 | 0.016 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, DCGEDAAQWISGFLK | 0.594 | 0.289 | 0.117 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LCEPSEQALCGK | 0.656 | 0.120 | 0.223 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, VMPCTR | 0.468 | 0.320 | 0.212 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, VHGLEVQGR | 0.504 | 0.423 | 0.051 | 0.000 | 0.000 | 0.022 | 0.000 | |||
| 3 spectra, VGDPVYLLS | 0.325 | 0.377 | 0.064 | 0.101 | 0.000 | 0.133 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
158 spectra |
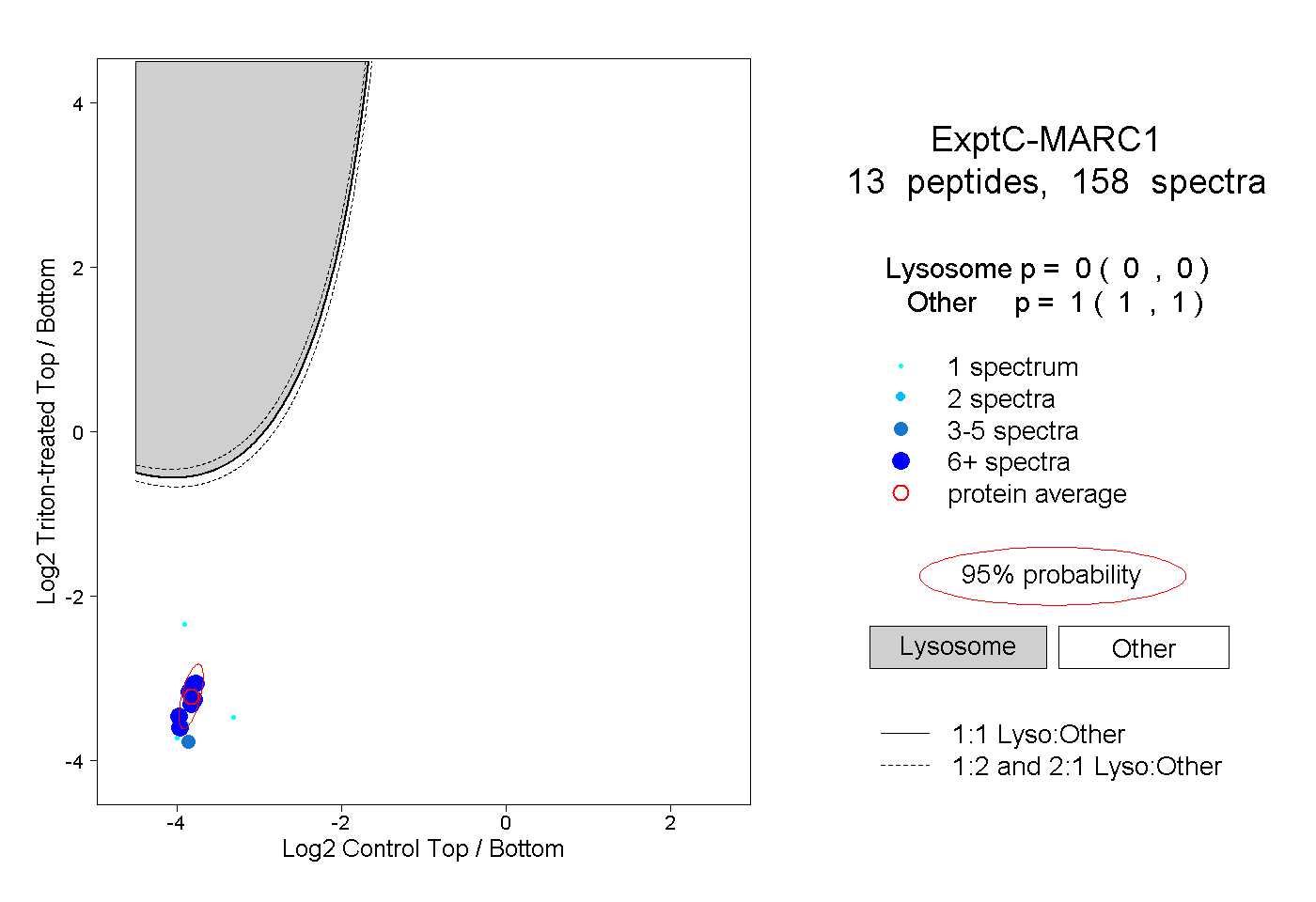 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
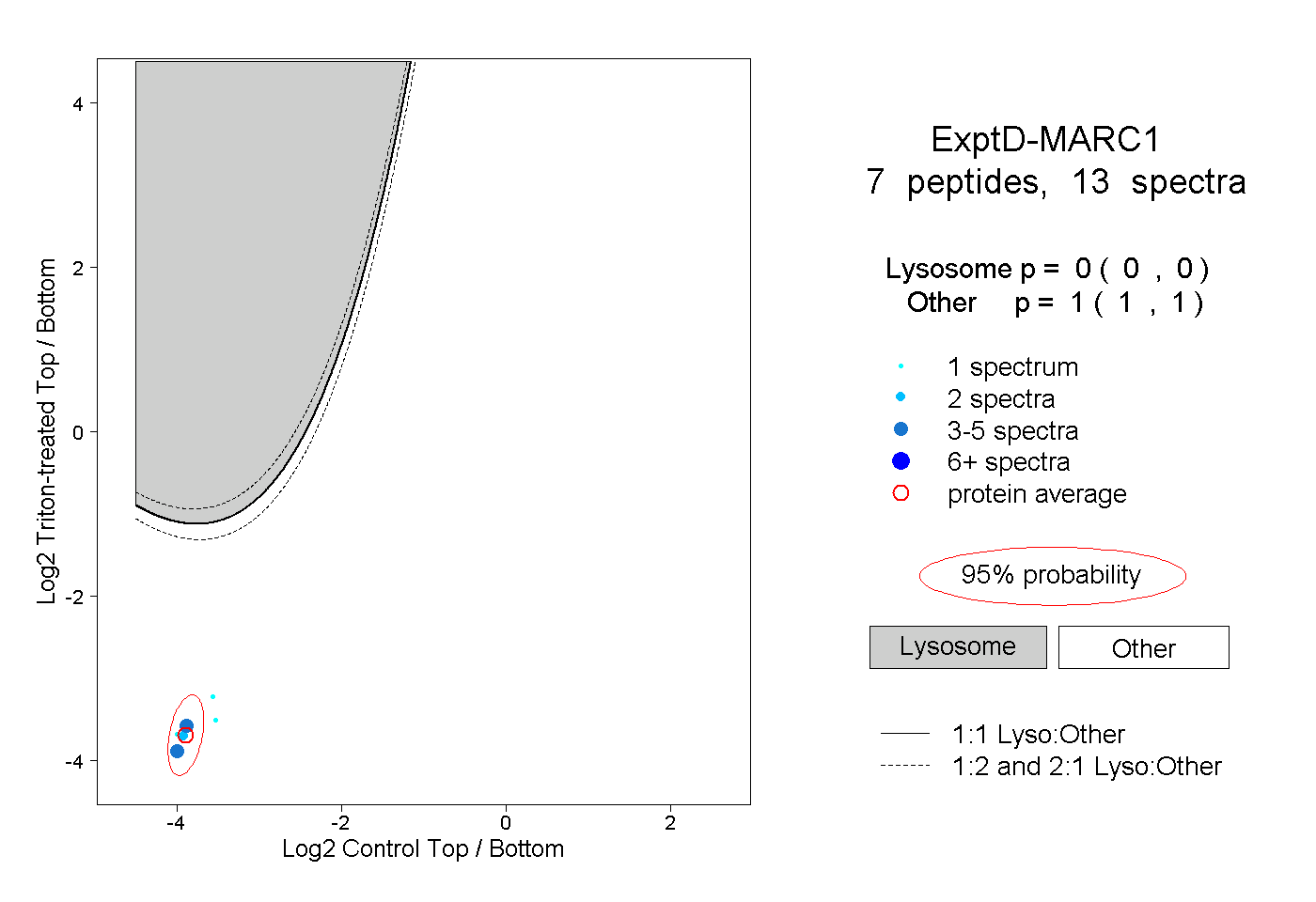 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |