peptides
spectra
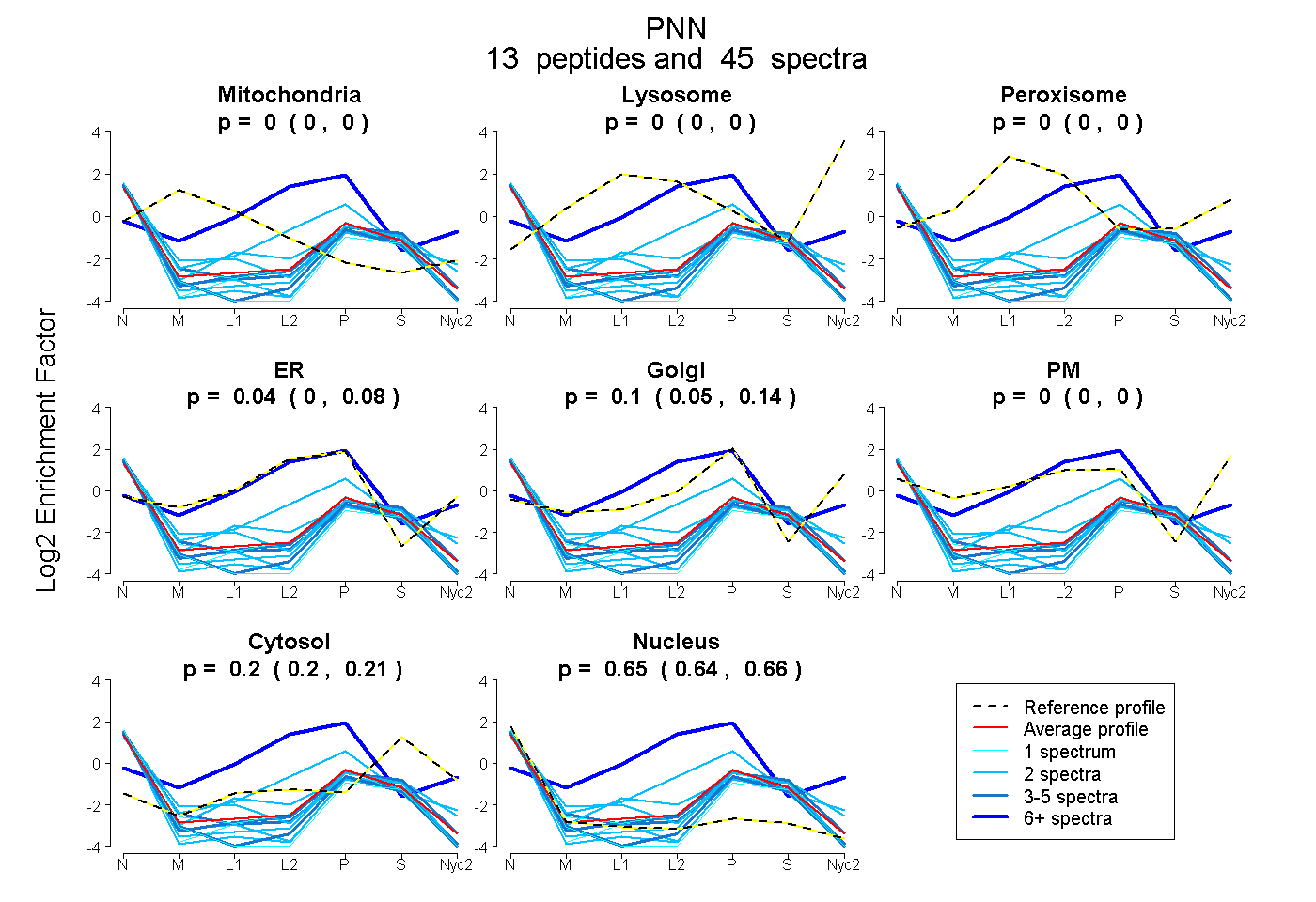
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.081
0.049 | 0.137
0.000 | 0.000
0.196 | 0.211
0.644 | 0.664
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
45 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.041 0.000 | 0.081 |
0.099 0.049 | 0.137 |
0.000 0.000 | 0.000 |
0.205 0.196 | 0.211 |
0.655 0.644 | 0.664 |
| 4 spectra, DLEGAVSR | 0.000 | 0.000 | 0.000 | 0.055 | 0.003 | 0.000 | 0.203 | 0.739 | ||
| 3 spectra, MEEETGVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.066 | 0.000 | 0.282 | 0.652 | ||
| 1 spectrum, GFSDSGGGPPAK | 0.000 | 0.000 | 0.000 | 0.015 | 0.000 | 0.000 | 0.282 | 0.703 | ||
| 2 spectra, LIEESQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.076 | 0.000 | 0.274 | 0.650 | ||
| 2 spectra, EHQVVR | 0.000 | 0.000 | 0.000 | 0.442 | 0.000 | 0.000 | 0.142 | 0.417 | ||
| 1 spectrum, MNALFEGR | 0.000 | 0.000 | 0.000 | 0.145 | 0.000 | 0.000 | 0.116 | 0.739 | ||
| 2 spectra, DTSGLER | 0.000 | 0.000 | 0.000 | 0.135 | 0.000 | 0.000 | 0.229 | 0.636 | ||
| 2 spectra, LLALSGPGGGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.188 | 0.812 | ||
| 2 spectra, NVDENIR | 0.000 | 0.000 | 0.000 | 0.115 | 0.000 | 0.000 | 0.212 | 0.673 | ||
| 2 spectra, LEVQAEEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.178 | 0.822 | ||
| 20 spectra, AVAVR | 0.000 | 0.000 | 0.000 | 0.870 | 0.000 | 0.000 | 0.130 | 0.000 | ||
| 3 spectra, TKPHLFYIPGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.006 | 0.000 | 0.155 | 0.839 | ||
| 1 spectrum, VELAQLQEEWNEHNAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.121 | 0.879 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
10 spectra |
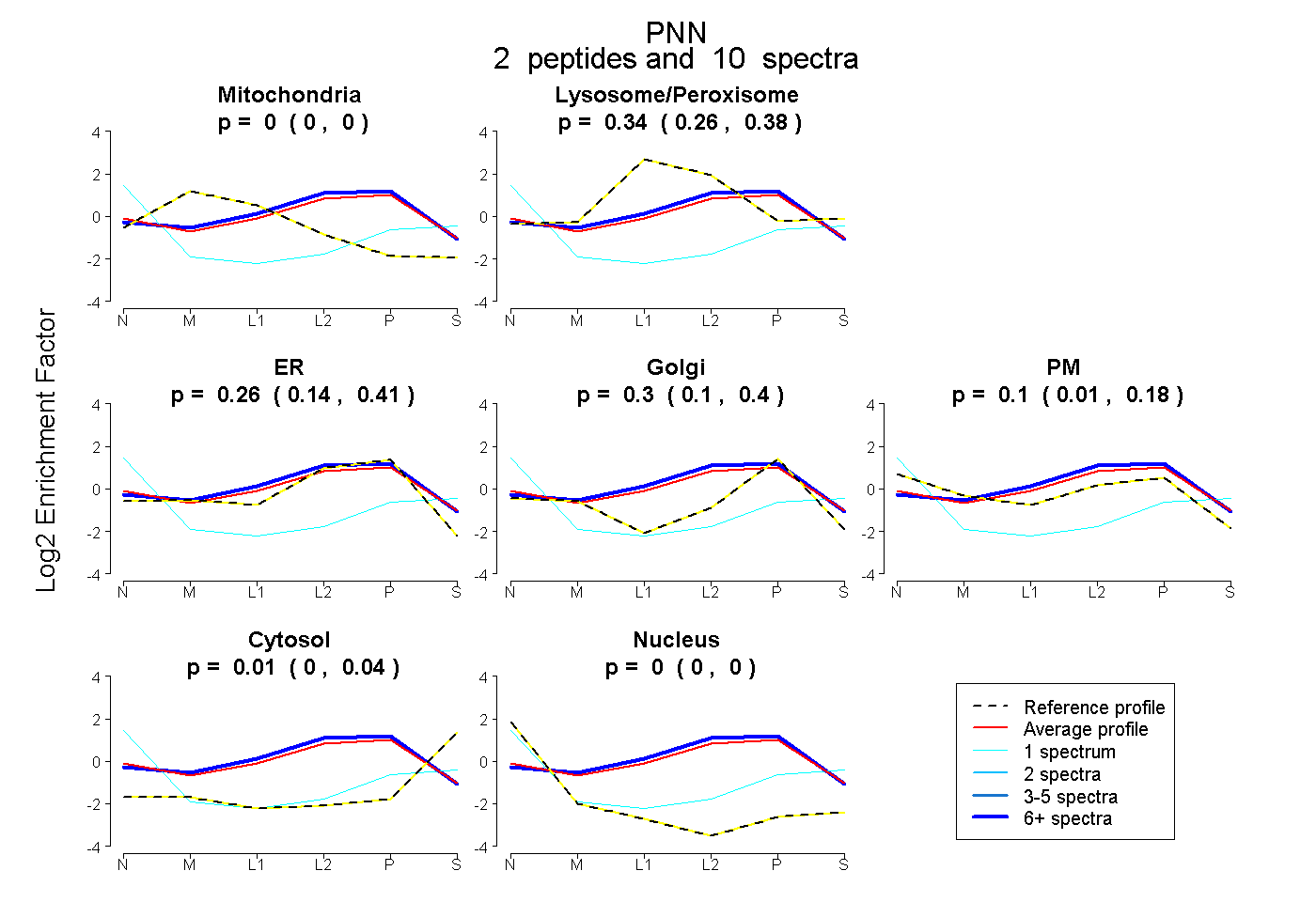 |
0.000 0.000 | 0.000 |
0.340 0.261 | 0.383 |
0.260 0.140 | 0.411 |
0.296 0.098 | 0.395 |
0.096 0.012 | 0.181 |
0.008 0.000 | 0.044 |
0.000 0.000 | 0.000 |