peptides
spectra
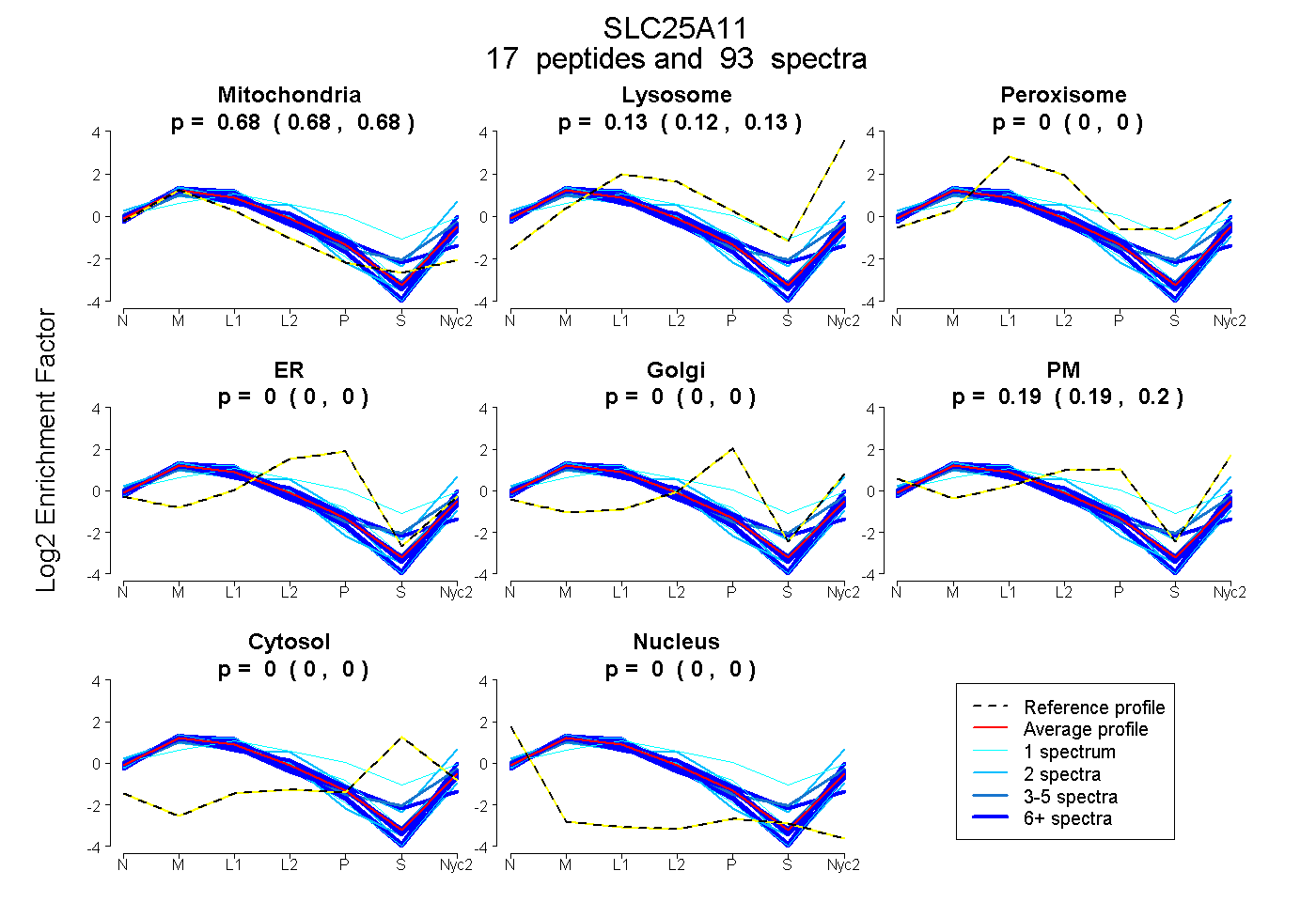
0.679 | 0.684
0.122 | 0.131
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.187 | 0.195
0.000 | 0.000
0.000 | 0.000
peptides
spectra
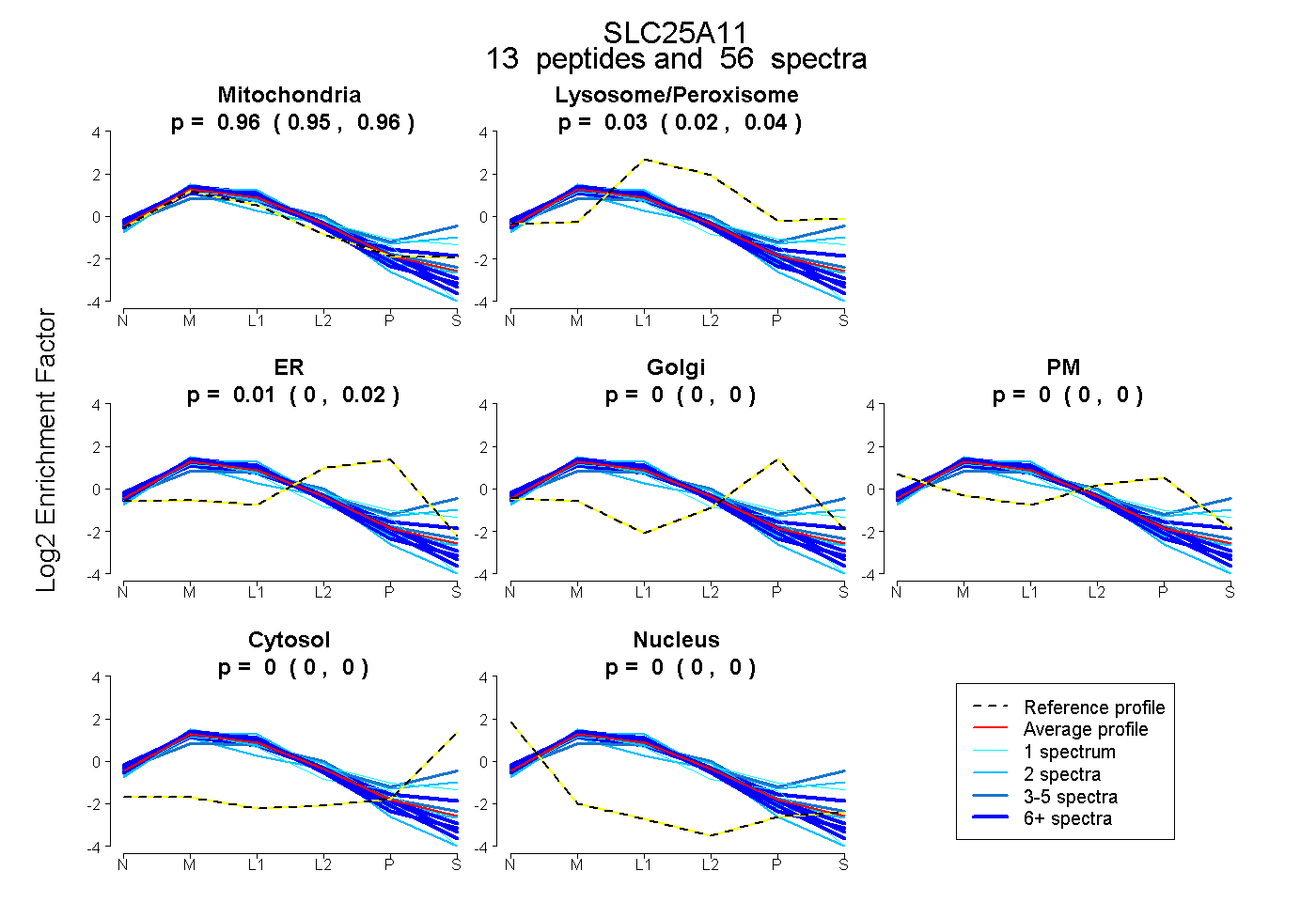
0.949 | 0.963
0.022 | 0.041
0.002 | 0.018
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
93 spectra |
 |
0.682 0.679 | 0.684 |
0.127 0.122 | 0.131 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.191 0.187 | 0.195 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
56 spectra |
 |
0.956 0.949 | 0.963 |
0.033 0.022 | 0.041 |
0.011 0.002 | 0.018 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, EEGVPTLWR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, NVFNALIR | 0.991 | 0.000 | 0.009 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, GCIPTMAR | 0.882 | 0.075 | 0.043 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, MDGKPR | 0.961 | 0.036 | 0.003 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GIYTGLSAGLLR | 0.913 | 0.000 | 0.087 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, QATYTTTR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, LGIYTVLFER | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, GFTPYYAR | 0.847 | 0.104 | 0.000 | 0.000 | 0.049 | 0.000 | 0.000 | |||
| 4 spectra, LTGADGTPPGFLLK | 0.552 | 0.302 | 0.000 | 0.000 | 0.000 | 0.146 | 0.000 | |||
| 6 spectra, YEGFFSLWK | 0.965 | 0.017 | 0.018 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, MIDGKPEYK | 0.704 | 0.237 | 0.000 | 0.059 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, AVVVNAAQLASYSQSK | 0.680 | 0.158 | 0.000 | 0.050 | 0.015 | 0.098 | 0.000 | |||
| 2 spectra, NGLDVLLK | 0.972 | 0.028 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
389 spectra |
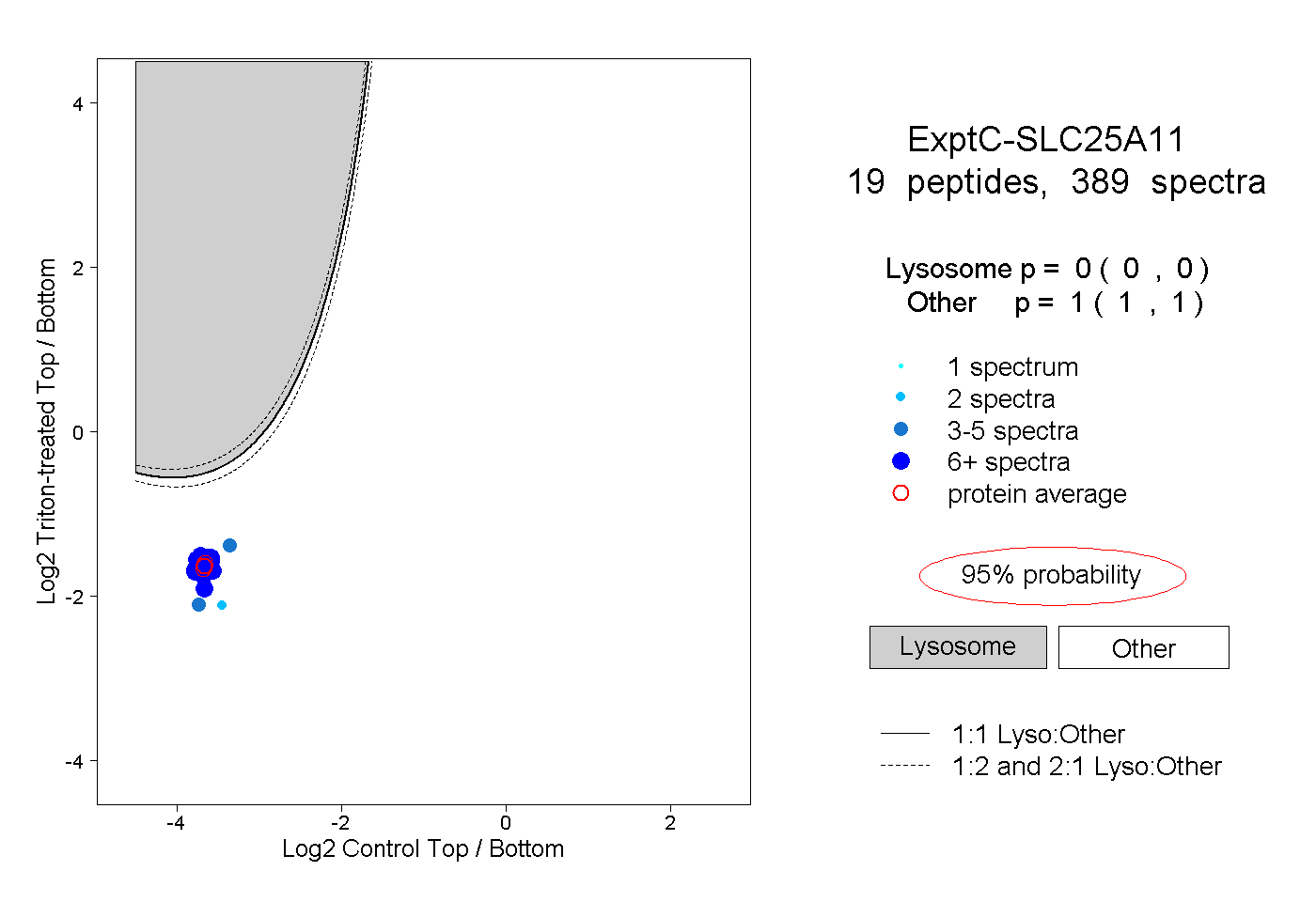 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
26 spectra |
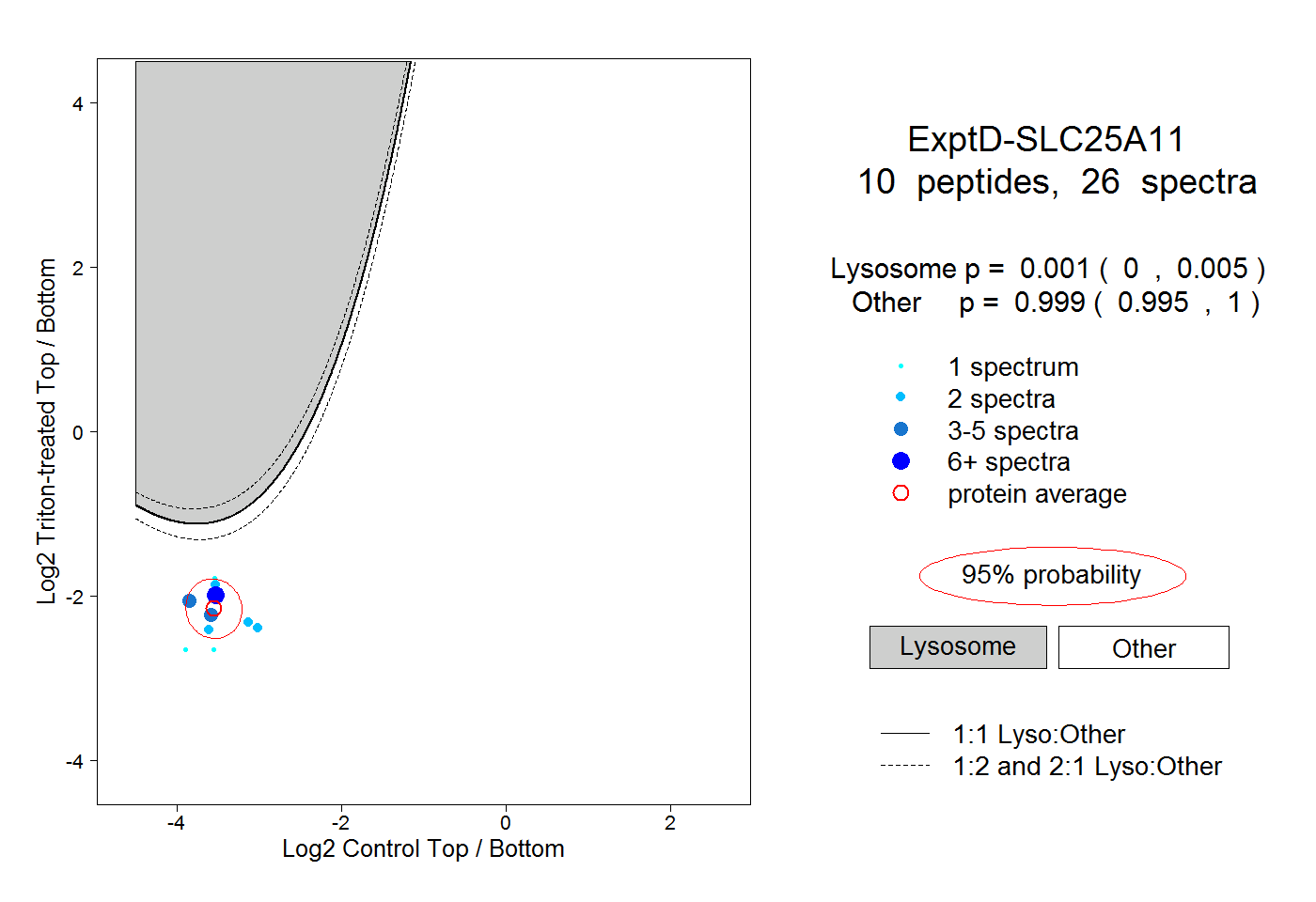 |
0.001 0.000 | 0.005 |
0.999 0.995 | 1.000 |