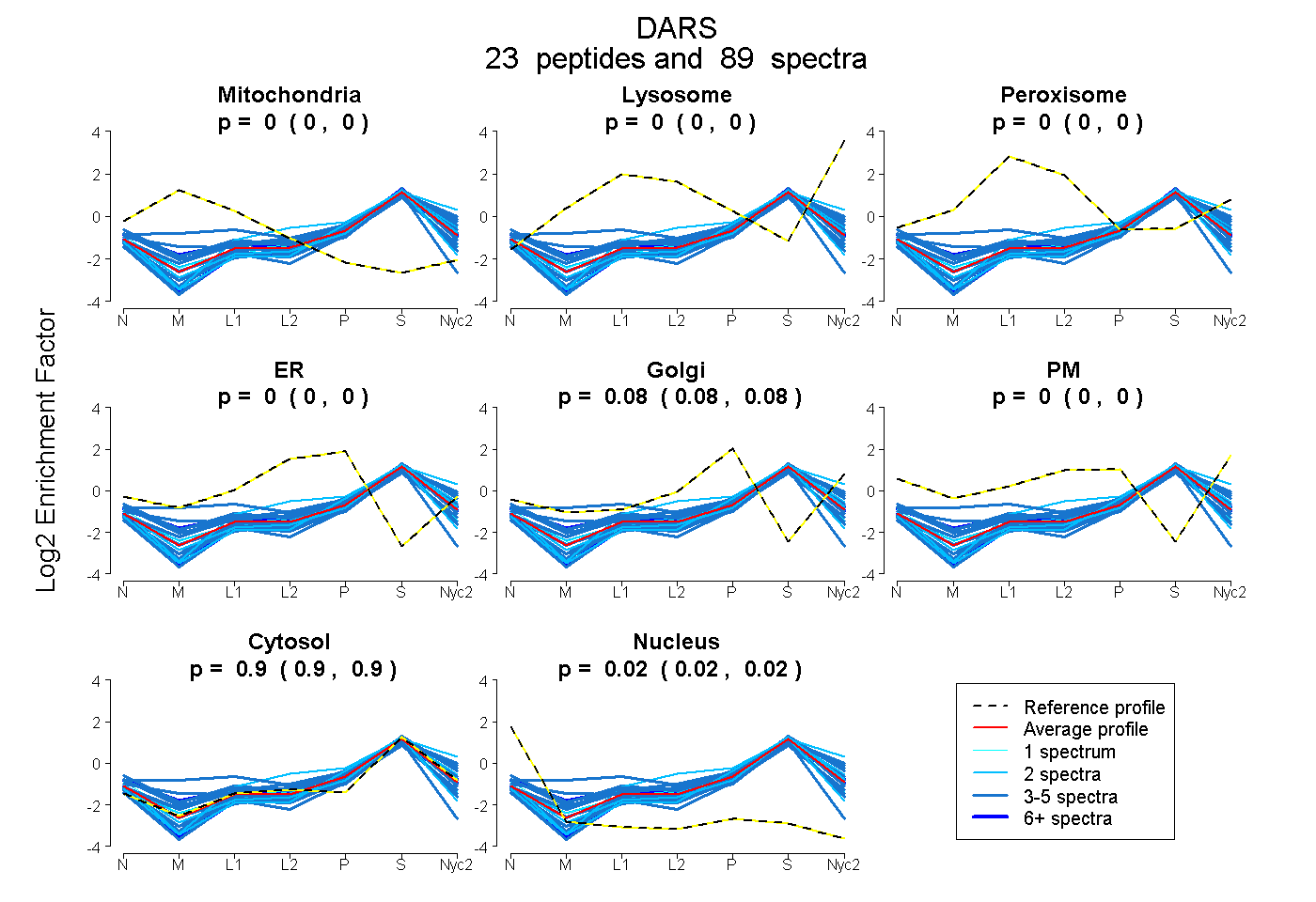
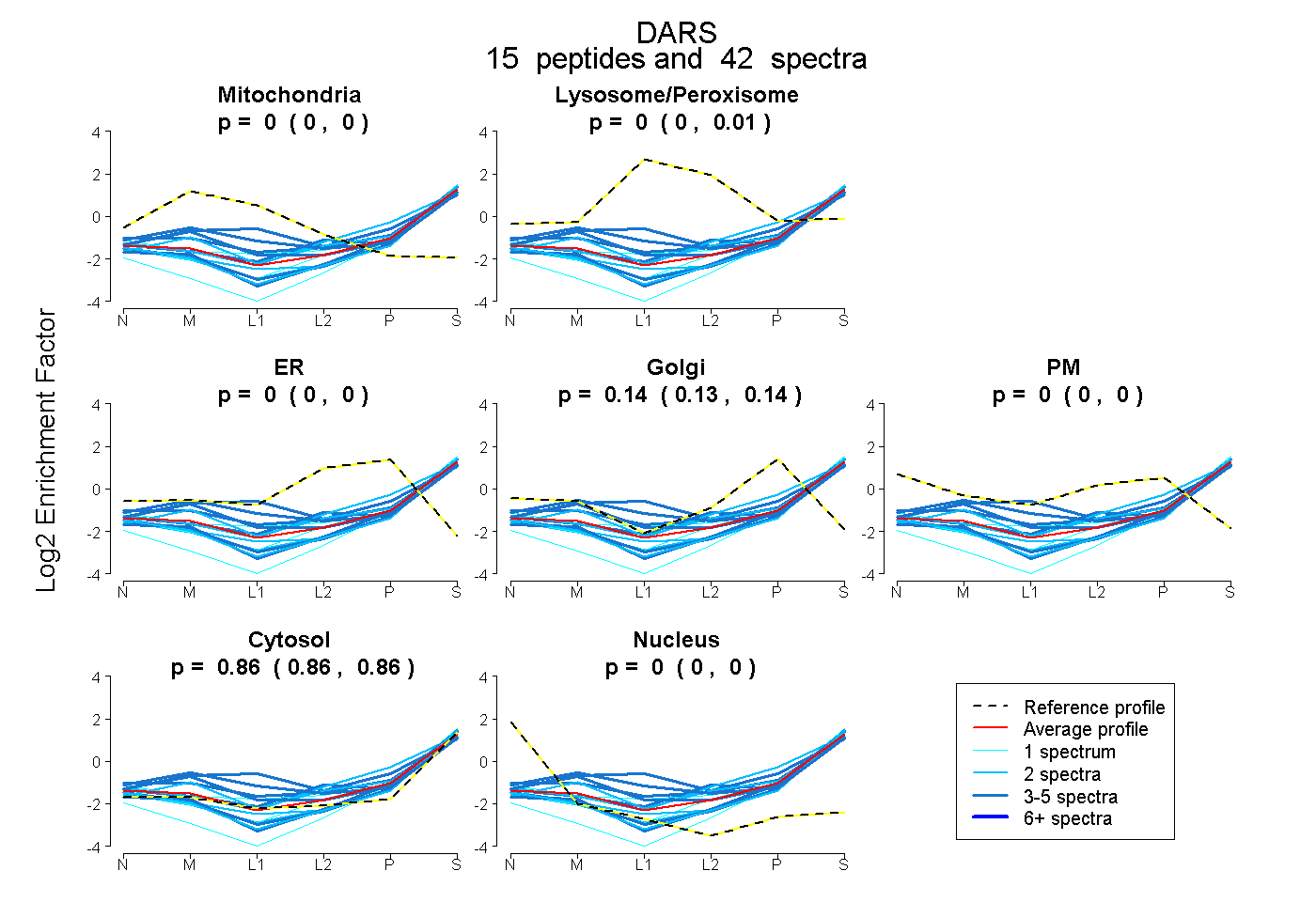
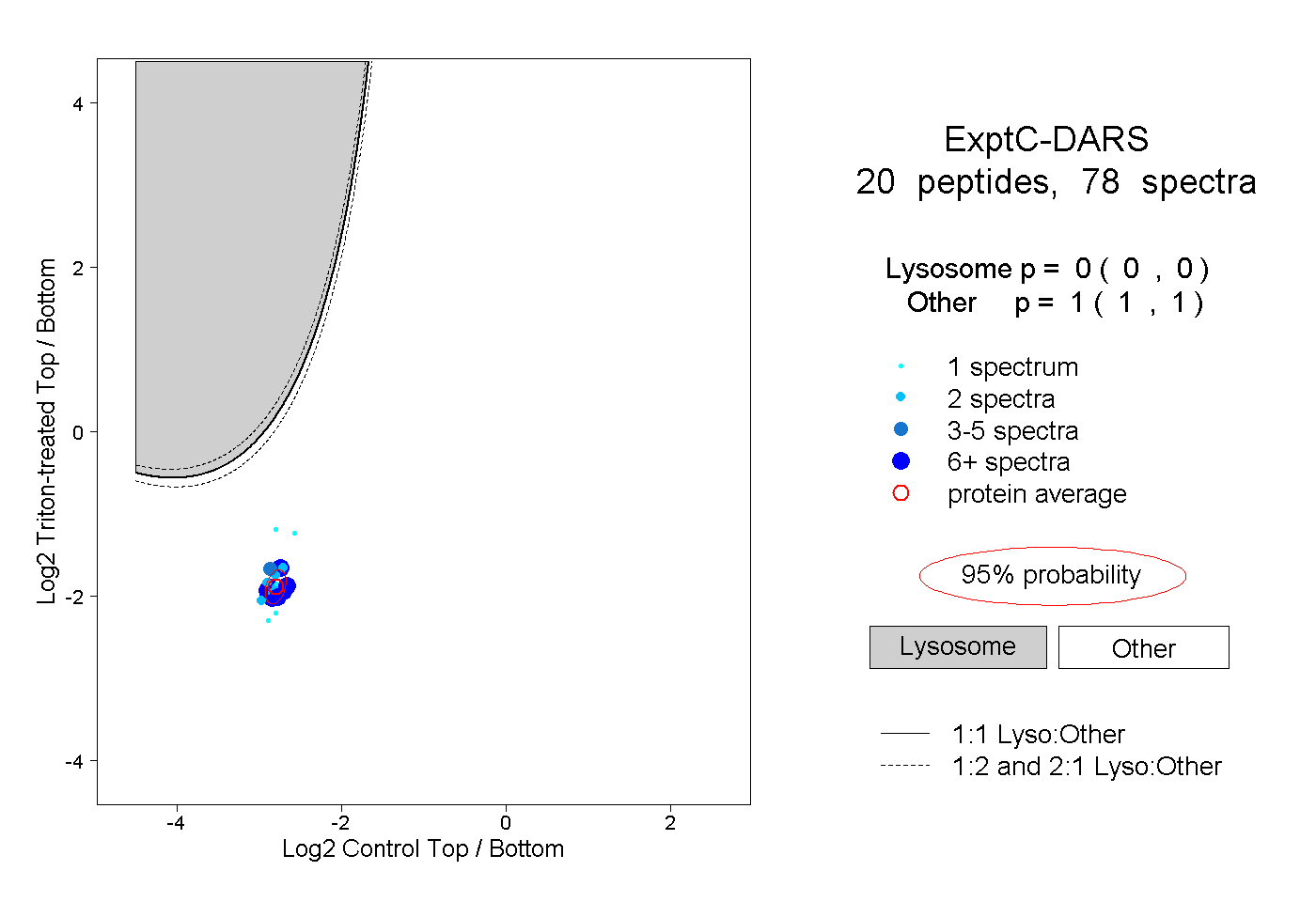
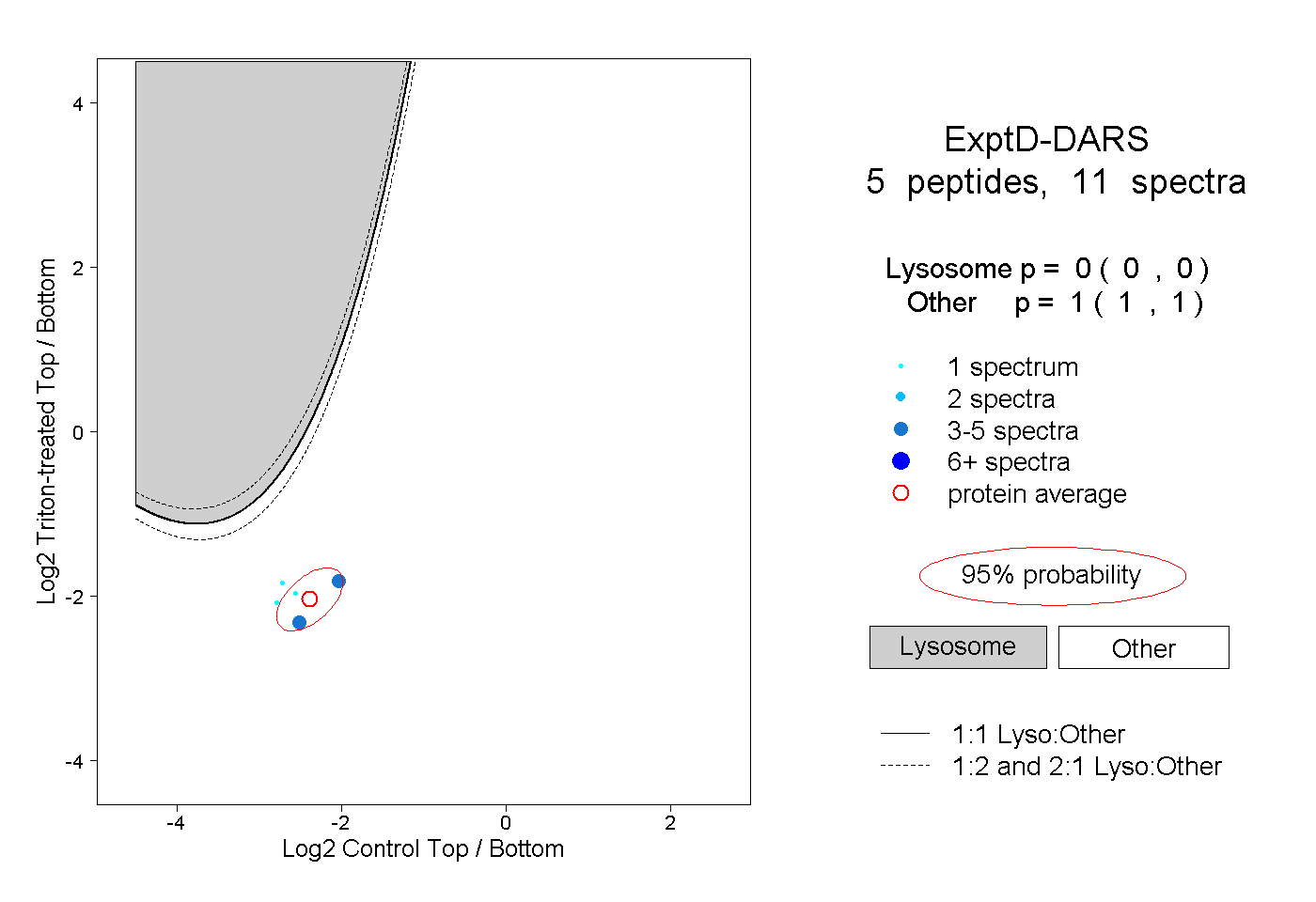
| 8 spectra, VFCIGPVFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, FGAPPHAGGGIGLER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ESIIDVEGIVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, QTSMFPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ADEVVWVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, FAANINK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, AYIDSFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IYVISLAEPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, FLEPTLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GFVEIQTPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IGSCTQQDVELHVQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, YGVSSMIQSQEKPDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, GEEILSGAQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LEYCEALAMLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QCFLVLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ETLINK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LPLQLDDAIRPEVEGEEDGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IHDPQLLTER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ATVNQDTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SNAYLAQSPQLYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |