peptides
spectra
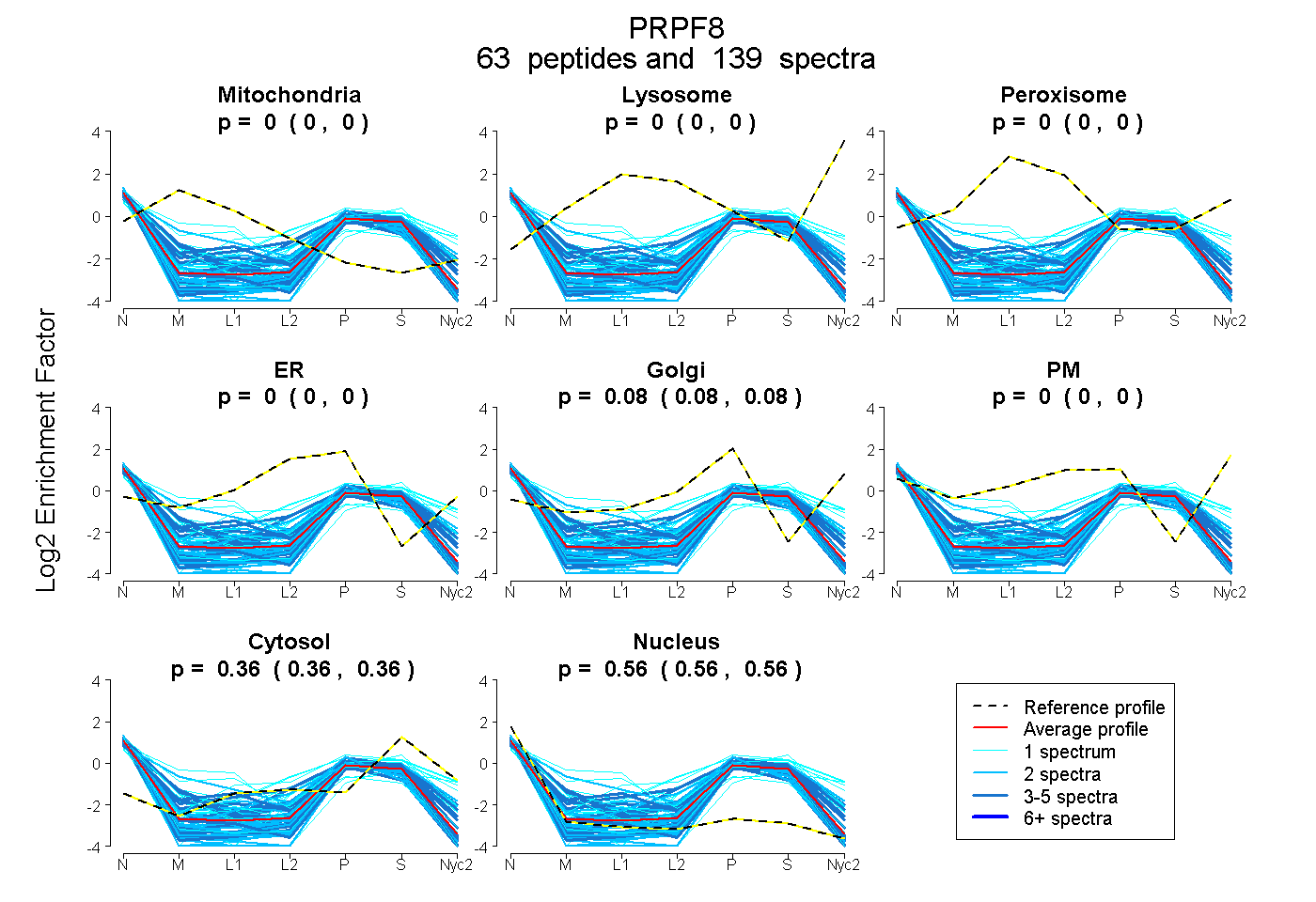
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.075 | 0.079
0.000 | 0.000
0.359 | 0.361
0.561 | 0.564
peptides
spectra
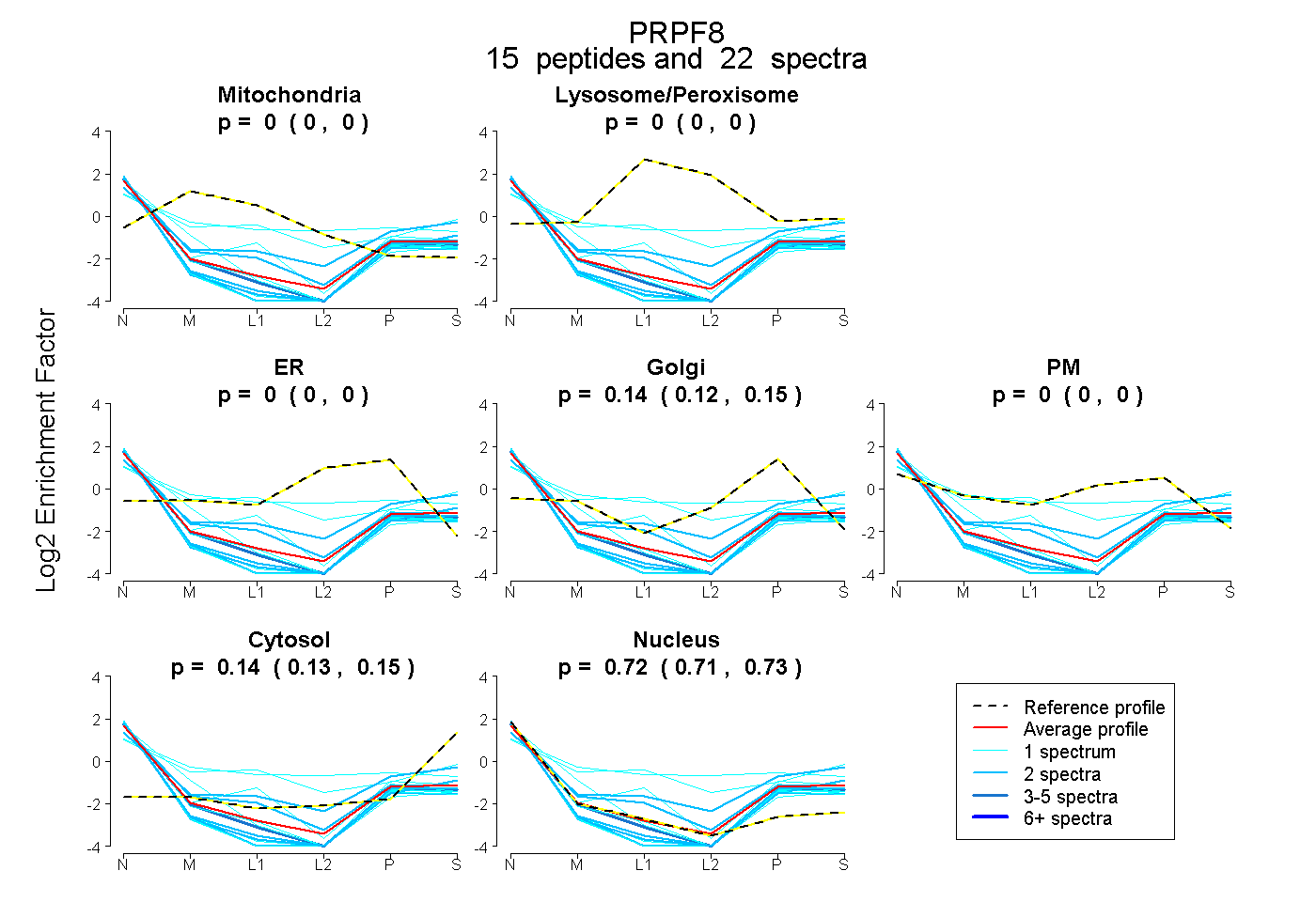
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.124 | 0.150
0.000 | 0.000
0.129 | 0.148
0.709 | 0.733
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
139 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.077 0.075 | 0.079 |
0.000 0.000 | 0.000 |
0.360 0.359 | 0.361 |
0.562 0.561 | 0.564 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.139 0.124 | 0.150 |
0.000 0.000 | 0.000 |
0.139 0.129 | 0.148 |
0.722 0.709 | 0.733 |
| 2 spectra, TAEEVAALIR | 0.000 | 0.000 | 0.000 | 0.042 | 0.000 | 0.110 | 0.847 | |||
| 3 spectra, ANPALYVLR | 0.000 | 0.000 | 0.000 | 0.071 | 0.000 | 0.104 | 0.824 | |||
| 1 spectrum, FTADEAR | 0.000 | 0.000 | 0.000 | 0.022 | 0.000 | 0.125 | 0.854 | |||
| 1 spectrum, LLLILR | 0.000 | 0.000 | 0.000 | 0.027 | 0.000 | 0.067 | 0.906 | |||
| 2 spectra, LLILALER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.177 | 0.823 | |||
| 1 spectrum, GYLPSHYER | 0.014 | 0.208 | 0.000 | 0.000 | 0.457 | 0.103 | 0.217 | |||
| 1 spectrum, GITPLLER | 0.000 | 0.000 | 0.000 | 0.093 | 0.000 | 0.094 | 0.813 | |||
| 1 spectrum, HILTQR | 0.000 | 0.116 | 0.000 | 0.088 | 0.000 | 0.080 | 0.716 | |||
| 1 spectrum, ISLIQIFR | 0.000 | 0.000 | 0.000 | 0.028 | 0.000 | 0.085 | 0.887 | |||
| 2 spectra, VQMLLSDR | 0.000 | 0.024 | 0.000 | 0.000 | 0.296 | 0.279 | 0.400 | |||
| 1 spectrum, EAVVNTQELLDLLVK | 0.000 | 0.000 | 0.000 | 0.080 | 0.000 | 0.086 | 0.834 | |||
| 1 spectrum, EQSQLTATQTR | 0.000 | 0.000 | 0.000 | 0.072 | 0.000 | 0.073 | 0.856 | |||
| 2 spectra, TAQCFLR | 0.000 | 0.051 | 0.000 | 0.152 | 0.009 | 0.100 | 0.688 | |||
| 2 spectra, IDLTLLNR | 0.000 | 0.000 | 0.000 | 0.021 | 0.000 | 0.073 | 0.906 | |||
| 1 spectrum, HTLAYDK | 0.012 | 0.328 | 0.000 | 0.000 | 0.121 | 0.189 | 0.350 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
11 spectra |
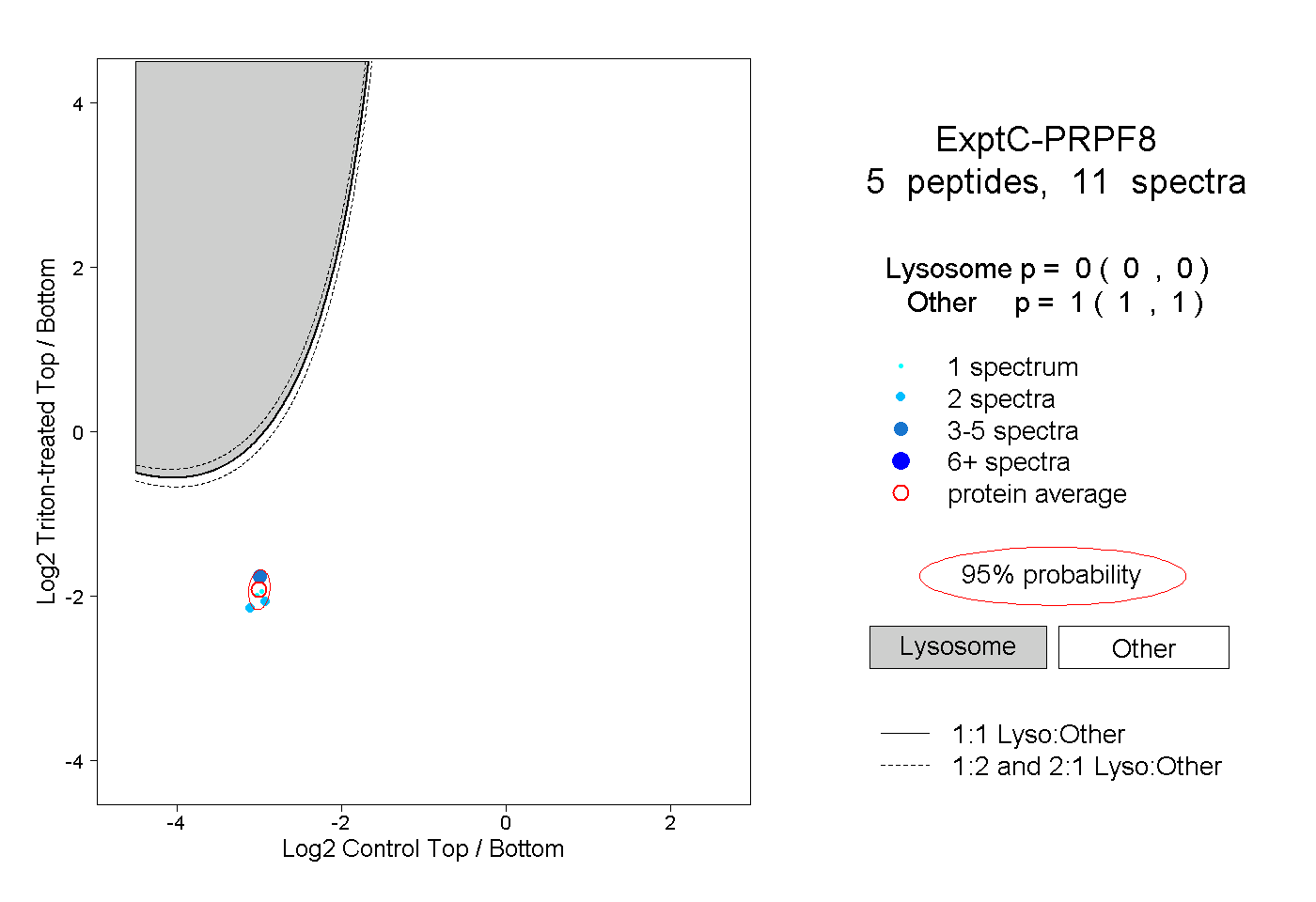 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |