peptides
spectra
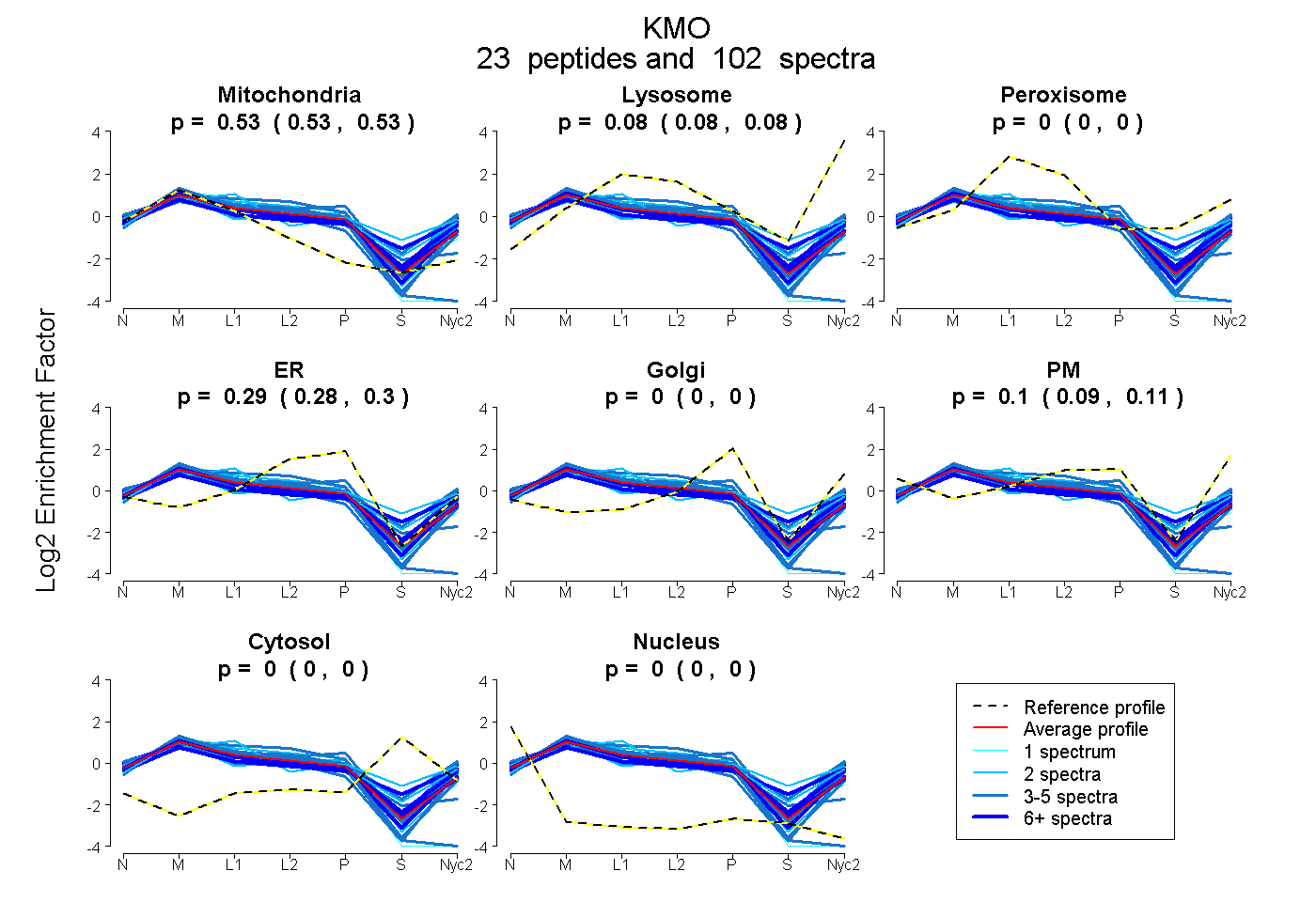
0.525 | 0.531
0.078 | 0.085
0.000 | 0.000
0.282 | 0.299
0.000 | 0.000
0.088 | 0.108
0.000 | 0.000
0.000 | 0.000
peptides
spectra
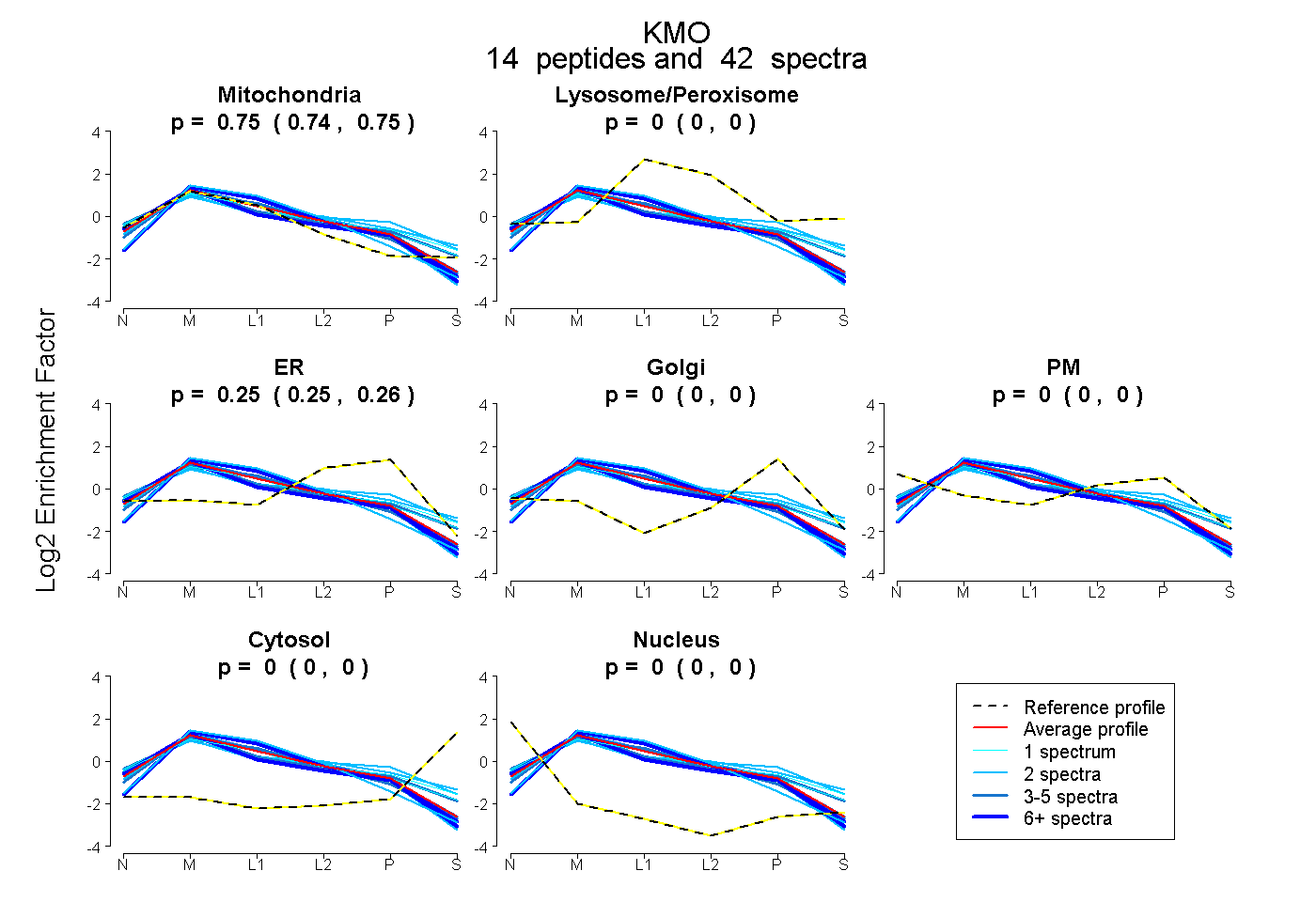
0.744 | 0.752
0.000 | 0.000
0.248 | 0.256
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
102 spectra |
 |
0.528 0.525 | 0.531 |
0.082 0.078 | 0.085 |
0.000 0.000 | 0.000 |
0.291 0.282 | 0.299 |
0.000 0.000 | 0.000 |
0.098 0.088 | 0.108 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
42 spectra |
 |
0.748 0.744 | 0.752 |
0.000 0.000 | 0.000 |
0.252 0.248 | 0.256 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, AVGLEDQIVSK | 0.769 | 0.000 | 0.231 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, SAIPYGNK | 0.713 | 0.061 | 0.136 | 0.006 | 0.084 | 0.000 | 0.000 | |||
| 8 spectra, VHFGHK | 0.795 | 0.000 | 0.205 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, SINLALSYR | 0.736 | 0.000 | 0.264 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, MIHSLSGK | 0.515 | 0.146 | 0.160 | 0.142 | 0.036 | 0.000 | 0.000 | |||
| 2 spectra, YHEAVLR | 0.878 | 0.020 | 0.103 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LPTHSDVLDFFQK | 0.742 | 0.000 | 0.258 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, NFQVDVYEAR | 0.733 | 0.000 | 0.267 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, NAFMMIALPNMDK | 0.557 | 0.162 | 0.113 | 0.169 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, WFLFQR | 0.629 | 0.160 | 0.082 | 0.129 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, SQYILSISR | 0.752 | 0.000 | 0.248 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, CSPFHLK | 0.795 | 0.000 | 0.205 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, DLLTAVESYPNAK | 0.681 | 0.094 | 0.178 | 0.000 | 0.047 | 0.000 | 0.000 | |||
| 4 spectra, DFFLLPAQPMISVK | 0.778 | 0.000 | 0.222 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
248 spectra |
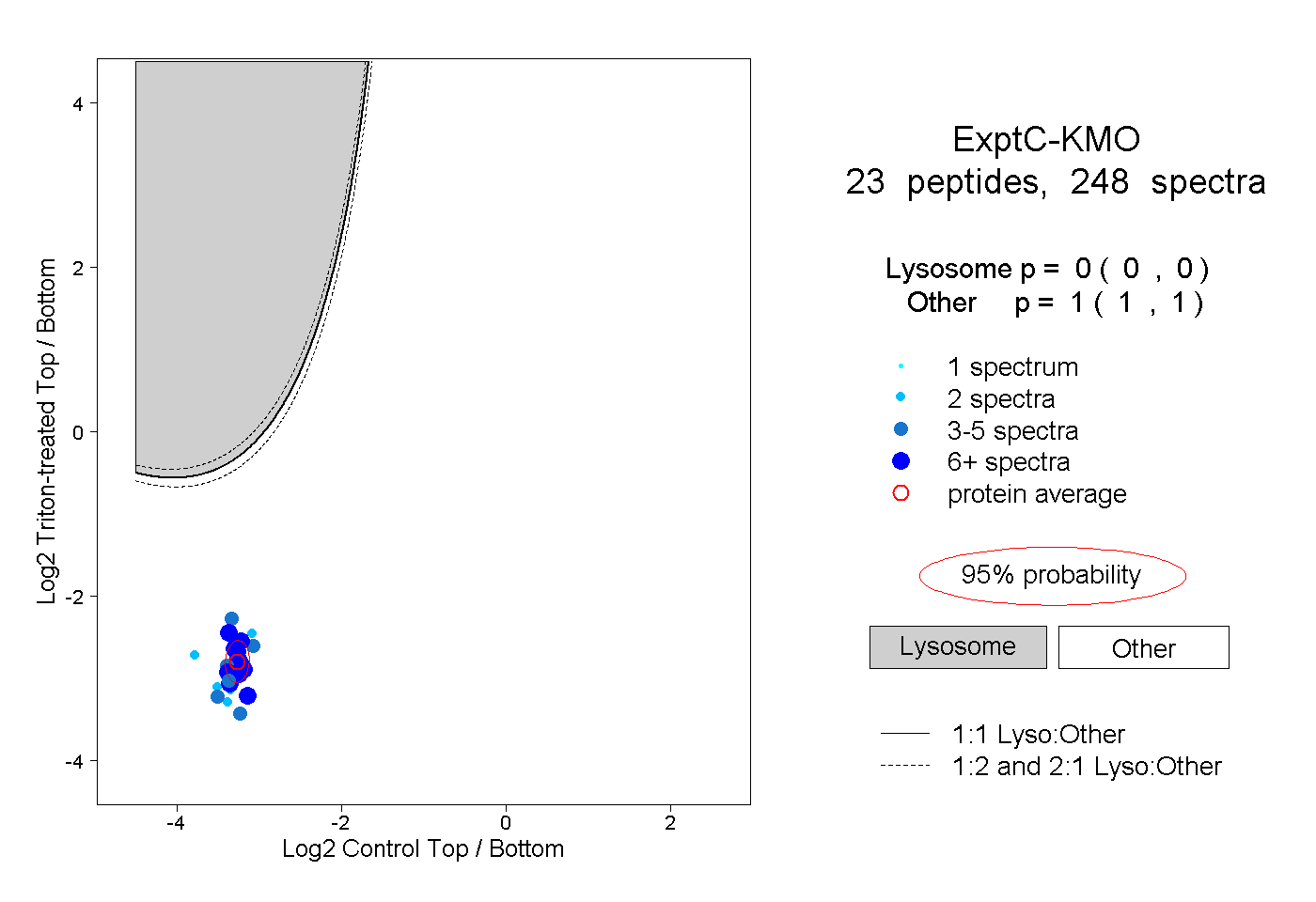 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
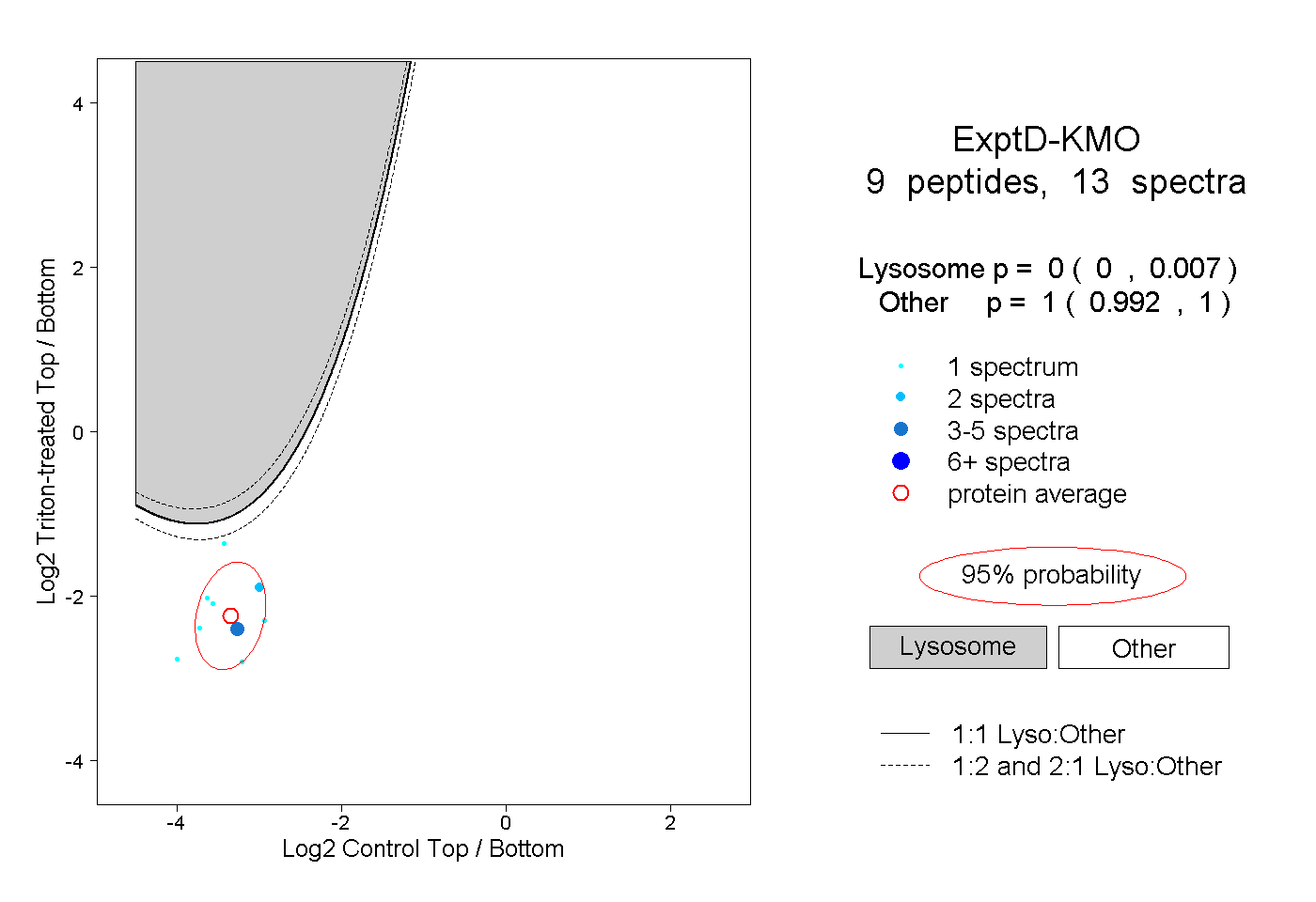 |
0.000 0.000 | 0.007 |
1.000 0.992 | 1.000 |