peptides
spectra
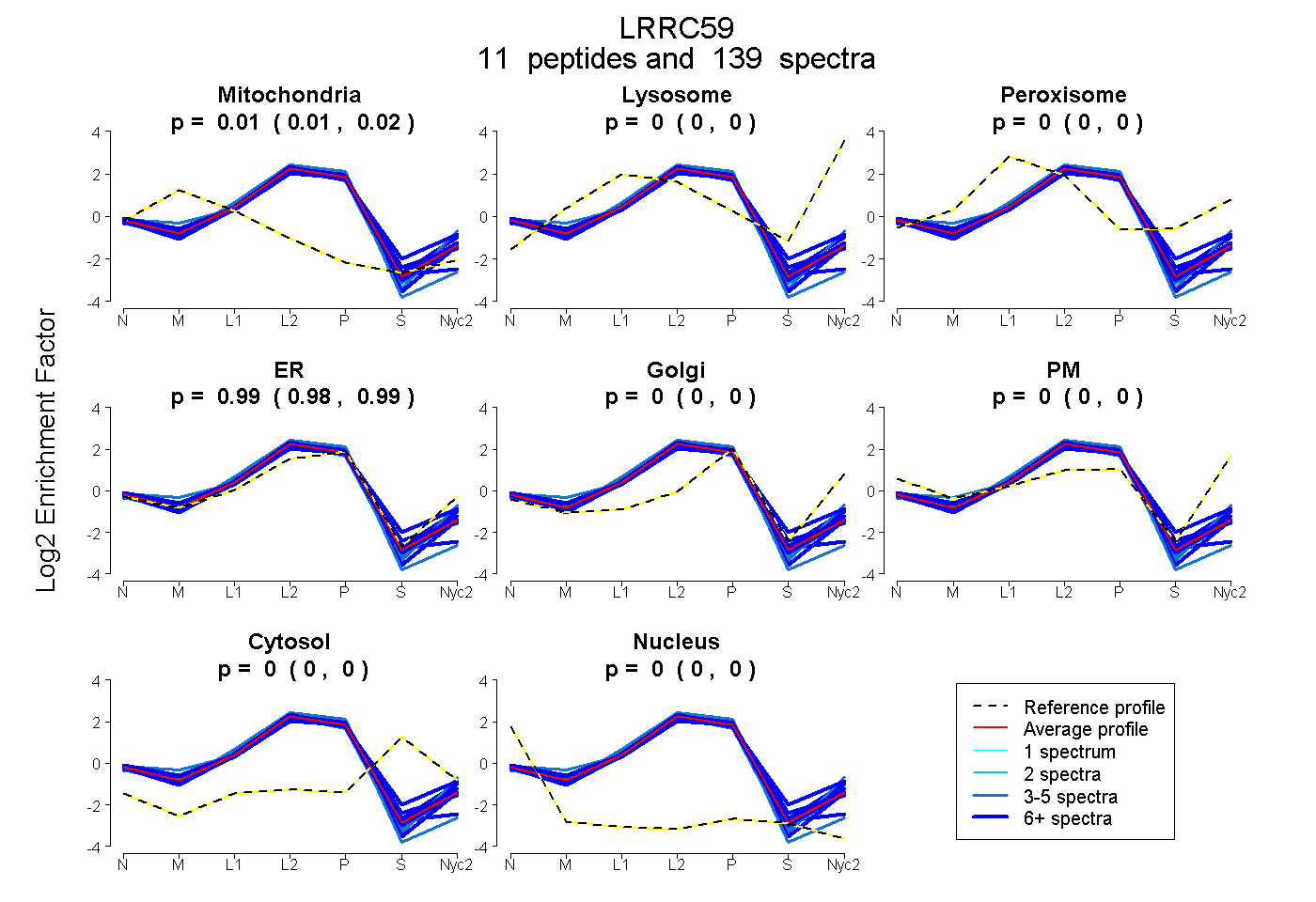
0.013 | 0.015
0.000 | 0.000
0.000 | 0.000
0.984 | 0.987
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
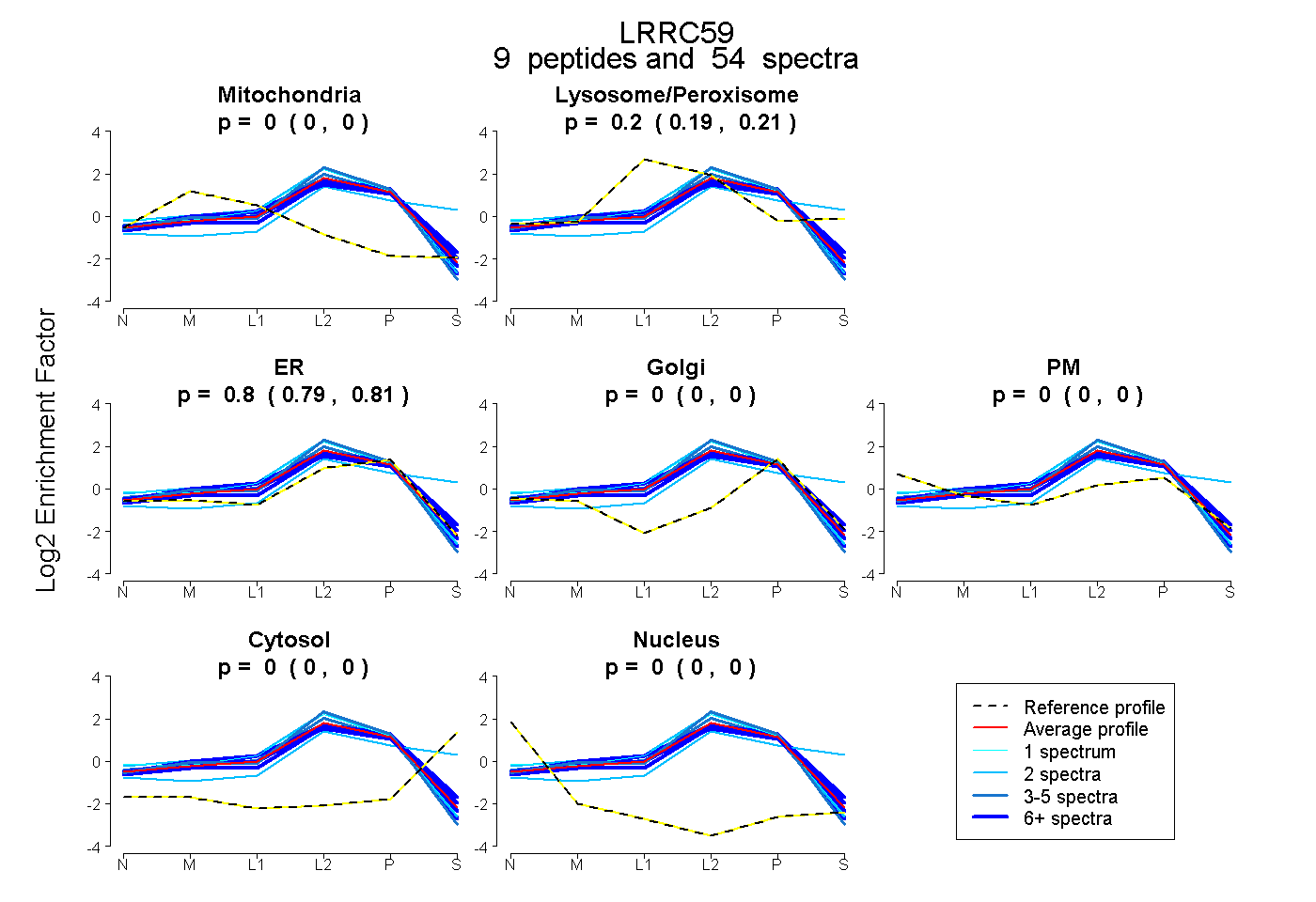
0.000 | 0.000
0.193 | 0.208
0.791 | 0.805
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
139 spectra |
 |
0.014 0.013 | 0.015 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.986 0.984 | 0.987 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
54 spectra |
 |
0.000 0.000 | 0.000 |
0.201 0.193 | 0.208 |
0.799 0.791 | 0.805 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, VAGDCLDEK | 0.000 | 0.222 | 0.778 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, AVQADQER | 0.000 | 0.179 | 0.821 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, VLQHMK | 0.000 | 0.111 | 0.889 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LSTLPSDFCGLTHLVK | 0.000 | 0.237 | 0.763 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, DNPLDPVLAK | 0.000 | 0.290 | 0.462 | 0.000 | 0.000 | 0.247 | 0.000 | |||
| 10 spectra, LVTLPVSFAQLK | 0.000 | 0.207 | 0.793 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, LQQLPADFGR | 0.000 | 0.124 | 0.876 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 17 spectra, LVNLQHLDLLNNR | 0.006 | 0.255 | 0.739 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ATVLDLSCNK | 0.000 | 0.169 | 0.831 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
272 spectra |
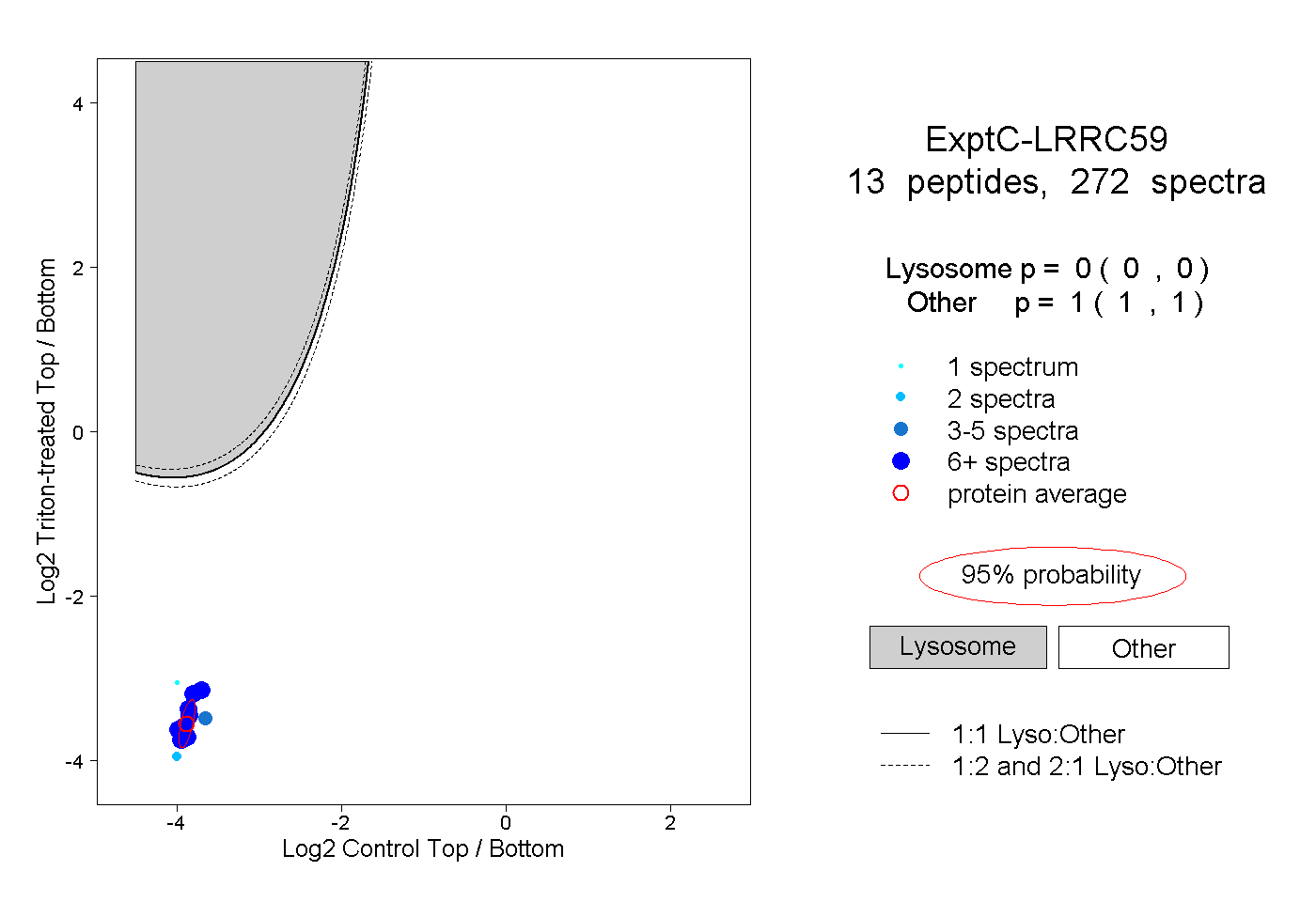 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
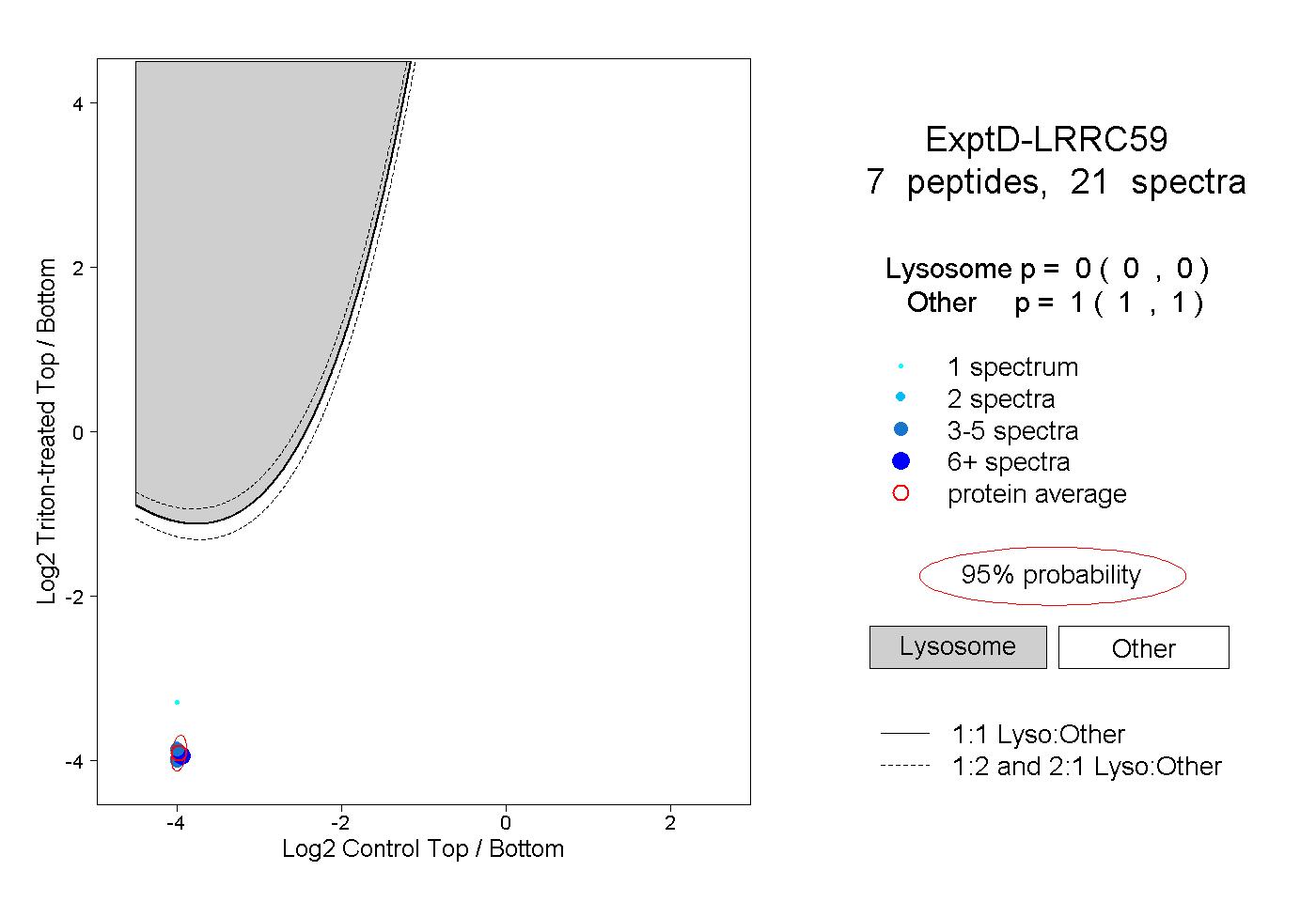 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |