peptides
spectra
0.000 | 0.026
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.040
0.000 | 0.049
0.919 | 0.953
0.000 | 0.031
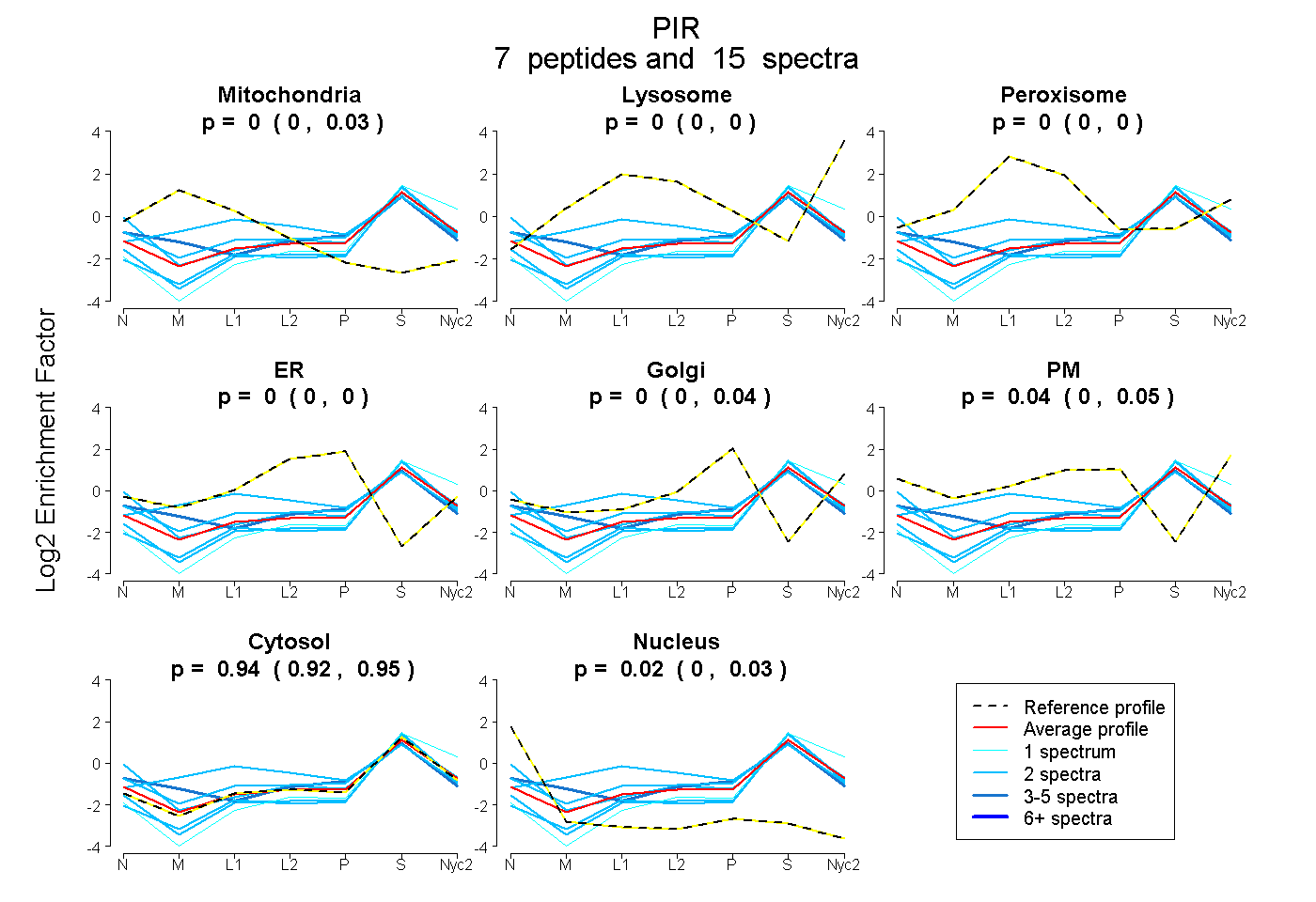
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
15 spectra |
 |
0.000 0.000 | 0.026 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.004 0.000 | 0.040 |
0.037 0.000 | 0.049 |
0.940 0.919 | 0.953 |
0.020 0.000 | 0.031 |
| 4 spectra, HSQPIPK | 0.133 | 0.000 | 0.000 | 0.000 | 0.083 | 0.000 | 0.772 | 0.012 | ||
| 2 spectra, EQSEGVGAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.962 | 0.038 | ||
| 2 spectra, GGRPGGFPDHPHR | 0.000 | 0.000 | 0.005 | 0.000 | 0.000 | 0.092 | 0.775 | 0.127 | ||
| 2 spectra, MNPGDLQWMTAGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, LDQGAK | 0.112 | 0.000 | 0.271 | 0.000 | 0.000 | 0.000 | 0.617 | 0.000 | ||
| 2 spectra, SIGGPELK | 0.000 | 0.000 | 0.063 | 0.000 | 0.000 | 0.078 | 0.834 | 0.025 | ||
| 1 spectrum, MVEPQYQELK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
8 spectra |
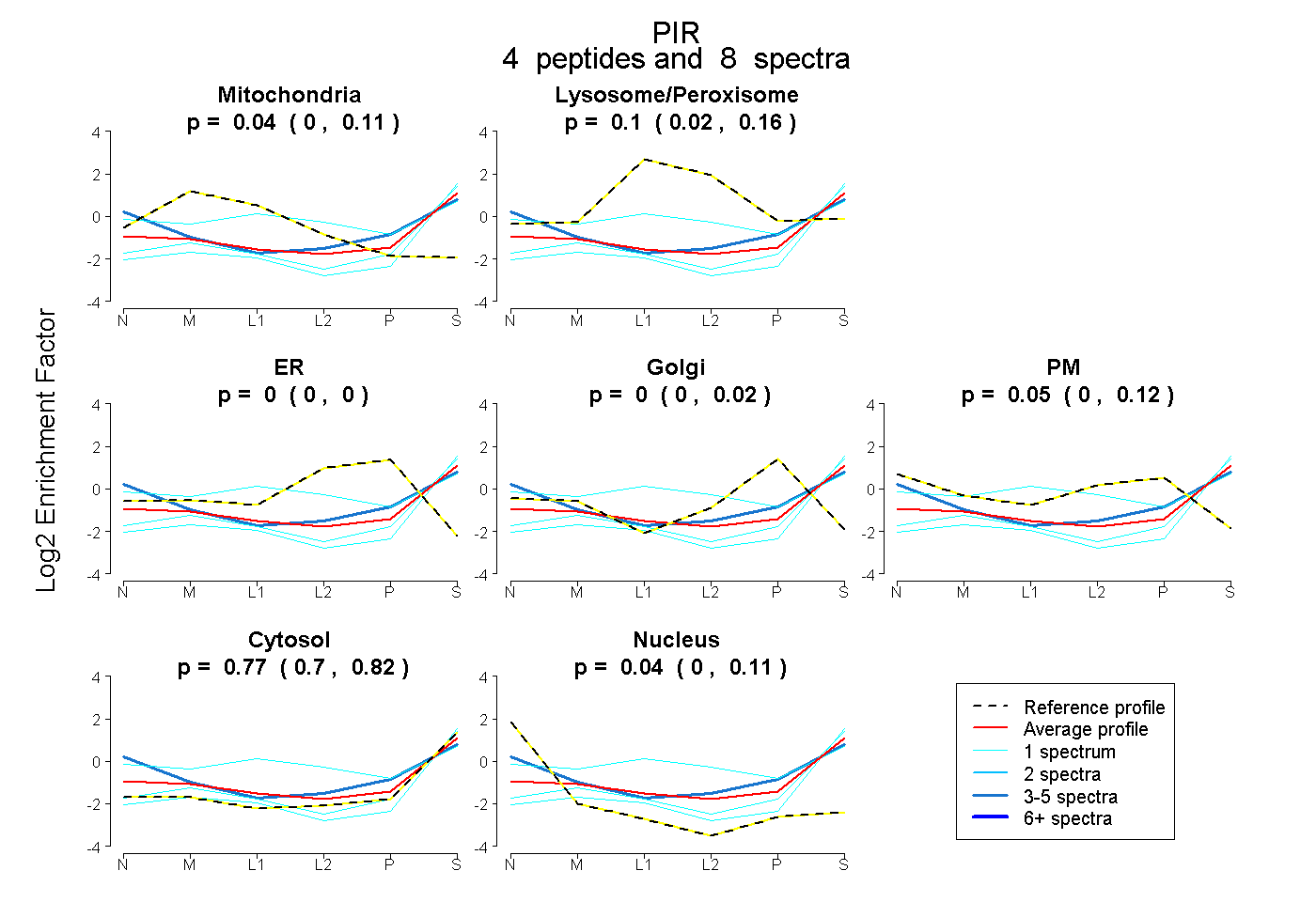 |
0.043 0.000 | 0.113 |
0.099 0.020 | 0.164 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.023 |
0.048 0.000 | 0.123 |
0.769 0.698 | 0.818 |
0.042 0.000 | 0.107 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
18 spectra |
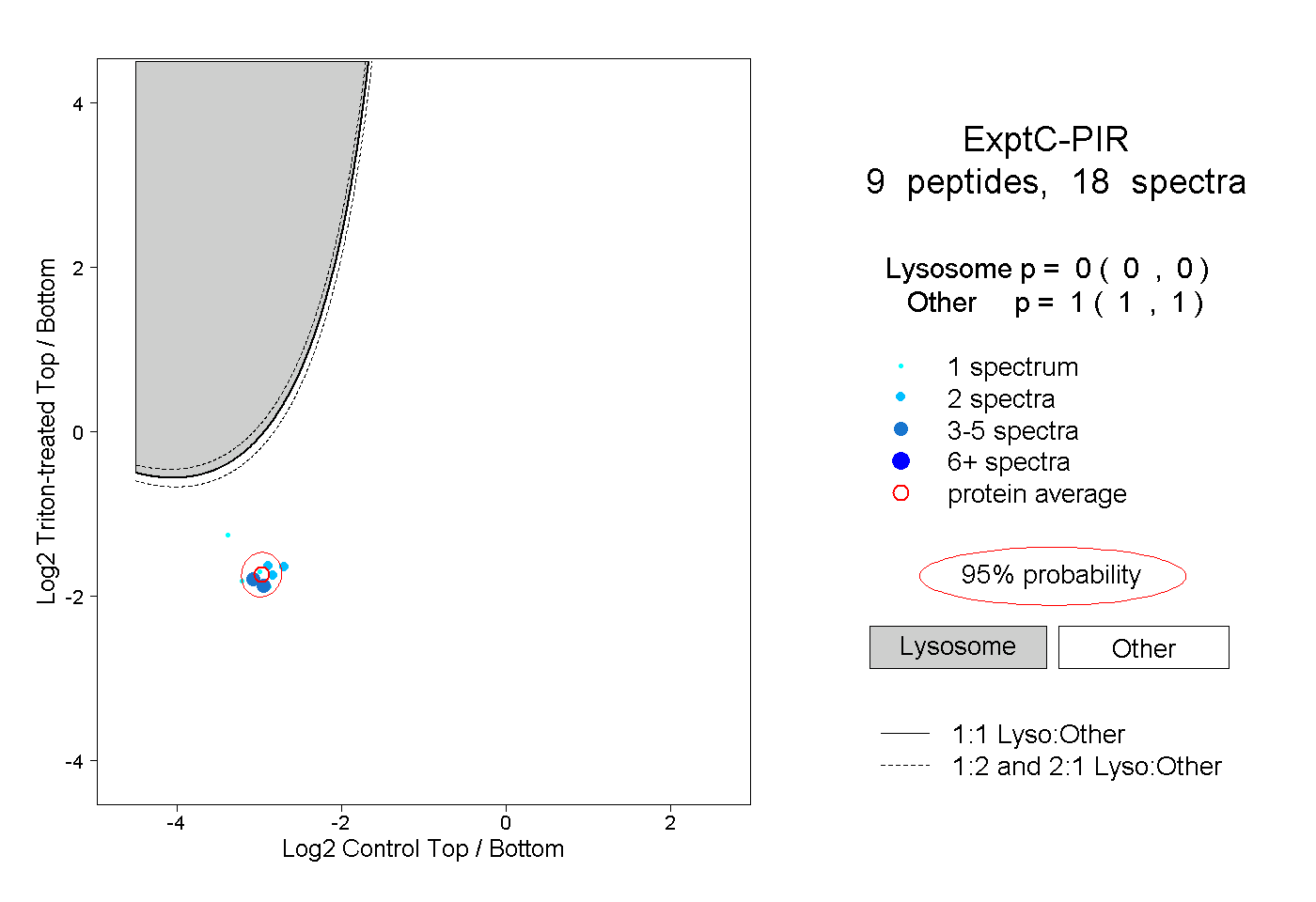 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |