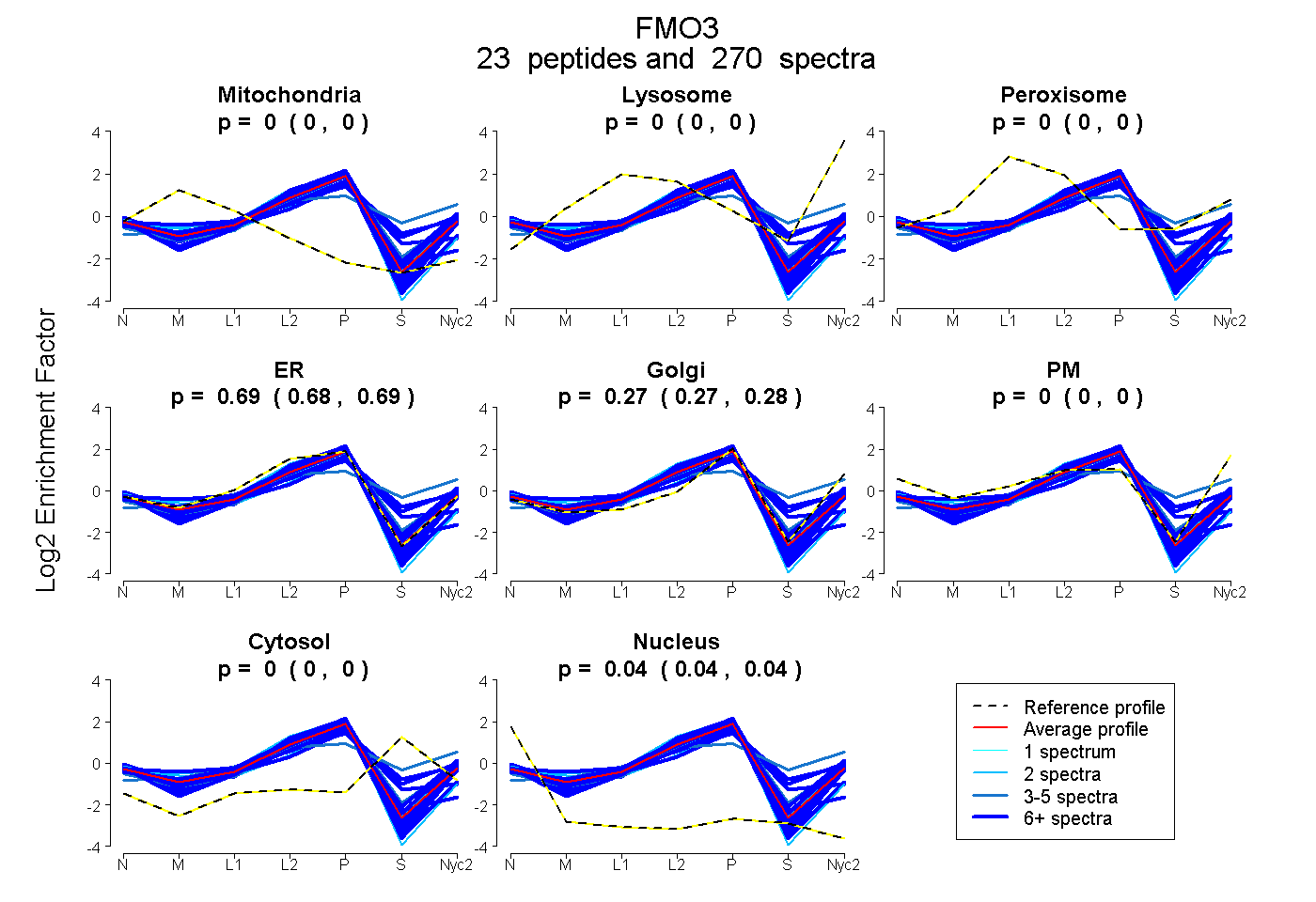
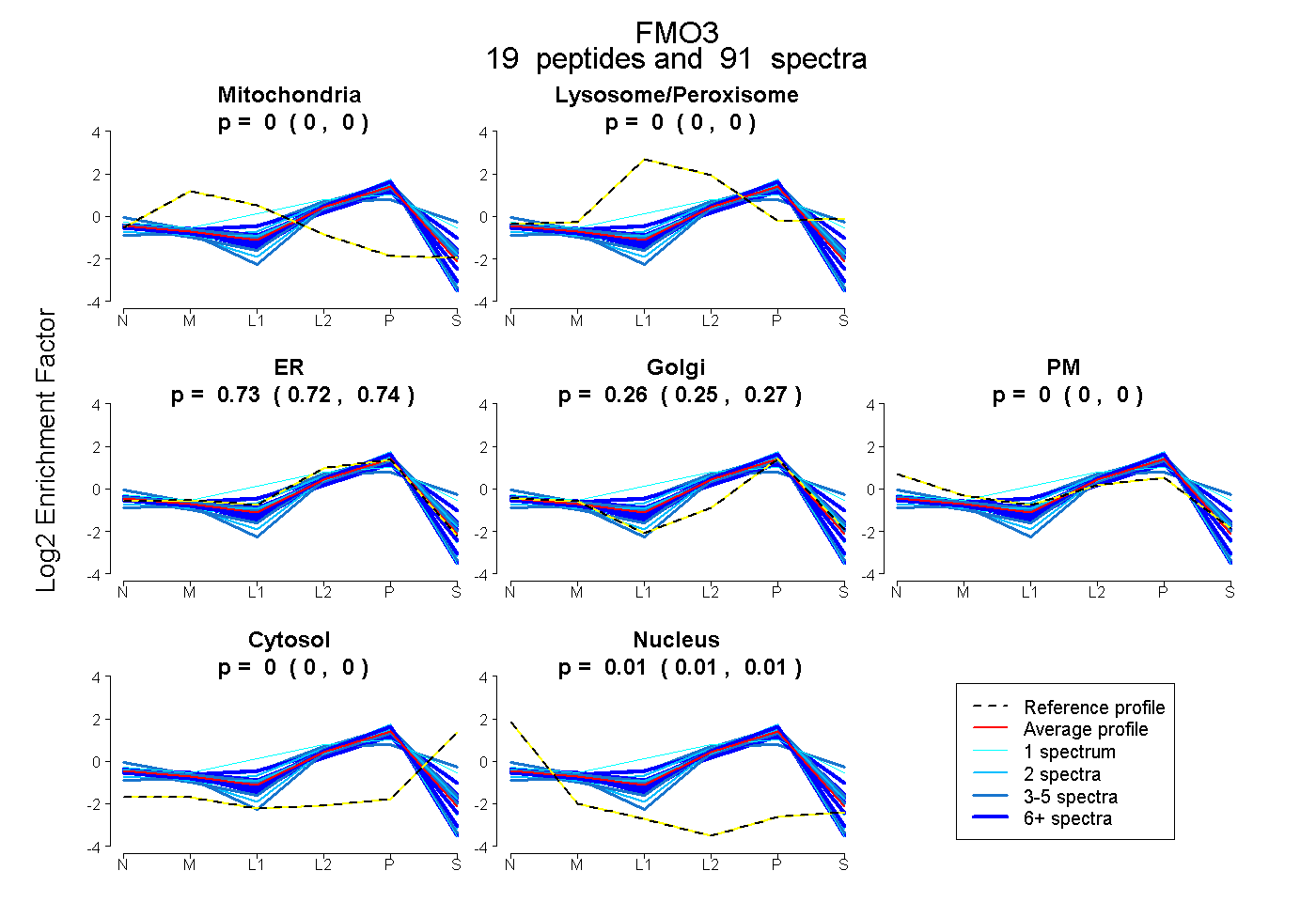
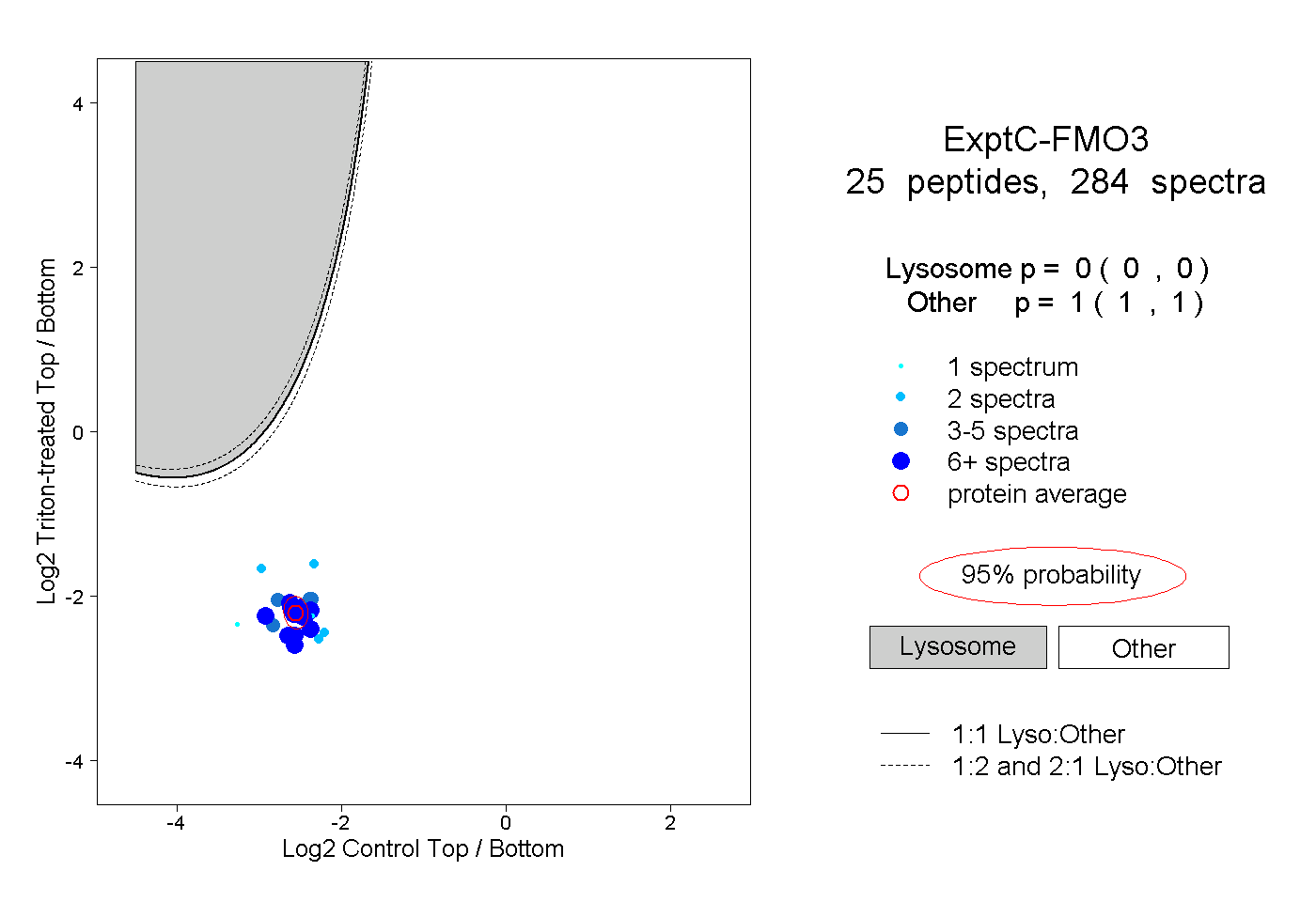
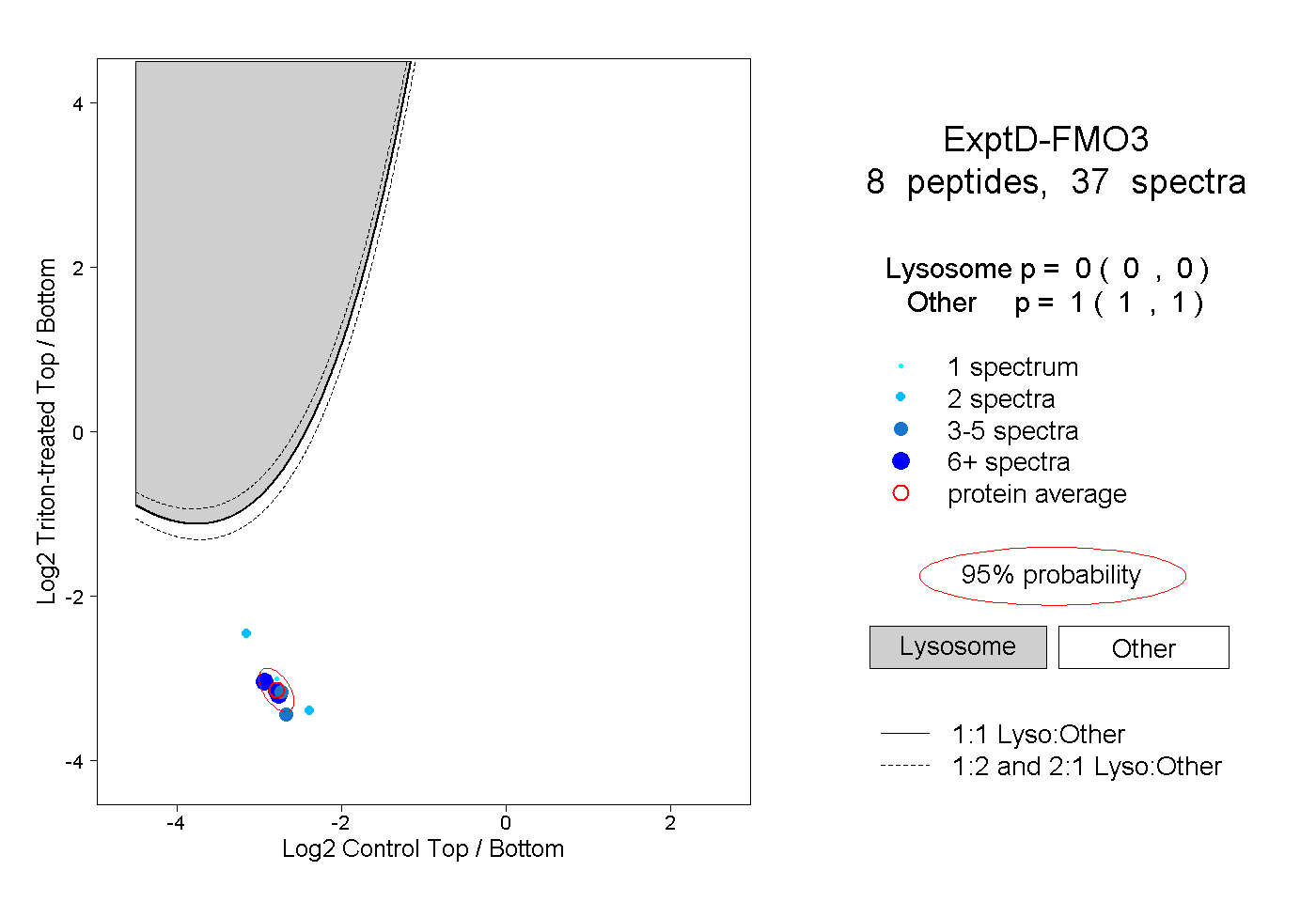
| 11 spectra, ASIYQSVFTNSSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, SGSWVMSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SCLEEGLEPTCFER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, WAAQVIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, DVGGIQKPCLYSHFLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, ILCGTVSIKPNVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, WEVTTEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, NAILTQWDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 27 spectra, EPVFNDELPAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, NNEVTLYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, FQTFLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, SLKPMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VLGPGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LQEYITSFATEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, VAVIGAGVSGLAAIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 31 spectra, DSFPGLNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NNLPTAISDWWYMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, VWNDGYPWDMVVITR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, FSDHTEEGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, YIQFETLVTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EPGTWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 36 spectra, LVGPGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GTCILPSVNDMMDDIDEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VAIVGAGVSGLAAIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, CPDFSTTGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |