peptides
spectra
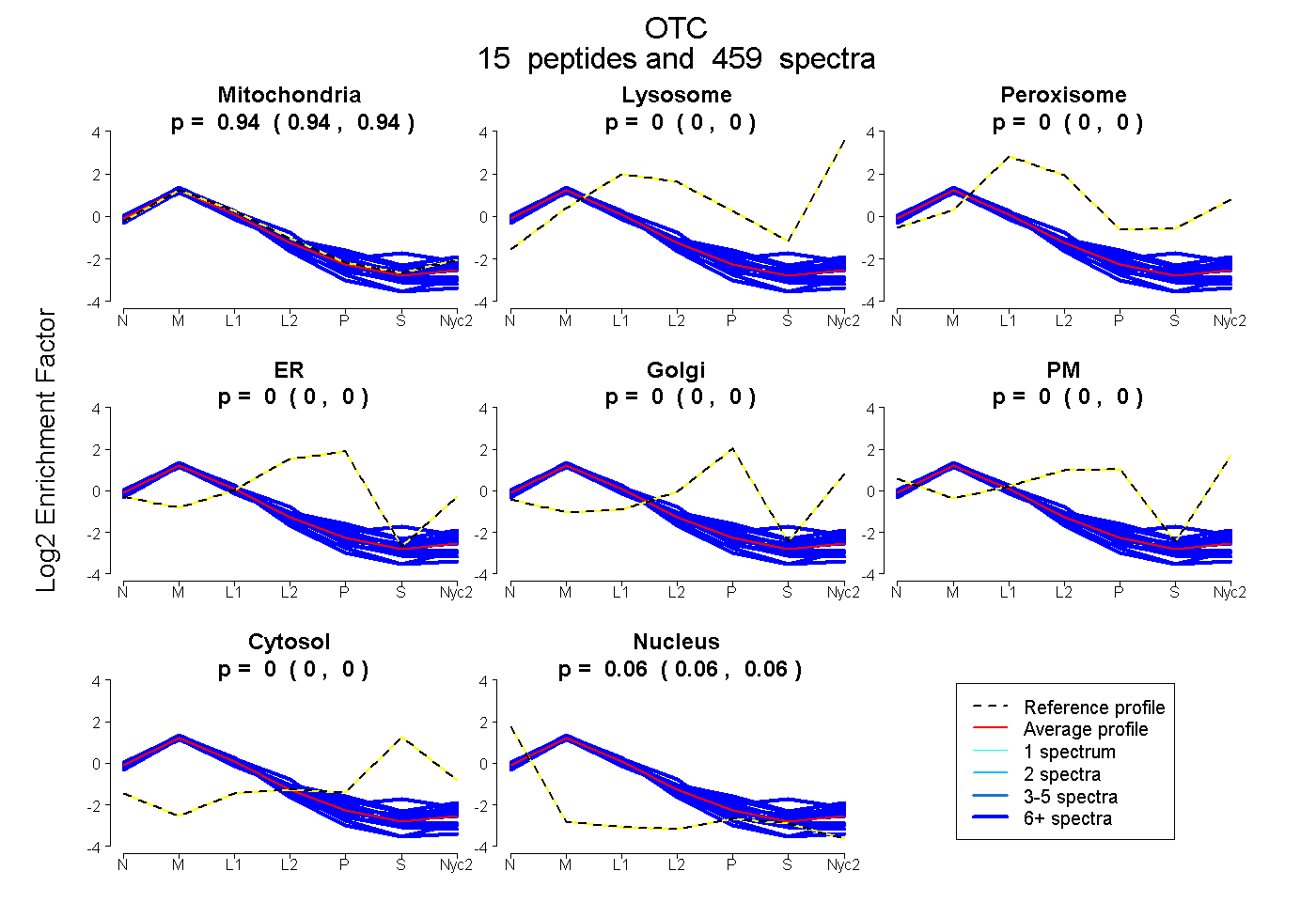
0.940 | 0.942
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.058 | 0.060
peptides
spectra
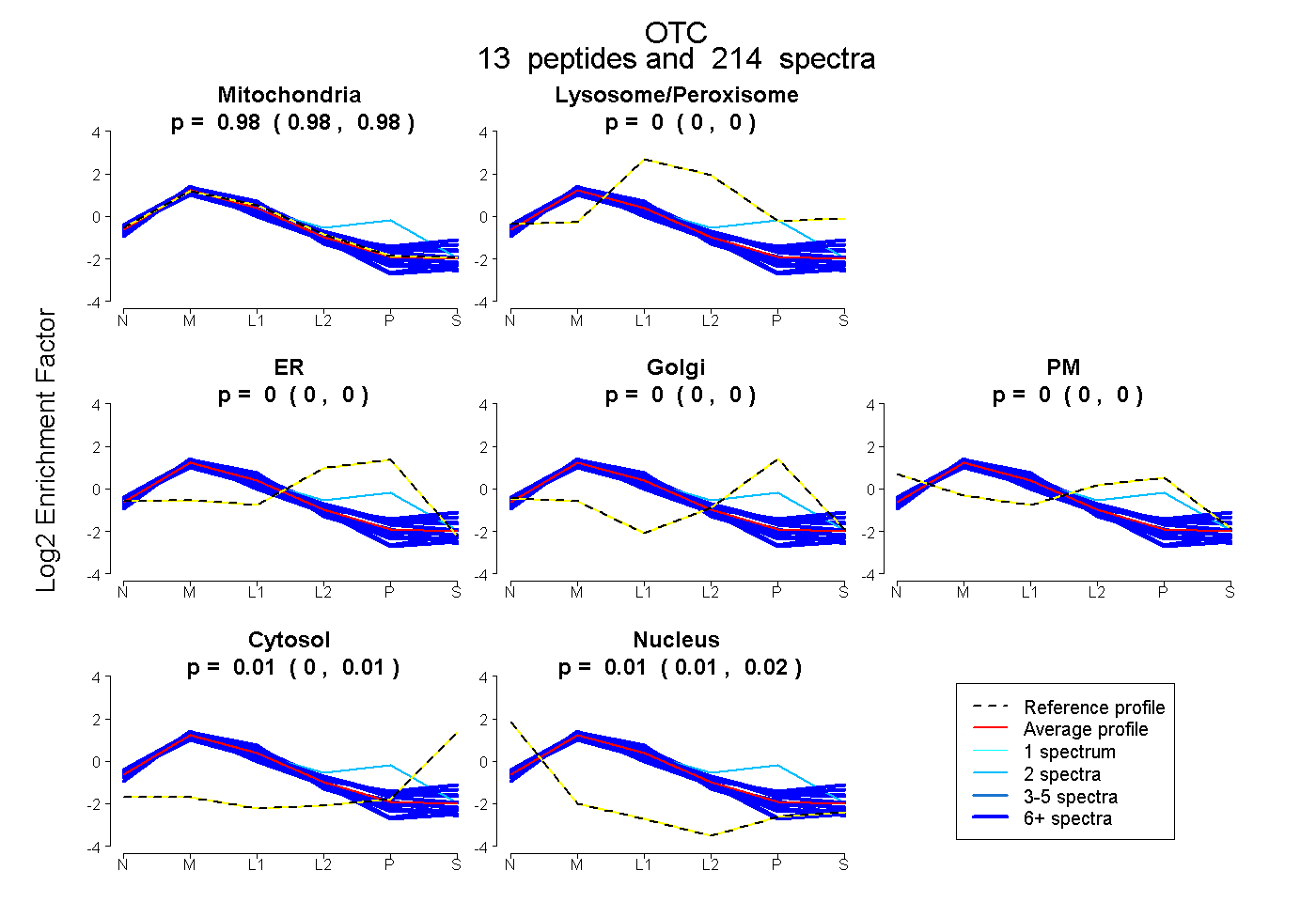
0.980 | 0.983
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.002 | 0.008
0.011 | 0.015
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
459 spectra |
 |
0.941 0.940 | 0.942 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.059 0.058 | 0.060 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
214 spectra |
 |
0.981 0.980 | 0.983 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.005 0.002 | 0.008 |
0.013 0.011 | 0.015 |
| 45 spectra, VLSSMTDAVLAR | 0.941 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.059 | |||
| 41 spectra, VAASDWTFLHCLPR | 0.988 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.012 | |||
| 13 spectra, SLVFPEAENR | 0.760 | 0.062 | 0.000 | 0.050 | 0.000 | 0.128 | 0.000 | |||
| 10 spectra, GEYLPLLQGK | 0.879 | 0.072 | 0.000 | 0.032 | 0.000 | 0.017 | 0.000 | |||
| 10 spectra, SLGMIFEK | 0.959 | 0.000 | 0.000 | 0.000 | 0.000 | 0.008 | 0.034 | |||
| 17 spectra, LSMTNDPLEAAR | 0.929 | 0.000 | 0.000 | 0.071 | 0.000 | 0.000 | 0.000 | |||
| 19 spectra, KPEEVDDEVFYSPR | 0.985 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.015 | |||
| 2 spectra, GGNVLITDTWISMGQEDEK | 0.625 | 0.038 | 0.233 | 0.103 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, LAEQYAK | 0.997 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.003 | |||
| 9 spectra, QSDLDILAK | 0.952 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.048 | |||
| 12 spectra, FGMHLQAATPK | 0.886 | 0.017 | 0.000 | 0.055 | 0.000 | 0.042 | 0.000 | |||
| 7 spectra, GYEPDPNIVK | 0.982 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.018 | |||
| 17 spectra, LQAFQGYQVTMK | 0.812 | 0.081 | 0.000 | 0.035 | 0.000 | 0.072 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1635 spectra |
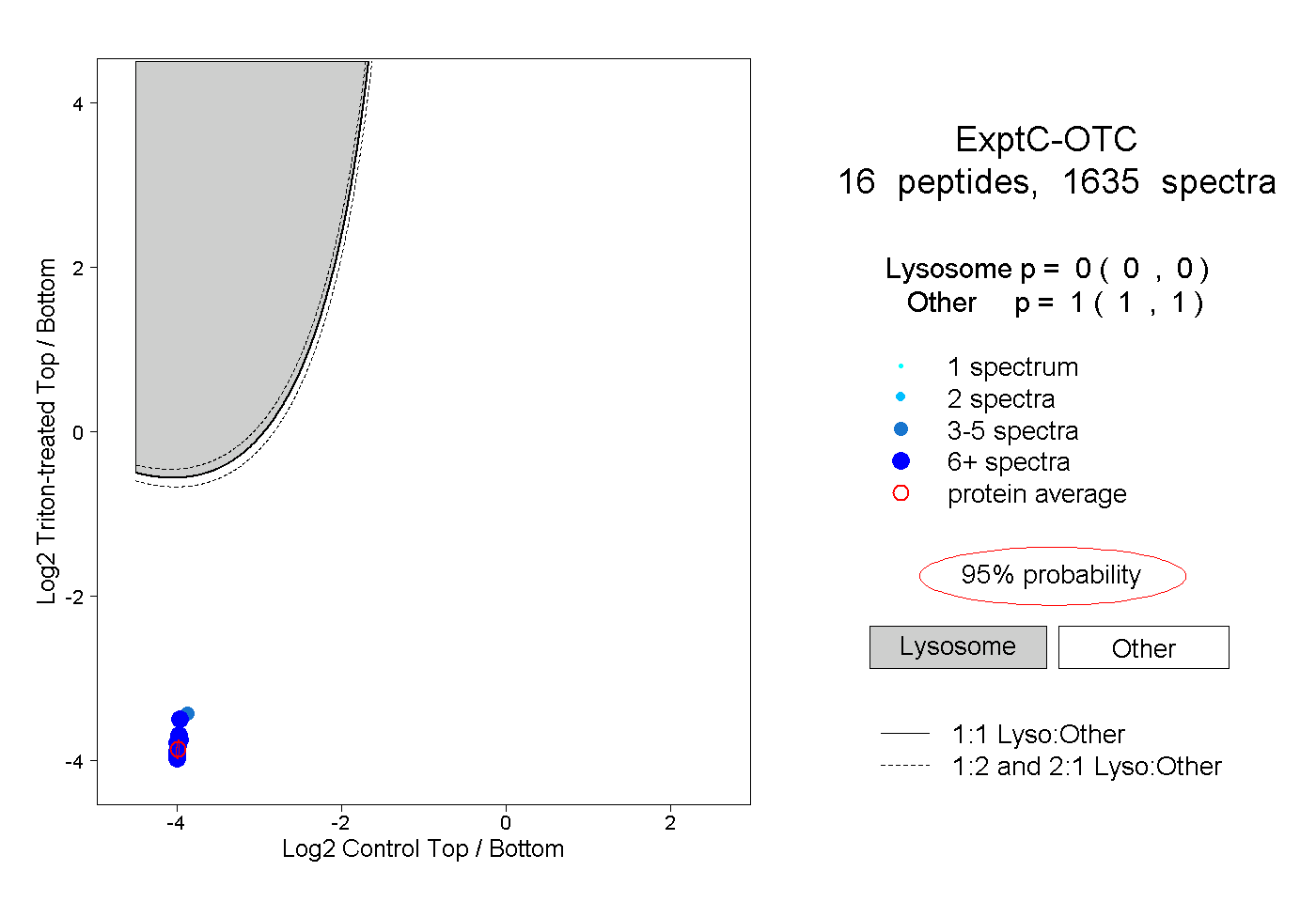 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
69 spectra |
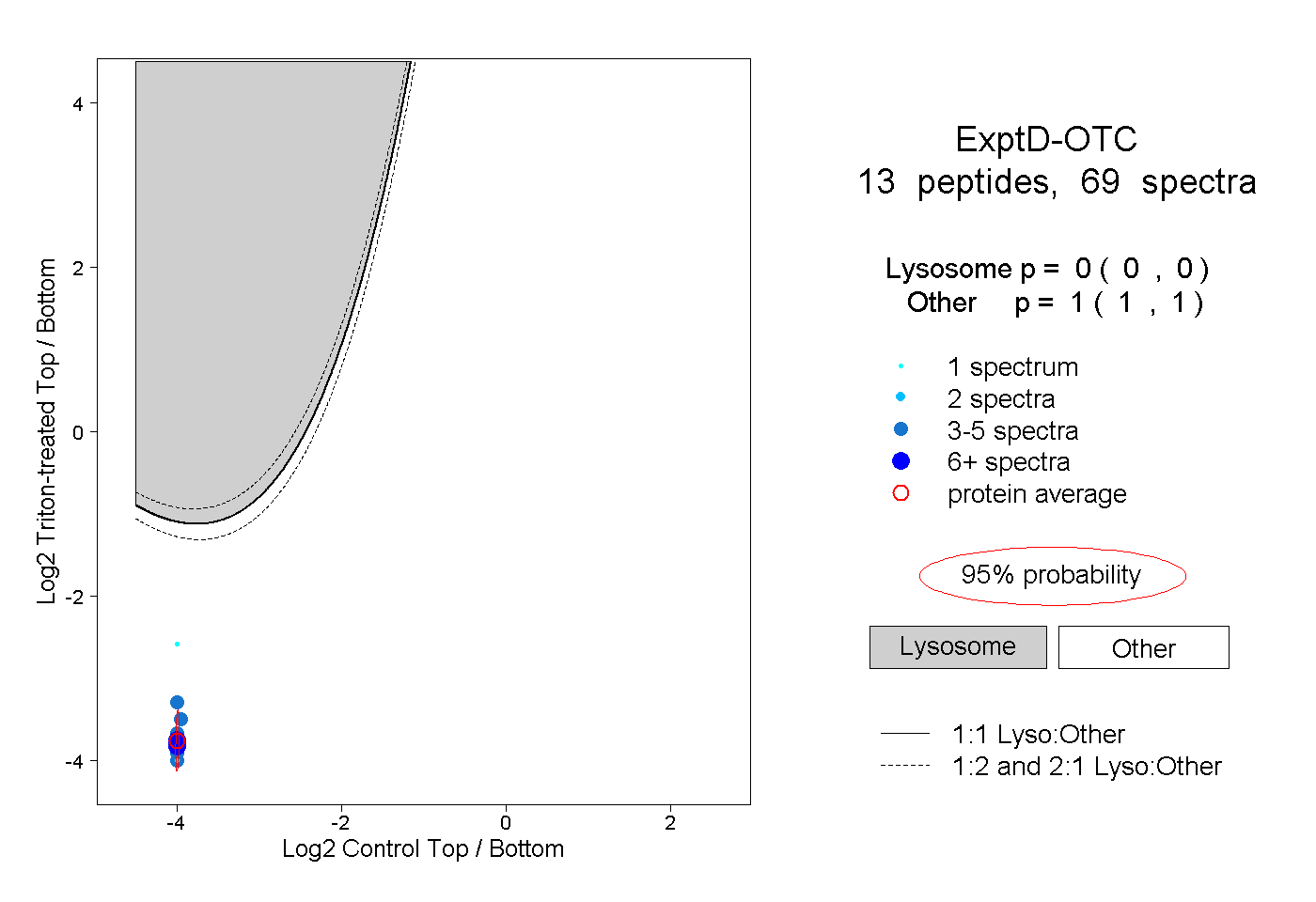 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |