peptides
spectra
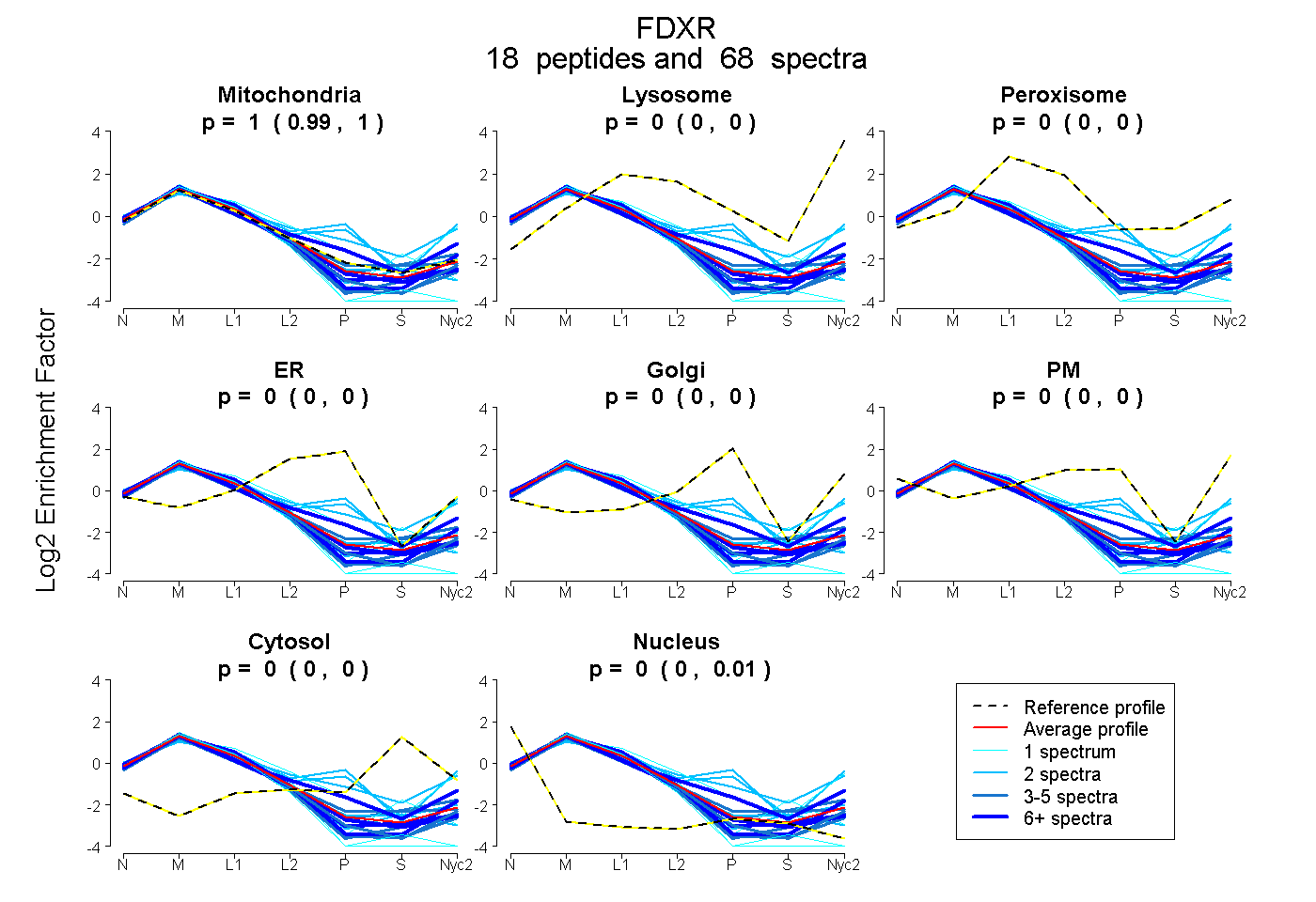
0.993 | 0.997
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.002 | 0.007
peptides
spectra
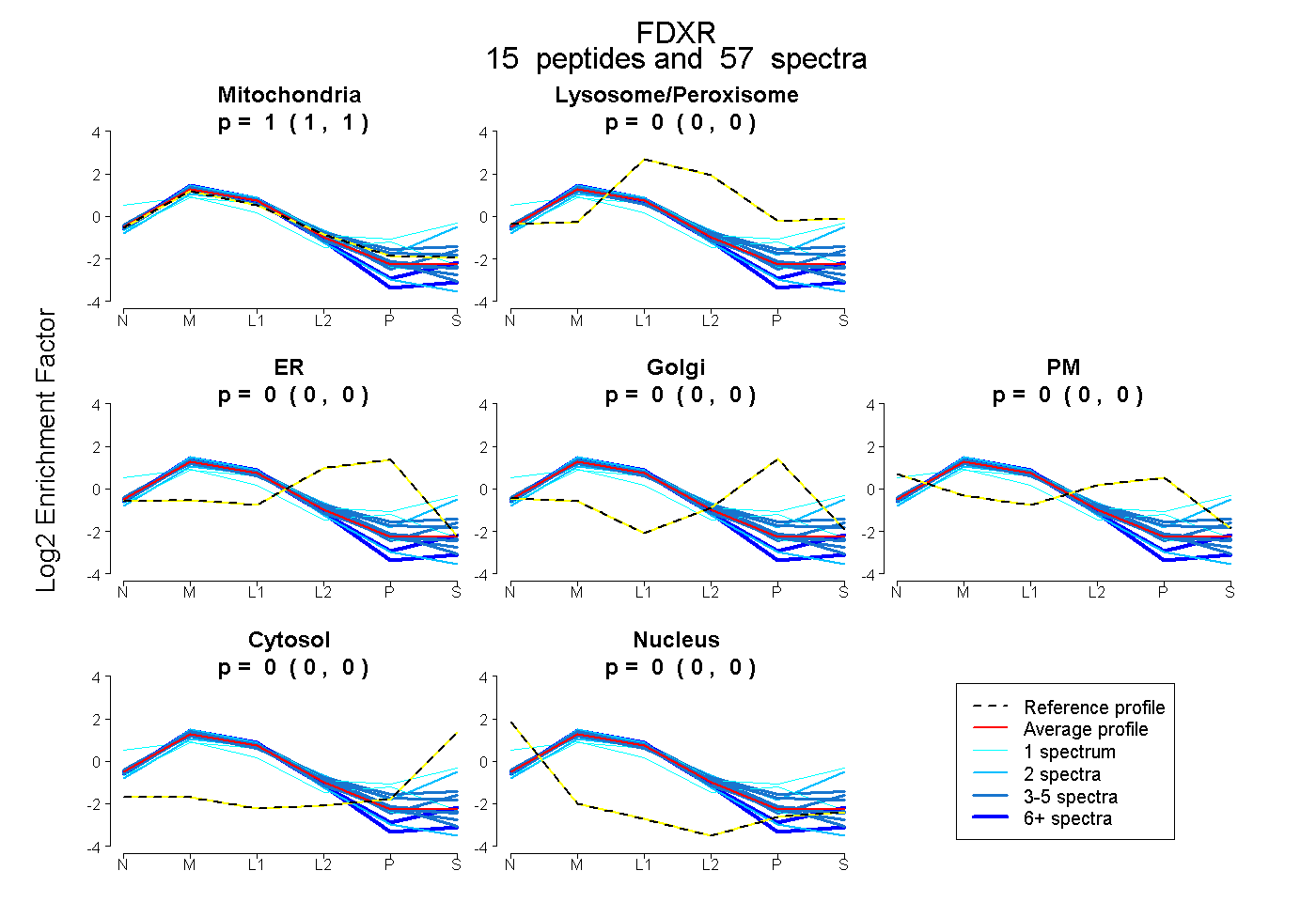
0.998 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.002
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
68 spectra |
 |
0.995 0.993 | 0.997 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.005 0.002 | 0.007 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
57 spectra |
 |
1.000 0.998 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.002 |
| 5 spectra, TVWIVGR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, NVINTFTQTAR | 0.984 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.016 | |||
| 14 spectra, LTELLLR | 0.987 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.013 | |||
| 3 spectra, EMLQLLGH | 0.978 | 0.000 | 0.000 | 0.000 | 0.000 | 0.022 | 0.000 | |||
| 1 spectrum, LDAEEVAR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GNVVVGR | 0.694 | 0.000 | 0.000 | 0.000 | 0.169 | 0.000 | 0.137 | |||
| 3 spectra, TDITEVALGVLR | 0.991 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.009 | |||
| 1 spectrum, GPLQVAFTIK | 0.568 | 0.225 | 0.000 | 0.000 | 0.000 | 0.207 | 0.000 | |||
| 5 spectra, DVSVPELR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, SRPIDPSVPFDPK | 0.964 | 0.019 | 0.000 | 0.001 | 0.016 | 0.000 | 0.000 | |||
| 2 spectra, QLVPFGLVR | 0.986 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.014 | |||
| 2 spectra, AHVDIYEK | 0.667 | 0.173 | 0.000 | 0.000 | 0.000 | 0.160 | 0.000 | |||
| 3 spectra, FGVAPDHPEVK | 0.858 | 0.095 | 0.000 | 0.005 | 0.000 | 0.041 | 0.000 | |||
| 3 spectra, LEGVGESTR | 0.999 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.001 | |||
| 3 spectra, LGIIPNTEGR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
320 spectra |
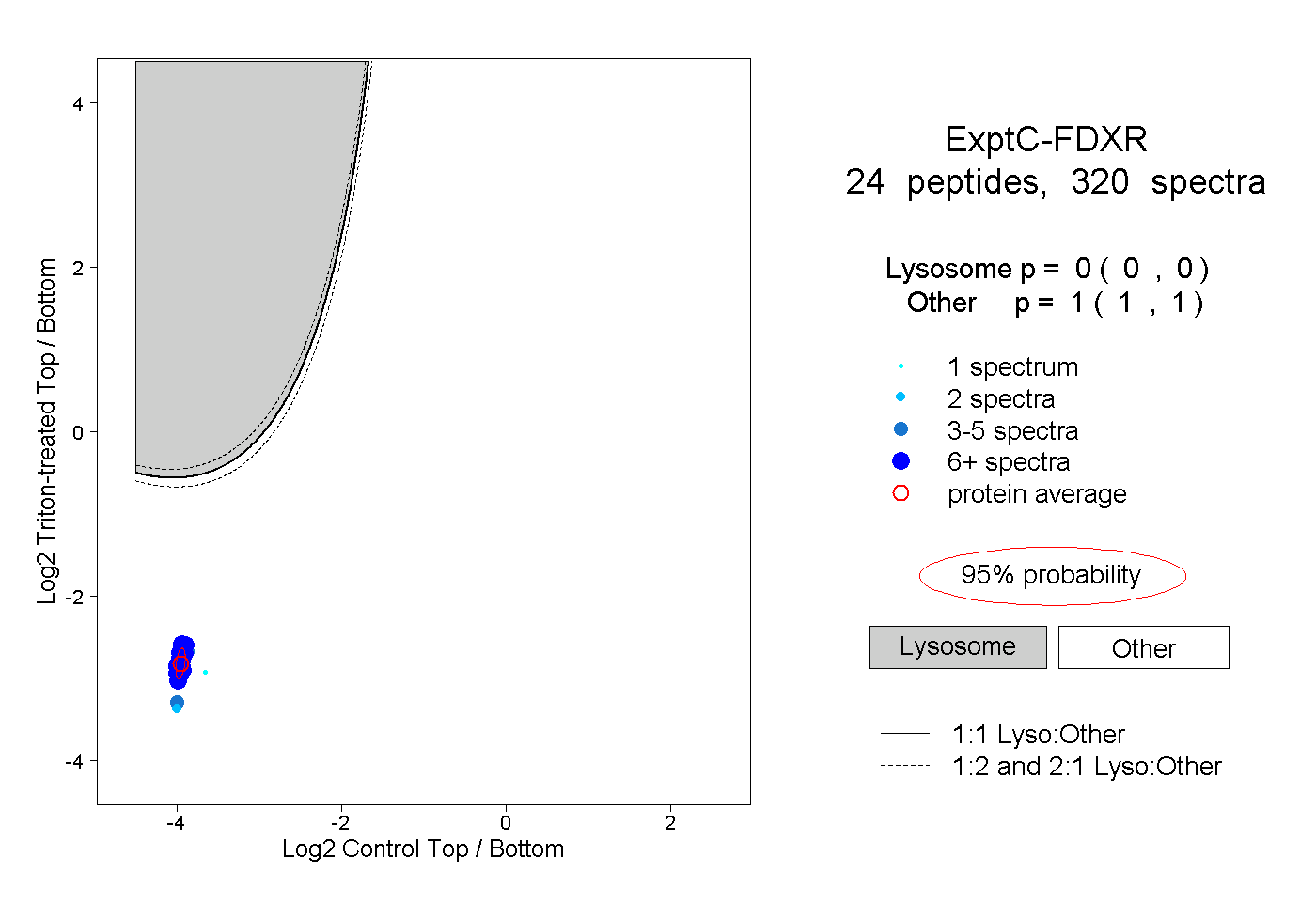 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
33 spectra |
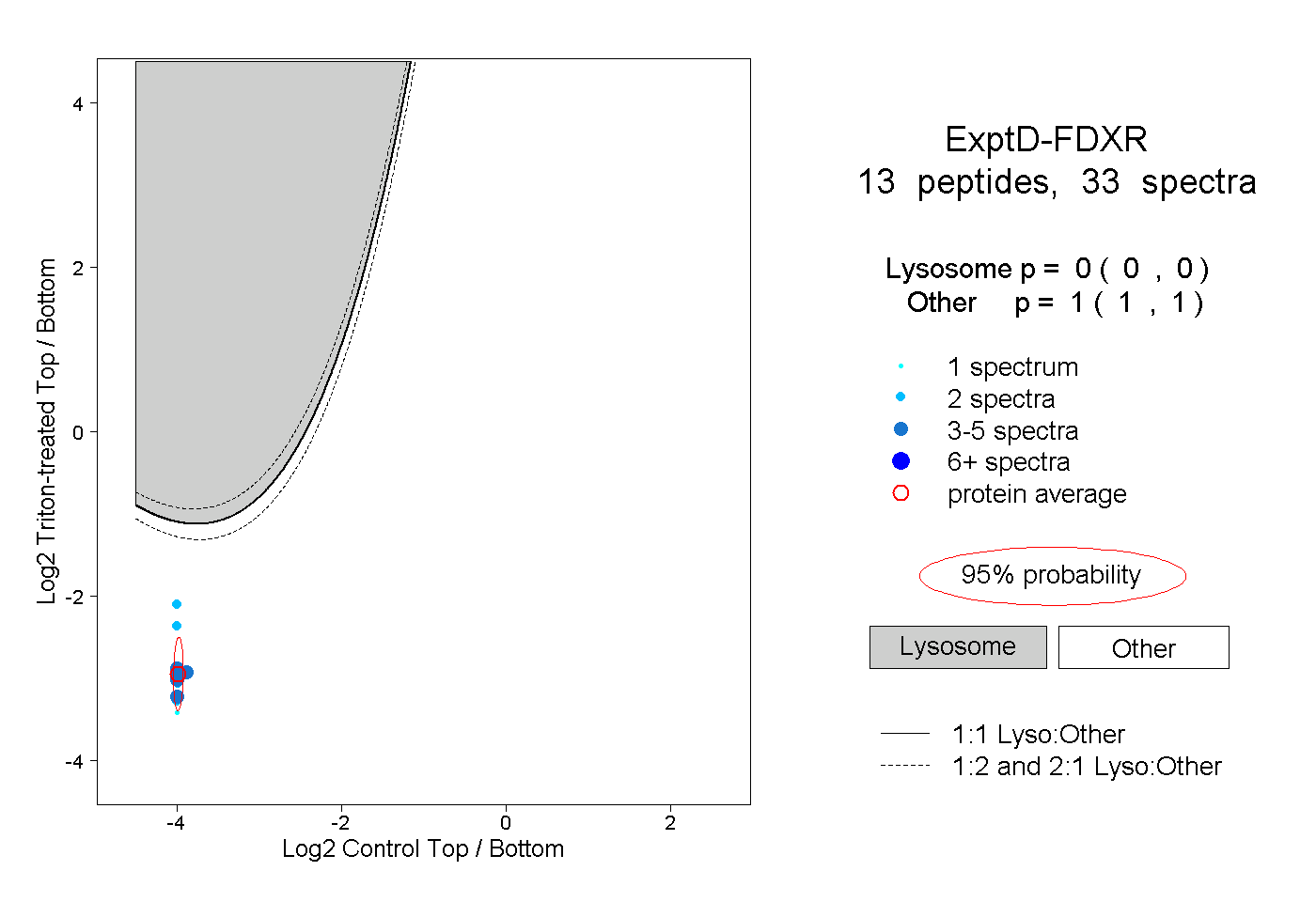 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |