peptides
spectra
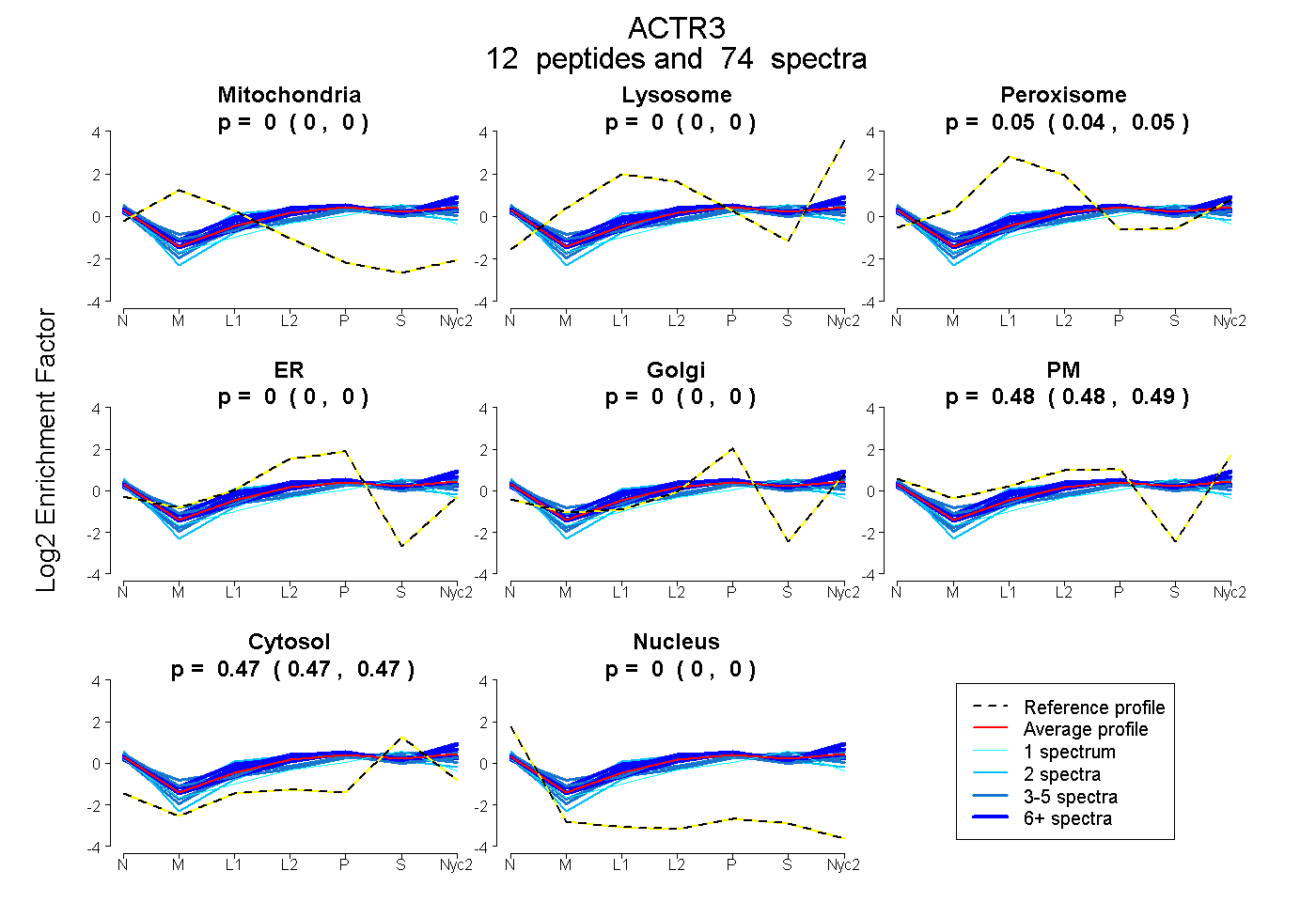
0.000 | 0.000
0.000 | 0.000
0.044 | 0.052
0.000 | 0.000
0.000 | 0.000
0.481 | 0.487
0.465 | 0.470
0.000 | 0.000
peptides
spectra
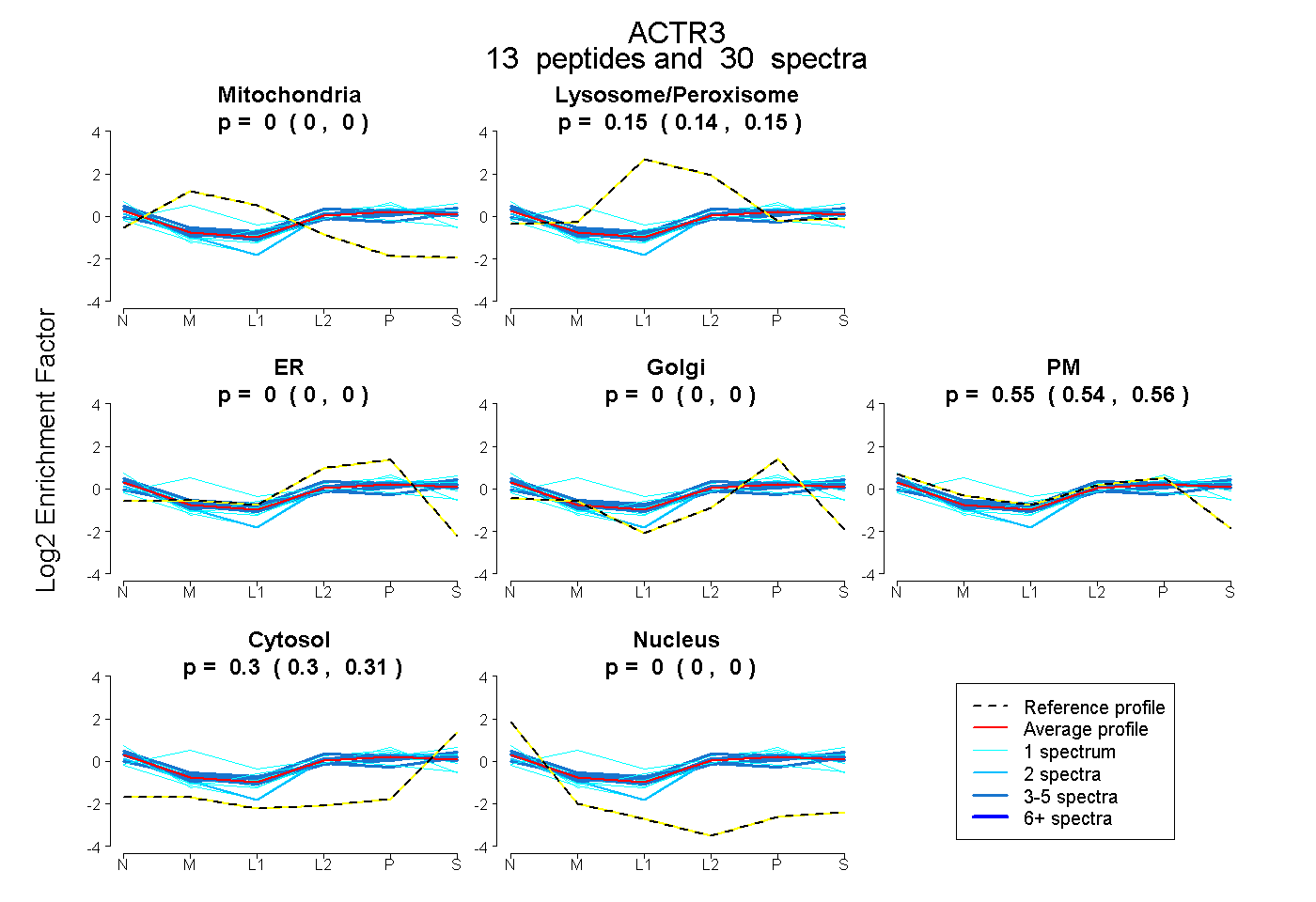
0.000 | 0.000
0.138 | 0.151
0.000 | 0.000
0.000 | 0.000
0.544 | 0.560
0.297 | 0.306
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
74 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.048 0.044 | 0.052 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.484 0.481 | 0.487 |
0.468 0.465 | 0.470 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
30 spectra |
 |
0.000 0.000 | 0.000 |
0.146 0.138 | 0.151 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.553 0.544 | 0.560 |
0.302 0.297 | 0.306 |
0.000 0.000 | 0.000 |
| 5 spectra, AEPEDHYFLLTEPPLNTPENR | 0.000 | 0.129 | 0.000 | 0.000 | 0.540 | 0.331 | 0.000 | |||
| 2 spectra, HGIVEDWDLMER | 0.000 | 0.011 | 0.159 | 0.000 | 0.450 | 0.380 | 0.000 | |||
| 1 spectrum, LGYAGNTEPQFIIPSCIAIK | 0.000 | 0.176 | 0.000 | 0.000 | 0.499 | 0.325 | 0.000 | |||
| 4 spectra, HNPVFGVMS | 0.000 | 0.215 | 0.000 | 0.028 | 0.392 | 0.365 | 0.000 | |||
| 1 spectrum, DITYFIQQLLR | 0.000 | 0.082 | 0.000 | 0.000 | 0.632 | 0.286 | 0.000 | |||
| 1 spectrum, QYTGVNAISK | 0.203 | 0.215 | 0.000 | 0.093 | 0.339 | 0.150 | 0.000 | |||
| 4 spectra, VGDQAQR | 0.000 | 0.130 | 0.000 | 0.000 | 0.582 | 0.287 | 0.000 | |||
| 1 spectrum, NIVLSGGSTMFR | 0.000 | 0.115 | 0.000 | 0.027 | 0.683 | 0.174 | 0.000 | |||
| 1 spectrum, FMEQVIFK | 0.000 | 0.062 | 0.249 | 0.000 | 0.232 | 0.457 | 0.000 | |||
| 1 spectrum, DYEEIGPSICR | 0.000 | 0.100 | 0.000 | 0.000 | 0.579 | 0.320 | 0.000 | |||
| 1 spectrum, EVGIPPEQSLETAK | 0.000 | 0.189 | 0.000 | 0.085 | 0.513 | 0.213 | 0.000 | |||
| 5 spectra, LPACVVDCGTGYTK | 0.000 | 0.199 | 0.000 | 0.000 | 0.488 | 0.313 | 0.000 | |||
| 3 spectra, HIPIAGR | 0.000 | 0.192 | 0.000 | 0.000 | 0.555 | 0.253 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
87 spectra |
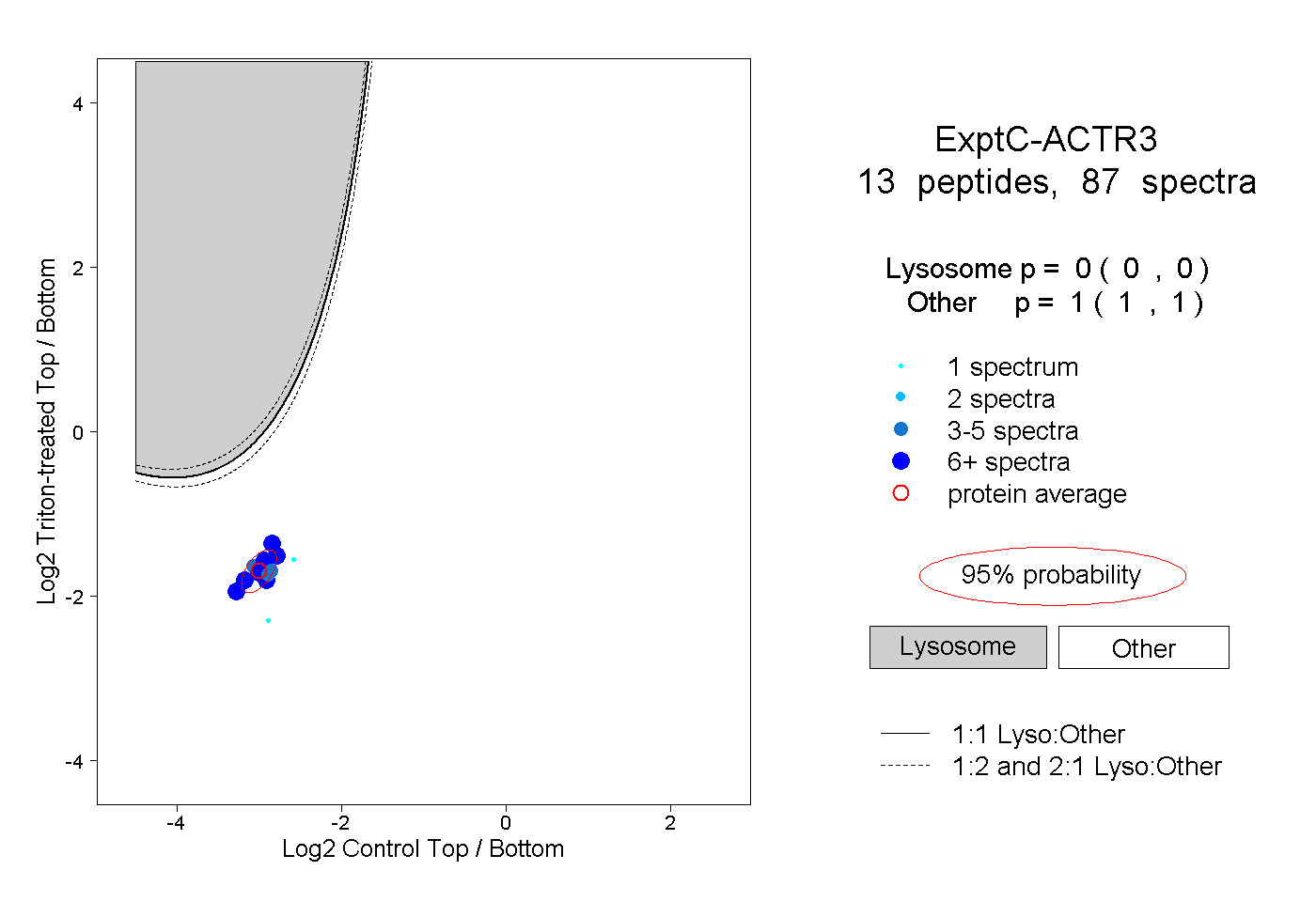 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
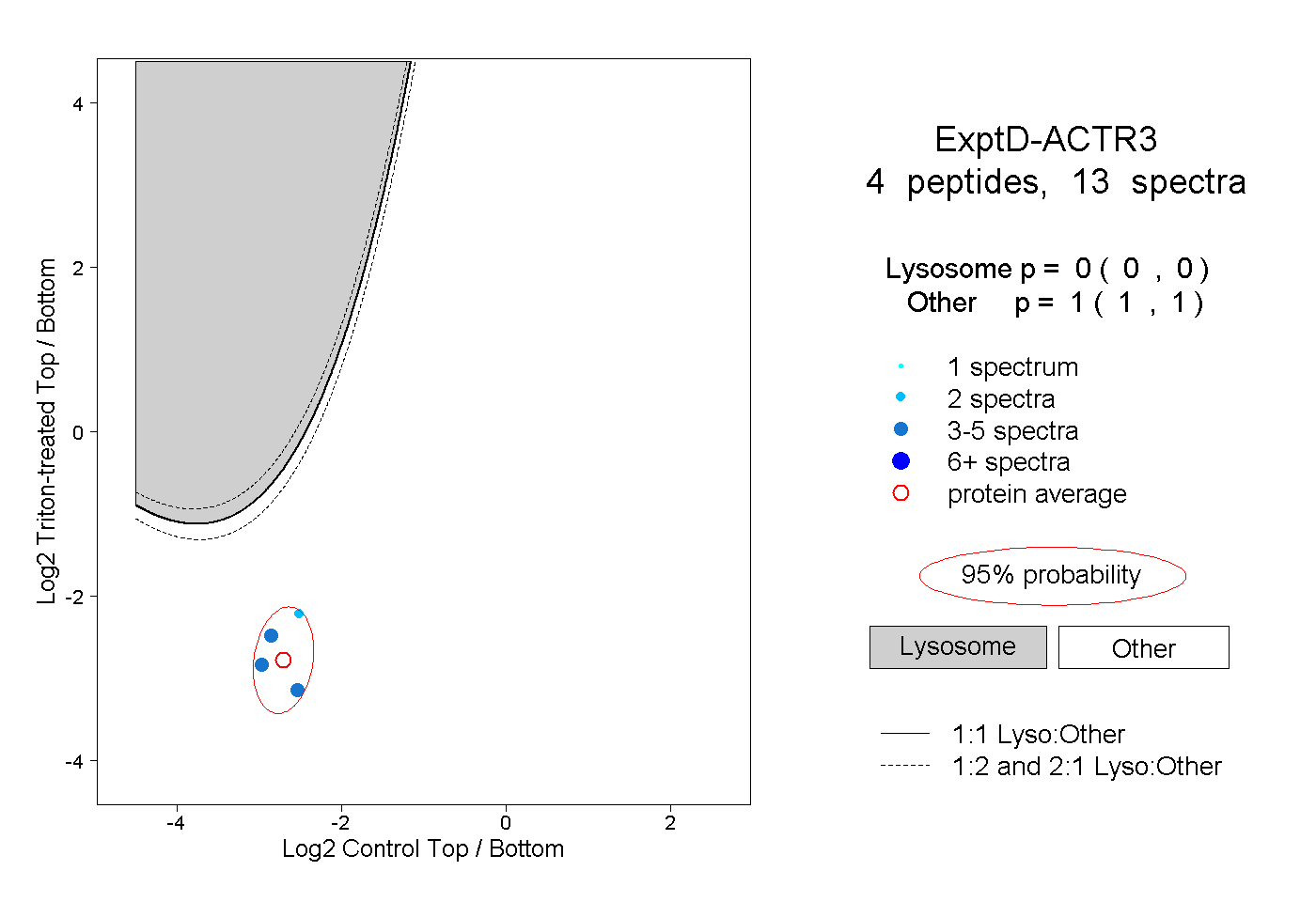 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |