peptides
spectra
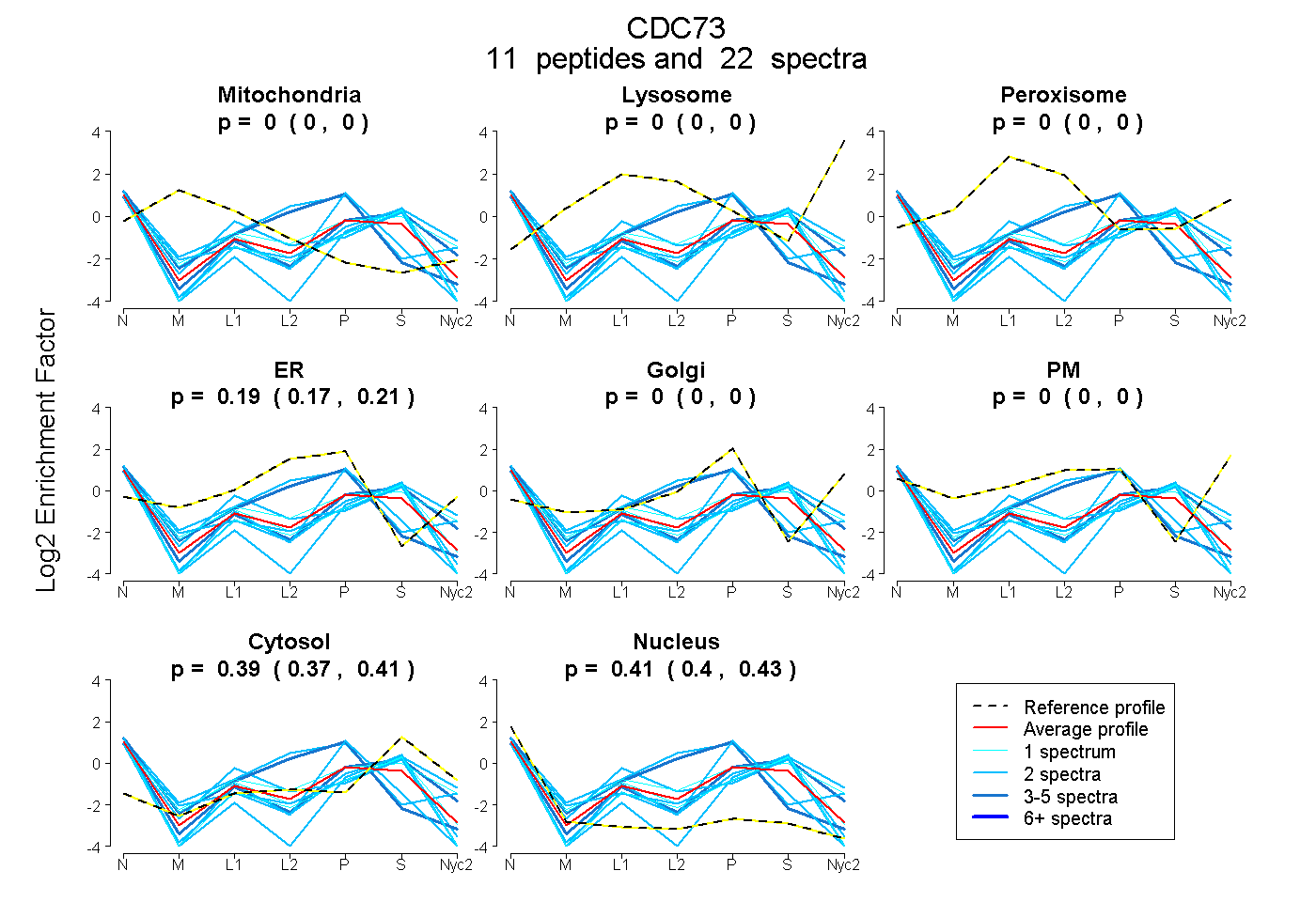
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.174 | 0.210
0.000 | 0.000
0.000 | 0.000
0.369 | 0.411
0.396 | 0.430
peptides
spectra
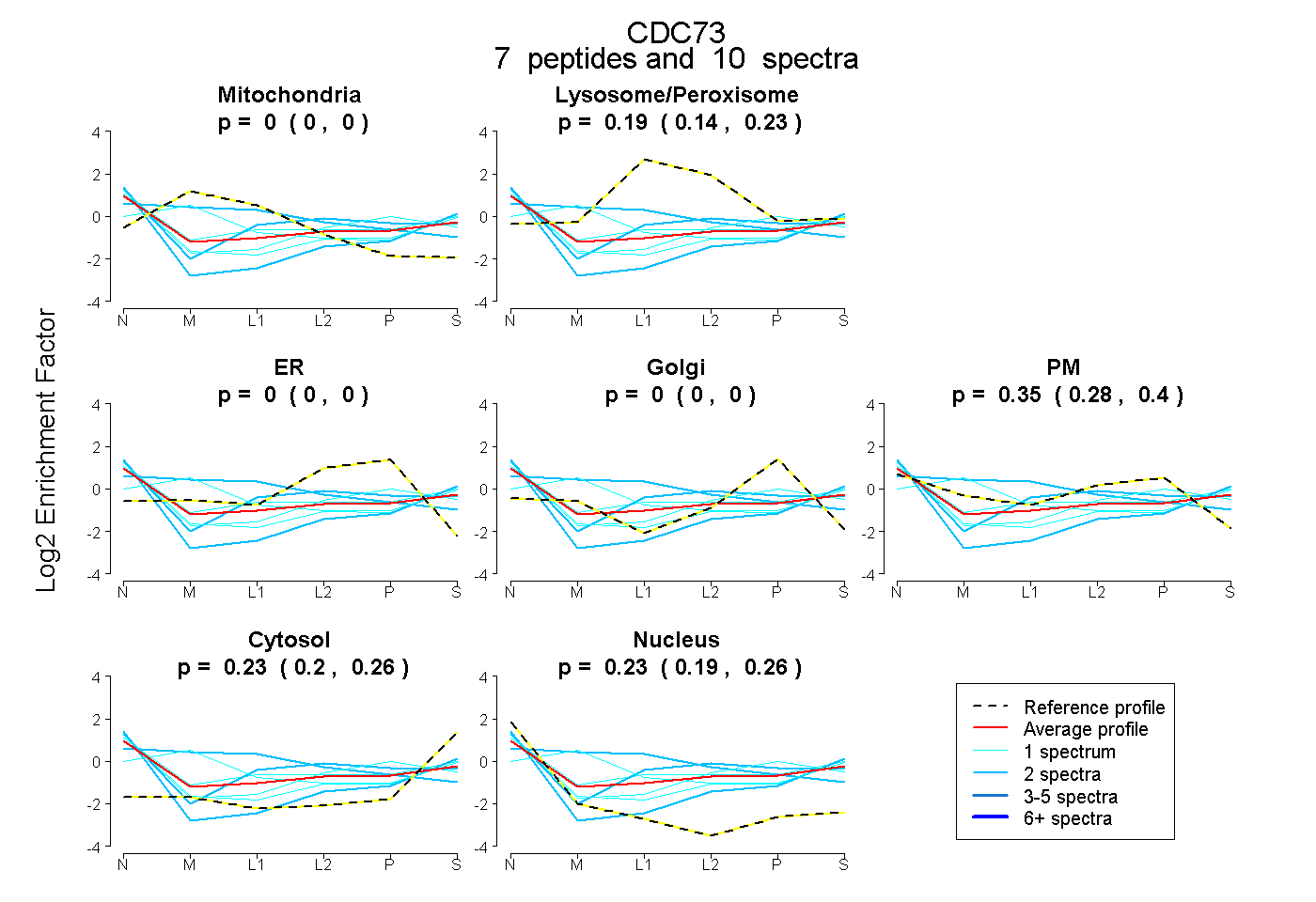
0.000 | 0.000
0.135 | 0.234
0.000 | 0.000
0.000 | 0.000
0.280 | 0.405
0.200 | 0.258
0.193 | 0.262
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.193 0.174 | 0.210 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.392 0.369 | 0.411 |
0.414 0.396 | 0.430 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
10 spectra |
 |
0.000 0.000 | 0.000 |
0.190 0.135 | 0.234 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.346 0.280 | 0.405 |
0.231 0.200 | 0.258 |
0.233 0.193 | 0.262 |
| 1 spectrum, AADEVLAEAK | 0.000 | 0.095 | 0.000 | 0.000 | 0.276 | 0.321 | 0.308 | |||
| 2 spectra, HLDRPVFLR | 0.000 | 0.342 | 0.000 | 0.000 | 0.285 | 0.101 | 0.272 | |||
| 1 spectrum, AATENIPVVR | 0.000 | 0.287 | 0.000 | 0.000 | 0.269 | 0.208 | 0.236 | |||
| 1 spectrum, SAPLEIGLQR | 0.376 | 0.032 | 0.000 | 0.000 | 0.261 | 0.332 | 0.000 | |||
| 2 spectra, ENETLIQR | 0.319 | 0.245 | 0.000 | 0.000 | 0.330 | 0.017 | 0.089 | |||
| 1 spectrum, SVTEGASAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.639 | 0.224 | 0.137 | |||
| 2 spectra, IEDEECVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.229 | 0.389 | 0.382 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
4 spectra |
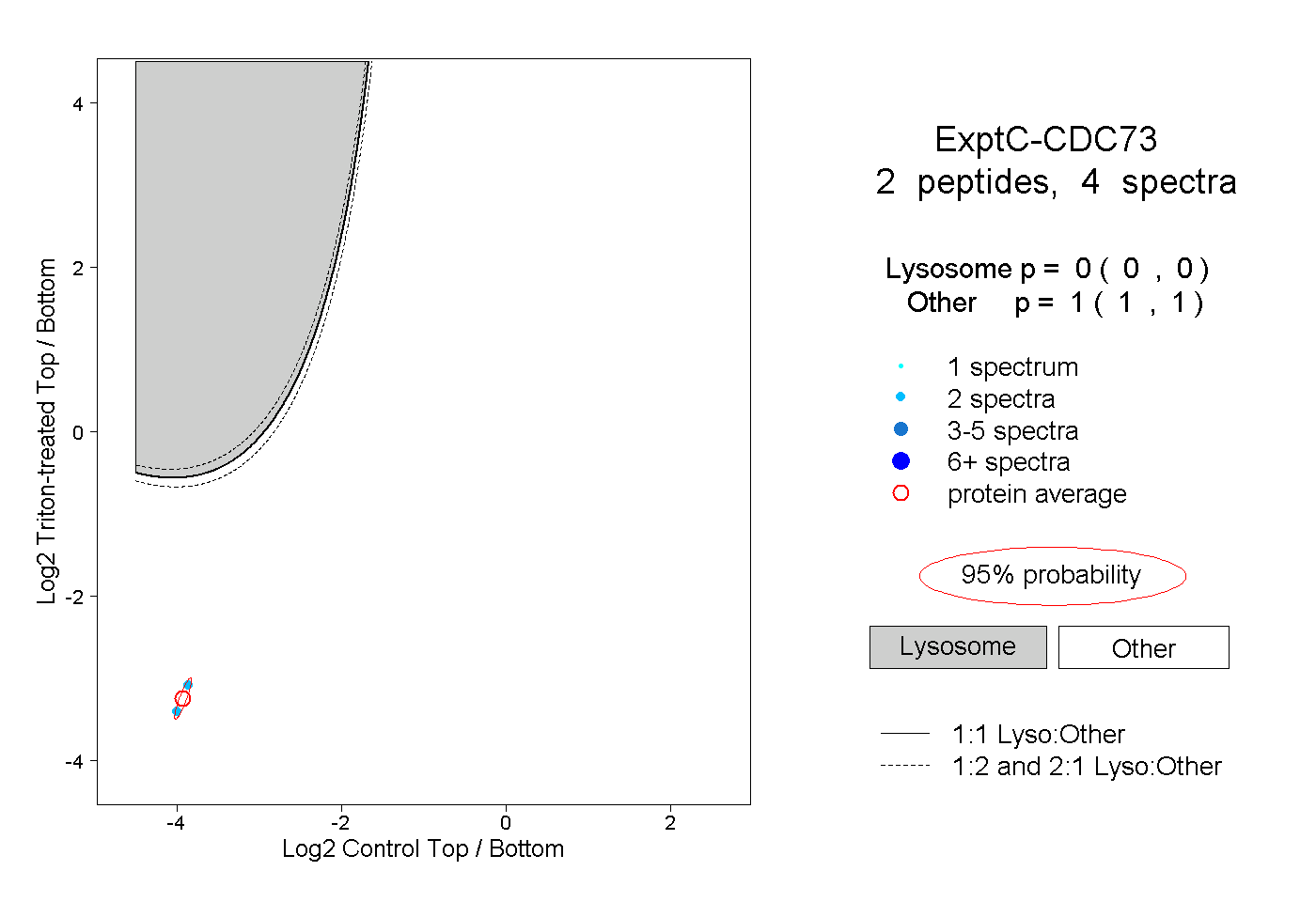 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
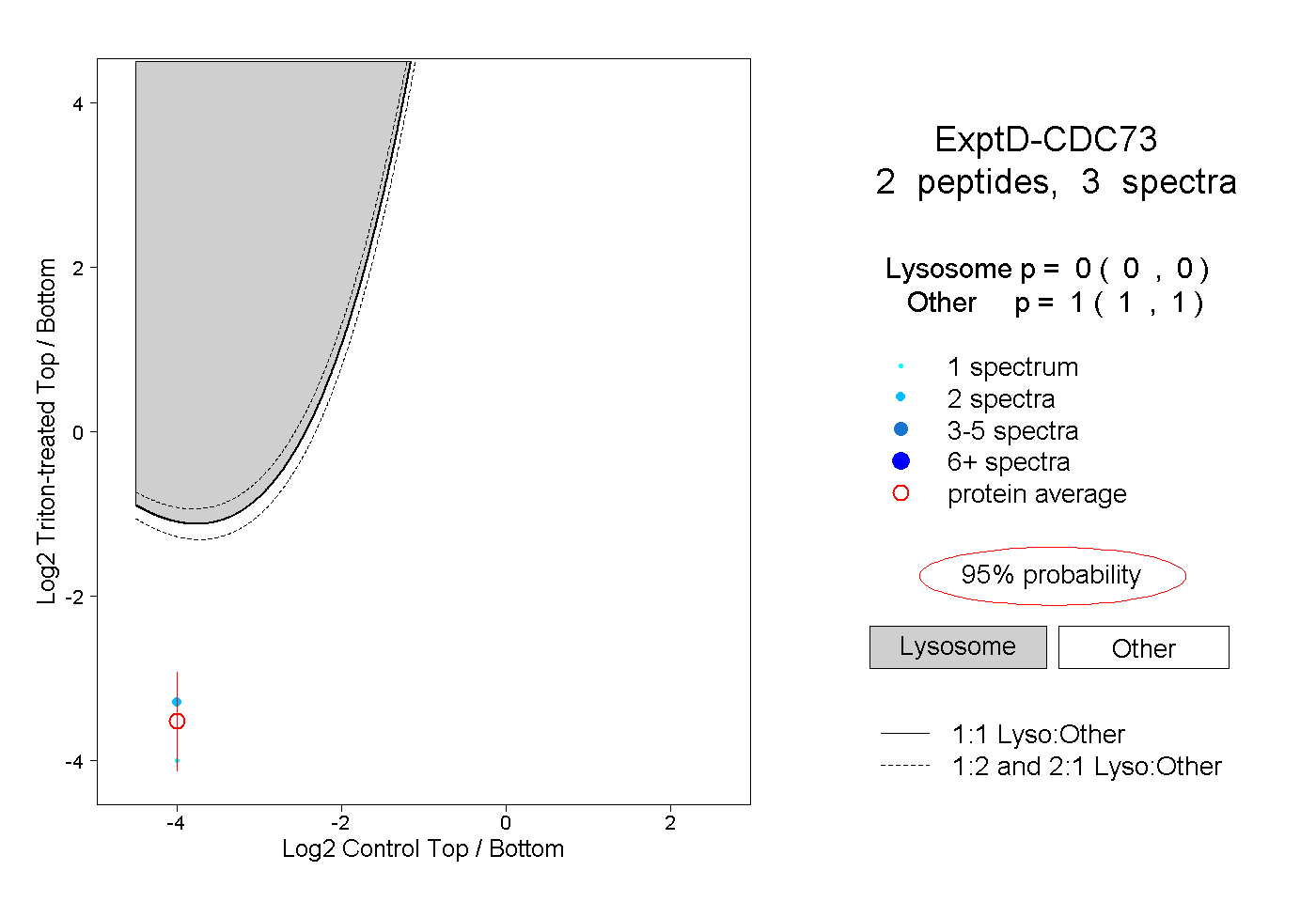 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |