peptides
spectra
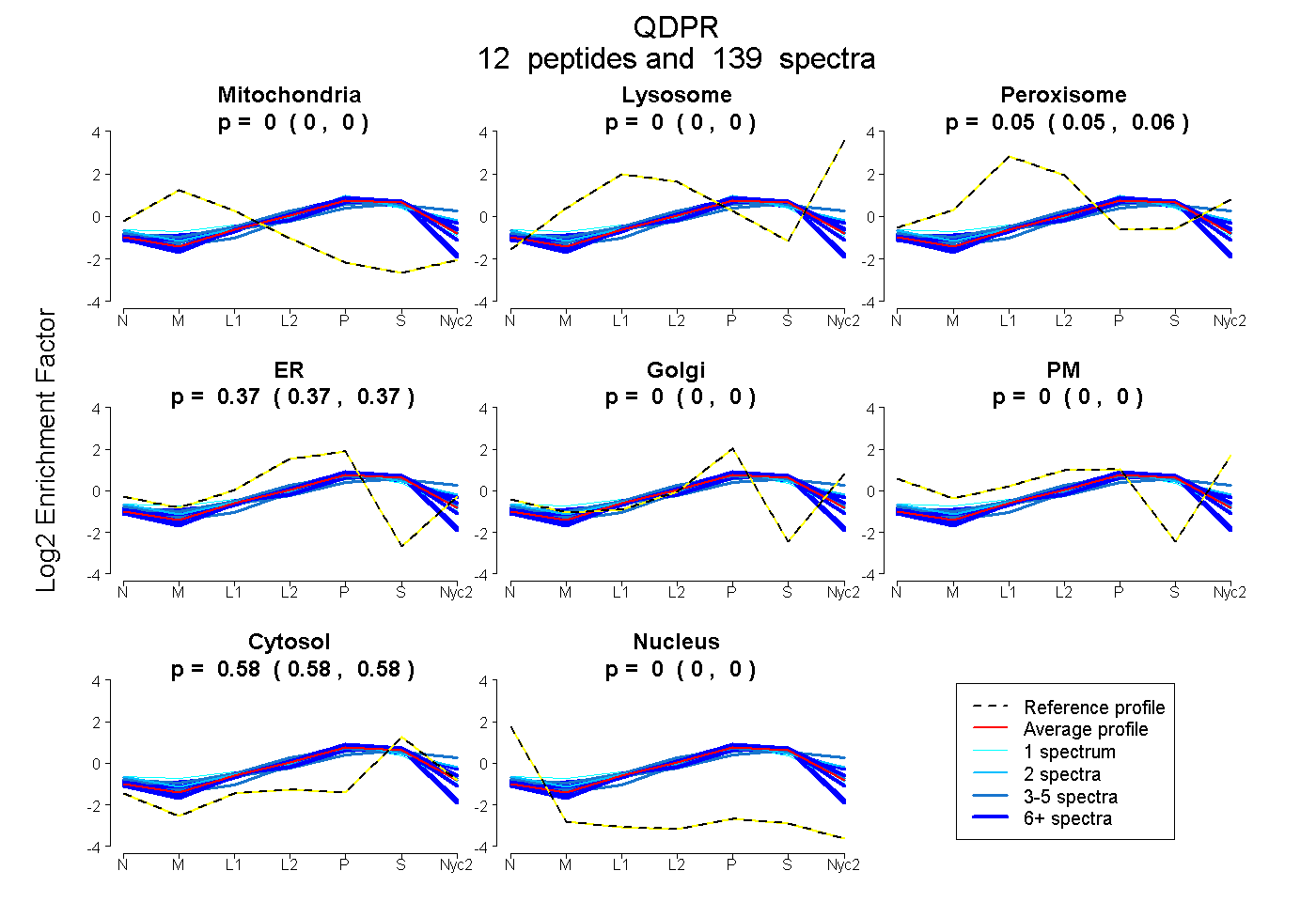
0.000 | 0.000
0.000 | 0.000
0.052 | 0.056
0.366 | 0.370
0.000 | 0.000
0.000 | 0.000
0.576 | 0.579
0.000 | 0.000
peptides
spectra
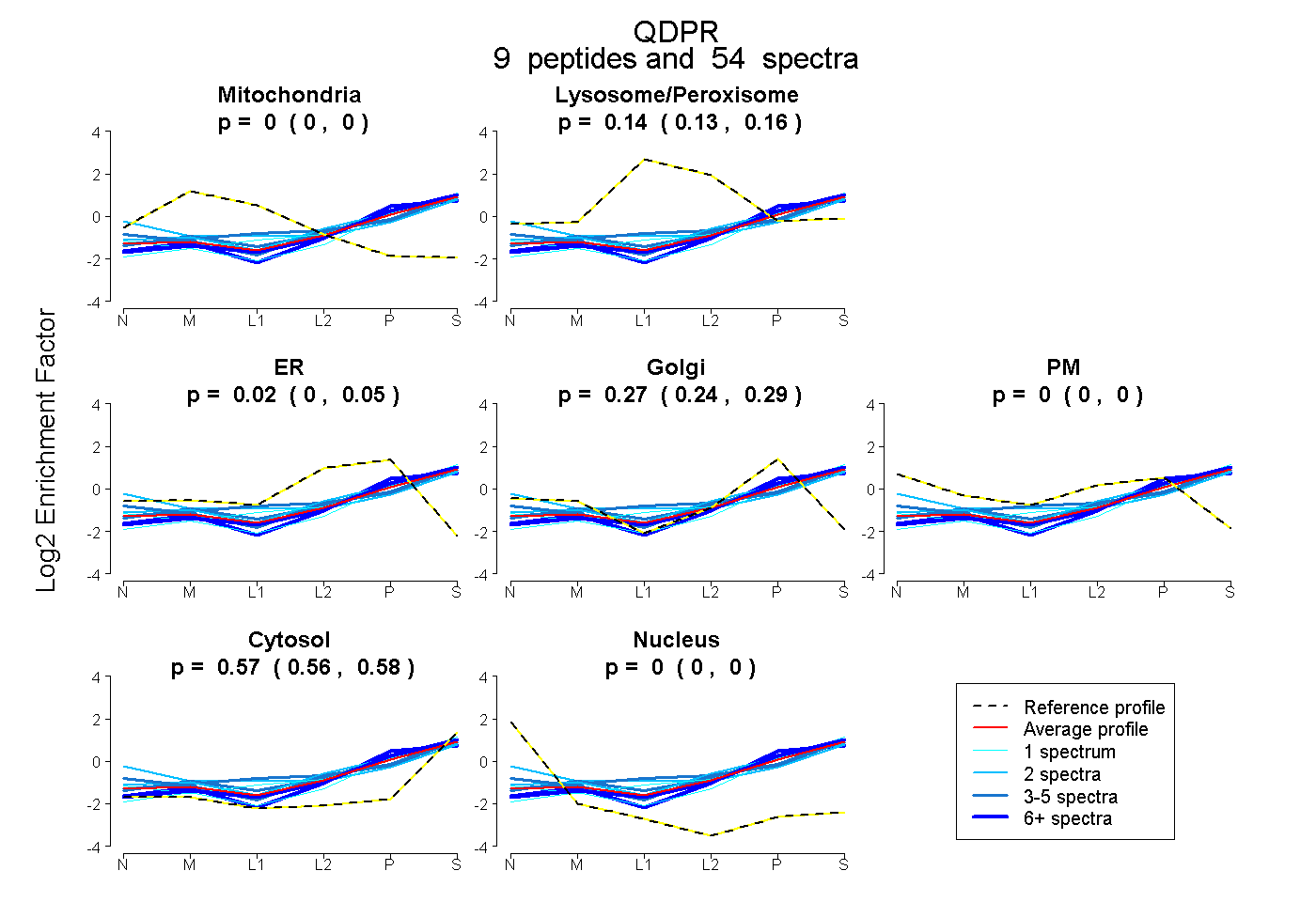
0.000 | 0.000
0.130 | 0.155
0.000 | 0.046
0.239 | 0.286
0.000 | 0.000
0.558 | 0.576
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
139 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.054 0.052 | 0.056 |
0.368 0.366 | 0.370 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.578 0.576 | 0.579 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
54 spectra |
 |
0.000 0.000 | 0.000 |
0.145 0.130 | 0.155 |
0.020 0.000 | 0.046 |
0.268 0.239 | 0.286 |
0.000 0.000 | 0.000 |
0.567 0.558 | 0.576 |
0.000 0.000 | 0.000 |
| 4 spectra, GAVHQLCQSLAGK | 0.000 | 0.289 | 0.000 | 0.160 | 0.000 | 0.551 | 0.000 | |||
| 1 spectrum, RPNSGSLIQVVTTDGK | 0.000 | 0.219 | 0.000 | 0.223 | 0.000 | 0.559 | 0.000 | |||
| 2 spectra, LLGDQK | 0.000 | 0.141 | 0.121 | 0.207 | 0.000 | 0.531 | 0.000 | |||
| 1 spectrum, GALGSR | 0.000 | 0.000 | 0.135 | 0.157 | 0.000 | 0.708 | 0.000 | |||
| 5 spectra, EGGLLTLAGAK | 0.000 | 0.187 | 0.000 | 0.283 | 0.000 | 0.529 | 0.000 | |||
| 2 spectra, CVQAFR | 0.000 | 0.168 | 0.000 | 0.003 | 0.301 | 0.528 | 0.000 | |||
| 27 spectra, VLVYGGR | 0.000 | 0.052 | 0.199 | 0.114 | 0.000 | 0.635 | 0.000 | |||
| 9 spectra, AALDGTPGMIGYGMAK | 0.000 | 0.000 | 0.157 | 0.264 | 0.000 | 0.580 | 0.000 | |||
| 3 spectra, MTDSFTEQADQVTAEVGK | 0.000 | 0.134 | 0.064 | 0.217 | 0.000 | 0.585 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
123 spectra |
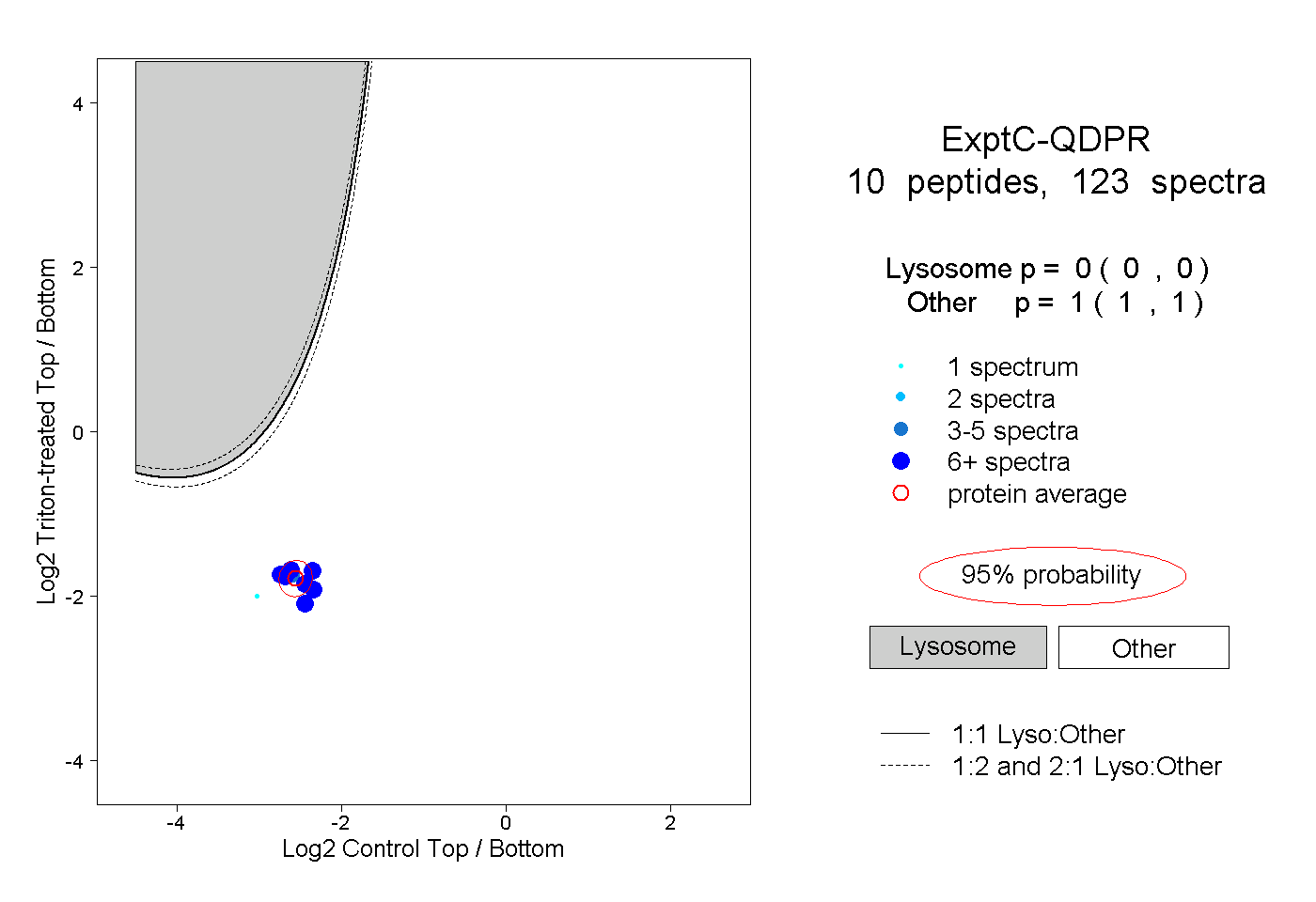 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
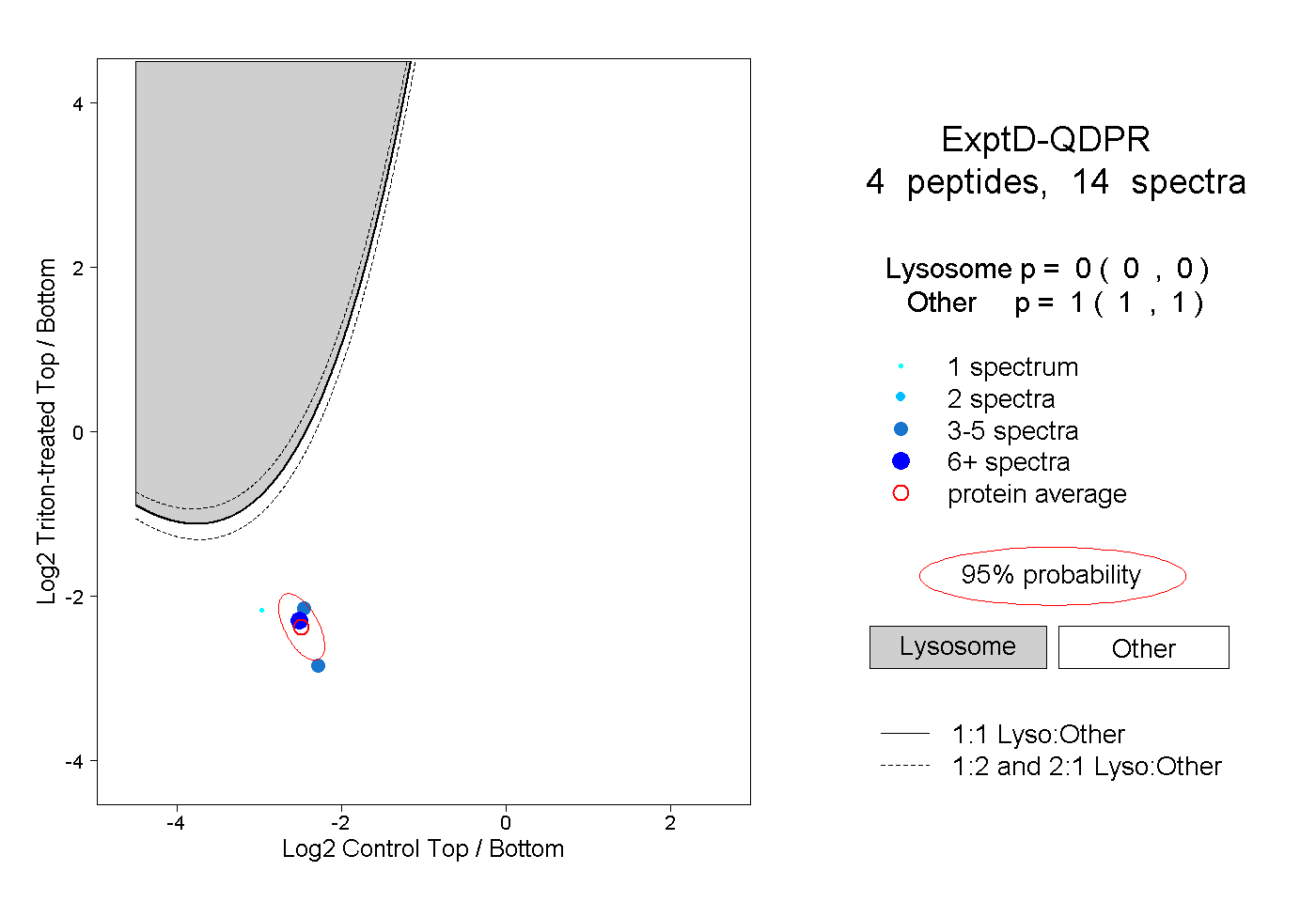 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |