peptides
spectra
0.000 | 0.000
0.001 | 0.003
0.000 | 0.000
0.997 | 0.999
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.031 | 0.037
0.963 | 0.969
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
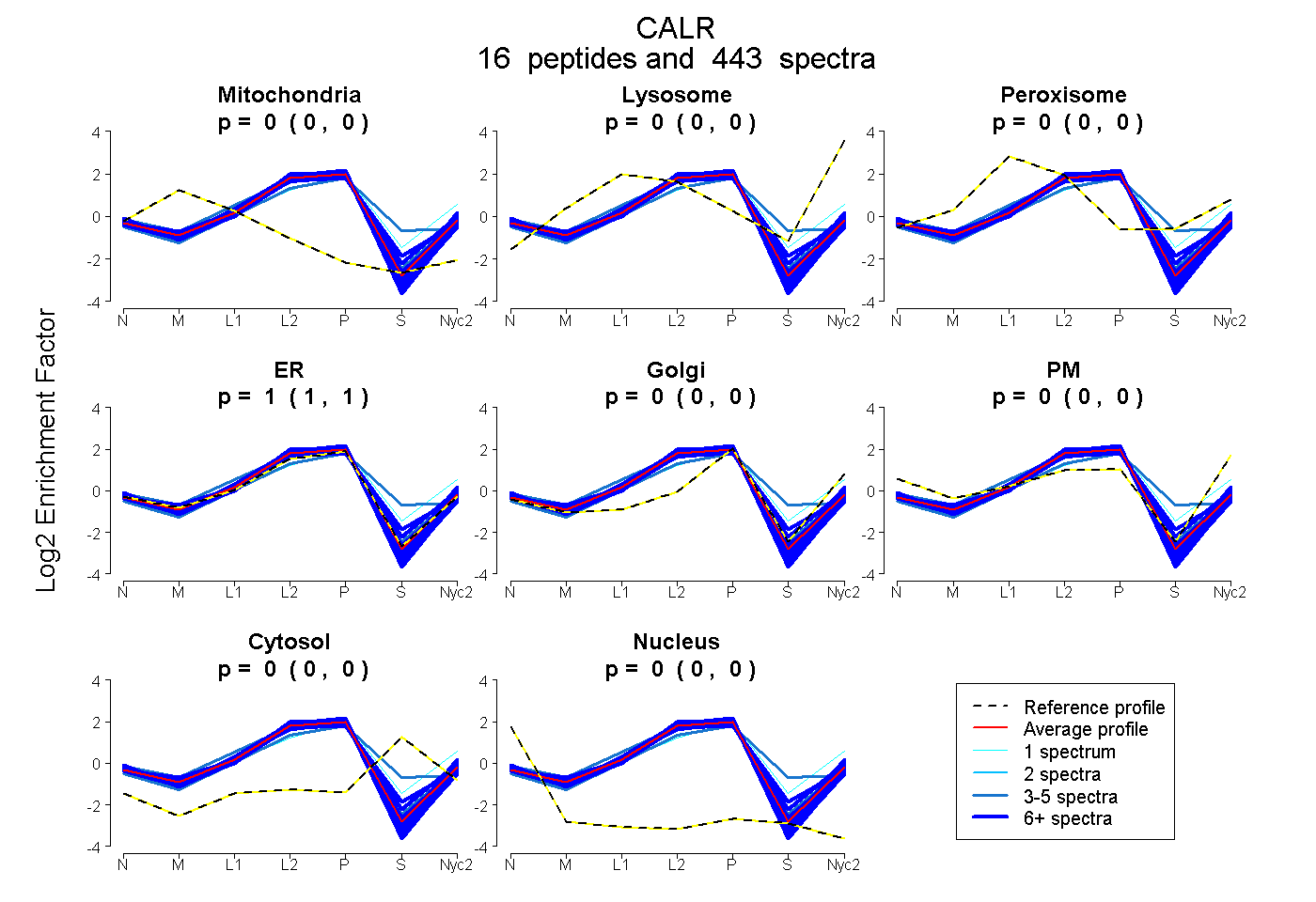
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
443 spectra |
 |
0.000 0.000 | 0.000 |
0.002 0.001 | 0.003 |
0.000 0.000 | 0.000 |
0.998 0.997 | 0.999 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
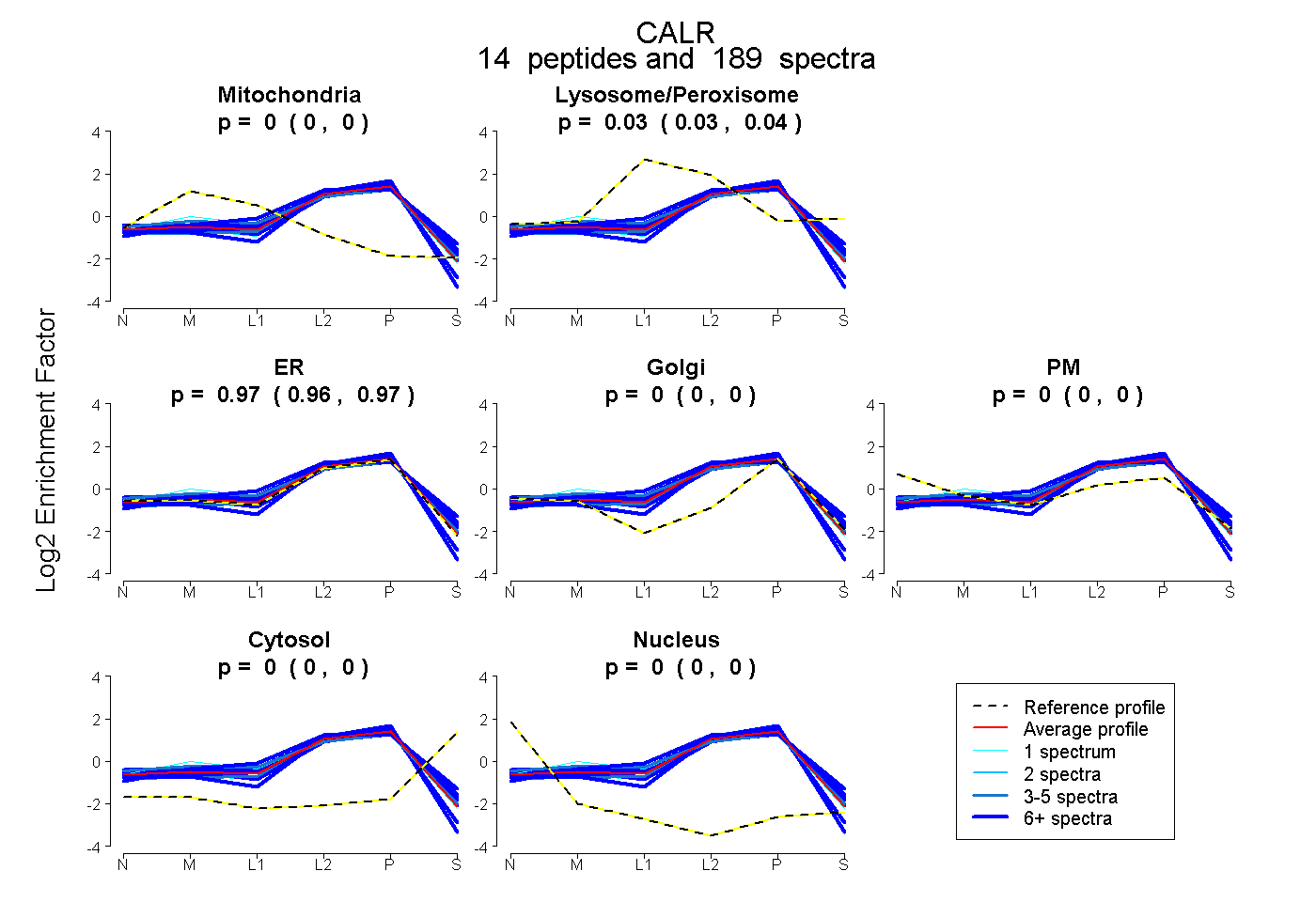
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
189 spectra |
 |
0.000 0.000 | 0.000 |
0.034 0.031 | 0.037 |
0.966 0.963 | 0.969 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, DPDAAKPEDWDER | 0.000 | 0.000 | 0.993 | 0.007 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, NVLINK | 0.078 | 0.043 | 0.879 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, VHVIFNYK | 0.000 | 0.222 | 0.743 | 0.000 | 0.000 | 0.035 | 0.000 | |||
| 13 spectra, GQTLVVQFTVK | 0.000 | 0.118 | 0.788 | 0.093 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, FYGDQEK | 0.000 | 0.092 | 0.891 | 0.000 | 0.000 | 0.017 | 0.000 | |||
| 44 spectra, FYALSAR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, GEWKPR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 14 spectra, FEPFSNK | 0.000 | 0.110 | 0.819 | 0.058 | 0.000 | 0.013 | 0.000 | |||
| 4 spectra, QIDNPDYK | 0.033 | 0.097 | 0.840 | 0.000 | 0.030 | 0.000 | 0.000 | |||
| 22 spectra, GLQTSQDAR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 26 spectra, LFPGGLDQK | 0.000 | 0.048 | 0.946 | 0.006 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, HEQNIDCGGGYVK | 0.000 | 0.130 | 0.819 | 0.014 | 0.037 | 0.000 | 0.000 | |||
| 12 spectra, EQFLDGDAWTNR | 0.000 | 0.051 | 0.881 | 0.000 | 0.000 | 0.068 | 0.000 | |||
| 20 spectra, FVLSSGK | 0.000 | 0.016 | 0.913 | 0.071 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
826 spectra |
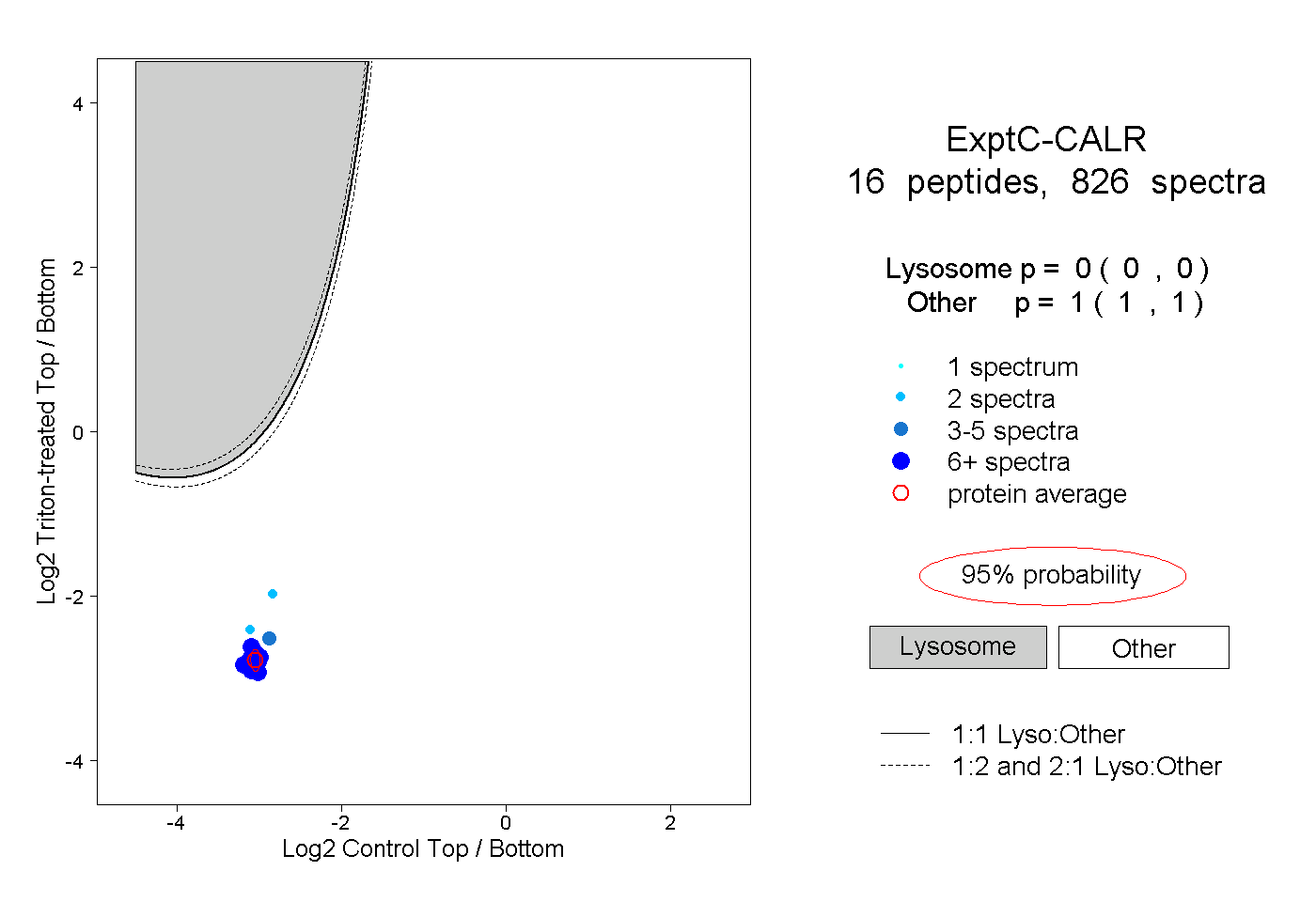 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
67 spectra |
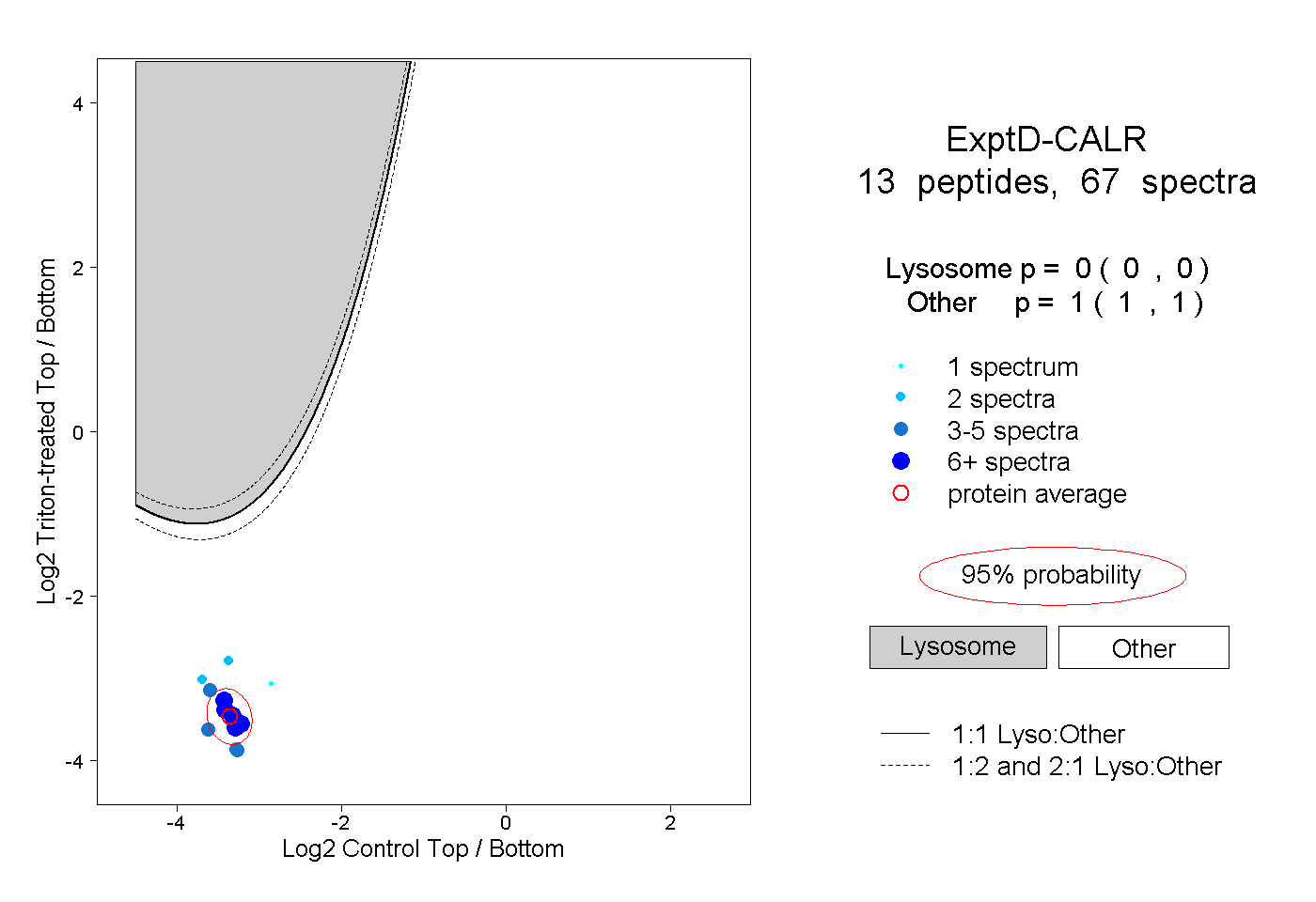 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |