peptides
spectra
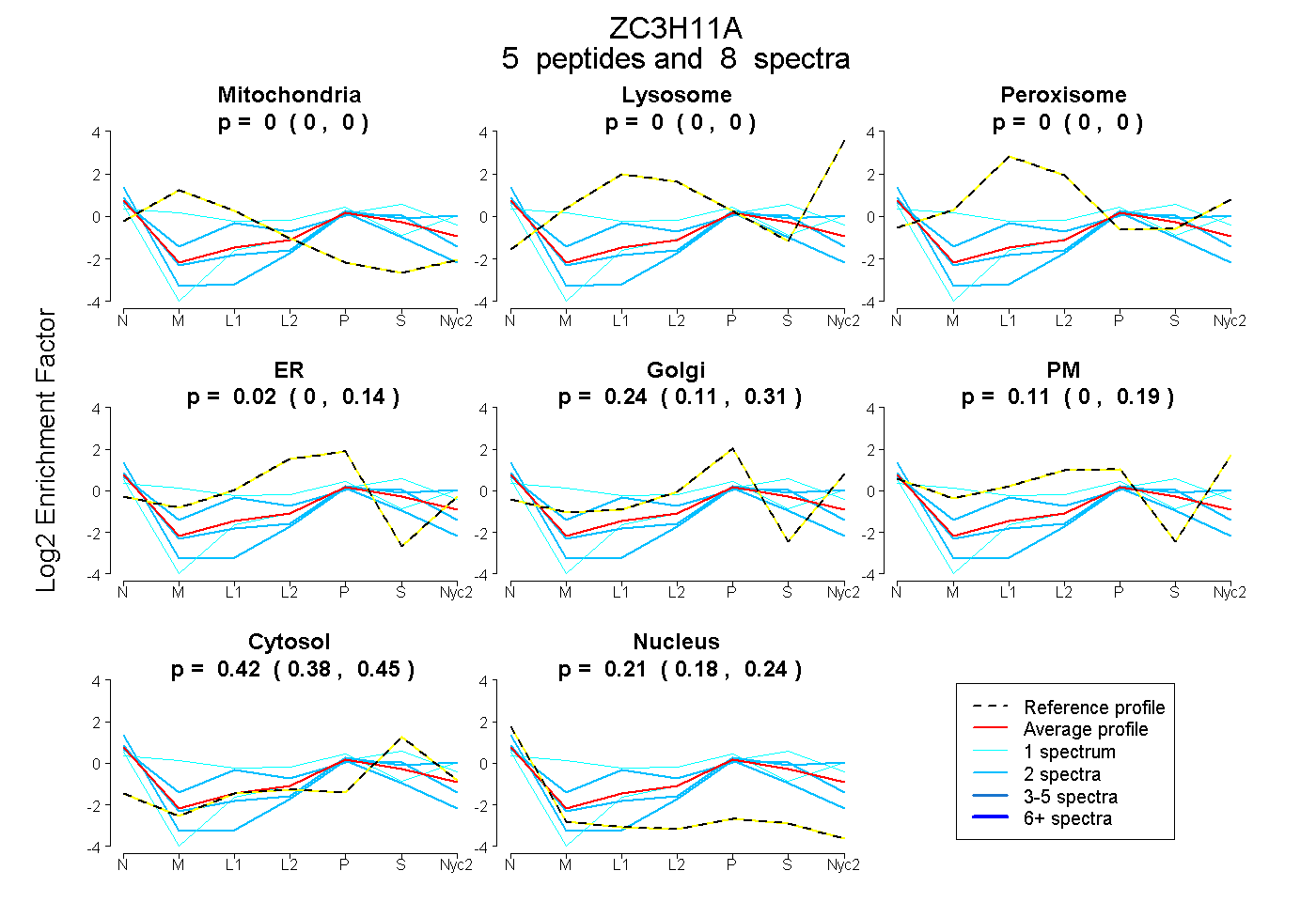
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.139
0.110 | 0.313
0.000 | 0.192
0.376 | 0.449
0.180 | 0.241
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
8 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.018 0.000 | 0.139 |
0.245 0.110 | 0.313 |
0.110 0.000 | 0.192 |
0.415 0.376 | 0.449 |
0.212 0.180 | 0.241 |
| 2 spectra, VQQSAER | 0.000 | 0.000 | 0.000 | 0.000 | 0.314 | 0.077 | 0.435 | 0.174 | ||
| 1 spectrum, TEEPSGAEDSPSGTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.232 | 0.000 | 0.653 | 0.114 | ||
| 2 spectra, LSVQSNPCPQLR | 0.000 | 0.000 | 0.192 | 0.228 | 0.000 | 0.000 | 0.377 | 0.203 | ||
| 1 spectrum, TPALQPTTDAHNGLR | 0.204 | 0.000 | 0.073 | 0.000 | 0.153 | 0.370 | 0.200 | 0.000 | ||
| 2 spectra, GQLEEEPAGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.253 | 0.000 | 0.231 | 0.516 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
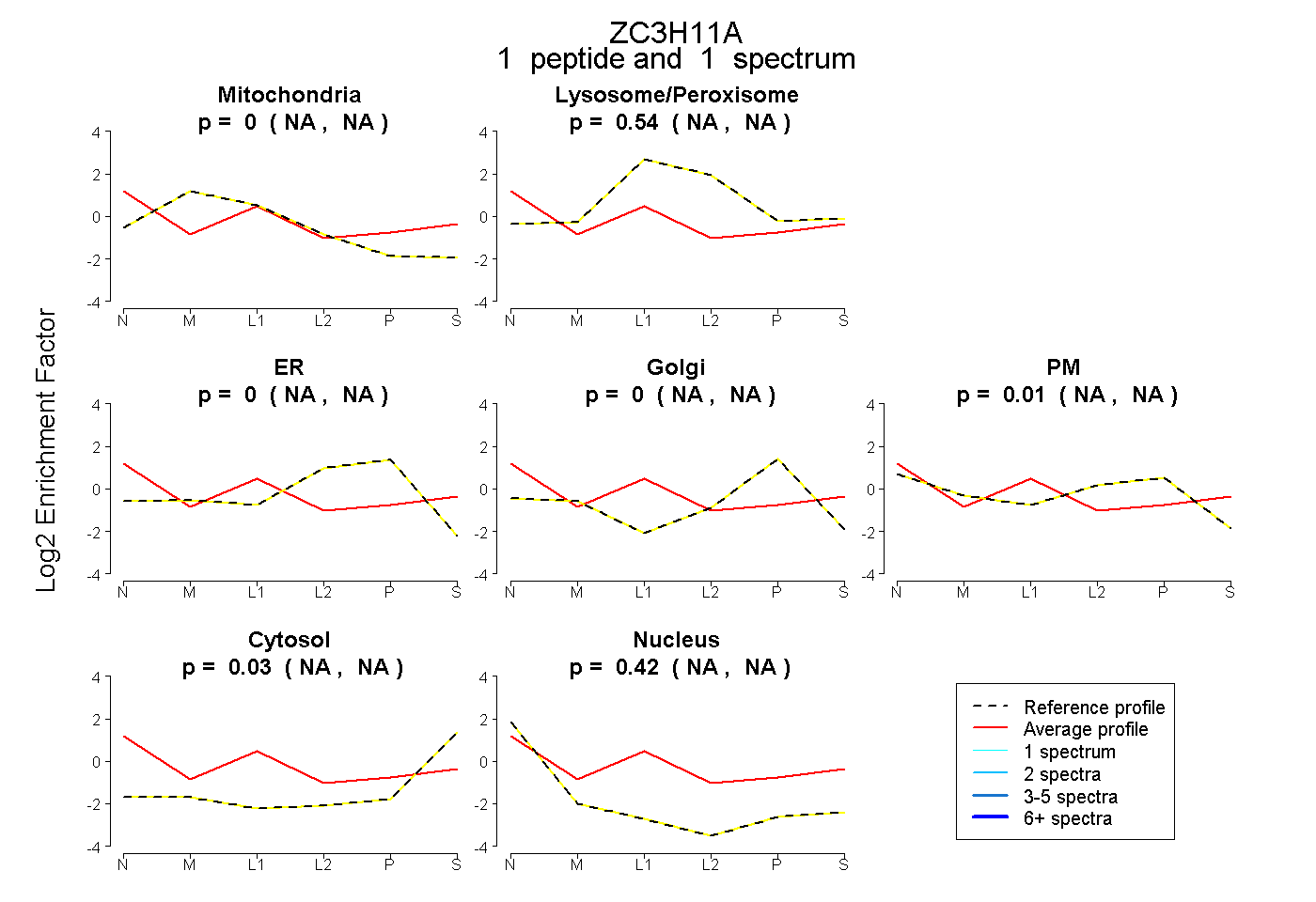 |
0.000 NA | NA |
0.541 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.005 NA | NA |
0.035 NA | NA |
0.419 NA | NA |