peptides
spectra
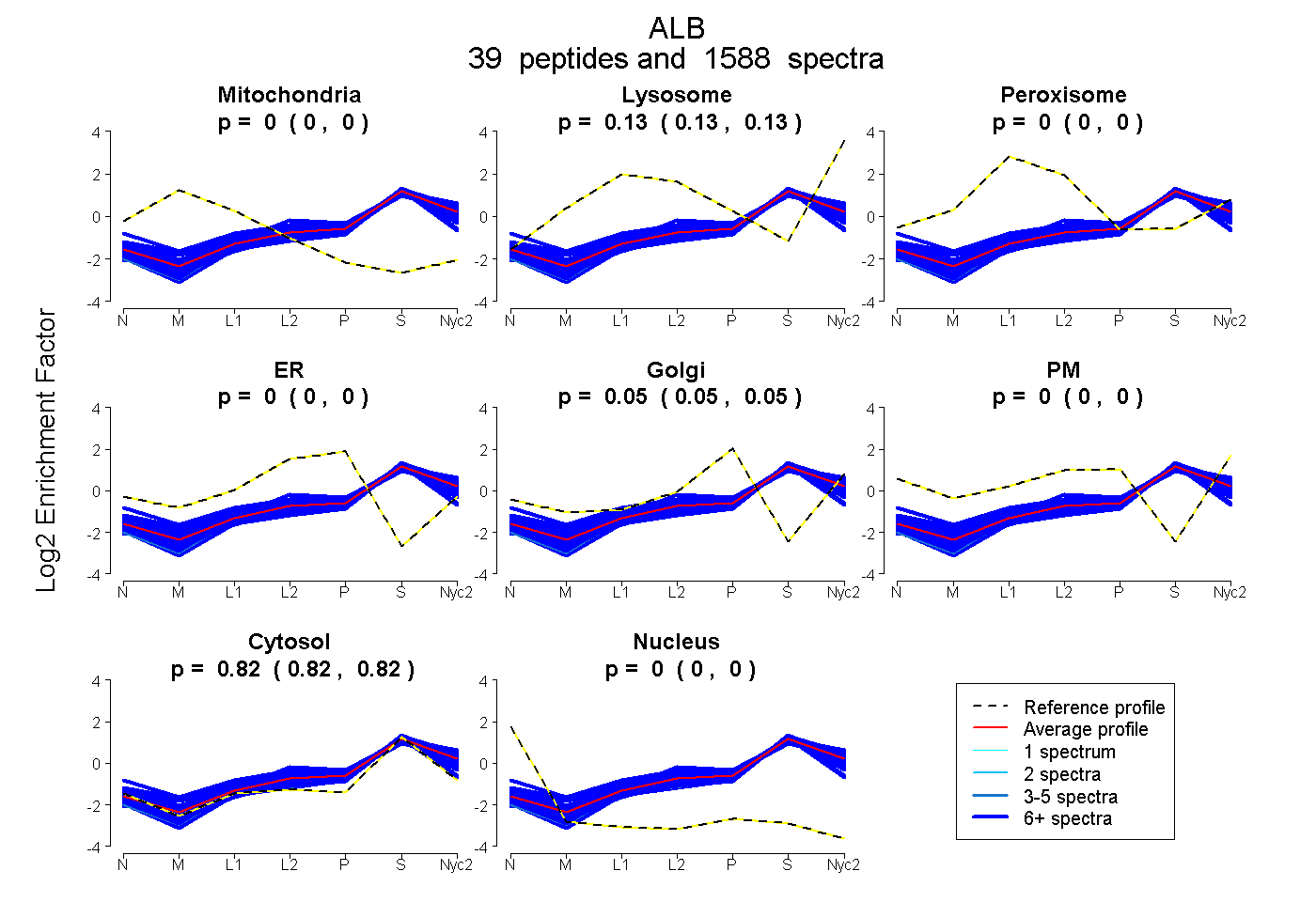
0.000 | 0.000
0.126 | 0.127
0.000 | 0.000
0.000 | 0.000
0.049 | 0.050
0.000 | 0.000
0.823 | 0.824
0.000 | 0.000
peptides
spectra
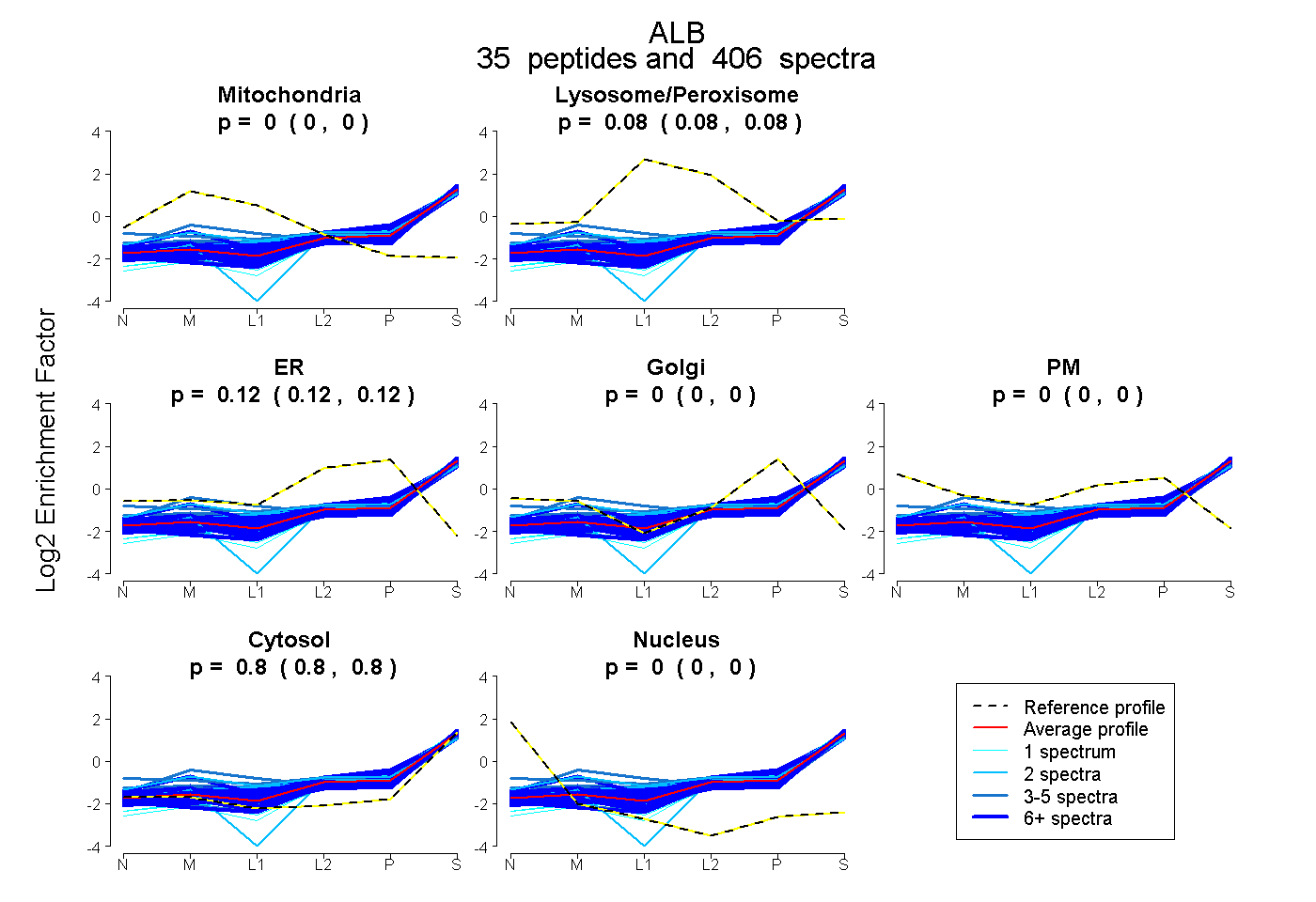
0.000 | 0.000
0.080 | 0.082
0.117 | 0.118
0.000 | 0.000
0.000 | 0.000
0.801 | 0.802
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
1588 spectra |
 |
0.000 0.000 | 0.000 |
0.127 0.126 | 0.127 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.050 0.049 | 0.050 |
0.000 0.000 | 0.000 |
0.823 0.823 | 0.824 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
406 spectra |
 |
0.000 0.000 | 0.000 |
0.081 0.080 | 0.082 |
0.118 0.117 | 0.118 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.802 0.801 | 0.802 |
0.000 0.000 | 0.000 |
| 12 spectra, DVFLGTFLYEYSR | 0.000 | 0.012 | 0.152 | 0.000 | 0.000 | 0.836 | 0.000 | |||
| 7 spectra, ECCHGDLLECADDR | 0.000 | 0.101 | 0.034 | 0.000 | 0.000 | 0.865 | 0.000 | |||
| 3 spectra, LATDLTK | 0.000 | 0.135 | 0.135 | 0.000 | 0.000 | 0.731 | 0.000 | |||
| 5 spectra, DNYGELADCCAK | 0.000 | 0.000 | 0.141 | 0.000 | 0.000 | 0.859 | 0.000 | |||
| 6 spectra, SIHTLFGDK | 0.000 | 0.125 | 0.047 | 0.000 | 0.000 | 0.829 | 0.000 | |||
| 10 spectra, CPYEEHIK | 0.000 | 0.180 | 0.097 | 0.000 | 0.000 | 0.723 | 0.000 | |||
| 2 spectra, LQACCDKPVLQK | 0.000 | 0.216 | 0.011 | 0.000 | 0.000 | 0.774 | 0.000 | |||
| 15 spectra, LCVLHEK | 0.000 | 0.100 | 0.058 | 0.000 | 0.000 | 0.842 | 0.000 | |||
| 3 spectra, AETFTFHSDICTLPDK | 0.110 | 0.227 | 0.000 | 0.000 | 0.000 | 0.664 | 0.000 | |||
| 42 spectra, ALVAAVR | 0.000 | 0.037 | 0.144 | 0.000 | 0.000 | 0.819 | 0.000 | |||
| 55 spectra, GLVLIAFSQYLQK | 0.000 | 0.094 | 0.196 | 0.000 | 0.000 | 0.710 | 0.000 | |||
| 6 spectra, RPCFSALTVDETYVPK | 0.017 | 0.154 | 0.000 | 0.115 | 0.000 | 0.714 | 0.000 | |||
| 2 spectra, YEATLEK | 0.000 | 0.255 | 0.000 | 0.113 | 0.000 | 0.633 | 0.000 | |||
| 13 spectra, QTALAELVK | 0.000 | 0.136 | 0.160 | 0.000 | 0.000 | 0.704 | 0.000 | |||
| 4 spectra, SEIAHR | 0.000 | 0.233 | 0.000 | 0.000 | 0.119 | 0.648 | 0.000 | |||
| 9 spectra, TNCELYEK | 0.000 | 0.142 | 0.046 | 0.000 | 0.000 | 0.812 | 0.000 | |||
| 26 spectra, TVMGDFAQFVDK | 0.000 | 0.000 | 0.123 | 0.000 | 0.000 | 0.877 | 0.000 | |||
| 19 spectra, LGEYGFQNAILVR | 0.000 | 0.072 | 0.140 | 0.000 | 0.000 | 0.788 | 0.000 | |||
| 7 spectra, APQVSTPTLVEAAR | 0.000 | 0.083 | 0.117 | 0.000 | 0.000 | 0.799 | 0.000 | |||
| 19 spectra, CCSGSLVER | 0.000 | 0.072 | 0.077 | 0.000 | 0.000 | 0.851 | 0.000 | |||
| 25 spectra, AWAVAR | 0.000 | 0.108 | 0.096 | 0.000 | 0.000 | 0.796 | 0.000 | |||
| 1 spectrum, ATEDQLK | 0.000 | 0.000 | 0.099 | 0.000 | 0.000 | 0.901 | 0.000 | |||
| 2 spectra, SQCLAEIEHDNIPADLPSIAADFVEDK | 0.000 | 0.000 | 0.000 | 0.157 | 0.000 | 0.843 | 0.000 | |||
| 25 spectra, LVQEVTDFAK | 0.000 | 0.037 | 0.167 | 0.000 | 0.000 | 0.796 | 0.000 | |||
| 12 spectra, YMCENQATISSK | 0.000 | 0.071 | 0.071 | 0.000 | 0.000 | 0.858 | 0.000 | |||
| 3 spectra, DLGEQHFK | 0.000 | 0.227 | 0.000 | 0.121 | 0.000 | 0.651 | 0.000 | |||
| 1 spectrum, NYAEAK | 0.000 | 0.048 | 0.048 | 0.000 | 0.000 | 0.904 | 0.000 | |||
| 9 spectra, HPDYSVSLLLR | 0.000 | 0.186 | 0.076 | 0.000 | 0.000 | 0.737 | 0.000 | |||
| 10 spectra, CCTLPEAQR | 0.000 | 0.070 | 0.048 | 0.000 | 0.000 | 0.882 | 0.000 | |||
| 7 spectra, LPCVEDYLSAILNR | 0.000 | 0.006 | 0.206 | 0.000 | 0.000 | 0.789 | 0.000 | |||
| 6 spectra, YNEVLTQCCTESDK | 0.000 | 0.050 | 0.098 | 0.000 | 0.000 | 0.852 | 0.000 | |||
| 15 spectra, HPYFYAPELLYYAEK | 0.000 | 0.087 | 0.142 | 0.000 | 0.000 | 0.770 | 0.000 | |||
| 11 spectra, FPNAEFAEITK | 0.000 | 0.055 | 0.183 | 0.000 | 0.000 | 0.762 | 0.000 | |||
| 13 spectra, TCVADENAENCDK | 0.000 | 0.000 | 0.084 | 0.000 | 0.000 | 0.916 | 0.000 | |||
| 1 spectrum, NECFLQHK | 0.000 | 0.000 | 0.118 | 0.000 | 0.000 | 0.882 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1786 spectra |
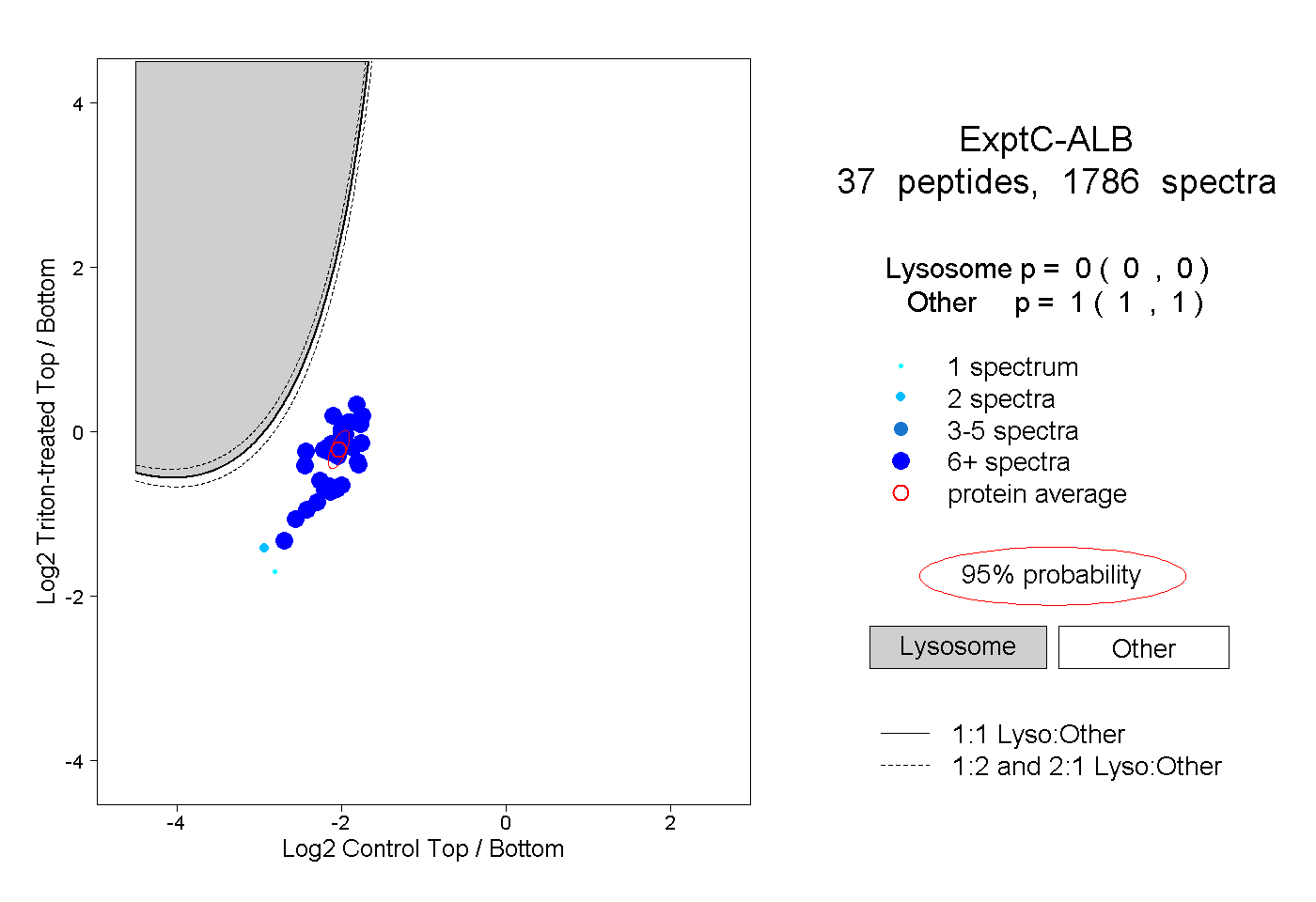 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
156 spectra |
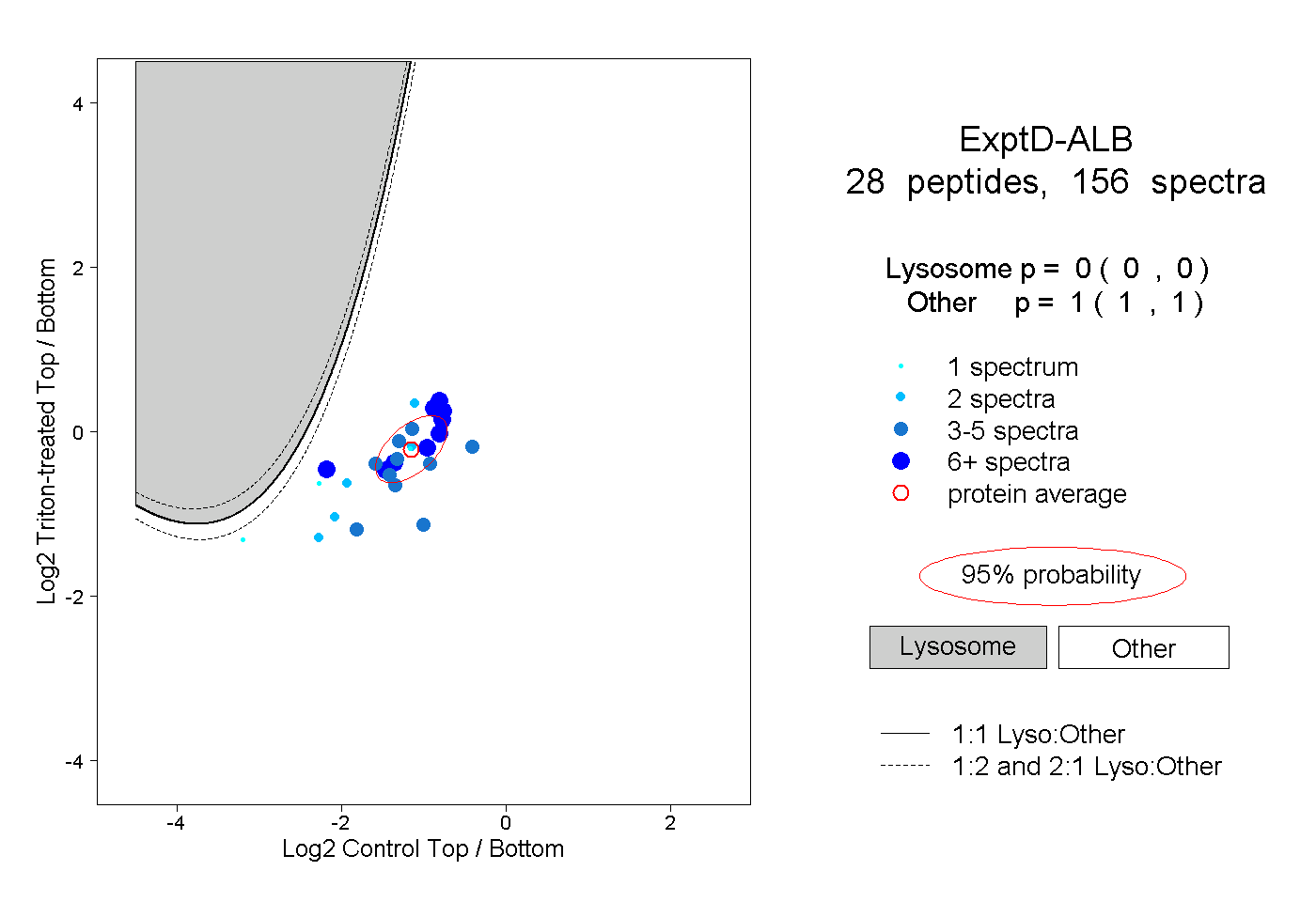 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |