peptides
spectra
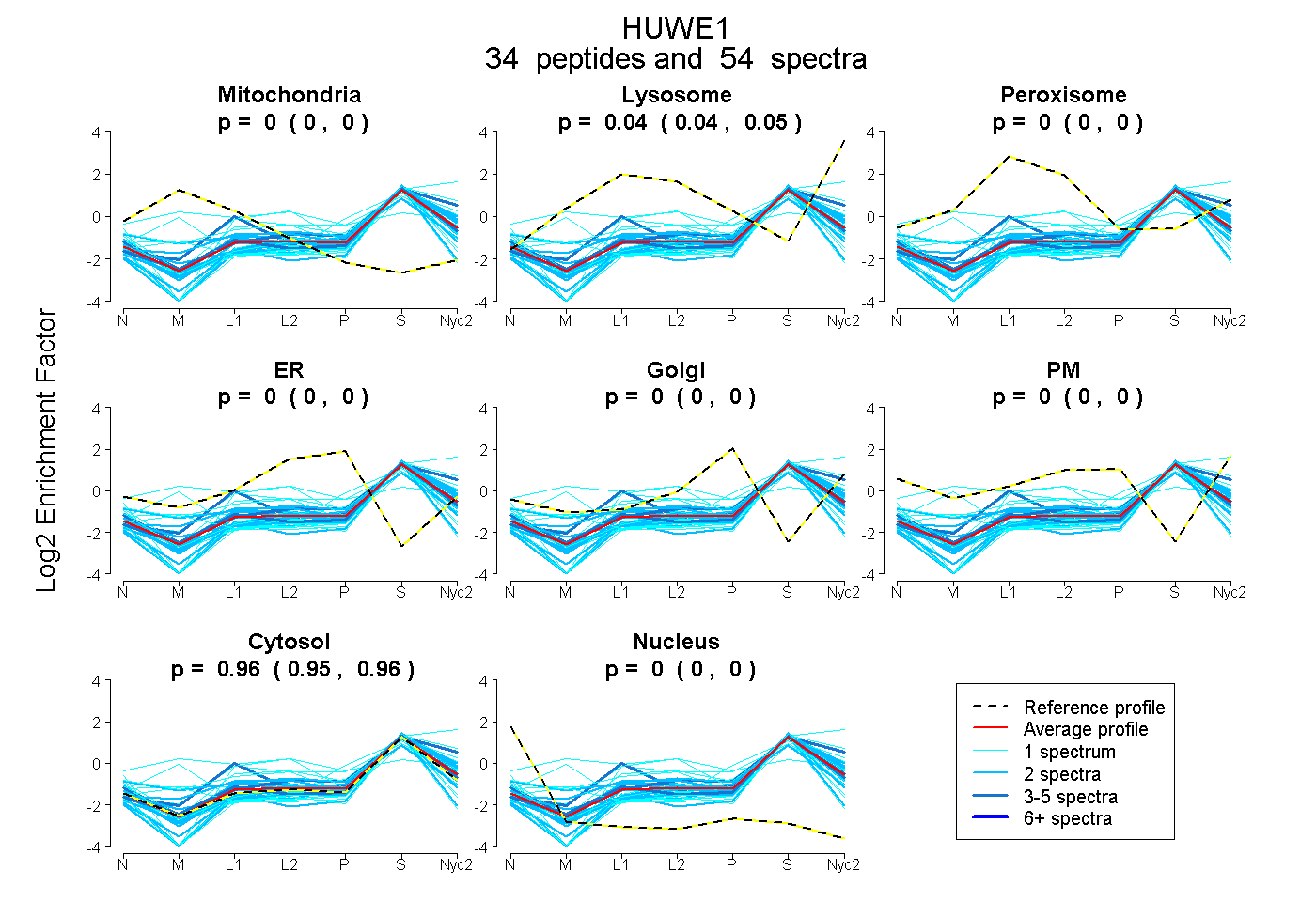
0.000 | 0.000
0.040 | 0.047
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.952 | 0.959
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
54 spectra |
 |
0.000 0.000 | 0.000 |
0.044 0.040 | 0.047 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.956 0.952 | 0.959 |
0.000 0.000 | 0.000 |
| 1 spectrum, VLGPAACR | 0.137 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.863 | 0.000 | ||
| 1 spectrum, AIQDPAFSDGIR | 0.148 | 0.000 | 0.316 | 0.000 | 0.037 | 0.144 | 0.355 | 0.000 | ||
| 1 spectrum, EMFNPMYALFR | 0.000 | 0.099 | 0.000 | 0.000 | 0.000 | 0.000 | 0.901 | 0.000 | ||
| 1 spectrum, ESKPPVR | 0.000 | 0.344 | 0.000 | 0.000 | 0.000 | 0.000 | 0.656 | 0.000 | ||
| 2 spectra, TVLNQILR | 0.000 | 0.053 | 0.000 | 0.000 | 0.000 | 0.000 | 0.947 | 0.000 | ||
| 4 spectra, LEHEVDLCR | 0.000 | 0.030 | 0.000 | 0.047 | 0.000 | 0.023 | 0.900 | 0.000 | ||
| 1 spectrum, LLAELVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, SMLNFLK | 0.004 | 0.007 | 0.140 | 0.000 | 0.000 | 0.000 | 0.848 | 0.000 | ||
| 2 spectra, NPDIFTEVANCCIR | 0.118 | 0.000 | 0.084 | 0.066 | 0.000 | 0.000 | 0.732 | 0.000 | ||
| 1 spectrum, HQPTLK | 0.254 | 0.043 | 0.000 | 0.000 | 0.000 | 0.000 | 0.703 | 0.000 | ||
| 3 spectra, ITPAMAAR | 0.000 | 0.228 | 0.000 | 0.000 | 0.000 | 0.000 | 0.772 | 0.000 | ||
| 1 spectrum, QPNPPLILQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, LCVGSPVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.922 | 0.078 | ||
| 1 spectrum, GLQSFVQCQPFER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.827 | 0.173 | ||
| 1 spectrum, GSGTASDDEFENLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, QIKPLLSASSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, QMLLFTHIR | 0.000 | 0.000 | 0.000 | 0.015 | 0.000 | 0.000 | 0.959 | 0.026 | ||
| 1 spectrum, HVLDTLIQLAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.075 | 0.000 | 0.925 | 0.000 | ||
| 2 spectra, IALPAPR | 0.000 | 0.091 | 0.000 | 0.000 | 0.000 | 0.000 | 0.909 | 0.000 | ||
| 1 spectrum, LSTSEER | 0.000 | 0.141 | 0.059 | 0.000 | 0.000 | 0.026 | 0.774 | 0.000 | ||
| 1 spectrum, TNIFQIQR | 0.000 | 0.000 | 0.196 | 0.069 | 0.061 | 0.000 | 0.674 | 0.000 | ||
| 1 spectrum, DGGSGNSTIIVSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.105 | 0.000 | 0.865 | 0.031 | ||
| 2 spectra, LLVGNDDVHIIAR | 0.000 | 0.004 | 0.000 | 0.000 | 0.000 | 0.000 | 0.996 | 0.000 | ||
| 1 spectrum, LLEEICNLGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.957 | 0.043 | ||
| 3 spectra, VLDFDVK | 0.000 | 0.021 | 0.000 | 0.000 | 0.000 | 0.000 | 0.979 | 0.000 | ||
| 1 spectrum, SLLSILQR | 0.000 | 0.203 | 0.000 | 0.000 | 0.000 | 0.000 | 0.797 | 0.000 | ||
| 2 spectra, EYNLEQQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.990 | 0.010 | ||
| 1 spectrum, DLQMLK | 0.065 | 0.143 | 0.000 | 0.000 | 0.000 | 0.000 | 0.791 | 0.000 | ||
| 1 spectrum, ISESPSEIMESLTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.997 | 0.003 | ||
| 1 spectrum, VCNDEQLLLELQQIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.936 | 0.064 | ||
| 2 spectra, EVLQNQLGIRPPTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, RPVMLTLLR | 0.000 | 0.028 | 0.000 | 0.000 | 0.005 | 0.000 | 0.967 | 0.000 | ||
| 2 spectra, GSKPLMPTSTILR | 0.000 | 0.019 | 0.000 | 0.000 | 0.000 | 0.000 | 0.981 | 0.000 | ||
| 2 spectra, DSAVAISGADSR | 0.000 | 0.000 | 0.063 | 0.000 | 0.000 | 0.000 | 0.934 | 0.004 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
8 spectra |
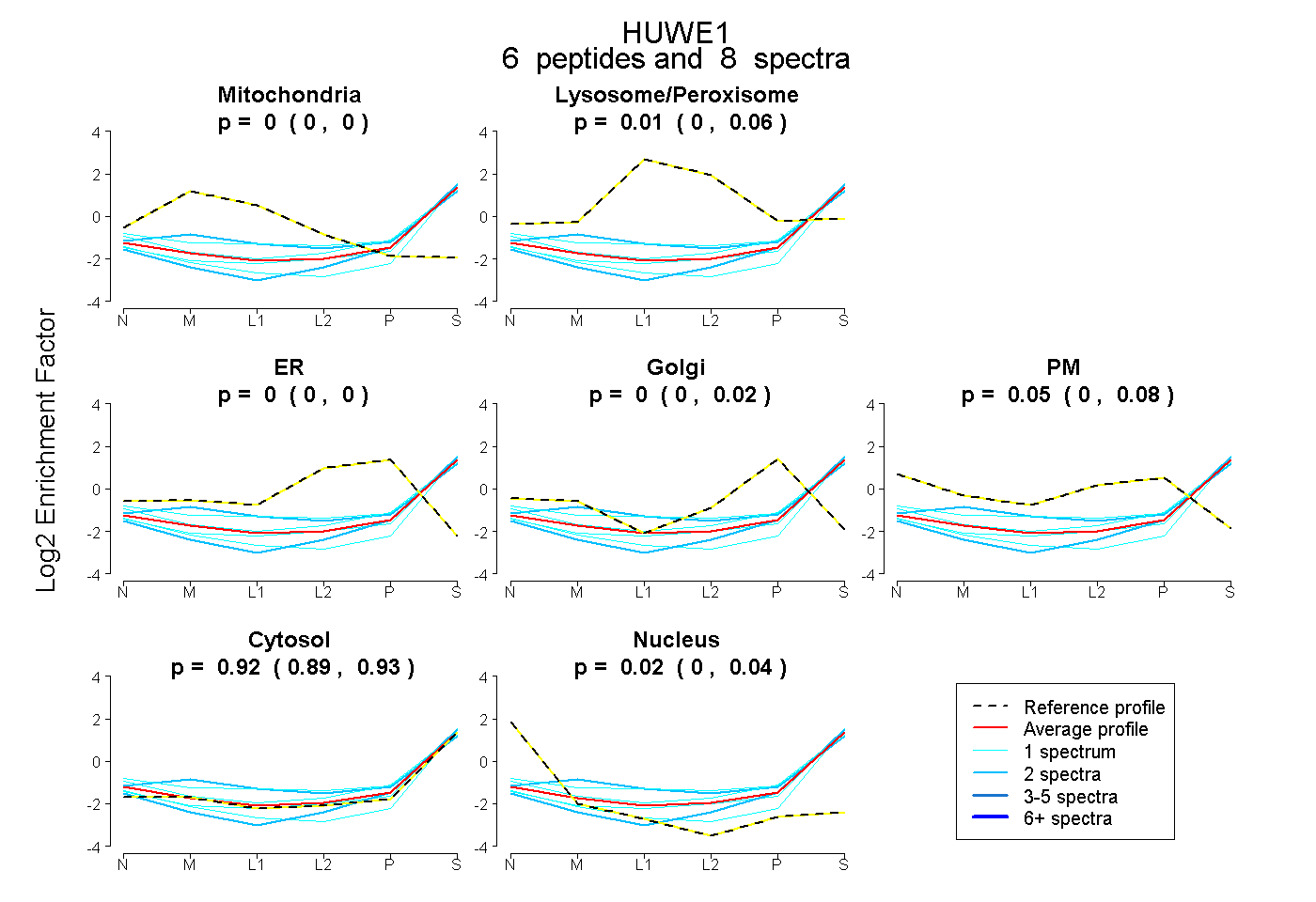 |
0.000 0.000 | 0.000 |
0.013 0.000 | 0.059 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.019 |
0.054 0.000 | 0.080 |
0.917 0.891 | 0.930 |
0.016 0.000 | 0.042 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
42 spectra |
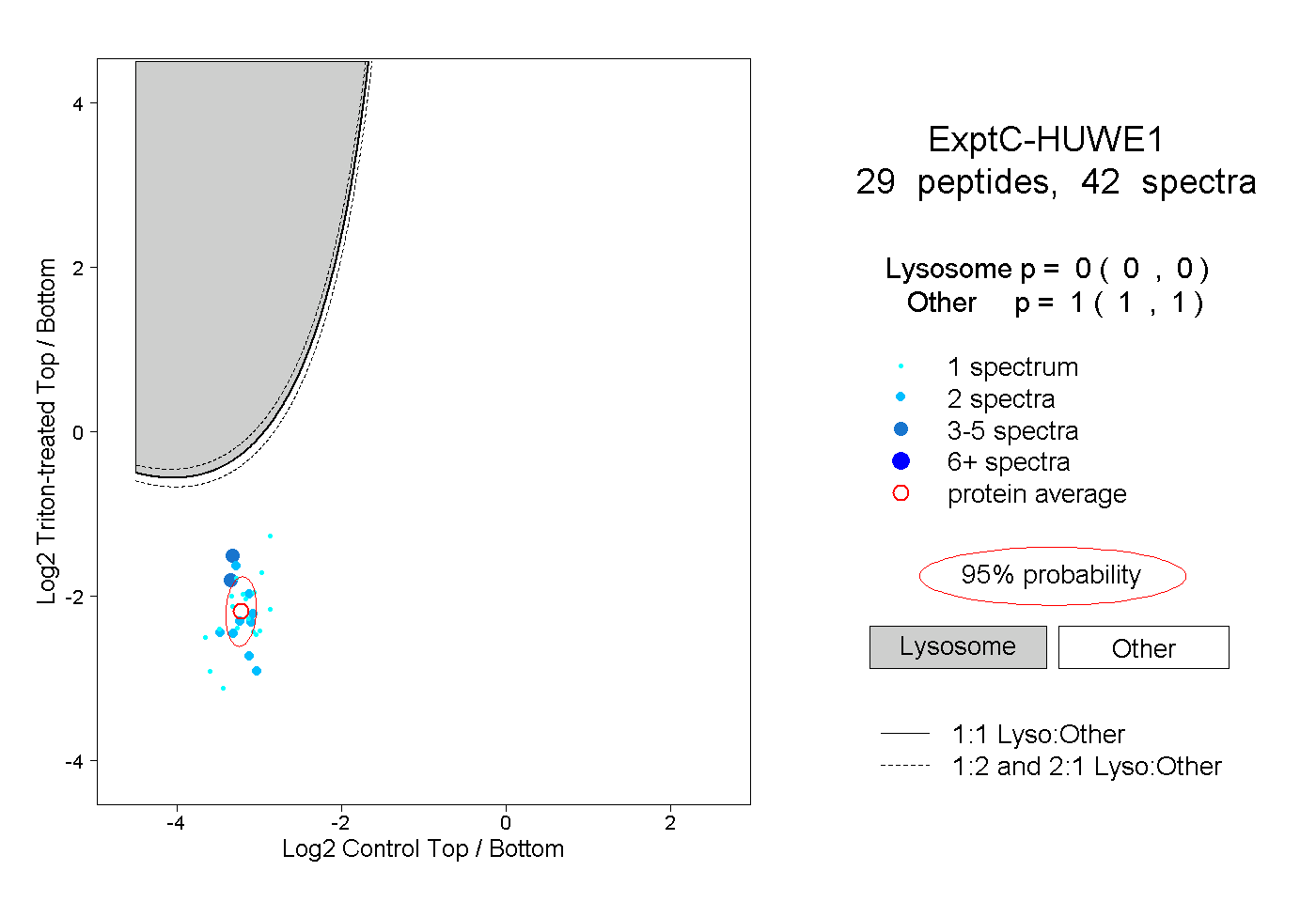 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
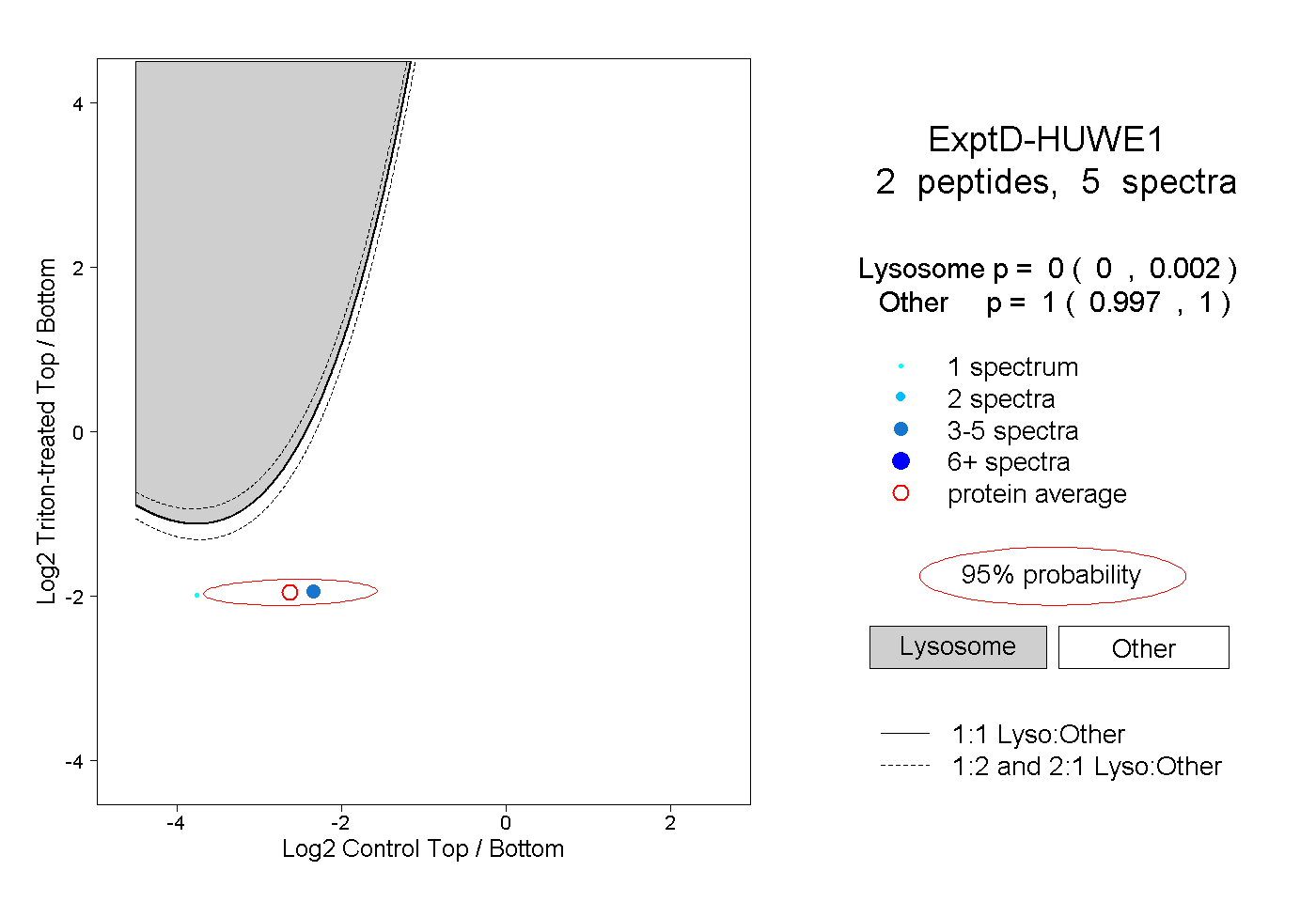 |
0.000 0.000 | 0.002 |
1.000 0.997 | 1.000 |