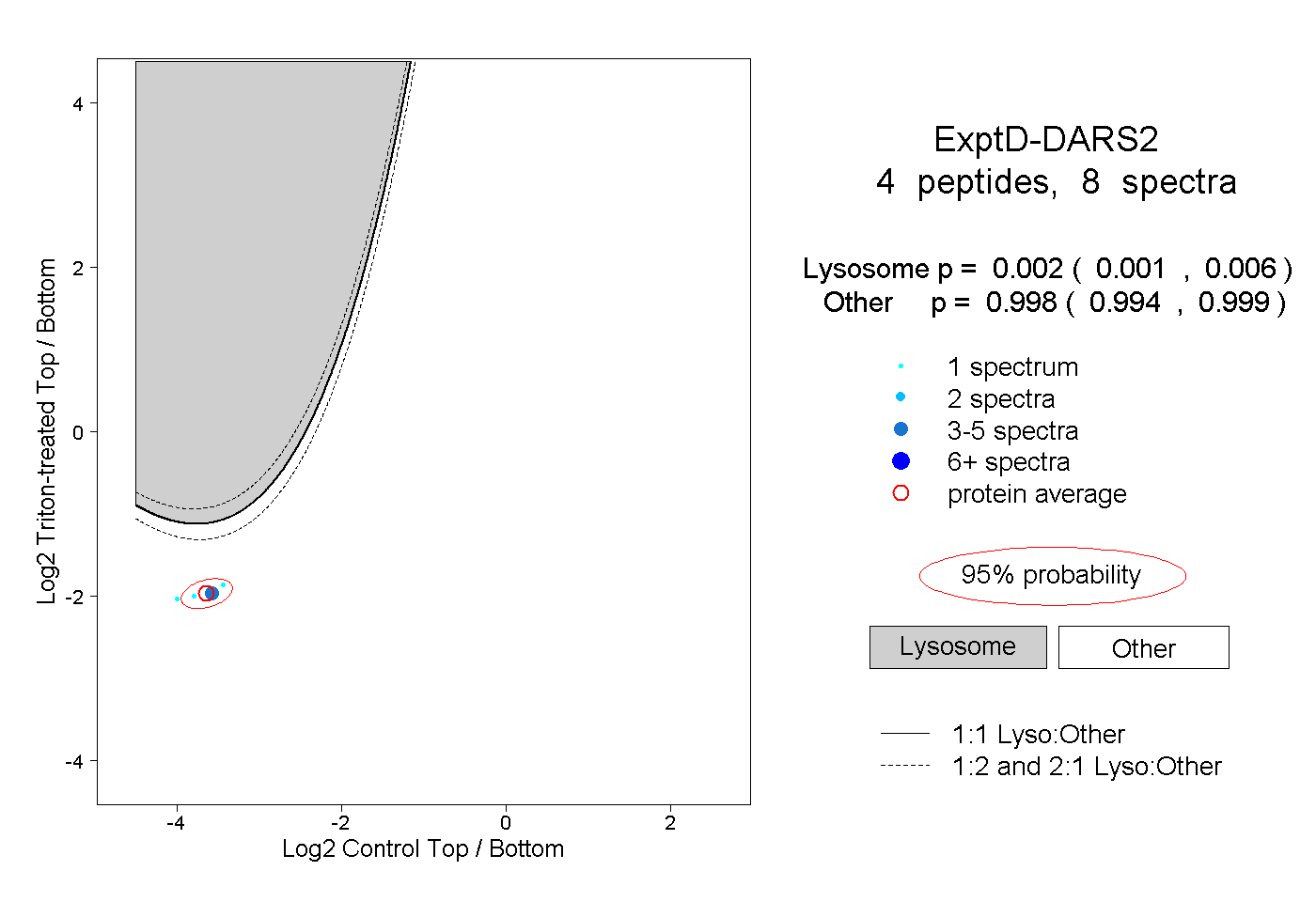
peptides
spectra
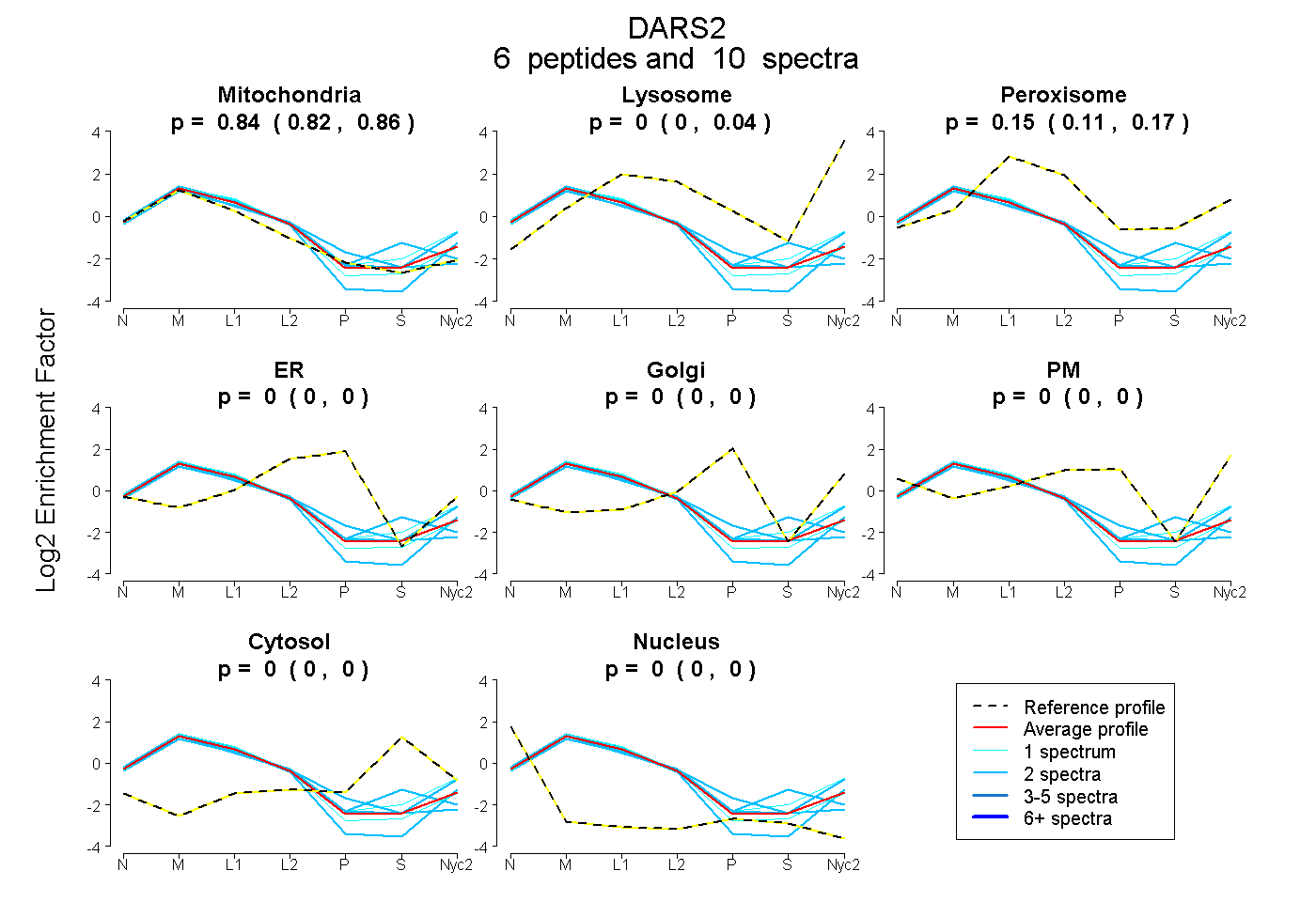
0.825 | 0.862
0.000 | 0.036
0.111 | 0.168
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptide
spectrum
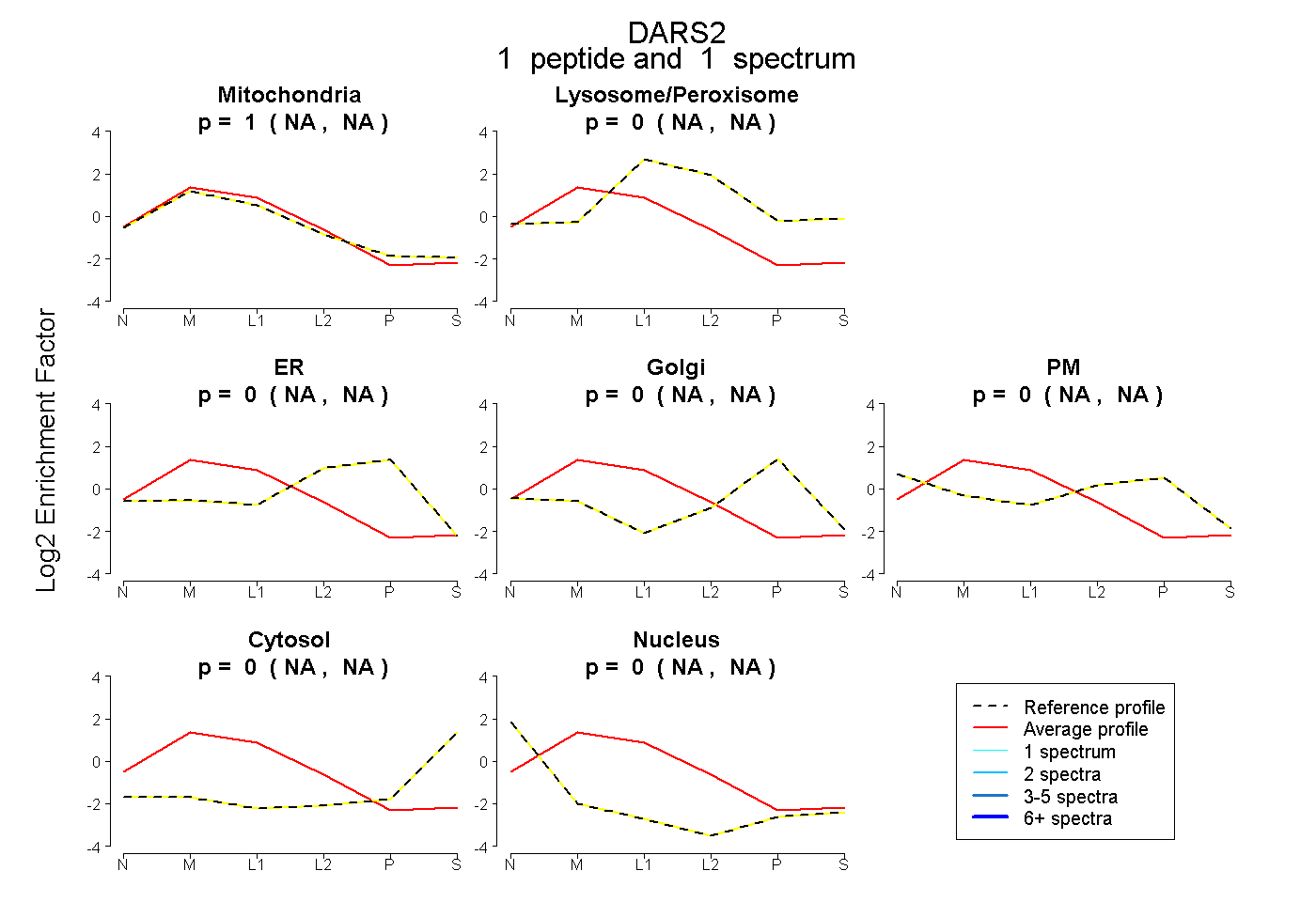
NA | NA
NA | NA
NA | NA
NA | NA
NA | NA
NA | NA
NA | NA
peptides
spectra
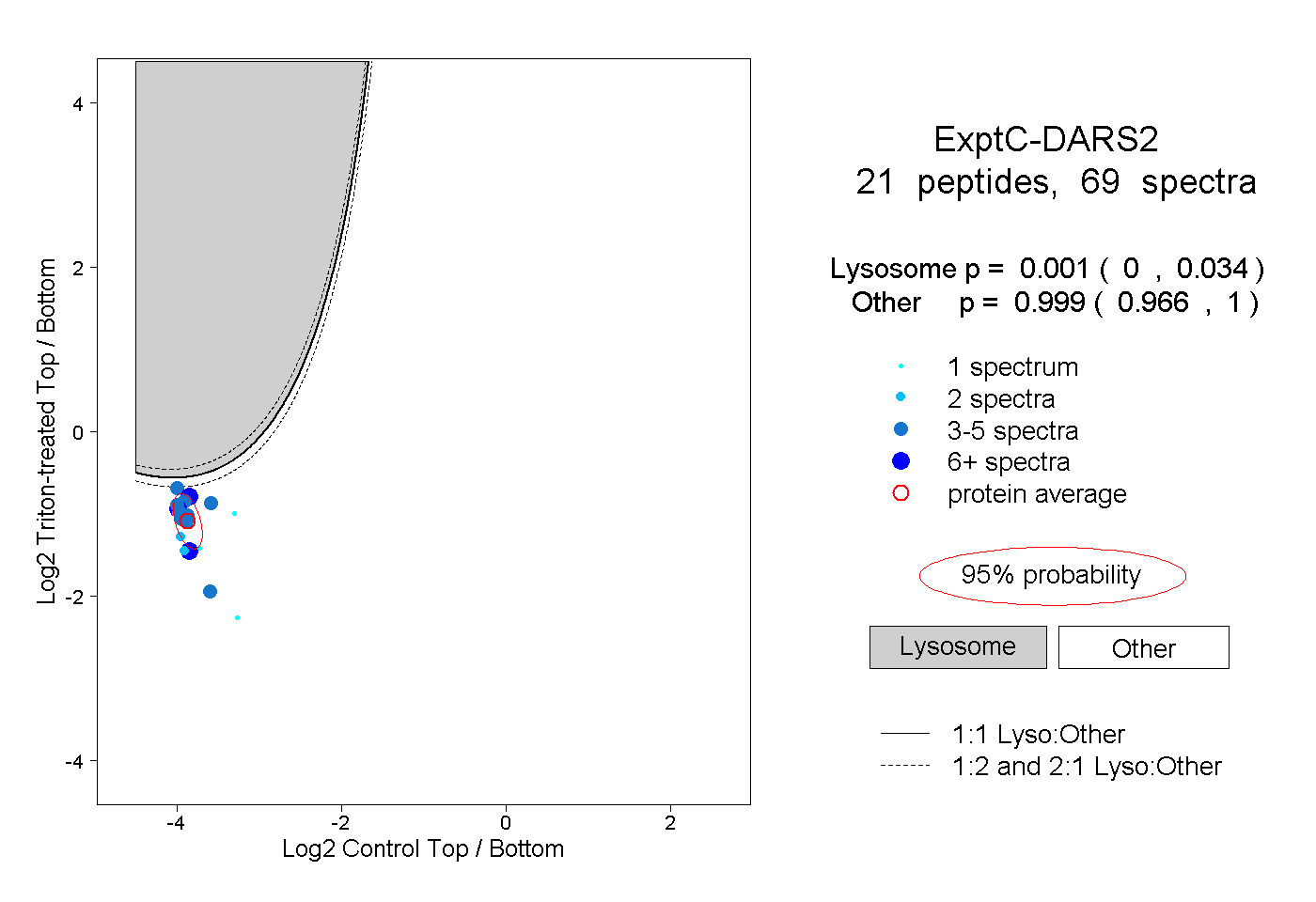
0.000 | 0.034
0.966 | 1.000