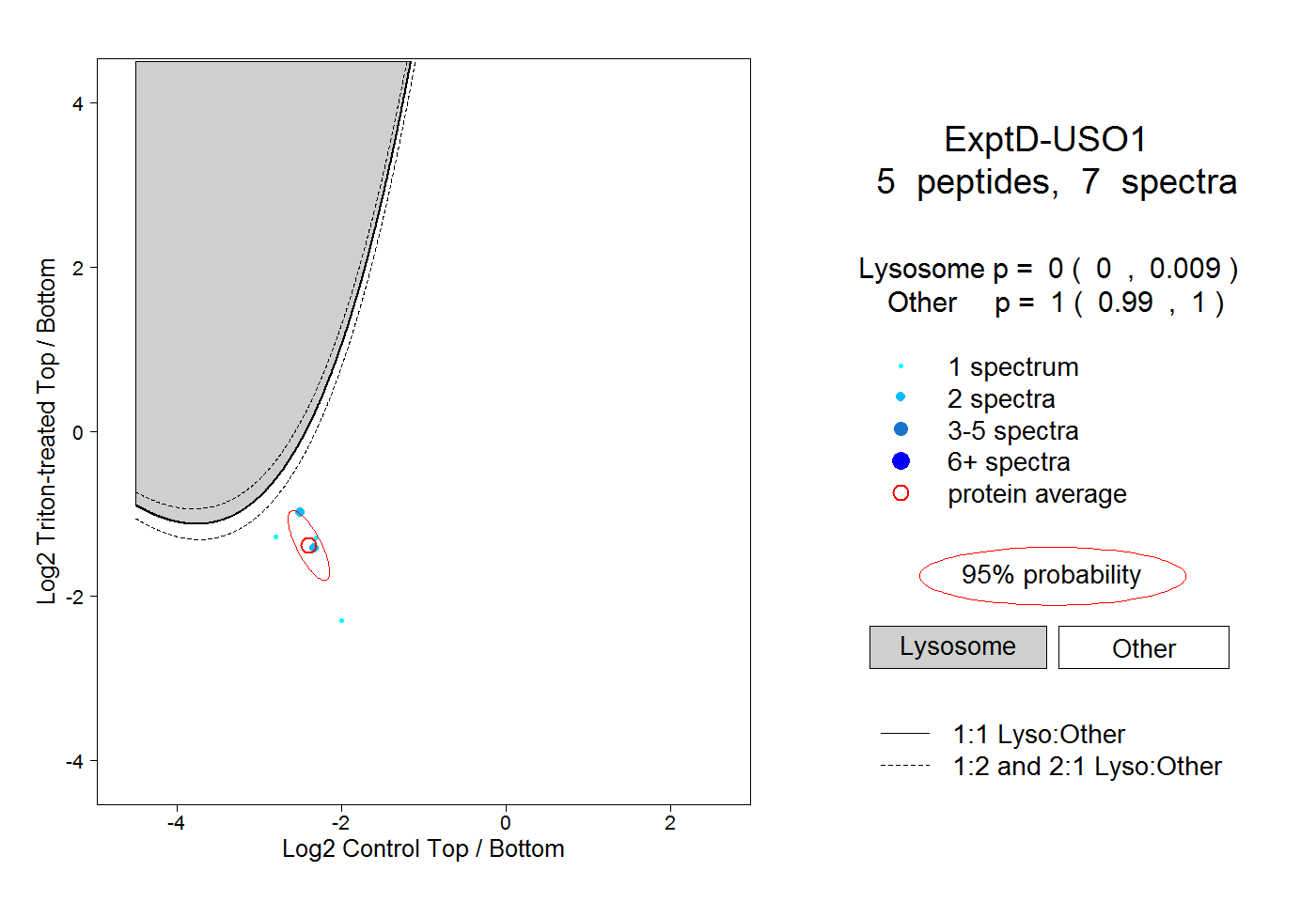
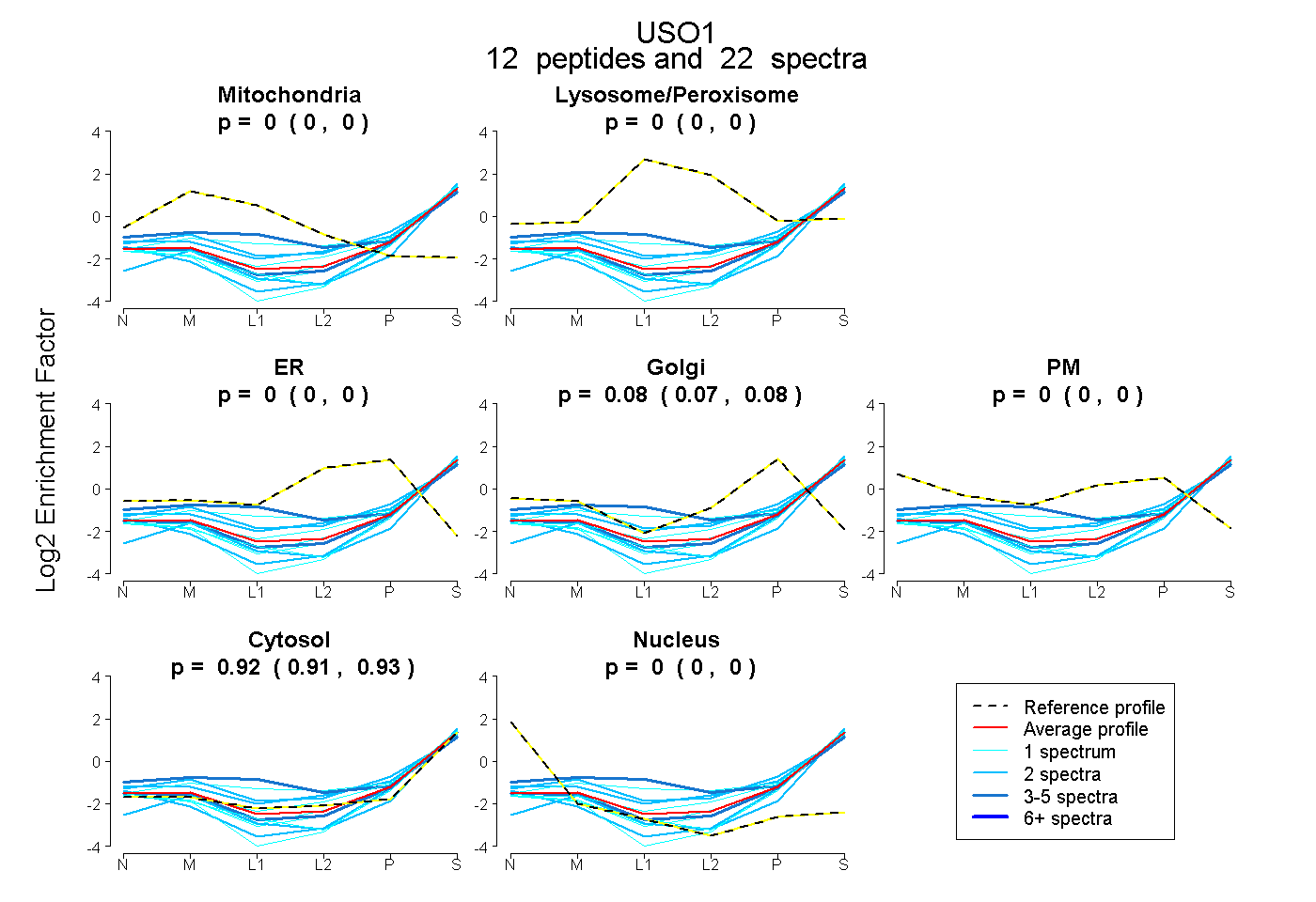
peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.055 | 0.059
0.000 | 0.000
0.940 | 0.944
0.000 | 0.001
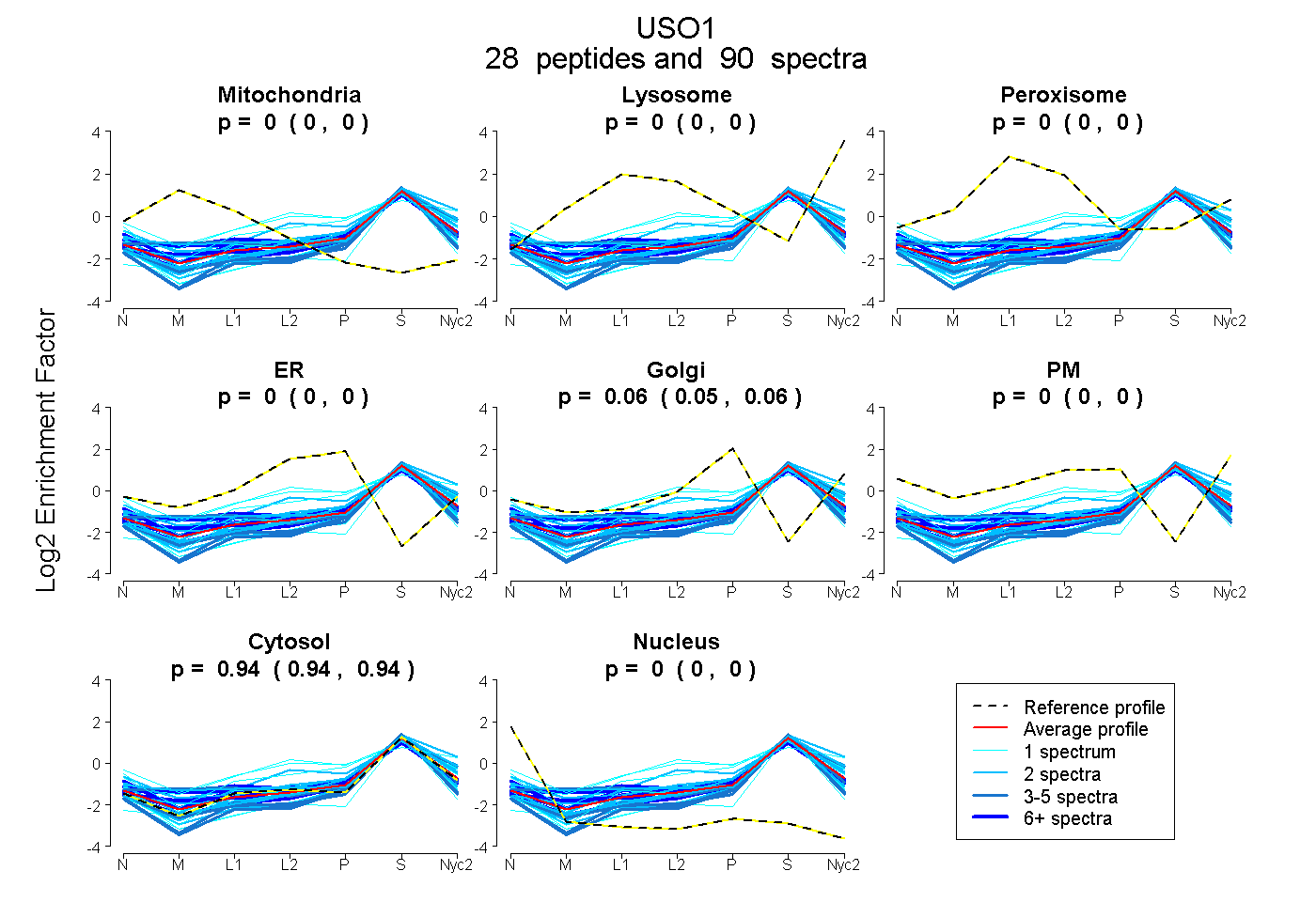
peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.071 | 0.085
0.000 | 0.000
0.914 | 0.927
0.000 | 0.000
peptides
spectra
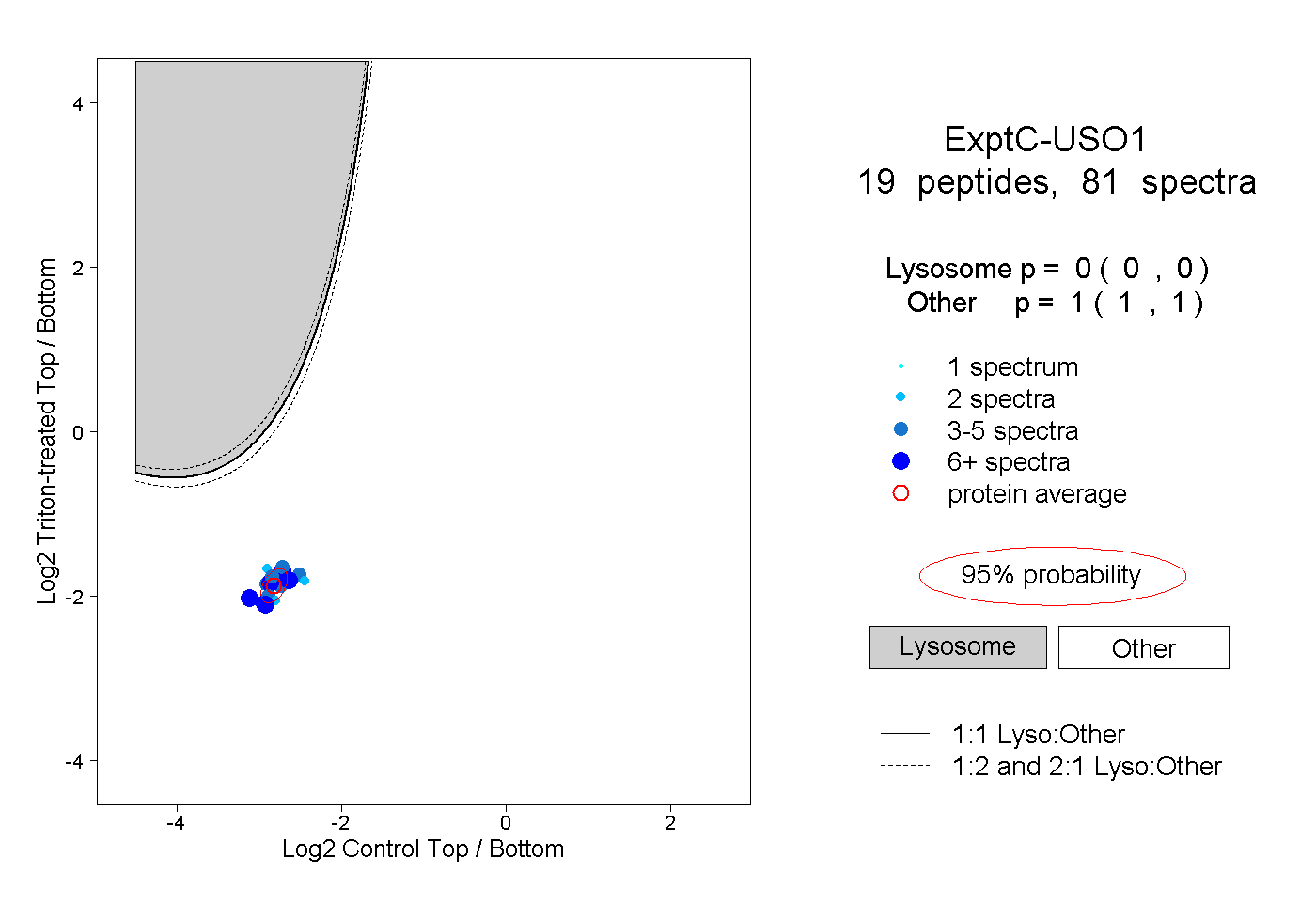
0.000 | 0.000
1.000 | 1.000