peptides
spectra
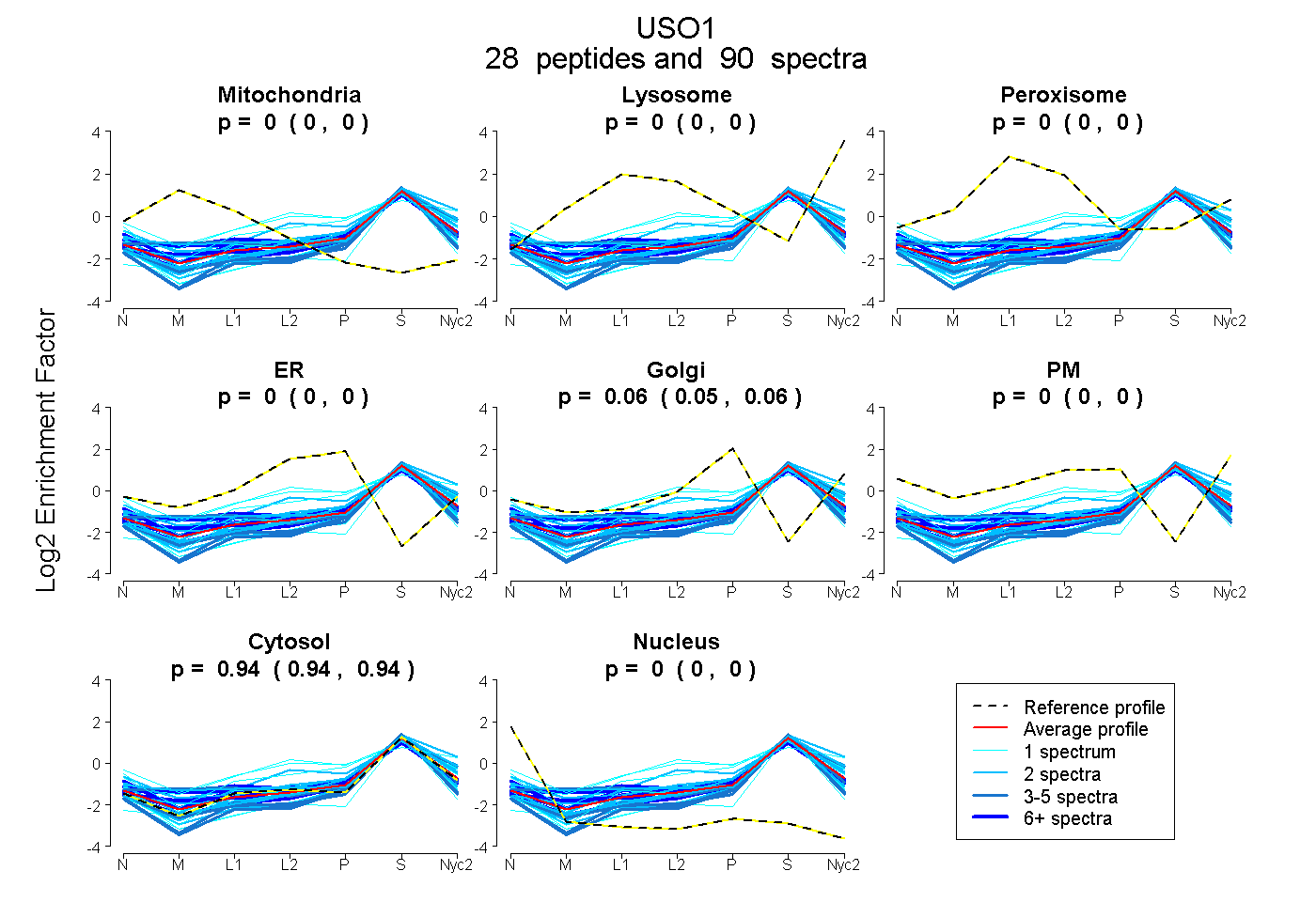
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.055 | 0.059
0.000 | 0.000
0.940 | 0.944
0.000 | 0.001
peptides
spectra
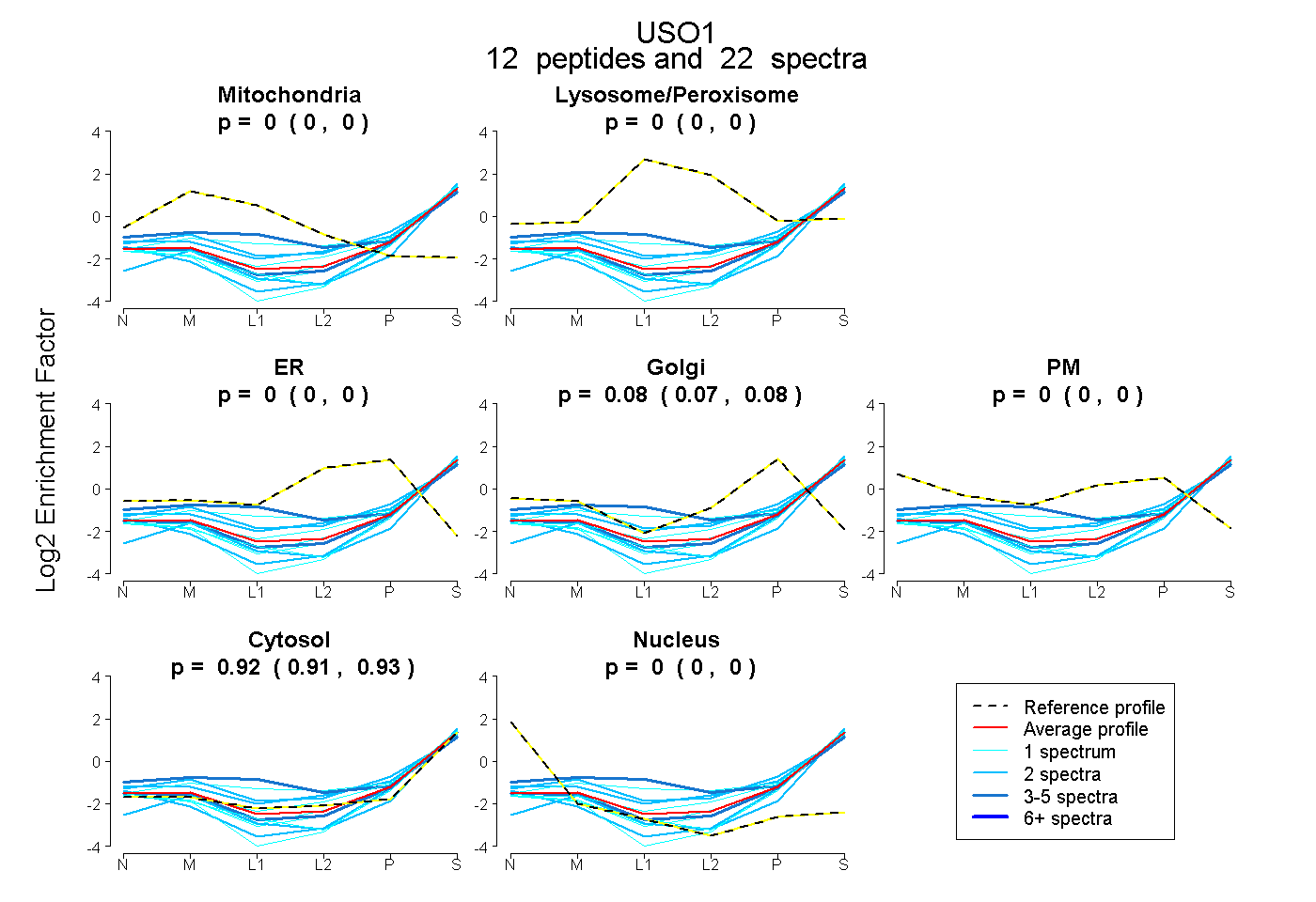
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.071 | 0.085
0.000 | 0.000
0.914 | 0.927
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
90 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.057 0.055 | 0.059 |
0.000 0.000 | 0.000 |
0.943 0.940 | 0.944 |
0.000 0.000 | 0.001 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.079 0.071 | 0.085 |
0.000 0.000 | 0.000 |
0.921 0.914 | 0.927 |
0.000 0.000 | 0.000 |
| 2 spectra, LMDLLADSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, EELEEIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.910 | 0.090 | |||
| 1 spectrum, VLVSPTNPPGATSSCQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.929 | 0.071 | |||
| 5 spectra, IVAFENAFER | 0.000 | 0.000 | 0.000 | 0.044 | 0.000 | 0.936 | 0.020 | |||
| 2 spectra, SQLCSQSLEITR | 0.000 | 0.069 | 0.000 | 0.191 | 0.000 | 0.740 | 0.000 | |||
| 2 spectra, LQTENSELQQR | 0.000 | 0.056 | 0.000 | 0.120 | 0.033 | 0.791 | 0.000 | |||
| 1 spectrum, VASSTLLDDR | 0.000 | 0.000 | 0.000 | 0.098 | 0.000 | 0.902 | 0.000 | |||
| 1 spectrum, QSEDLGSQFTEIFIK | 0.000 | 0.181 | 0.000 | 0.045 | 0.000 | 0.774 | 0.000 | |||
| 1 spectrum, EQDLQLEELK | 0.000 | 0.000 | 0.000 | 0.029 | 0.000 | 0.970 | 0.001 | |||
| 3 spectra, TLEQHDNIVTHYK | 0.080 | 0.201 | 0.000 | 0.000 | 0.021 | 0.698 | 0.000 | |||
| 1 spectrum, ELEGVITK | 0.000 | 0.000 | 0.000 | 0.034 | 0.000 | 0.959 | 0.007 | |||
| 1 spectrum, SVPVEGESELVTAAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.926 | 0.074 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
81 spectra |
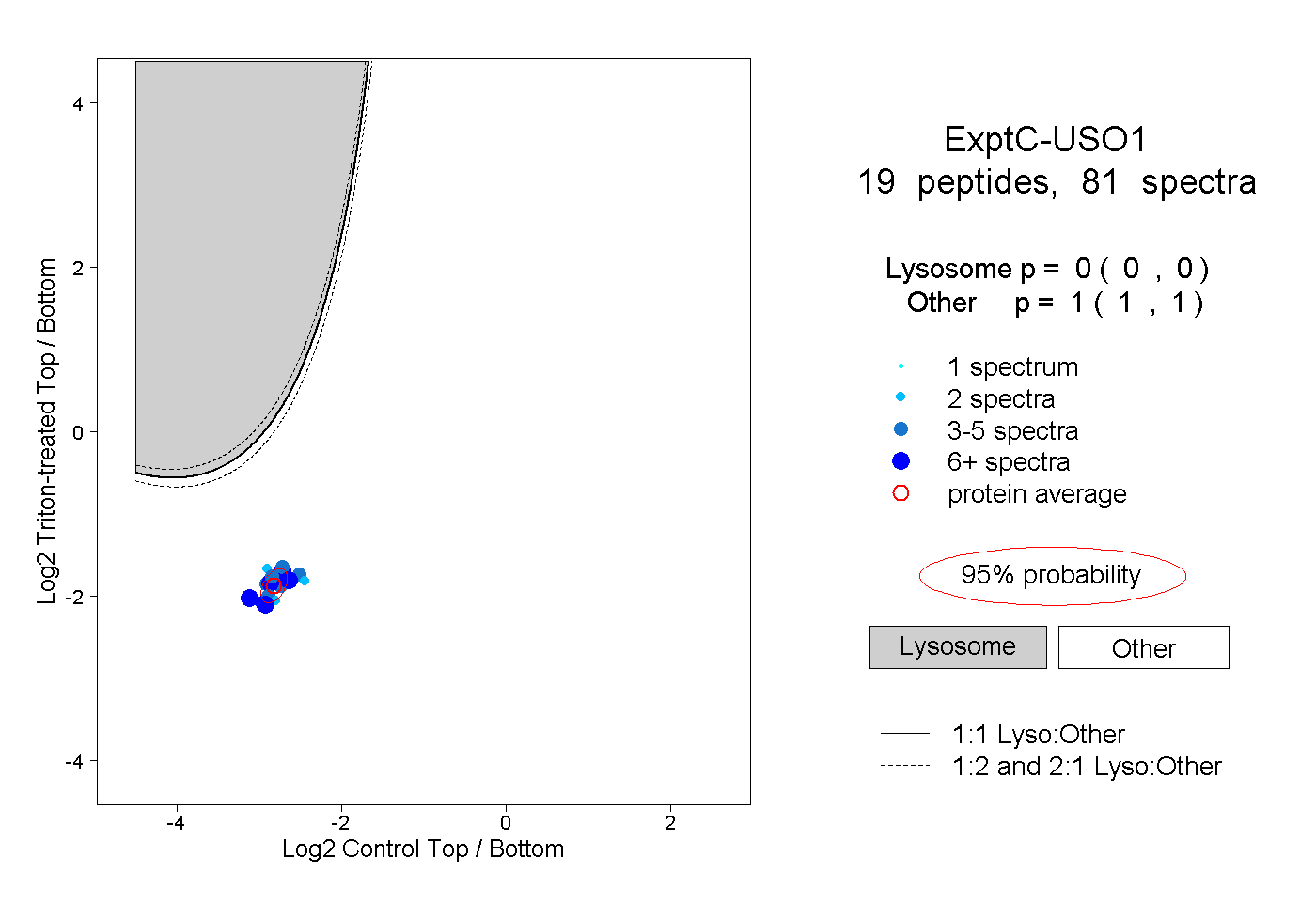 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
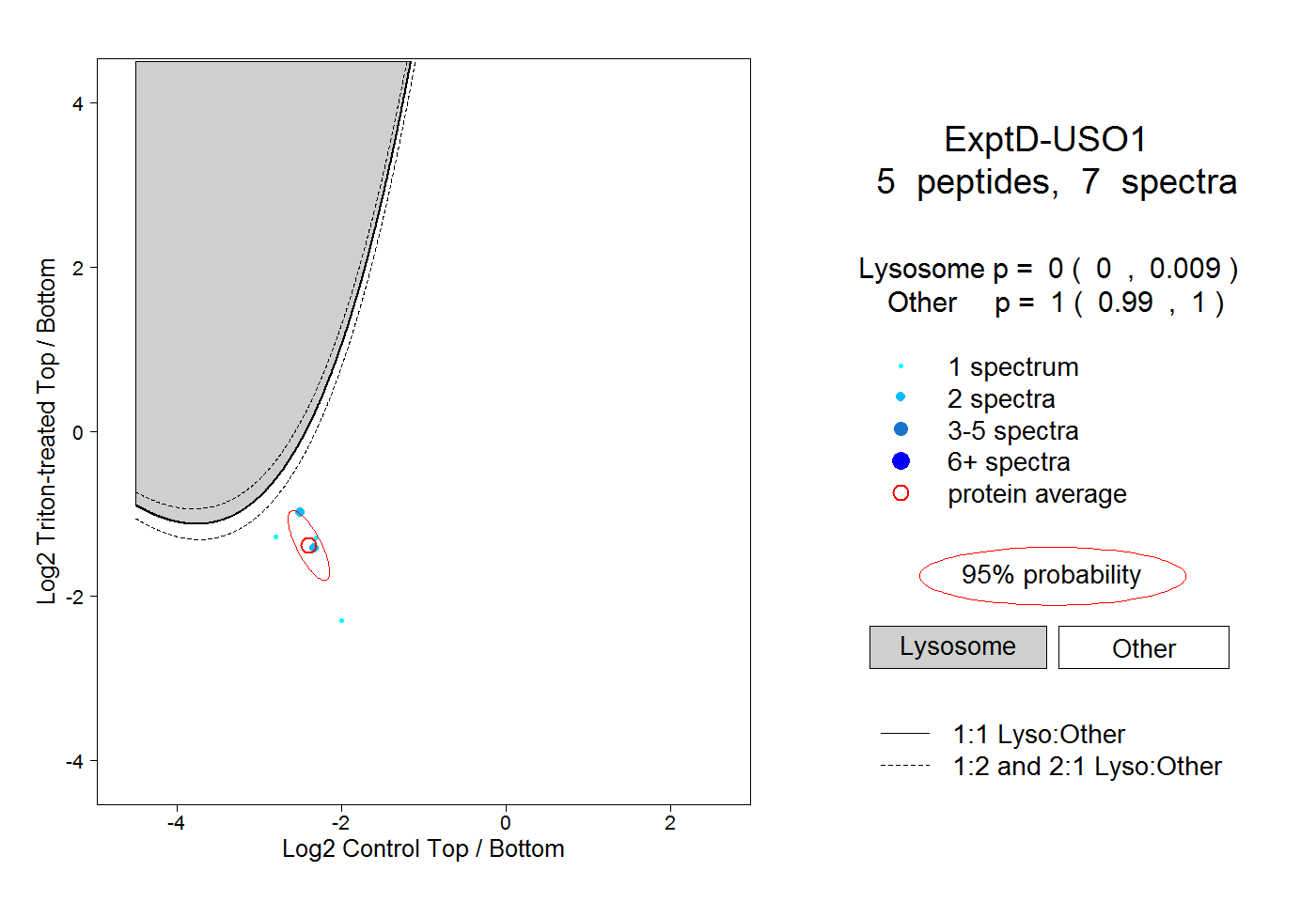 |
0.000 0.000 | 0.009 |
1.000 0.990 | 1.000 |