peptides
spectra
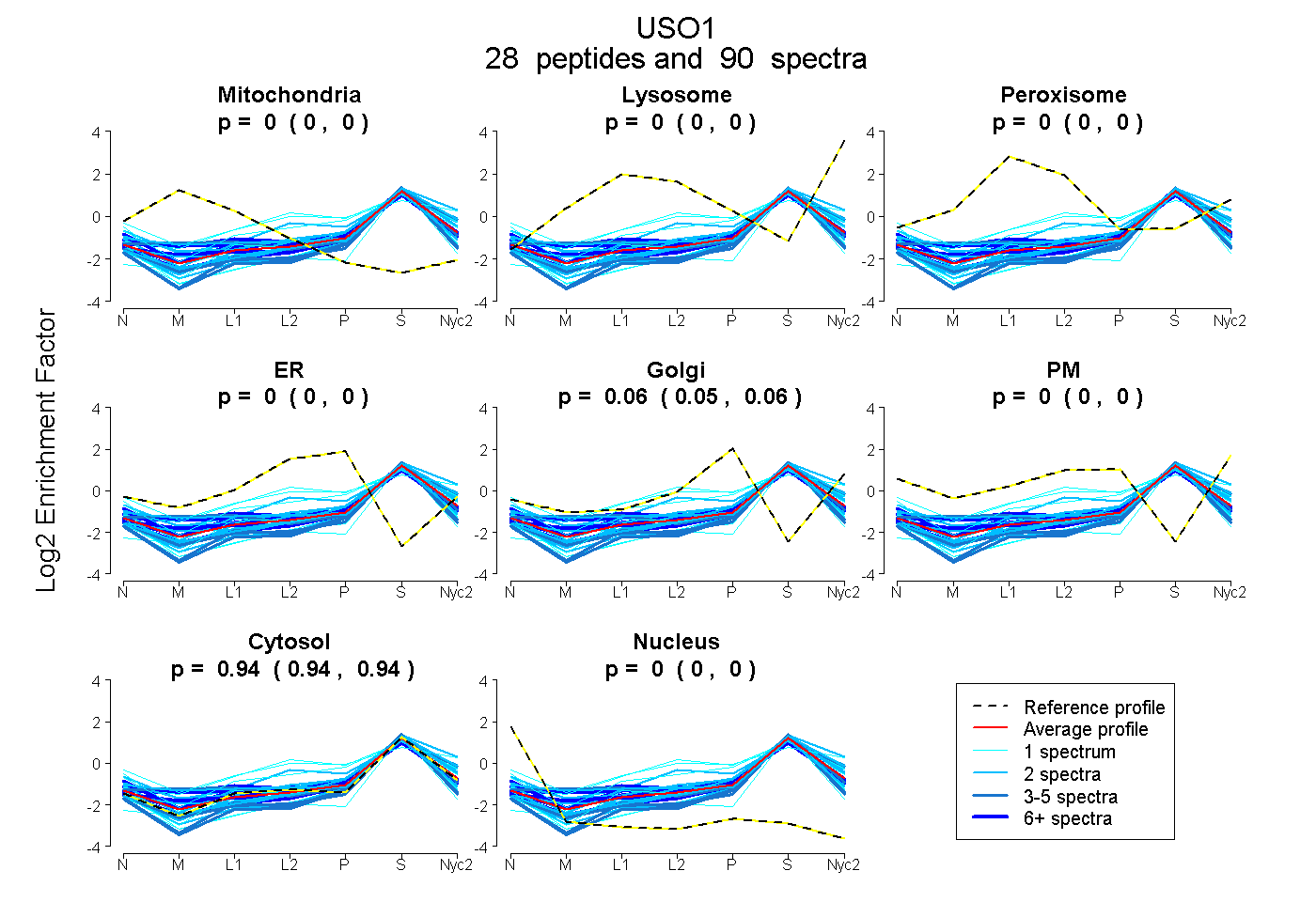
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.055 | 0.059
0.000 | 0.000
0.940 | 0.944
0.000 | 0.001
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
90 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.057 0.055 | 0.059 |
0.000 0.000 | 0.000 |
0.943 0.940 | 0.944 |
0.000 0.000 | 0.001 |
| 2 spectra, NDGVLLLQALTR | 0.000 | 0.003 | 0.000 | 0.000 | 0.066 | 0.000 | 0.930 | 0.000 | ||
| 1 spectrum, QELSALK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.935 | 0.065 | ||
| 5 spectra, SQLCSQSLEITR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.917 | 0.083 | ||
| 3 spectra, QQVSTLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.958 | 0.042 | ||
| 2 spectra, VASSTLLDDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.045 | 0.000 | 0.955 | 0.000 | ||
| 2 spectra, LGFISK | 0.000 | 0.000 | 0.000 | 0.000 | 0.049 | 0.000 | 0.951 | 0.000 | ||
| 7 spectra, LMDLLADSR | 0.053 | 0.000 | 0.000 | 0.000 | 0.015 | 0.000 | 0.931 | 0.000 | ||
| 1 spectrum, QPFVLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.852 | 0.148 | ||
| 1 spectrum, QSEDLGSQFTEIFIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.994 | 0.006 | ||
| 2 spectra, DQYNLLK | 0.000 | 0.048 | 0.000 | 0.000 | 0.000 | 0.000 | 0.952 | 0.000 | ||
| 2 spectra, LLTSLLK | 0.000 | 0.031 | 0.000 | 0.000 | 0.032 | 0.111 | 0.826 | 0.000 | ||
| 6 spectra, DAEQVAELK | 0.107 | 0.016 | 0.000 | 0.000 | 0.065 | 0.000 | 0.813 | 0.000 | ||
| 1 spectrum, ASQKPQPNFPSPEYMIFDHEFTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.087 | 0.865 | 0.047 | ||
| 6 spectra, ELEGVITK | 0.000 | 0.000 | 0.000 | 0.000 | 0.029 | 0.061 | 0.880 | 0.029 | ||
| 2 spectra, EELEEIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.928 | 0.072 | ||
| 13 spectra, IVAFENAFER | 0.000 | 0.000 | 0.000 | 0.000 | 0.007 | 0.000 | 0.967 | 0.026 | ||
| 2 spectra, VLVSPTNPPGATSSCQK | 0.149 | 0.000 | 0.033 | 0.000 | 0.000 | 0.000 | 0.818 | 0.000 | ||
| 2 spectra, LQTENSELQQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.020 | 0.000 | 0.967 | 0.013 | ||
| 2 spectra, ALSEER | 0.000 | 0.000 | 0.025 | 0.019 | 0.000 | 0.202 | 0.754 | 0.000 | ||
| 9 spectra, EQDLQLEELK | 0.001 | 0.000 | 0.022 | 0.000 | 0.063 | 0.000 | 0.913 | 0.000 | ||
| 1 spectrum, LEVGIQAMEHLIHVLQTDR | 0.000 | 0.141 | 0.071 | 0.141 | 0.000 | 0.000 | 0.647 | 0.000 | ||
| 1 spectrum, AWFEVGDENPGWSAQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, HELYSR | 0.000 | 0.000 | 0.000 | 0.010 | 0.092 | 0.000 | 0.898 | 0.000 | ||
| 1 spectrum, SHQVLLQSQLAEK | 0.000 | 0.014 | 0.106 | 0.000 | 0.000 | 0.294 | 0.586 | 0.000 | ||
| 6 spectra, EGSYIQR | 0.104 | 0.032 | 0.039 | 0.000 | 0.008 | 0.000 | 0.817 | 0.000 | ||
| 1 spectrum, TLEQHDNIVTHYK | 0.000 | 0.000 | 0.045 | 0.155 | 0.001 | 0.046 | 0.754 | 0.000 | ||
| 4 spectra, LSALLQETK | 0.079 | 0.106 | 0.000 | 0.000 | 0.000 | 0.000 | 0.815 | 0.000 | ||
| 3 spectra, SVPVEGESELVTAAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.937 | 0.063 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
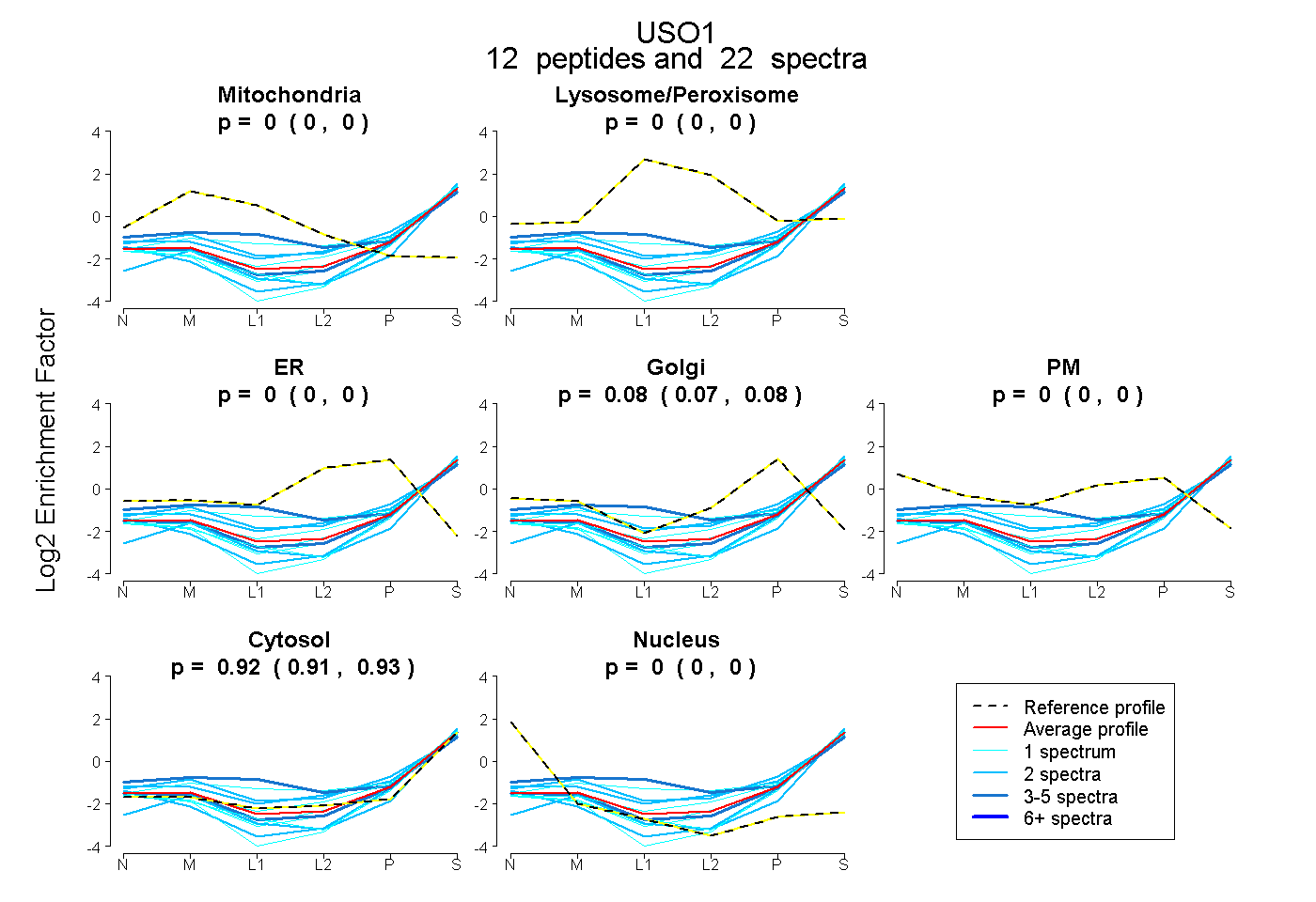 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.079 0.071 | 0.085 |
0.000 0.000 | 0.000 |
0.921 0.914 | 0.927 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
81 spectra |
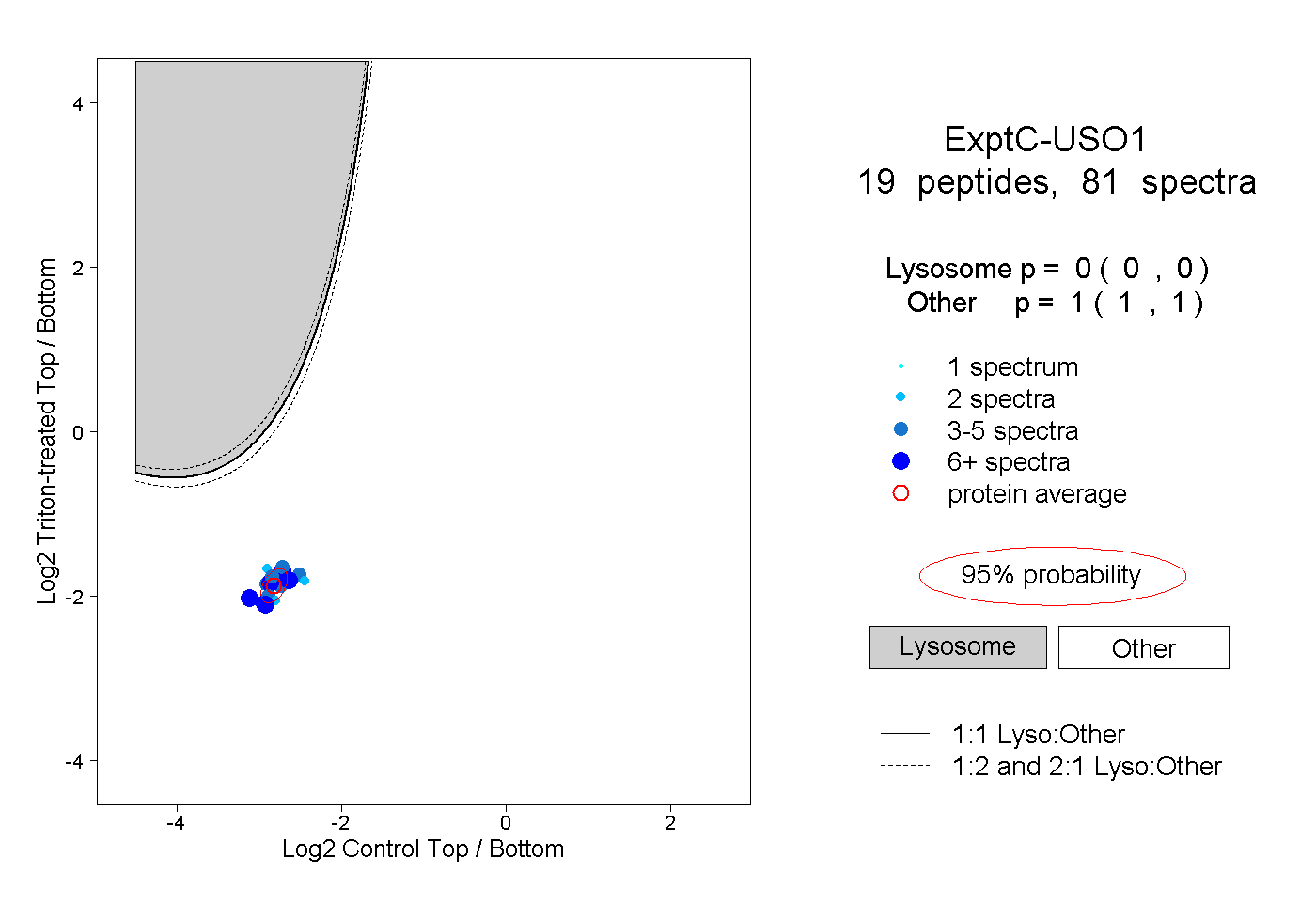 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
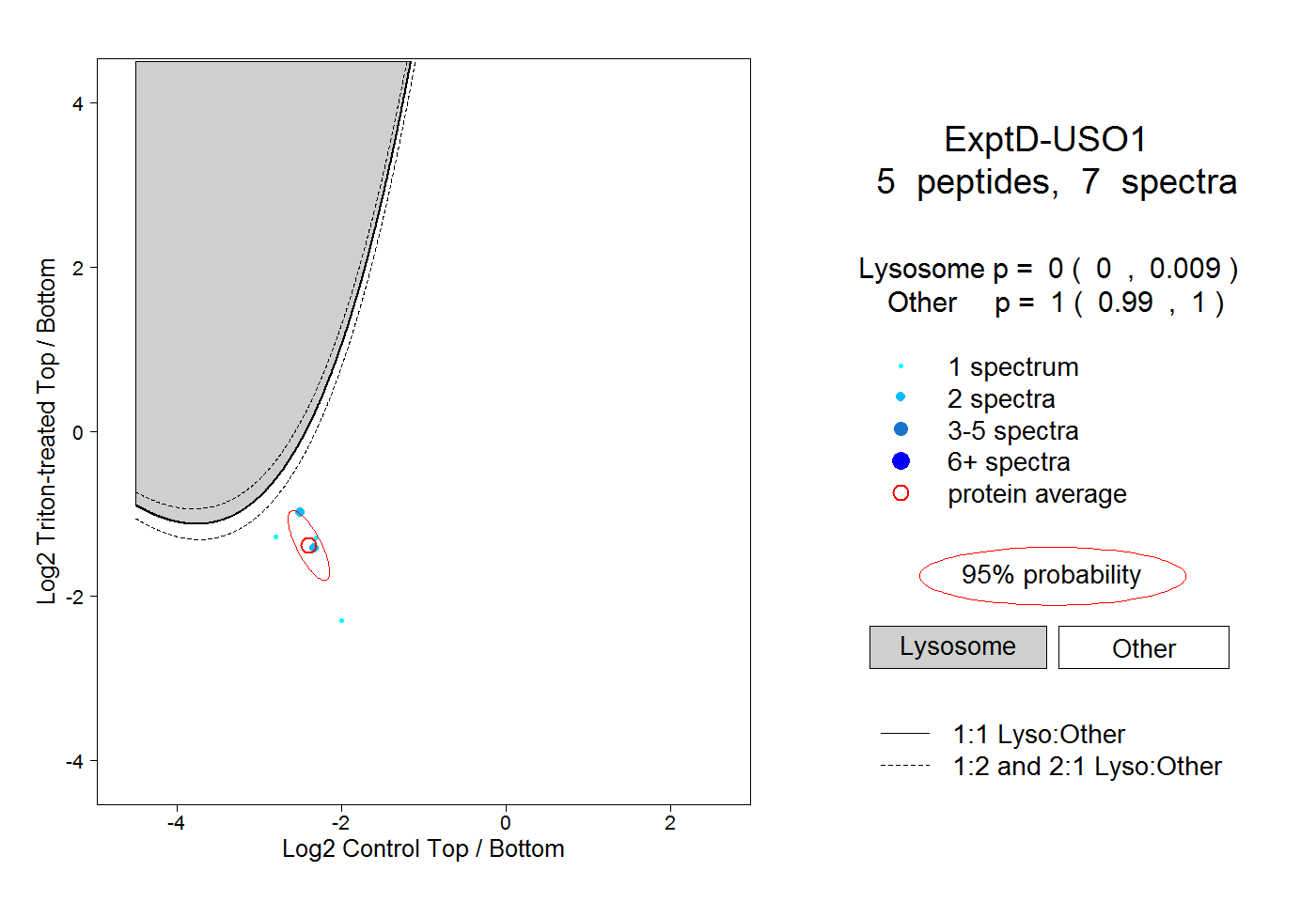 |
0.000 0.000 | 0.009 |
1.000 0.990 | 1.000 |