peptides
spectra
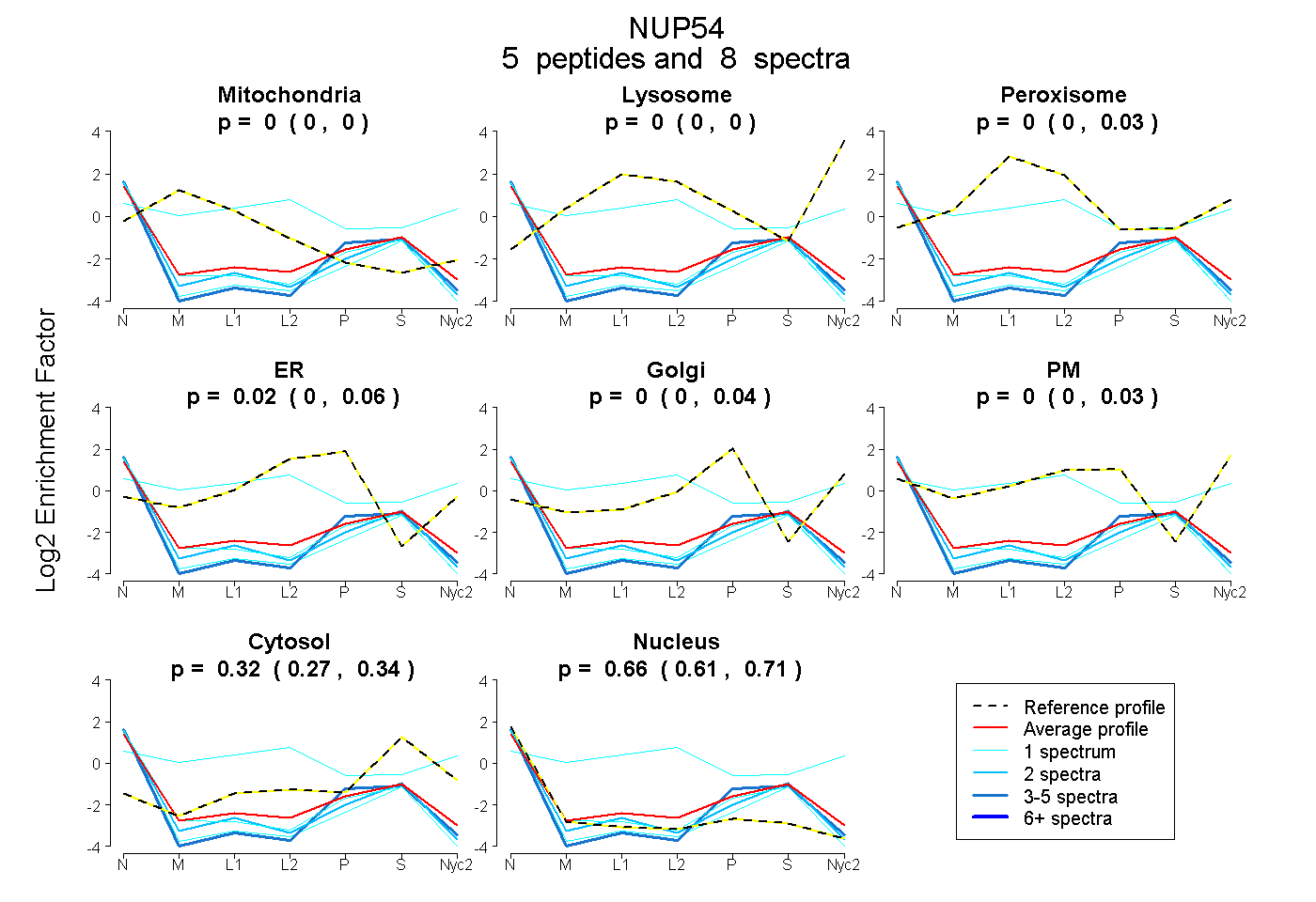
0.000 | 0.000
0.000 | 0.000
0.000 | 0.031
0.000 | 0.055
0.000 | 0.038
0.000 | 0.032
0.269 | 0.337
0.610 | 0.709
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
8 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.031 |
0.017 0.000 | 0.055 |
0.000 0.000 | 0.038 |
0.000 0.000 | 0.032 |
0.319 0.269 | 0.337 |
0.664 0.610 | 0.709 |
| 2 spectra, SGYAIQAEEEQLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.223 | 0.777 | ||
| 1 spectrum, LDIISEDISELQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.131 | 0.869 | ||
| 3 spectra, LIPVPMVGFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.195 | 0.805 | ||
| 1 spectrum, TQLQQLGVTLSMTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.197 | 0.803 | ||
| 1 spectrum, SQQQQLVESLHK | 0.066 | 0.000 | 0.406 | 0.000 | 0.000 | 0.301 | 0.154 | 0.072 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
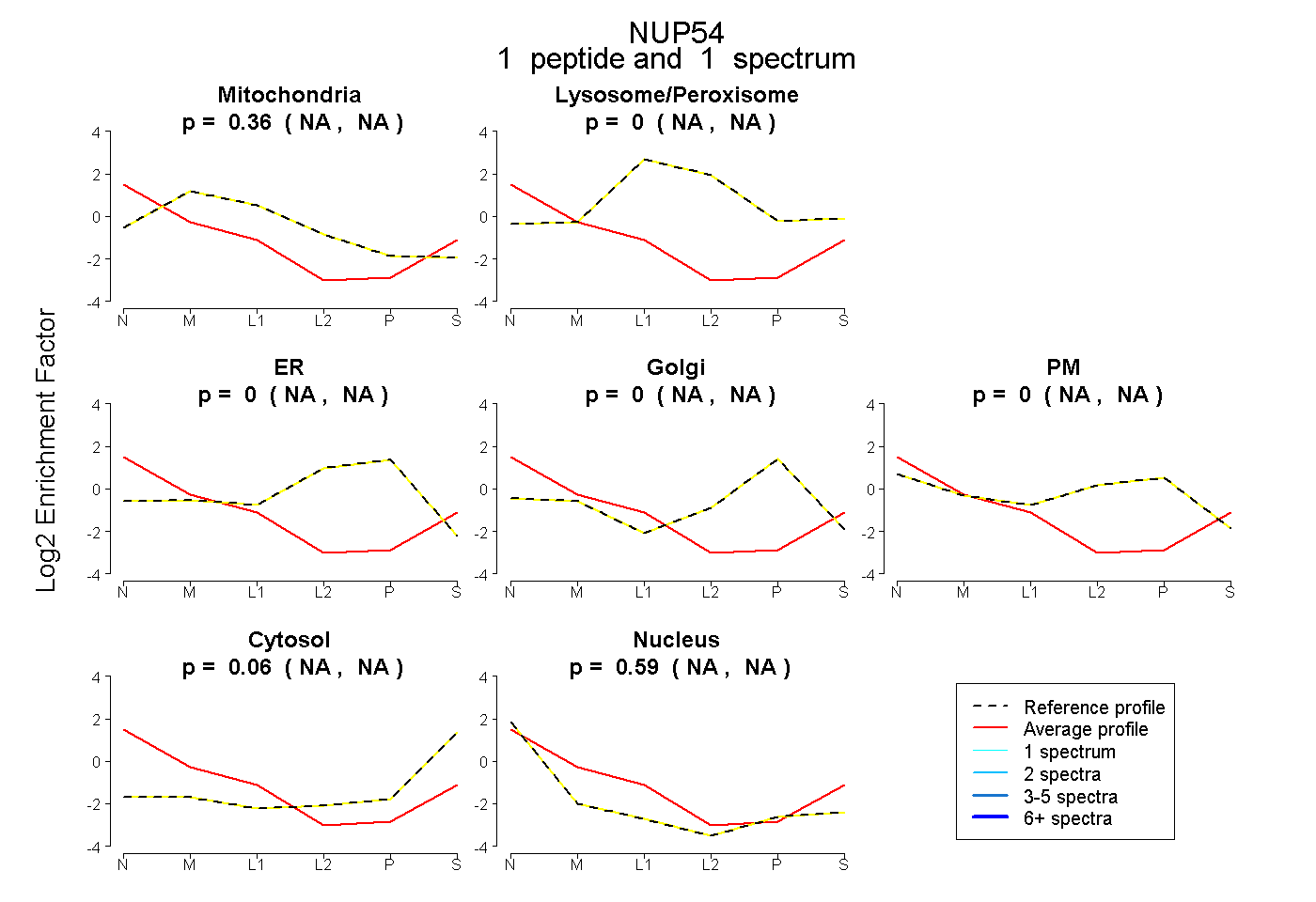 |
0.355 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.056 NA | NA |
0.588 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
3 spectra |
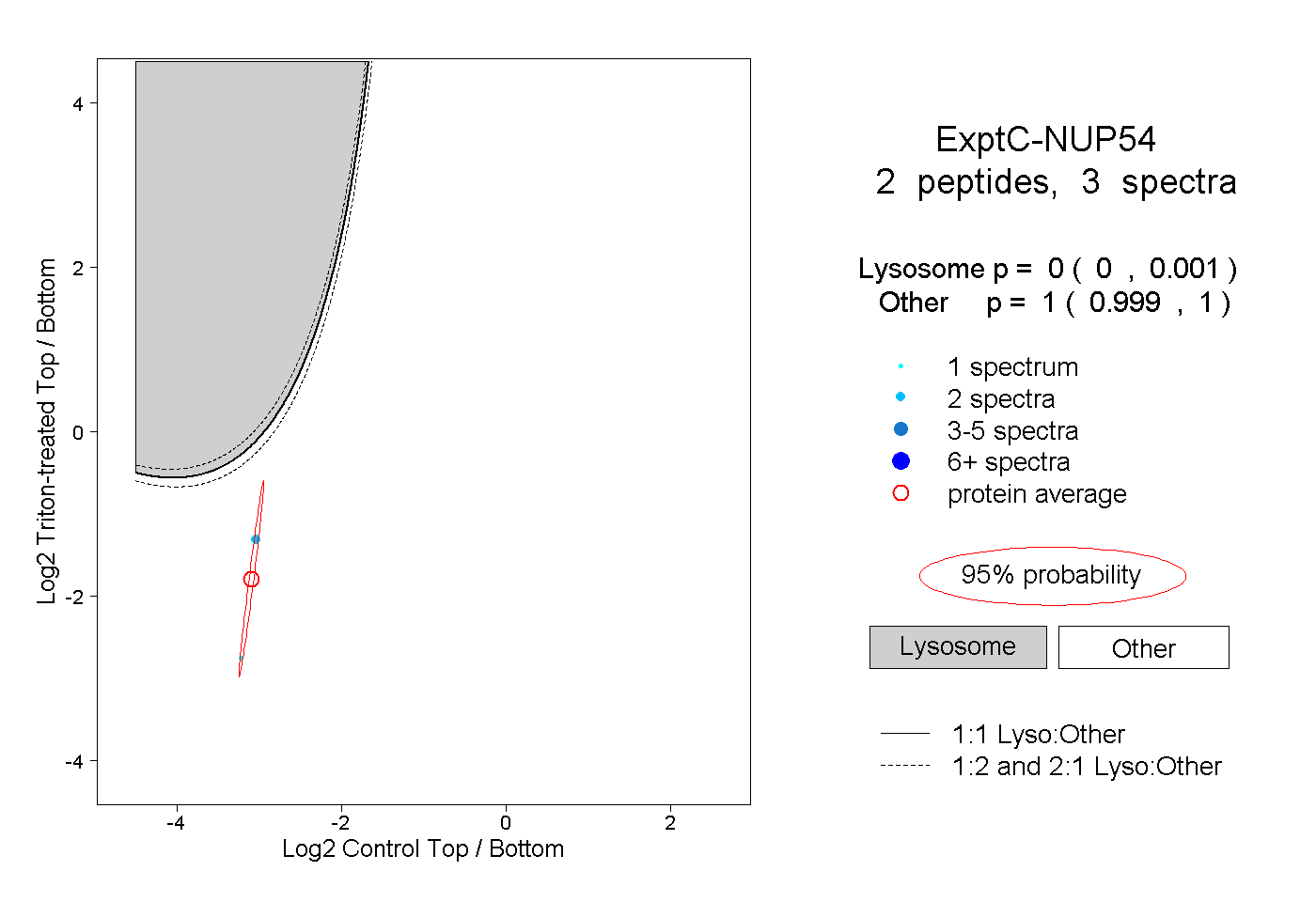 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |