peptides
spectra
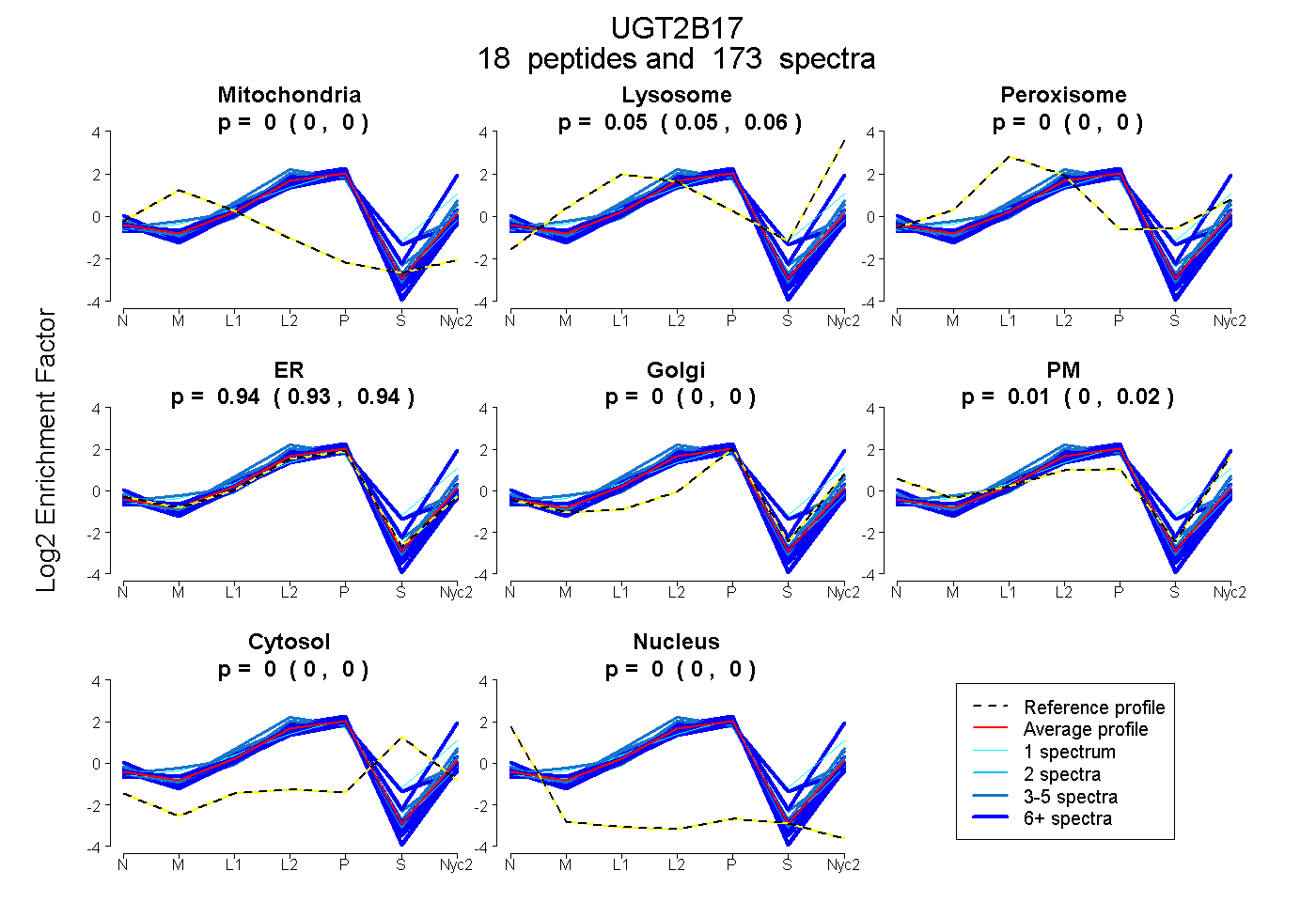
0.000 | 0.000
0.049 | 0.056
0.000 | 0.000
0.931 | 0.943
0.000 | 0.000
0.002 | 0.015
0.000 | 0.000
0.000 | 0.000
peptides
spectra
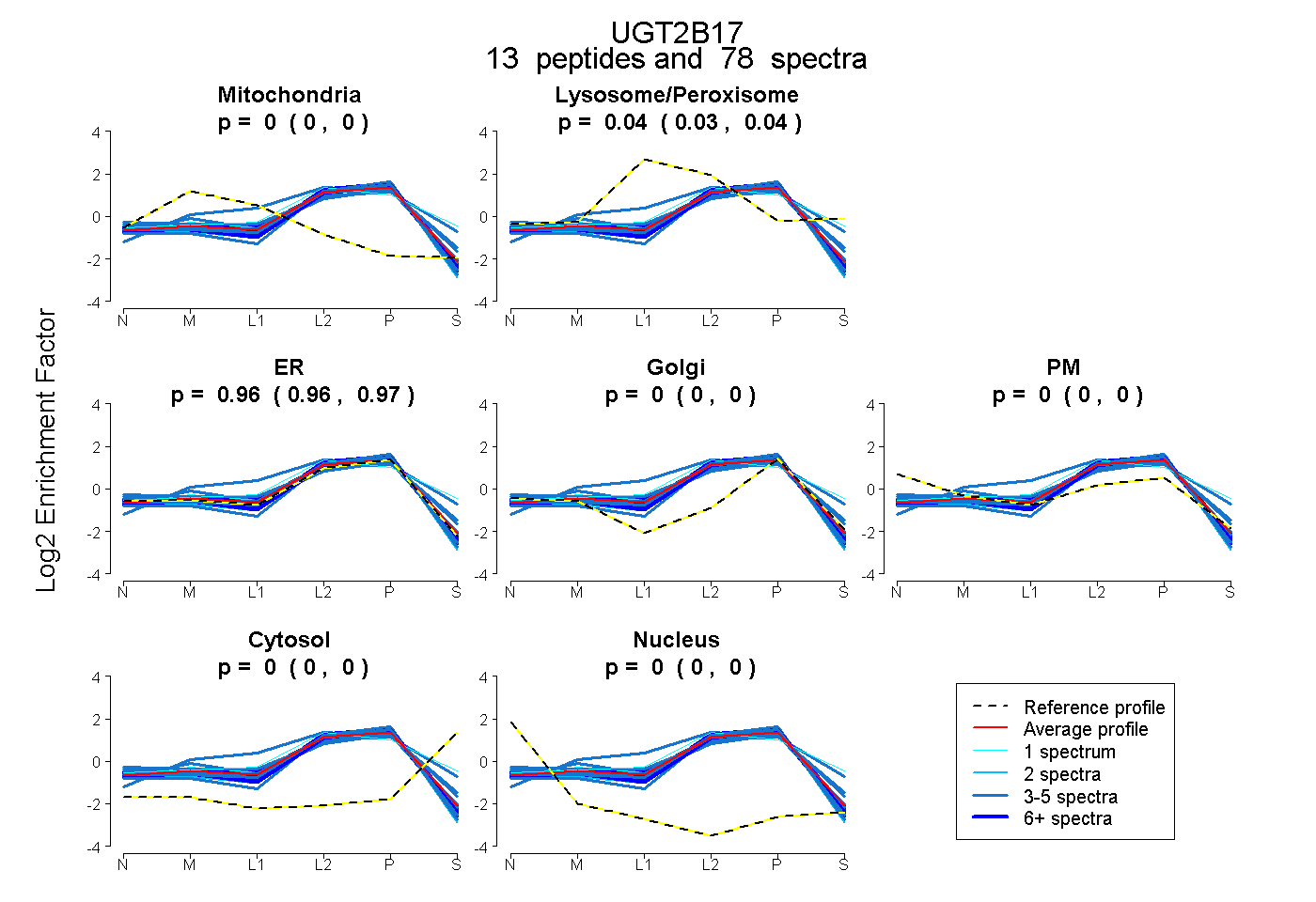
0.000 | 0.000
0.033 | 0.043
0.956 | 0.966
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
173 spectra |
 |
0.000 0.000 | 0.000 |
0.053 0.049 | 0.056 |
0.000 0.000 | 0.000 |
0.938 0.931 | 0.943 |
0.000 0.000 | 0.000 |
0.009 0.002 | 0.015 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
78 spectra |
 |
0.000 0.000 | 0.000 |
0.038 0.033 | 0.043 |
0.962 0.956 | 0.966 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 17 spectra, TPLVYSLR | 0.000 | 0.000 | 0.994 | 0.006 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, SDLEYSFAK | 0.000 | 0.000 | 0.978 | 0.022 | 0.000 | 0.000 | 0.000 | |||
| 17 spectra, KPDTLGSNTR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, WIDEWTR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, ADIWLIR | 0.000 | 0.048 | 0.952 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ANVVASALAQIPQK | 0.080 | 0.020 | 0.900 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, VFNEYSDVVENLCK | 0.000 | 0.097 | 0.873 | 0.000 | 0.000 | 0.030 | 0.000 | |||
| 7 spectra, IILNELAQR | 0.000 | 0.018 | 0.982 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, IHHDQPVKPLDR | 0.000 | 0.309 | 0.691 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, ESSINFEIYSVPLSK | 0.000 | 0.106 | 0.860 | 0.007 | 0.000 | 0.027 | 0.000 | |||
| 1 spectrum, VLVWPTEYSHWINIK | 0.000 | 0.297 | 0.588 | 0.000 | 0.000 | 0.116 | 0.000 | |||
| 2 spectra, DFETLSIWTYYSK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, FCPGYR | 0.000 | 0.222 | 0.549 | 0.127 | 0.000 | 0.102 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
199 spectra |
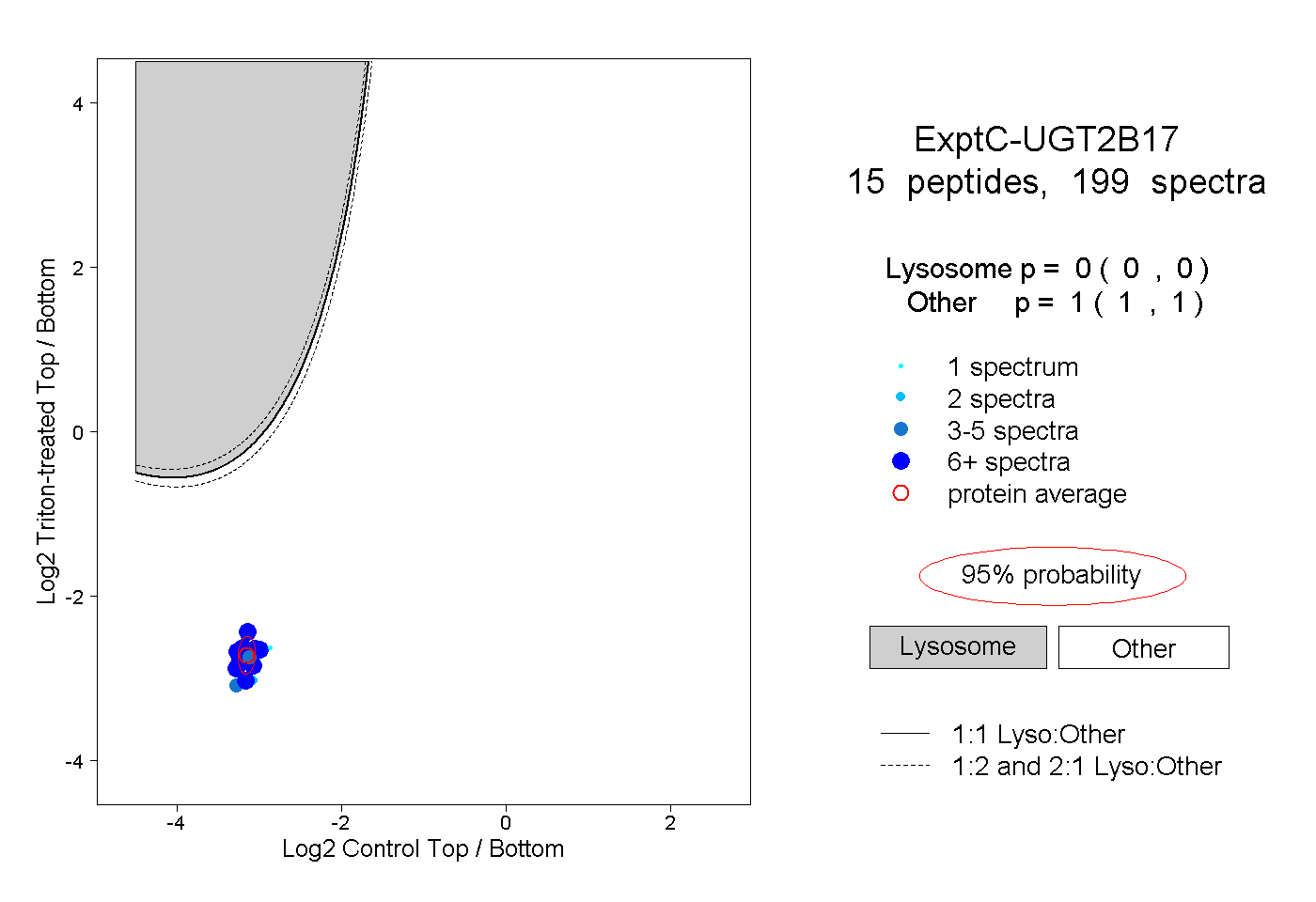 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
27 spectra |
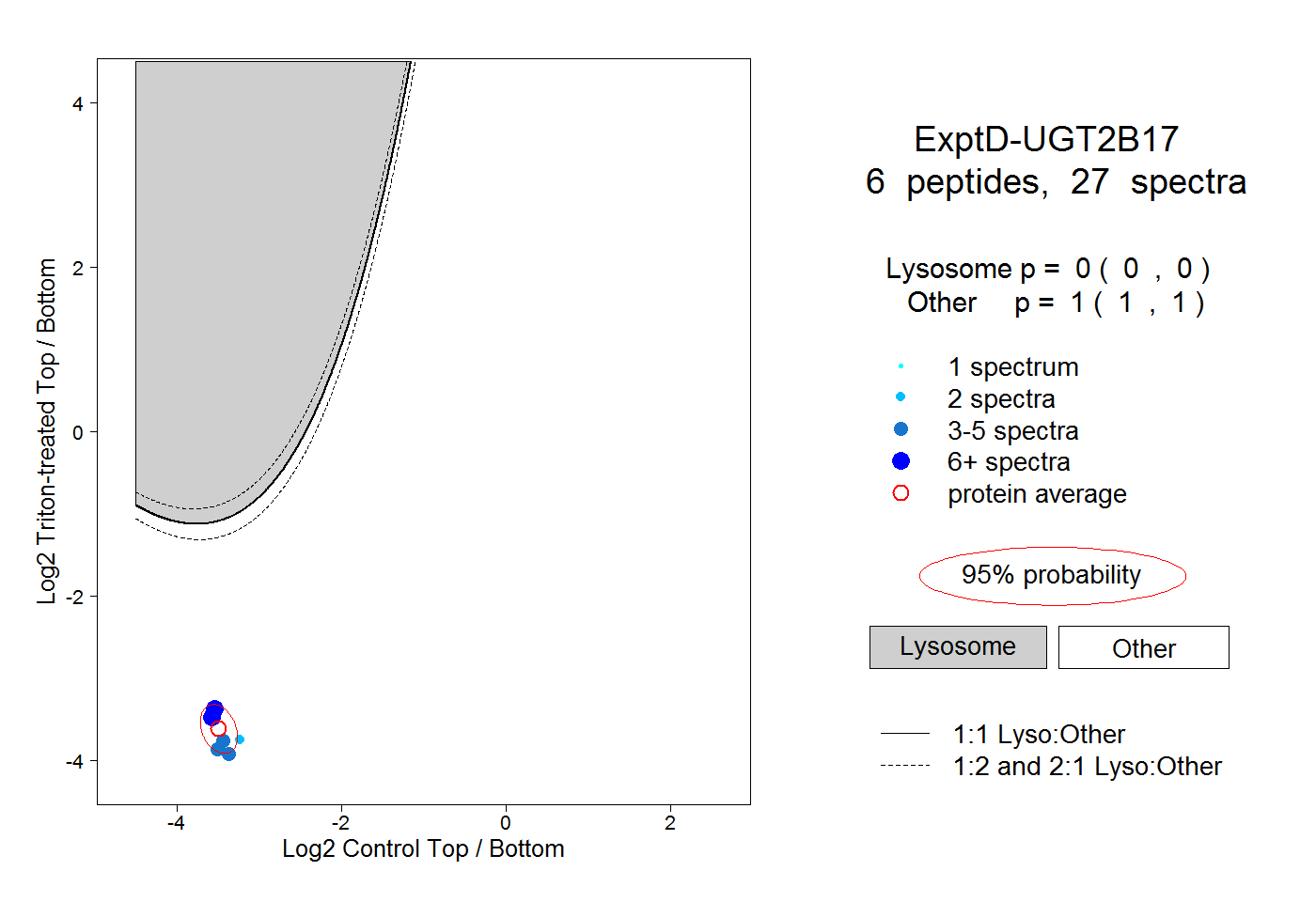 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |