peptides
spectra
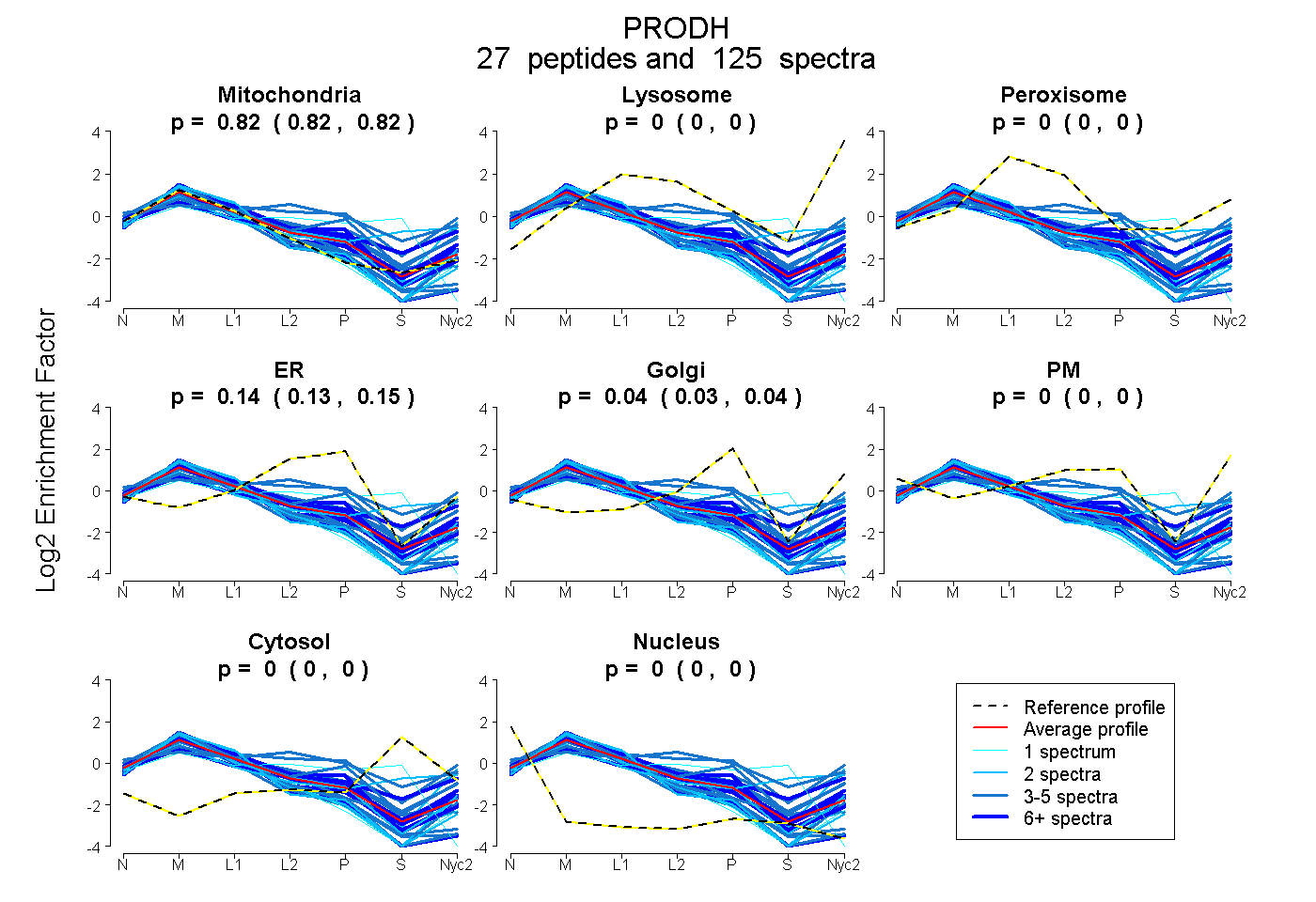
0.817 | 0.824
0.000 | 0.000
0.000 | 0.000
0.134 | 0.152
0.025 | 0.044
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
125 spectra |
 |
0.821 0.817 | 0.824 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.144 0.134 | 0.152 |
0.035 0.025 | 0.044 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, YVPYGPVMEVLPYLSR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, MDVLAK | 0.939 | 0.000 | 0.000 | 0.061 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, GCGAAEAVRPPVPAVDFTNTQEAYR | 0.937 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.063 | ||
| 11 spectra, GAYMAQER | 0.900 | 0.000 | 0.000 | 0.083 | 0.017 | 0.000 | 0.000 | 0.000 | ||
| 22 spectra, NLIVIR | 0.581 | 0.075 | 0.000 | 0.000 | 0.124 | 0.100 | 0.120 | 0.000 | ||
| 2 spectra, AVEIGYEDPINPTYEATNAMYHR | 0.747 | 0.133 | 0.000 | 0.000 | 0.072 | 0.047 | 0.000 | 0.000 | ||
| 3 spectra, TYFYASEAK | 0.577 | 0.000 | 0.048 | 0.042 | 0.329 | 0.005 | 0.000 | 0.000 | ||
| 6 spectra, LTLEMQR | 0.791 | 0.000 | 0.000 | 0.084 | 0.097 | 0.029 | 0.000 | 0.000 | ||
| 3 spectra, LCASPVLLAHHEQLFQVAR | 0.845 | 0.000 | 0.000 | 0.117 | 0.000 | 0.000 | 0.012 | 0.026 | ||
| 8 spectra, FTEEEEQQMK | 0.855 | 0.010 | 0.000 | 0.106 | 0.029 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LEVAVLQESIAK | 0.980 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.020 | ||
| 3 spectra, AEVMVASHNEDTVSFTLCR | 0.600 | 0.120 | 0.020 | 0.000 | 0.183 | 0.055 | 0.022 | 0.000 | ||
| 5 spectra, AQEQPPANPEALR | 0.347 | 0.000 | 0.197 | 0.031 | 0.201 | 0.224 | 0.000 | 0.000 | ||
| 5 spectra, TGSLFHHPA | 0.286 | 0.000 | 0.205 | 0.192 | 0.000 | 0.204 | 0.112 | 0.000 | ||
| 2 spectra, QYQVHPAFGDR | 0.818 | 0.000 | 0.000 | 0.158 | 0.025 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, DGVISAR | 0.759 | 0.000 | 0.000 | 0.090 | 0.041 | 0.110 | 0.000 | 0.000 | ||
| 3 spectra, DAYDNVTIDMELSR | 0.759 | 0.000 | 0.000 | 0.241 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, QLLWQELCR | 0.969 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 | ||
| 1 spectrum, LMIDAEQSYFQPAISR | 0.992 | 0.000 | 0.000 | 0.000 | 0.000 | 0.008 | 0.000 | 0.000 | ||
| 7 spectra, MTFYGHFVAGEDQESIRPLIR | 0.746 | 0.000 | 0.000 | 0.254 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, CLNYVLEELK | 0.896 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.104 | ||
| 2 spectra, SWELAR | 0.549 | 0.148 | 0.000 | 0.000 | 0.000 | 0.052 | 0.251 | 0.000 | ||
| 2 spectra, EGWCFGAK | 0.883 | 0.000 | 0.000 | 0.117 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, MGISSR | 0.949 | 0.000 | 0.000 | 0.000 | 0.000 | 0.051 | 0.000 | 0.000 | ||
| 9 spectra, EMESCTSEAER | 0.970 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.030 | ||
| 1 spectrum, QFFHQMAAEQGQAGRPAVDTK | 0.558 | 0.000 | 0.000 | 0.147 | 0.000 | 0.000 | 0.295 | 0.000 | ||
| 3 spectra, HLVVPNVQTGQLEPLLSR | 0.670 | 0.041 | 0.049 | 0.059 | 0.090 | 0.092 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
50 spectra |
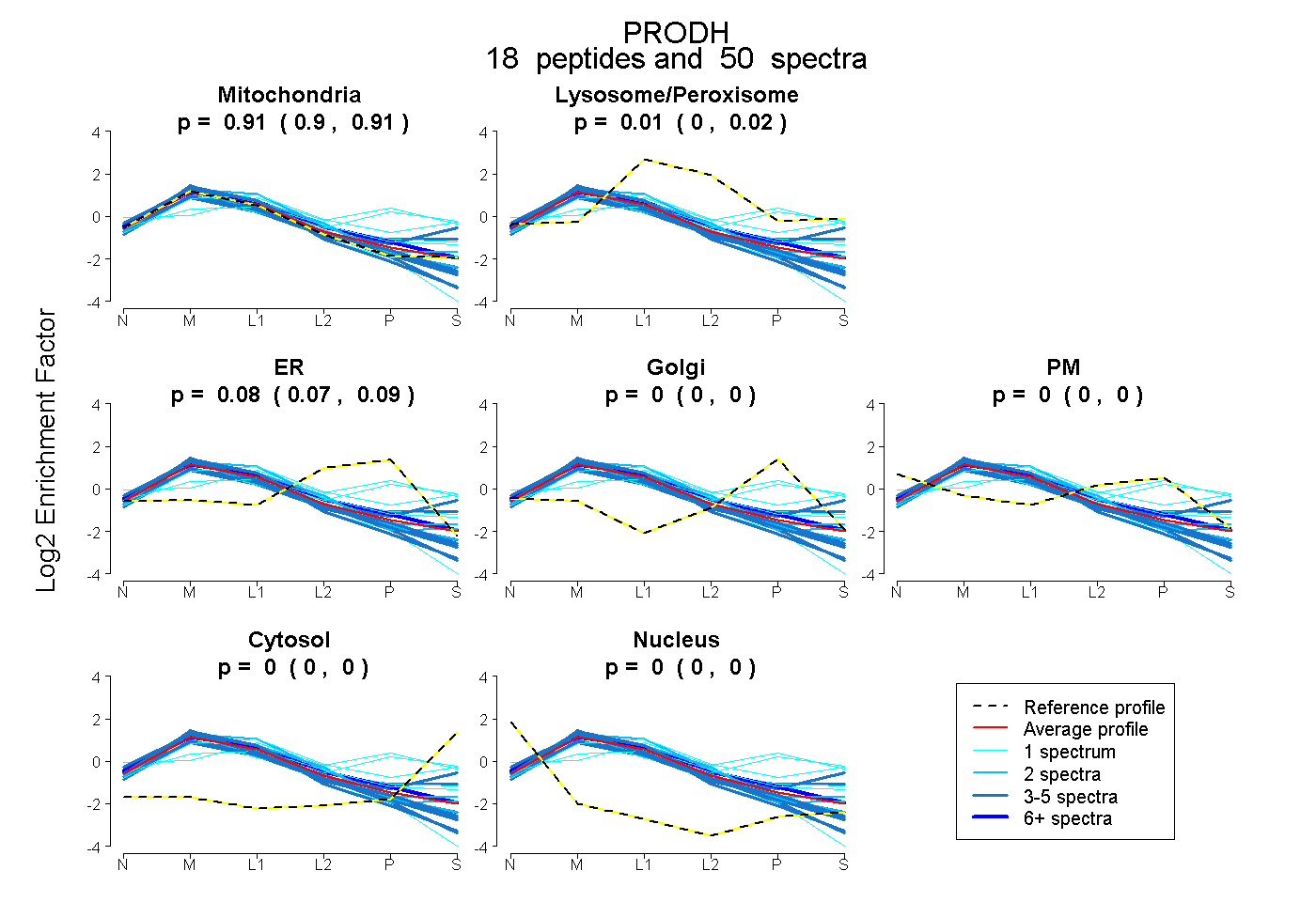 |
0.906 0.899 | 0.912 |
0.012 0.003 | 0.020 |
0.082 0.071 | 0.089 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
227 spectra |
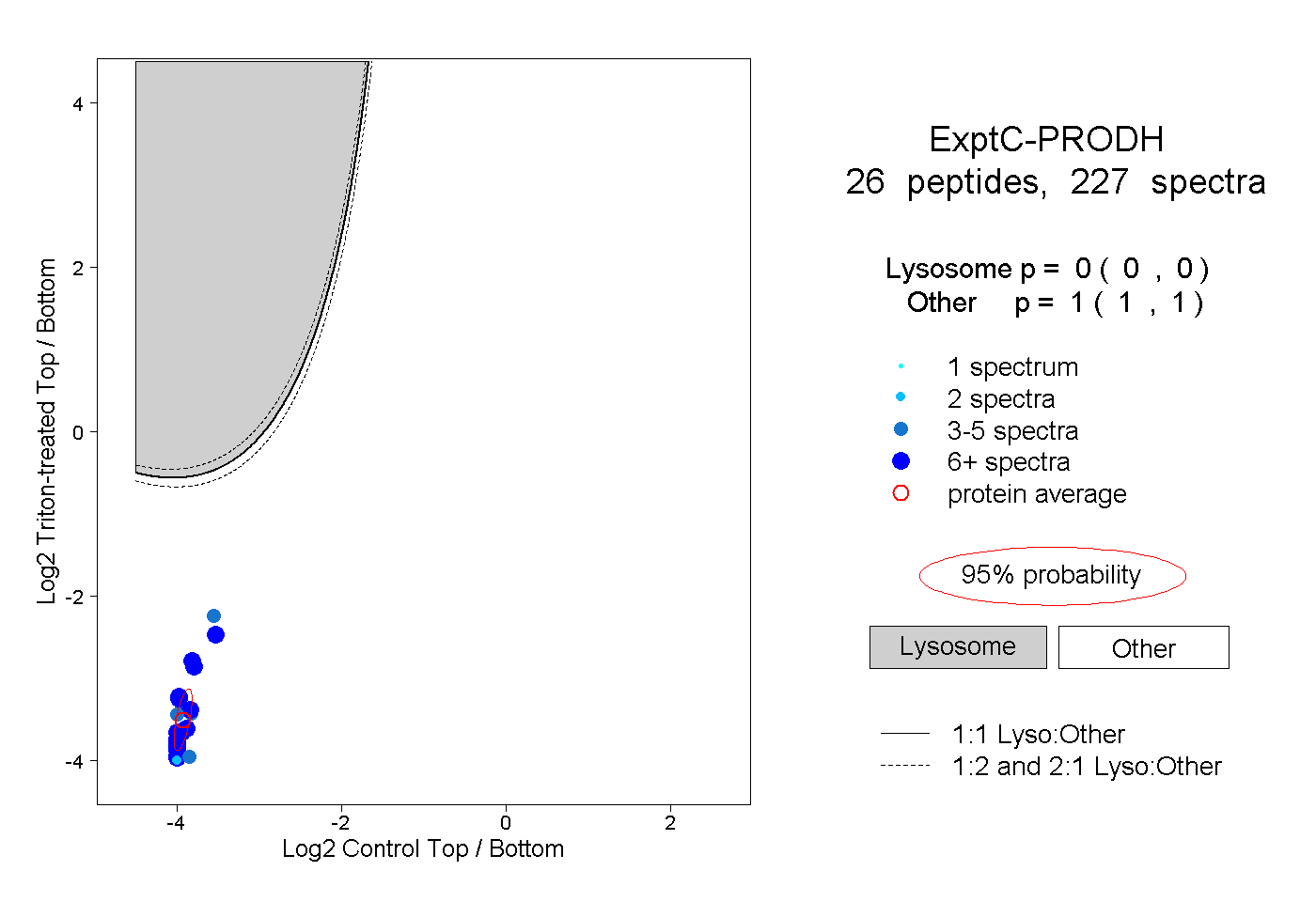 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
35 spectra |
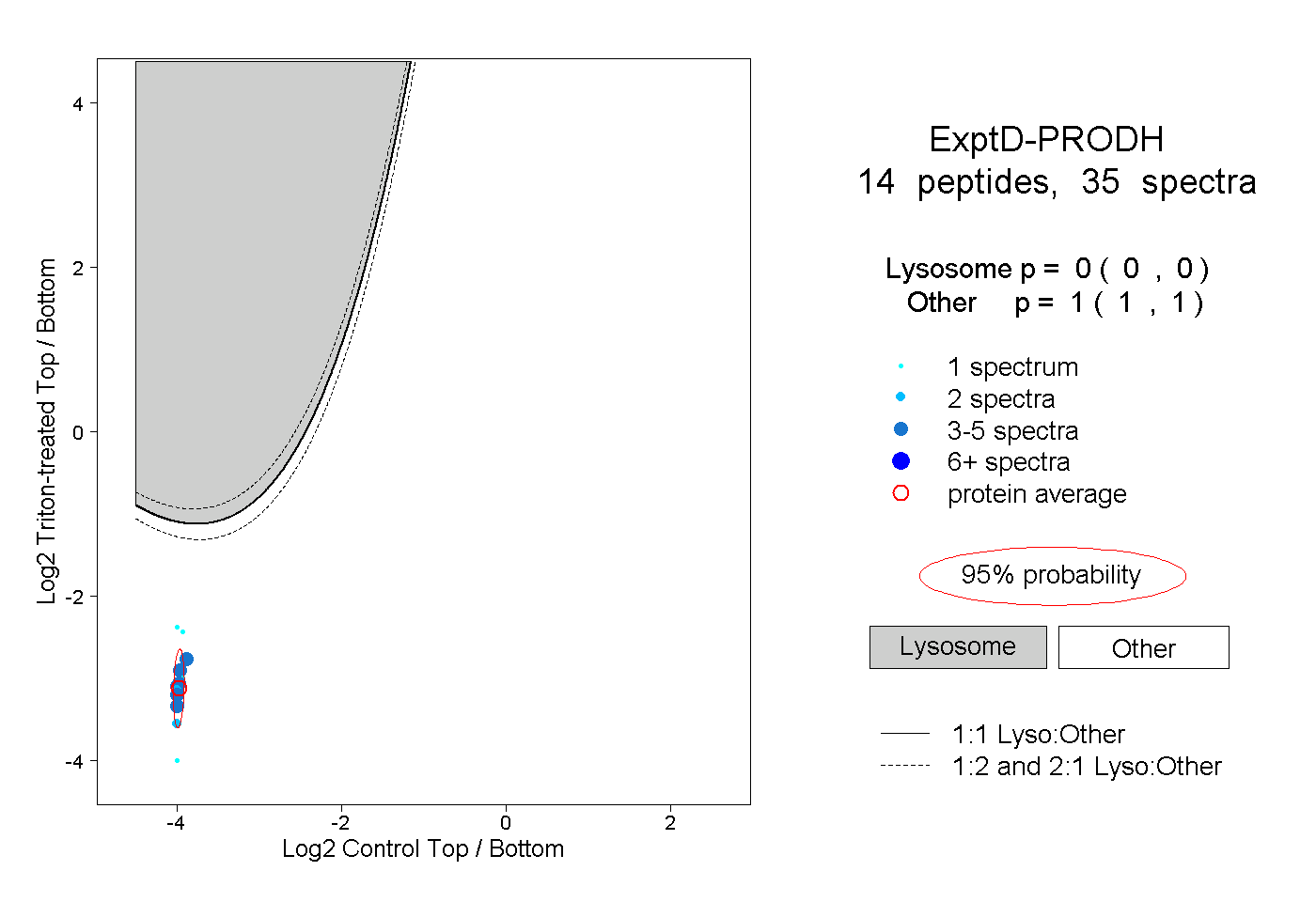 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |