peptides
spectra
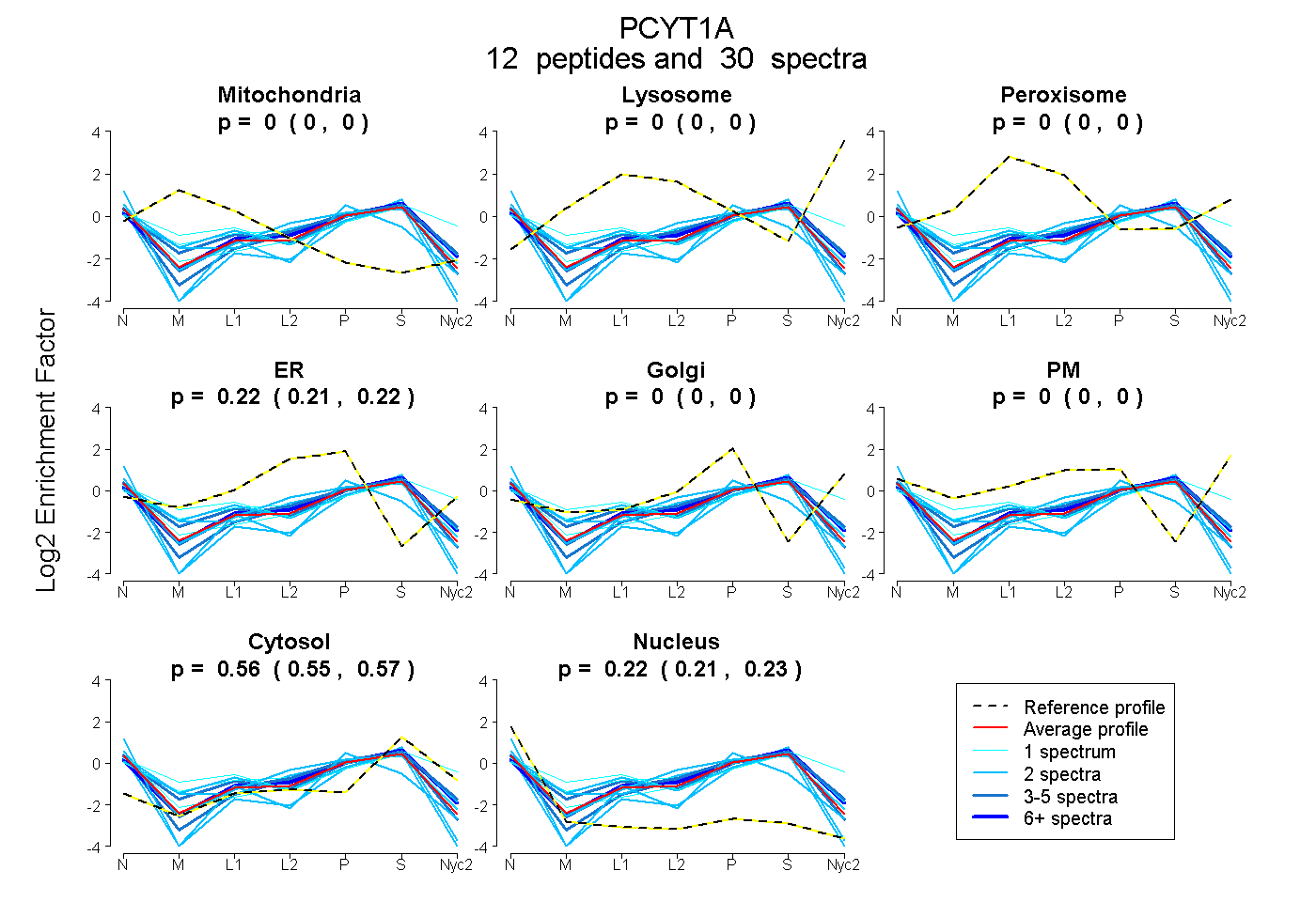
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.209 | 0.223
0.000 | 0.000
0.000 | 0.000
0.553 | 0.568
0.213 | 0.229
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
30 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.217 0.209 | 0.223 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.561 0.553 | 0.568 |
0.222 0.213 | 0.229 |
| 2 spectra, VYADGIFDLFHSGHAR | 0.142 | 0.000 | 0.000 | 0.130 | 0.000 | 0.000 | 0.472 | 0.256 | ||
| 1 spectrum, YVDEVVR | 0.211 | 0.000 | 0.034 | 0.138 | 0.000 | 0.000 | 0.511 | 0.106 | ||
| 2 spectra, GTPCERPVR | 0.000 | 0.000 | 0.000 | 0.280 | 0.000 | 0.000 | 0.590 | 0.131 | ||
| 4 spectra, TEGISTSDIITR | 0.000 | 0.000 | 0.000 | 0.254 | 0.000 | 0.000 | 0.594 | 0.152 | ||
| 1 spectrum, IDFVAHDDIPYSSAGSDDVYK | 0.000 | 0.000 | 0.019 | 0.062 | 0.032 | 0.257 | 0.619 | 0.011 | ||
| 3 spectra, DYDVYAR | 0.000 | 0.000 | 0.035 | 0.220 | 0.000 | 0.000 | 0.582 | 0.164 | ||
| 4 spectra, EAGMFAPTQR | 0.000 | 0.000 | 0.000 | 0.180 | 0.000 | 0.000 | 0.582 | 0.238 | ||
| 2 spectra, ELNVSFINEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.616 | 0.384 | ||
| 6 spectra, GFTVMNENER | 0.000 | 0.000 | 0.000 | 0.227 | 0.000 | 0.000 | 0.630 | 0.143 | ||
| 1 spectrum, QPAPFSDEIEVDFSKPYVR | 0.000 | 0.000 | 0.000 | 0.163 | 0.000 | 0.000 | 0.494 | 0.344 | ||
| 2 spectra, VTMEEACR | 0.000 | 0.000 | 0.000 | 0.292 | 0.000 | 0.000 | 0.516 | 0.192 | ||
| 2 spectra, TSPSSSPASLSR | 0.000 | 0.000 | 0.000 | 0.155 | 0.045 | 0.000 | 0.368 | 0.432 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
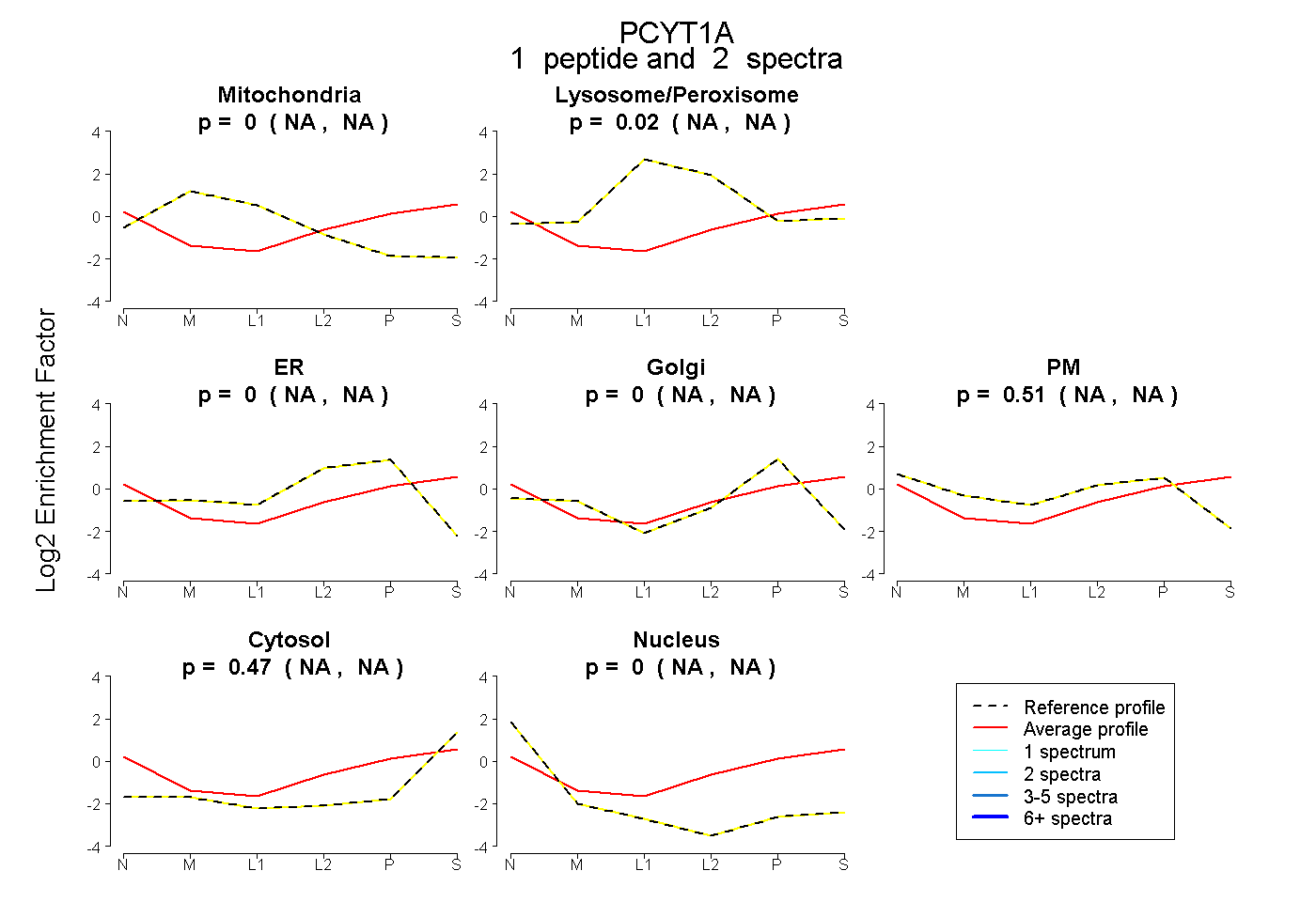 |
0.000 NA | NA |
0.018 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.509 NA | NA |
0.473 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
20 spectra |
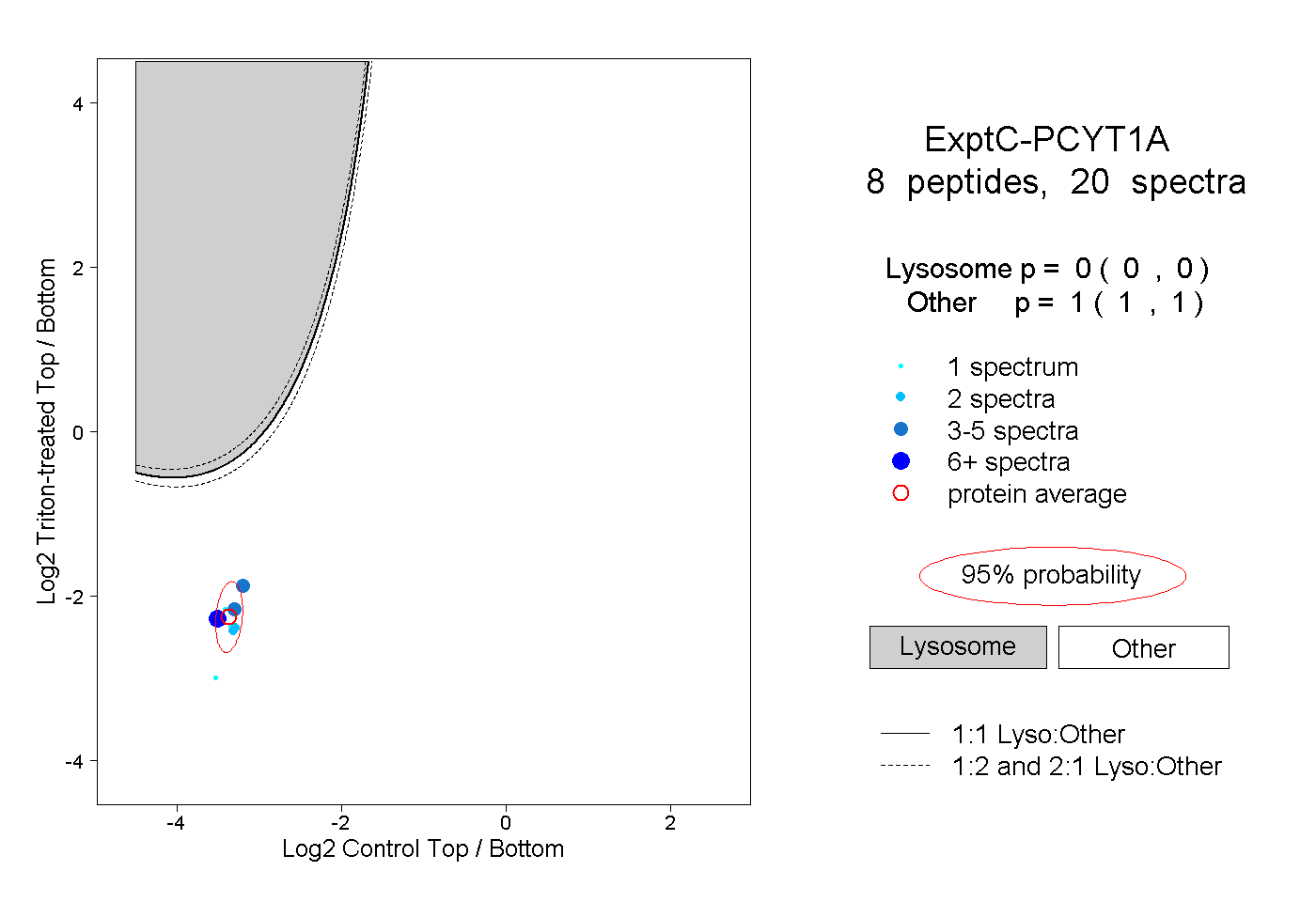 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |