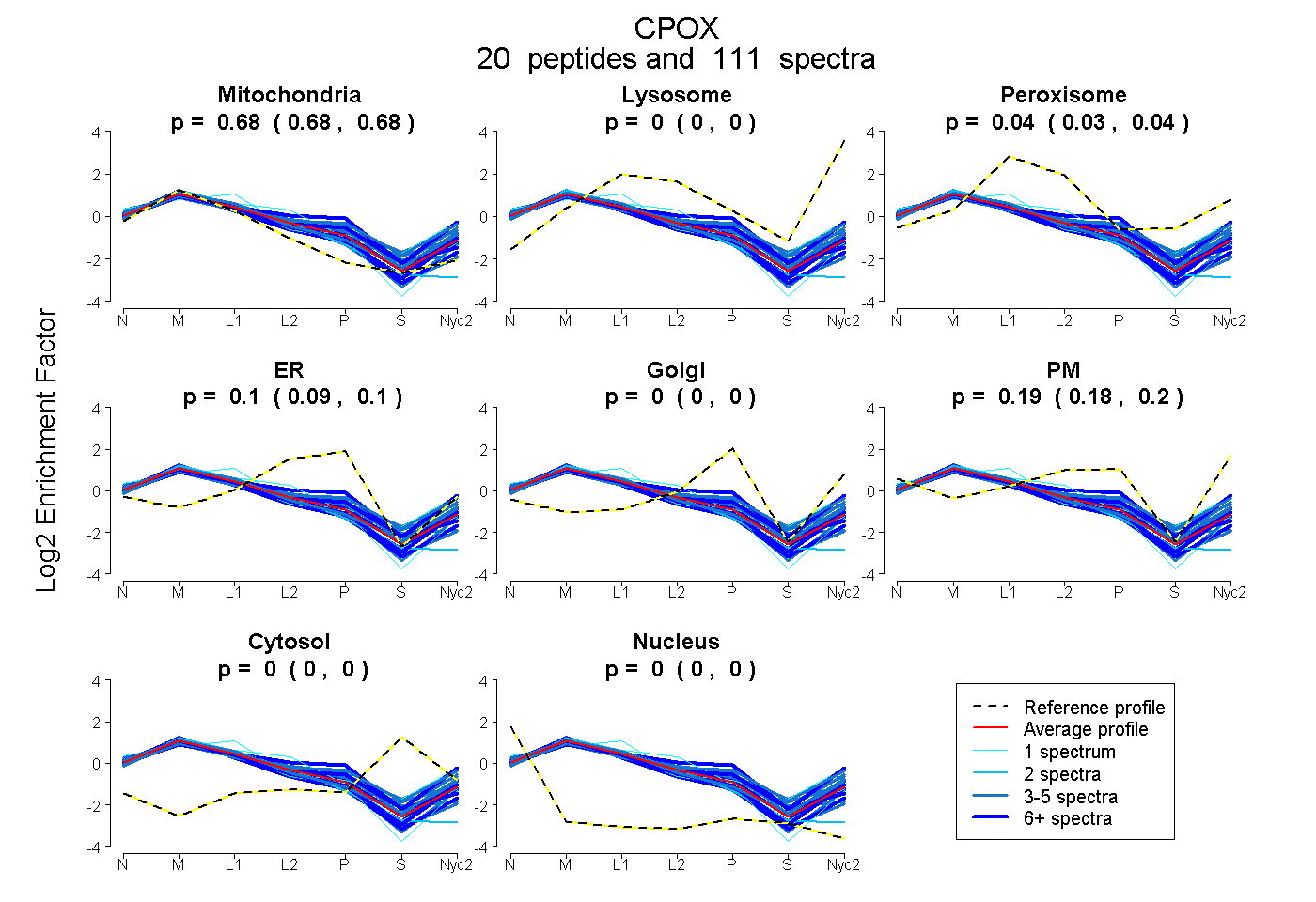
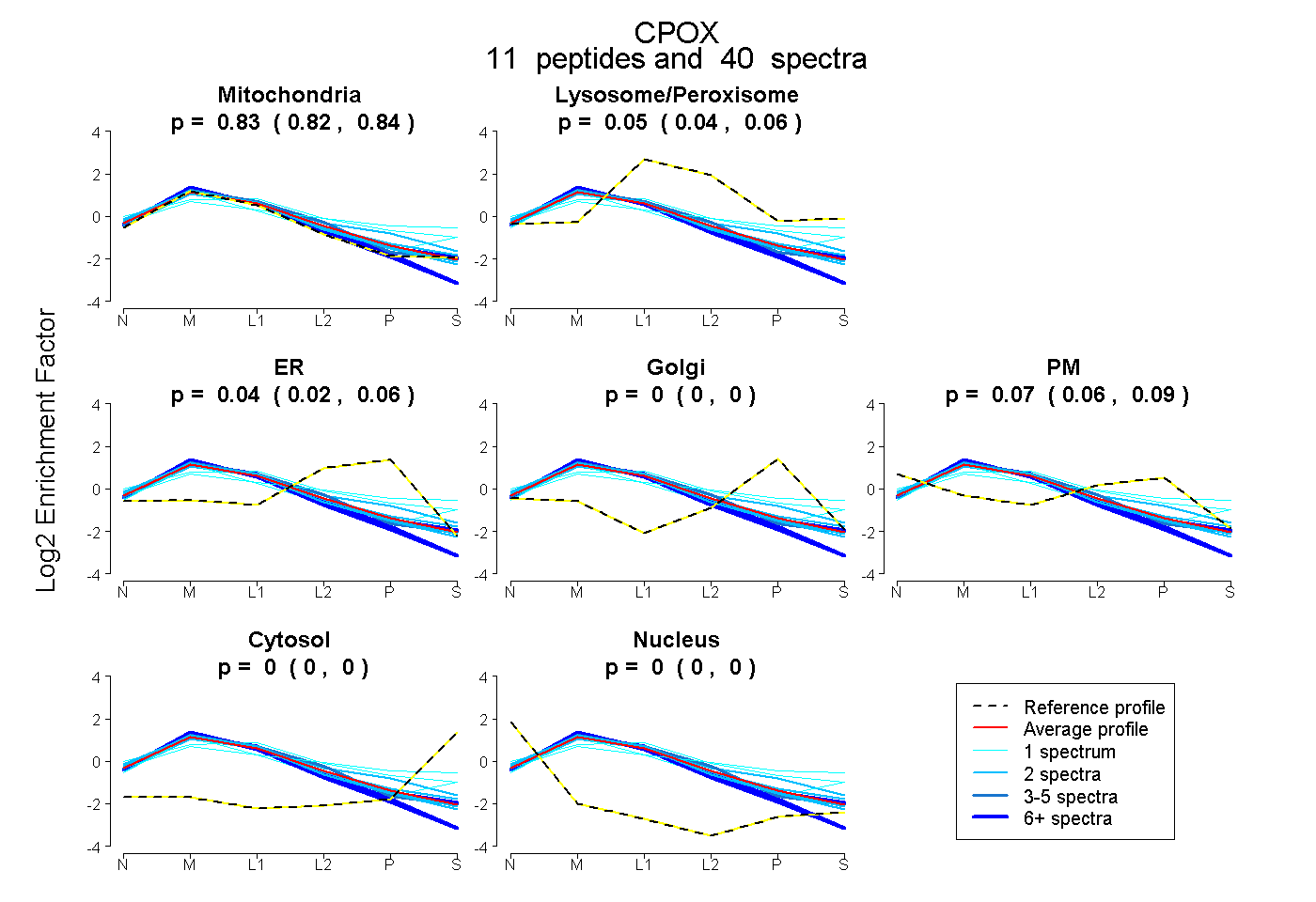
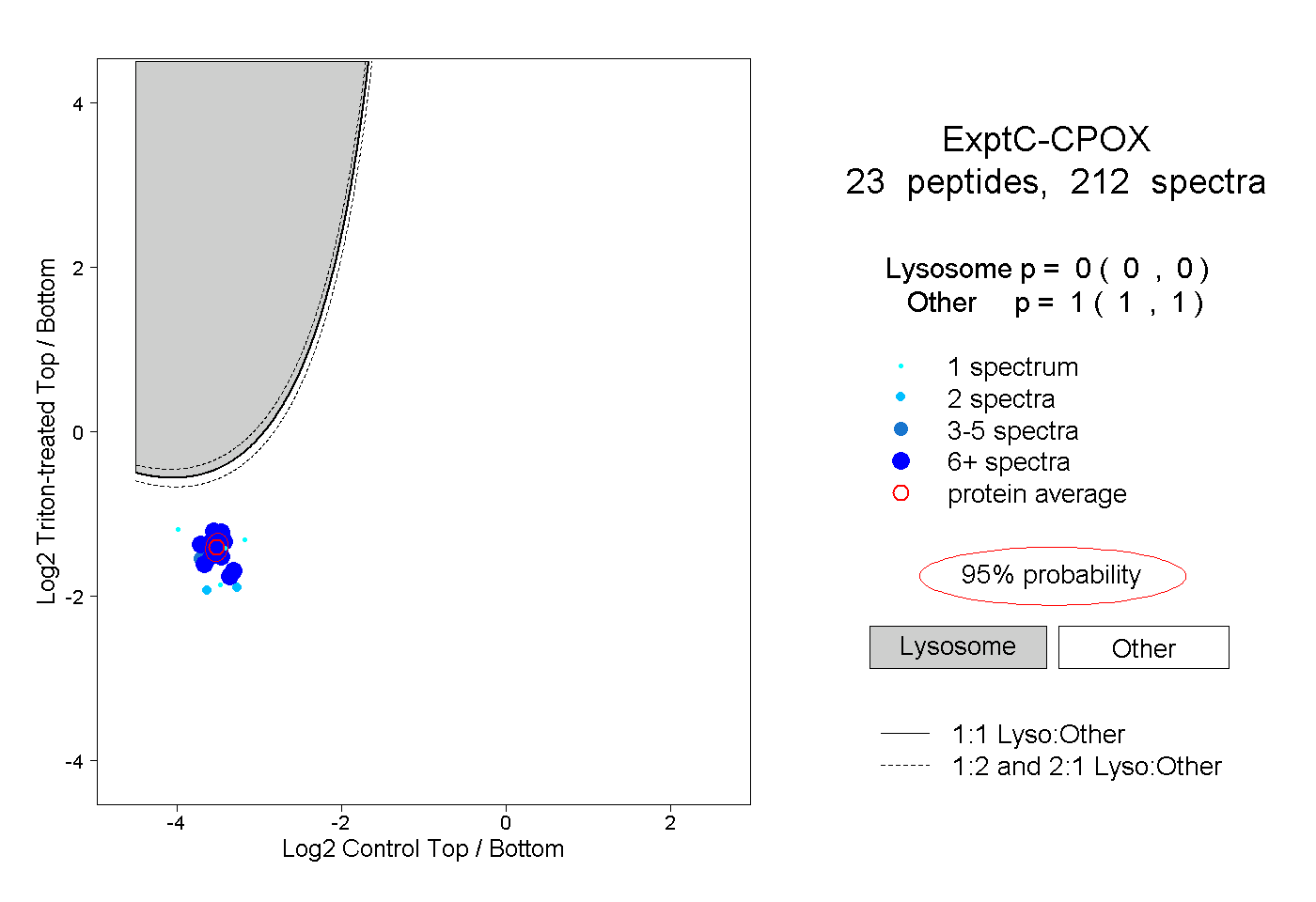
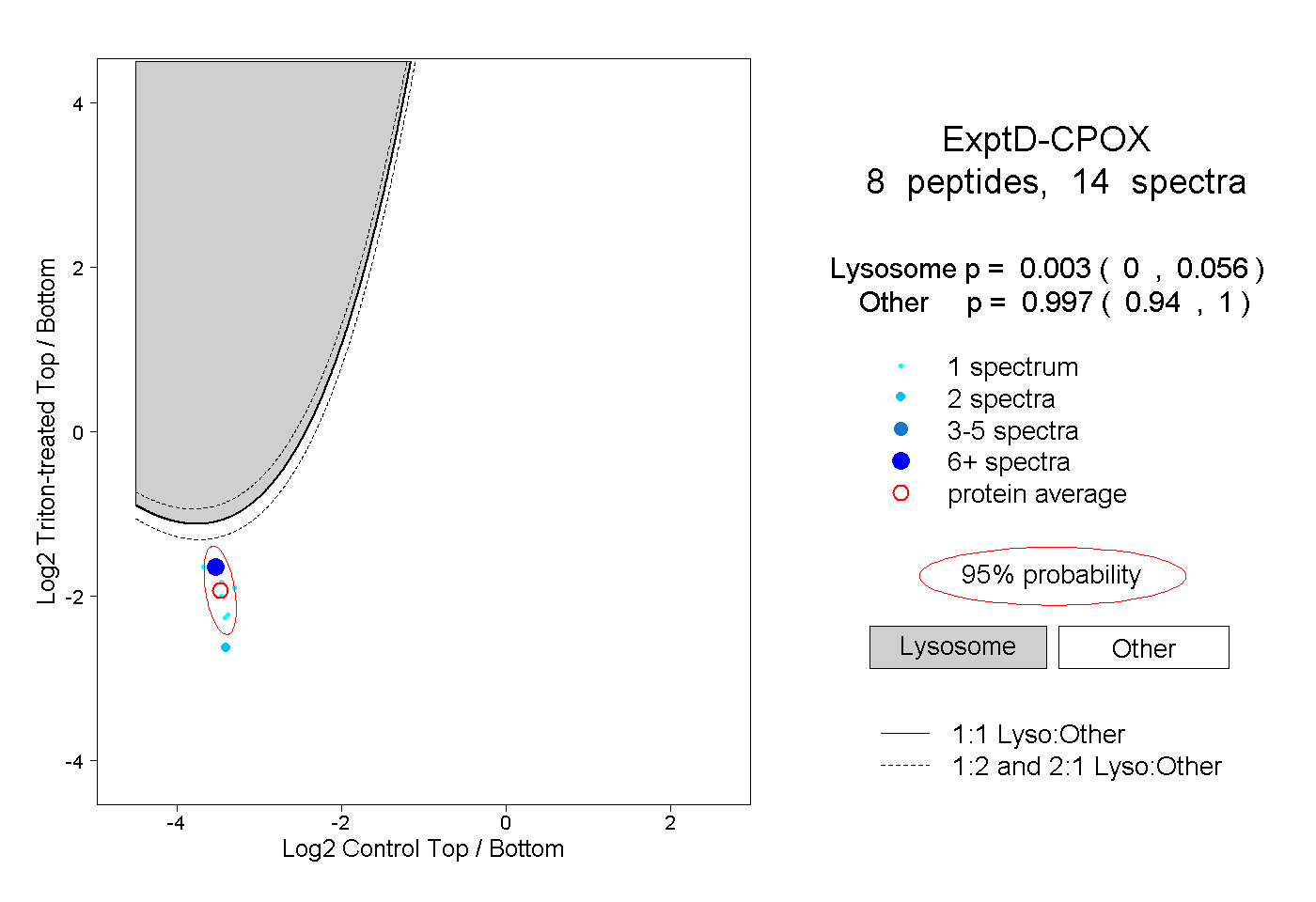
| 8 spectra, EDAVHFHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TCAEAVVPSYVPIVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, YFEVEEADGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, NPYAPTMHFNYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, IESILMSLPLTAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, AEMVPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ALAQVDGVADFSVDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, MELMIMETQAQVCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, LWQQLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, MHWWFGGGCDLTPTYLNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, HCDDSYTPQDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, YVEFNLVYDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, WCDDYFFIAHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, CSTFMSSPVTELR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, EGGGGITCVLQDGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, FGLFTPGSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, EACDQHGPDIYPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, WEYMHSPPENSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LEEDGDELAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GIGGIFFDDLDSPSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 27 spectra, EAEILEVLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AGVNISVVHGNLSEEAANQMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, RPDDMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |