peptides
spectra
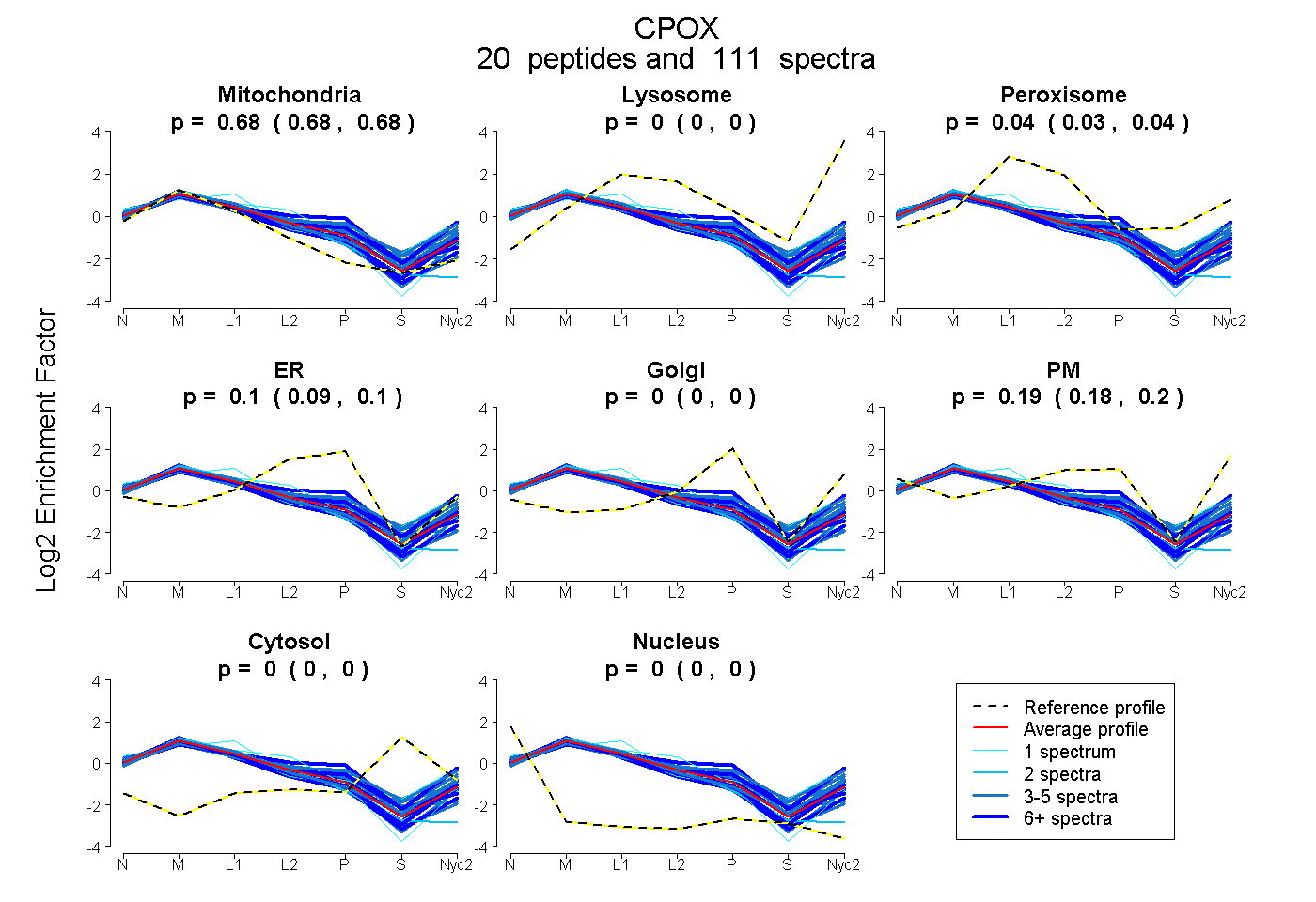
0.677 | 0.682
0.000 | 0.000
0.032 | 0.039
0.088 | 0.103
0.000 | 0.000
0.178 | 0.196
0.000 | 0.000
0.000 | 0.000
peptides
spectra
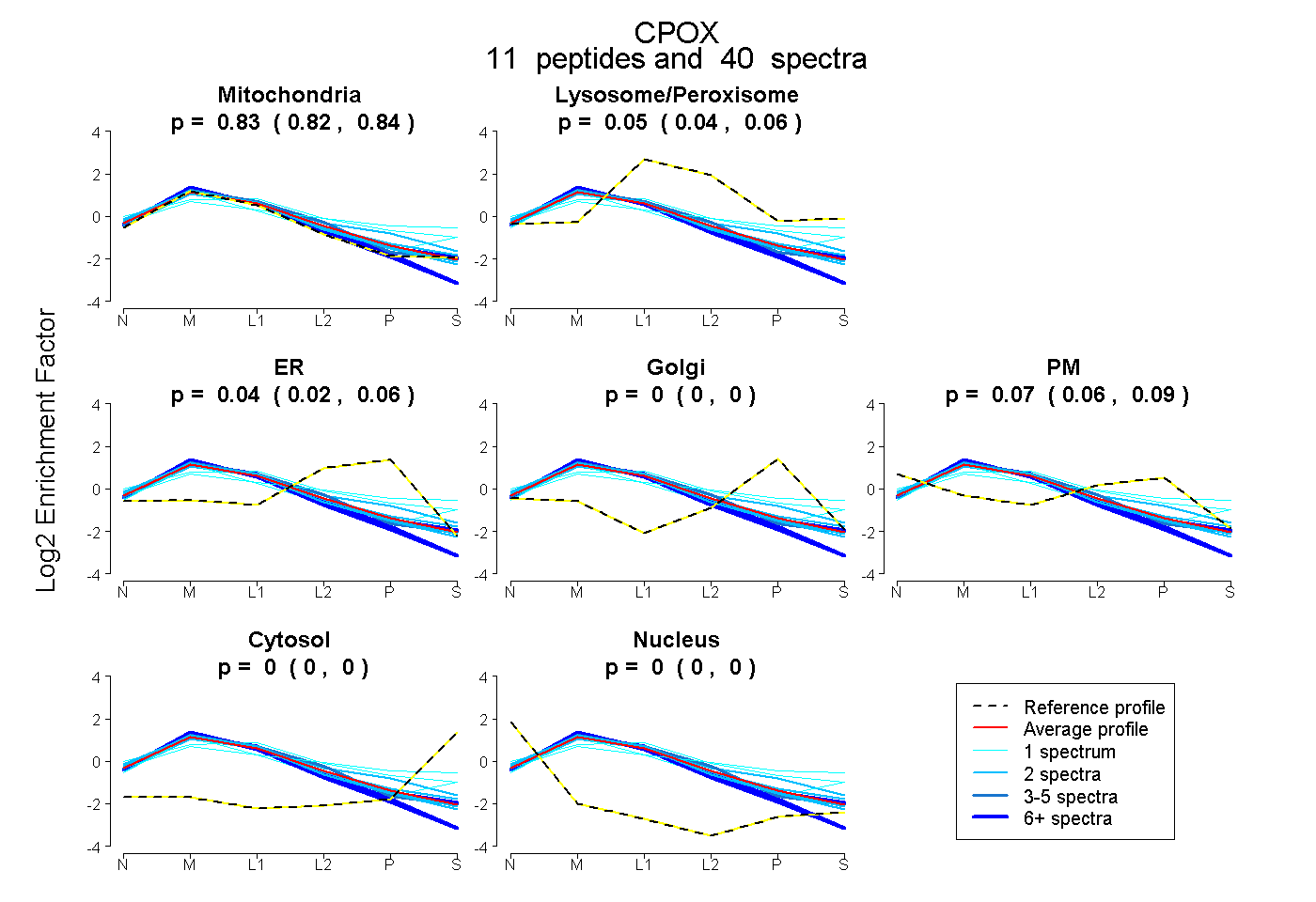
0.821 | 0.842
0.041 | 0.060
0.025 | 0.060
0.000 | 0.000
0.056 | 0.086
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
111 spectra |
 |
0.680 0.677 | 0.682 |
0.000 0.000 | 0.000 |
0.036 0.032 | 0.039 |
0.096 0.088 | 0.103 |
0.000 0.000 | 0.000 |
0.188 0.178 | 0.196 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
40 spectra |
 |
0.832 0.821 | 0.842 |
0.051 0.041 | 0.060 |
0.044 0.025 | 0.060 |
0.000 0.000 | 0.000 |
0.072 0.056 | 0.086 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, YVEFNLVYDR | 0.905 | 0.004 | 0.023 | 0.000 | 0.068 | 0.000 | 0.000 | |||
| 2 spectra, EDAVHFHR | 0.677 | 0.160 | 0.063 | 0.100 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, WCDDYFFIAHR | 0.794 | 0.081 | 0.000 | 0.000 | 0.124 | 0.000 | 0.000 | |||
| 1 spectrum, TCAEAVVPSYVPIVK | 0.368 | 0.308 | 0.000 | 0.150 | 0.068 | 0.106 | 0.000 | |||
| 2 spectra, YFEVEEADGK | 0.849 | 0.046 | 0.000 | 0.000 | 0.105 | 0.000 | 0.000 | |||
| 1 spectrum, EGGGGITCVLQDGR | 0.780 | 0.094 | 0.000 | 0.000 | 0.000 | 0.126 | 0.000 | |||
| 6 spectra, FGLFTPGSR | 0.997 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.003 | |||
| 10 spectra, LEEDGDELAR | 0.962 | 0.000 | 0.038 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, EAEILEVLR | 0.892 | 0.047 | 0.024 | 0.000 | 0.036 | 0.000 | 0.000 | |||
| 4 spectra, LWQQLR | 0.880 | 0.091 | 0.028 | 0.000 | 0.001 | 0.000 | 0.000 | |||
| 1 spectrum, HCDDSYTPQDK | 0.483 | 0.281 | 0.000 | 0.000 | 0.215 | 0.021 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
212 spectra |
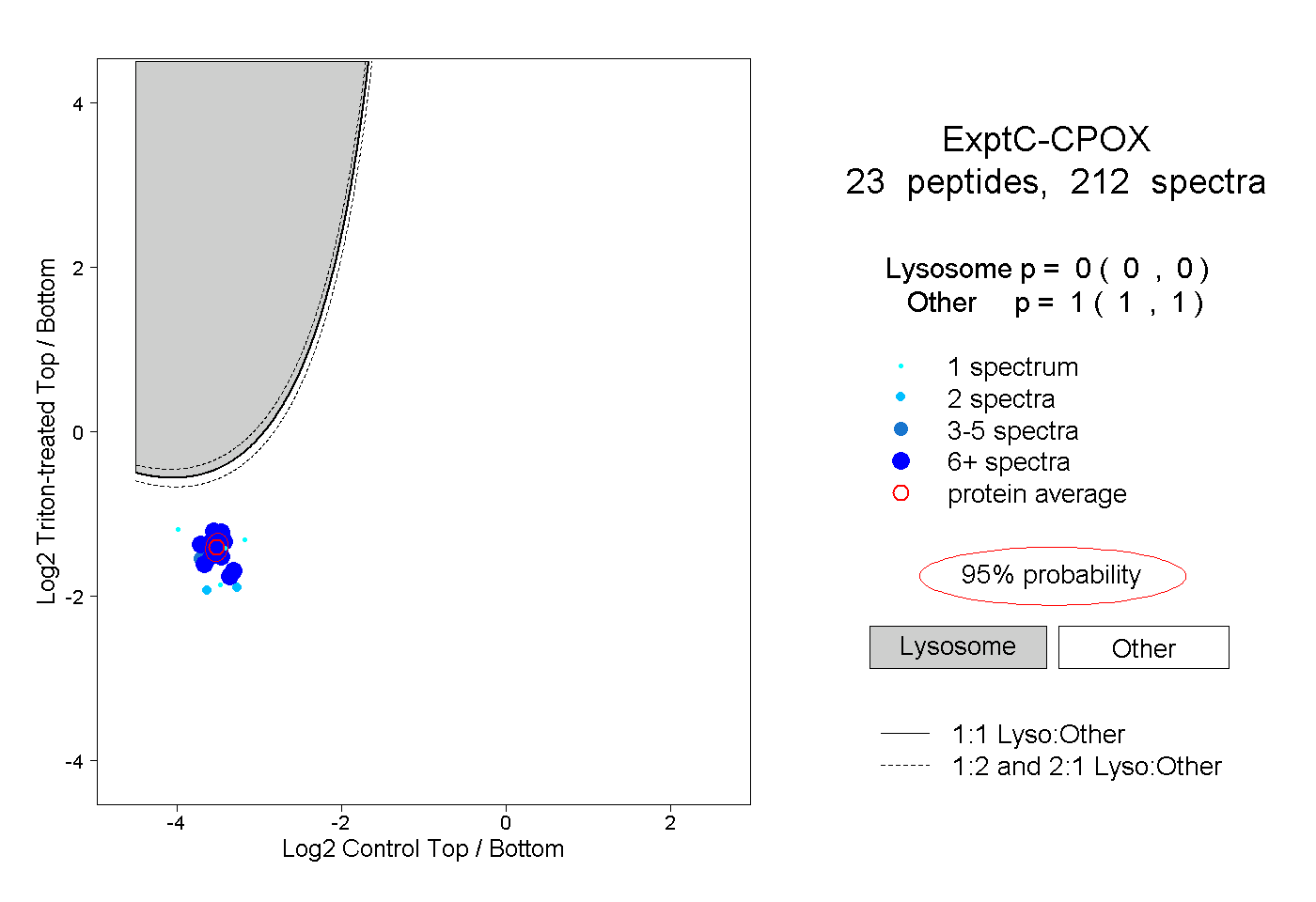 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
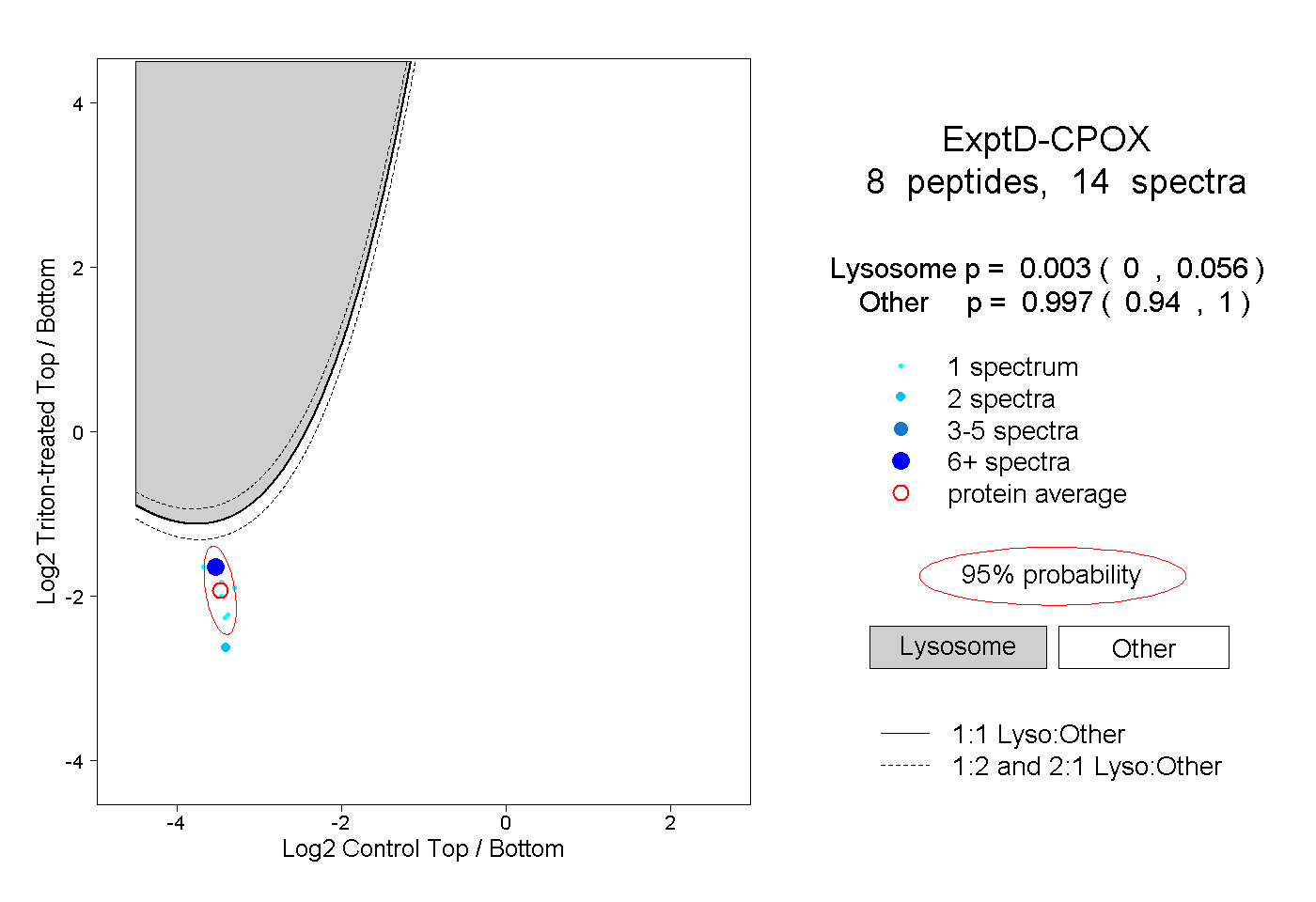 |
0.003 0.000 | 0.056 |
0.997 0.940 | 1.000 |