peptides
spectra
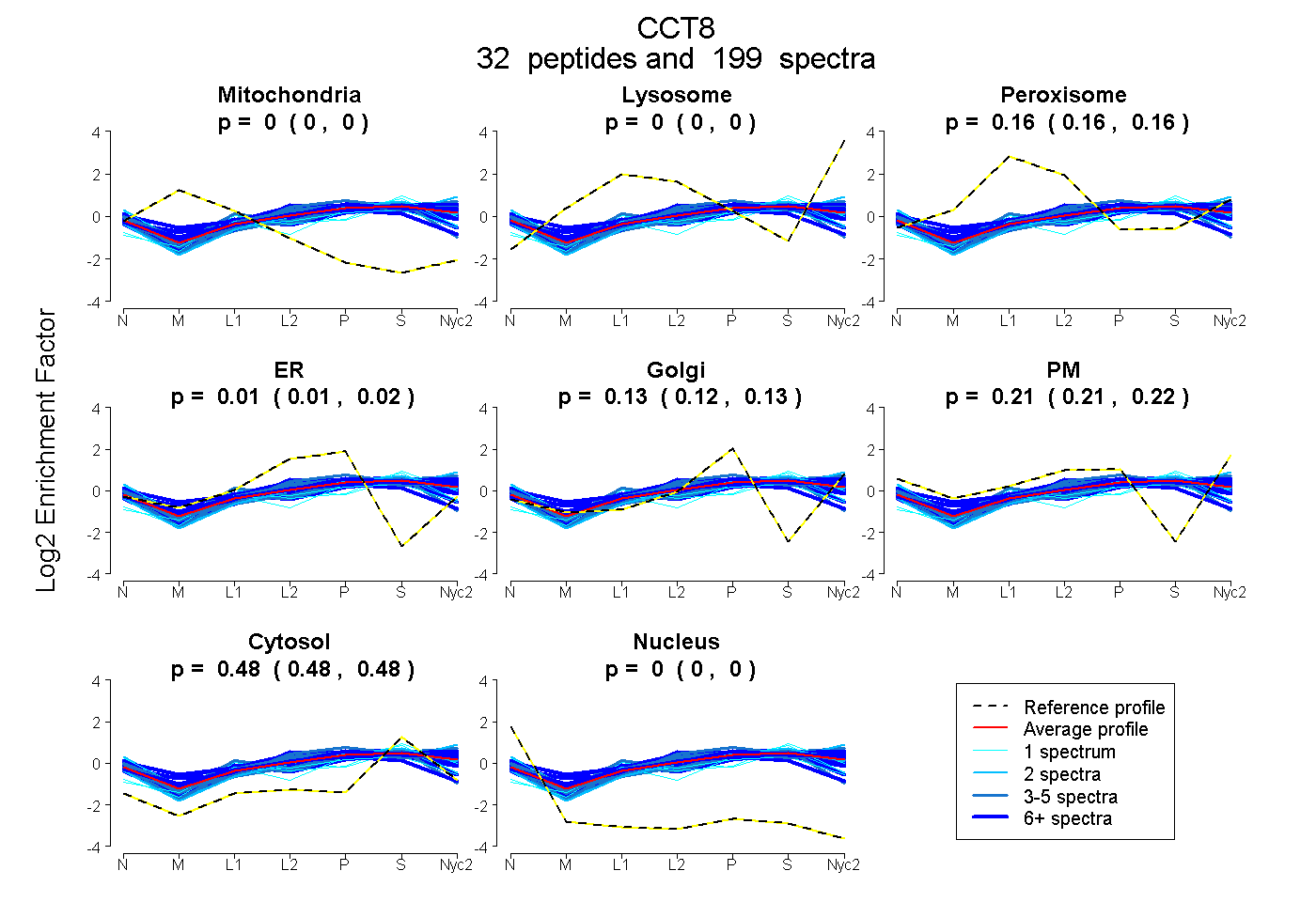
0.000 | 0.000
0.000 | 0.000
0.159 | 0.163
0.009 | 0.019
0.123 | 0.134
0.210 | 0.217
0.480 | 0.483
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
199 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.161 0.159 | 0.163 |
0.014 0.009 | 0.019 |
0.129 0.123 | 0.134 |
0.214 0.210 | 0.217 |
0.482 0.480 | 0.483 |
0.000 0.000 | 0.000 |
| 5 spectra, ETEGDVTSVK | 0.000 | 0.000 | 0.066 | 0.000 | 0.089 | 0.285 | 0.560 | 0.000 | ||
| 5 spectra, QYGSEEFLAK | 0.000 | 0.000 | 0.114 | 0.035 | 0.000 | 0.374 | 0.477 | 0.000 | ||
| 1 spectrum, AHEILPDLVCCSAK | 0.000 | 0.000 | 0.278 | 0.000 | 0.051 | 0.152 | 0.519 | 0.000 | ||
| 4 spectra, LYSVHQEGNK | 0.000 | 0.000 | 0.272 | 0.000 | 0.225 | 0.046 | 0.457 | 0.000 | ||
| 15 spectra, AVDDGVNTFK | 0.000 | 0.000 | 0.135 | 0.000 | 0.000 | 0.423 | 0.441 | 0.000 | ||
| 9 spectra, GEENLMDAQVK | 0.000 | 0.000 | 0.184 | 0.000 | 0.270 | 0.046 | 0.500 | 0.000 | ||
| 4 spectra, TAYGPNGMNK | 0.000 | 0.069 | 0.055 | 0.222 | 0.042 | 0.147 | 0.464 | 0.000 | ||
| 5 spectra, EDGAISTIVLR | 0.000 | 0.027 | 0.058 | 0.000 | 0.000 | 0.383 | 0.531 | 0.000 | ||
| 9 spectra, DVDEVSSLLR | 0.000 | 0.000 | 0.110 | 0.000 | 0.065 | 0.333 | 0.493 | 0.000 | ||
| 1 spectrum, ILGSGVYSSSVLHGMVFK | 0.000 | 0.028 | 0.261 | 0.000 | 0.112 | 0.000 | 0.599 | 0.000 | ||
| 3 spectra, TVGATALPK | 0.000 | 0.000 | 0.125 | 0.035 | 0.040 | 0.365 | 0.434 | 0.000 | ||
| 4 spectra, LFVTNDAATILR | 0.000 | 0.000 | 0.087 | 0.131 | 0.000 | 0.268 | 0.514 | 0.000 | ||
| 8 spectra, APGFAQMLK | 0.000 | 0.000 | 0.194 | 0.083 | 0.180 | 0.090 | 0.454 | 0.000 | ||
| 1 spectrum, TAEELMNFSK | 0.000 | 0.000 | 0.182 | 0.000 | 0.217 | 0.000 | 0.601 | 0.000 | ||
| 29 spectra, GSTDNLMDDIER | 0.000 | 0.040 | 0.116 | 0.000 | 0.170 | 0.183 | 0.492 | 0.000 | ||
| 8 spectra, VADMALHYANK | 0.000 | 0.000 | 0.176 | 0.000 | 0.112 | 0.231 | 0.481 | 0.000 | ||
| 11 spectra, LATNAAVTVLR | 0.000 | 0.022 | 0.086 | 0.018 | 0.000 | 0.414 | 0.460 | 0.000 | ||
| 11 spectra, YNIMLVR | 0.000 | 0.004 | 0.195 | 0.000 | 0.230 | 0.147 | 0.424 | 0.000 | ||
| 6 spectra, LVPGGGATEIELAK | 0.000 | 0.074 | 0.092 | 0.000 | 0.089 | 0.268 | 0.477 | 0.000 | ||
| 7 spectra, NIQACK | 0.059 | 0.000 | 0.189 | 0.348 | 0.000 | 0.000 | 0.404 | 0.000 | ||
| 5 spectra, ALAENSGVK | 0.000 | 0.106 | 0.116 | 0.000 | 0.103 | 0.223 | 0.451 | 0.000 | ||
| 2 spectra, AIAGTGANVIVTGGK | 0.000 | 0.000 | 0.071 | 0.110 | 0.000 | 0.282 | 0.537 | 0.000 | ||
| 1 spectrum, QITSYGETCPGLEQYAIK | 0.000 | 0.000 | 0.146 | 0.155 | 0.000 | 0.174 | 0.481 | 0.044 | ||
| 11 spectra, ELAQTTR | 0.000 | 0.000 | 0.105 | 0.095 | 0.000 | 0.273 | 0.527 | 0.000 | ||
| 4 spectra, ANEVISK | 0.000 | 0.053 | 0.010 | 0.000 | 0.000 | 0.447 | 0.490 | 0.000 | ||
| 2 spectra, GTVLIK | 0.000 | 0.000 | 0.180 | 0.133 | 0.156 | 0.000 | 0.530 | 0.000 | ||
| 7 spectra, FAEAFEAIPR | 0.000 | 0.045 | 0.060 | 0.043 | 0.000 | 0.393 | 0.459 | 0.000 | ||
| 6 spectra, IAVYSCPFDGMITETK | 0.000 | 0.000 | 0.193 | 0.172 | 0.124 | 0.000 | 0.511 | 0.000 | ||
| 2 spectra, DMLEASILDTYLGK | 0.000 | 0.014 | 0.104 | 0.000 | 0.000 | 0.469 | 0.413 | 0.000 | ||
| 2 spectra, TSIMSK | 0.000 | 0.001 | 0.084 | 0.089 | 0.104 | 0.156 | 0.565 | 0.000 | ||
| 4 spectra, IGLSVSEVITGYEIACK | 0.000 | 0.000 | 0.092 | 0.295 | 0.000 | 0.000 | 0.613 | 0.000 | ||
| 7 spectra, HFSGLEEAVYR | 0.000 | 0.001 | 0.205 | 0.000 | 0.095 | 0.227 | 0.473 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
56 spectra |
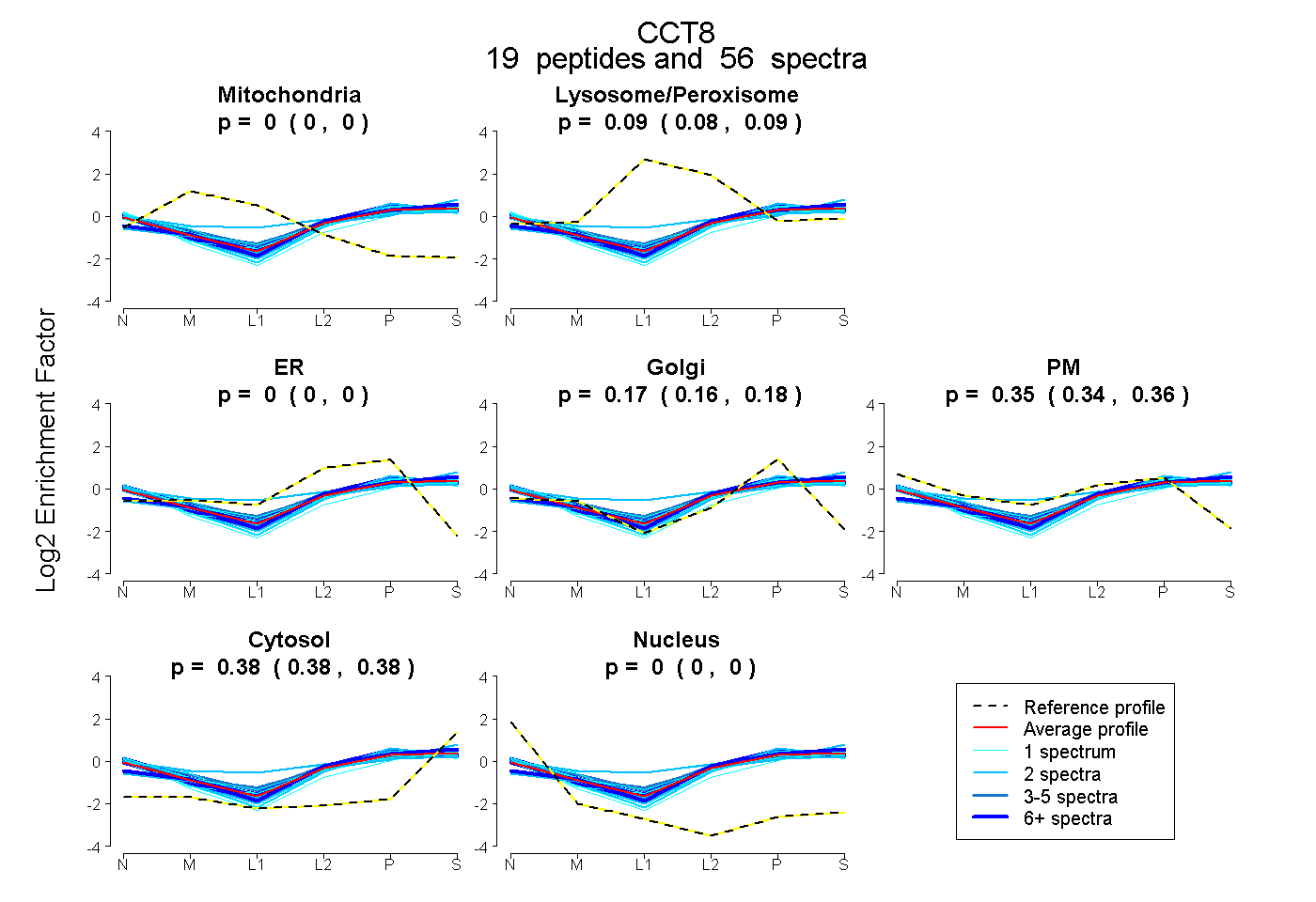 |
0.000 0.000 | 0.000 |
0.089 0.084 | 0.094 |
0.000 0.000 | 0.000 |
0.173 0.164 | 0.180 |
0.355 0.343 | 0.364 |
0.383 0.381 | 0.385 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
255 spectra |
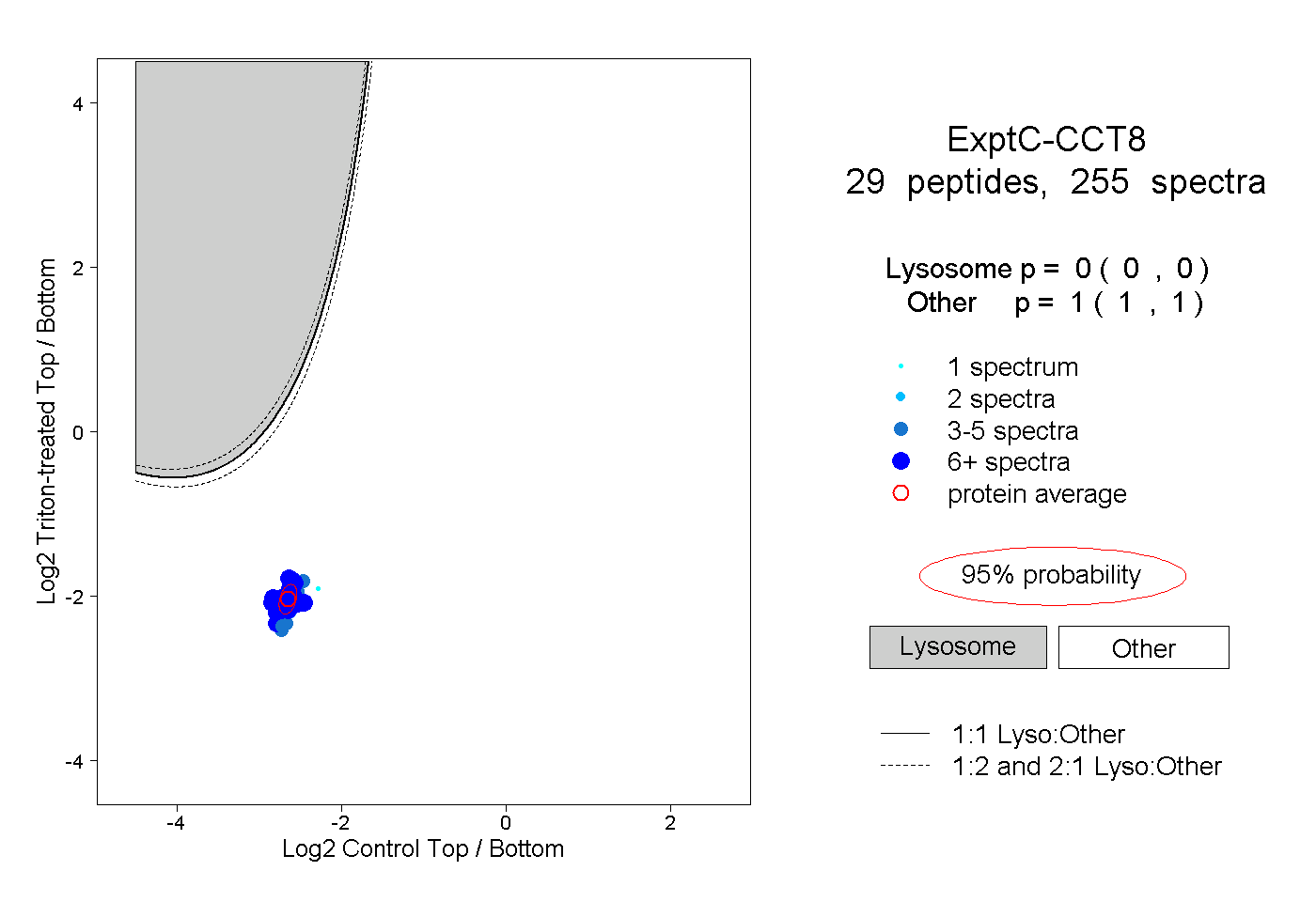 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
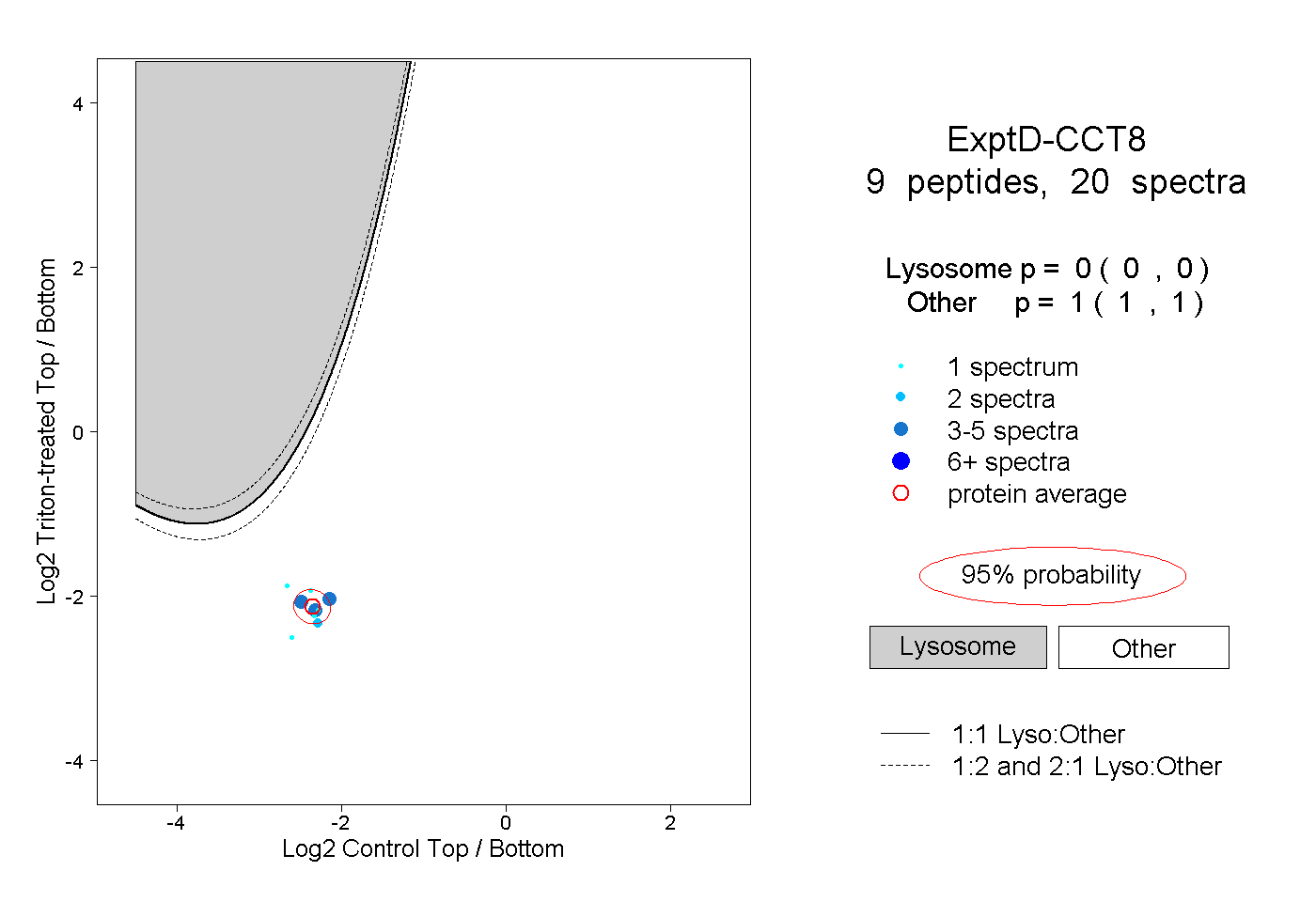 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |