peptides
spectra
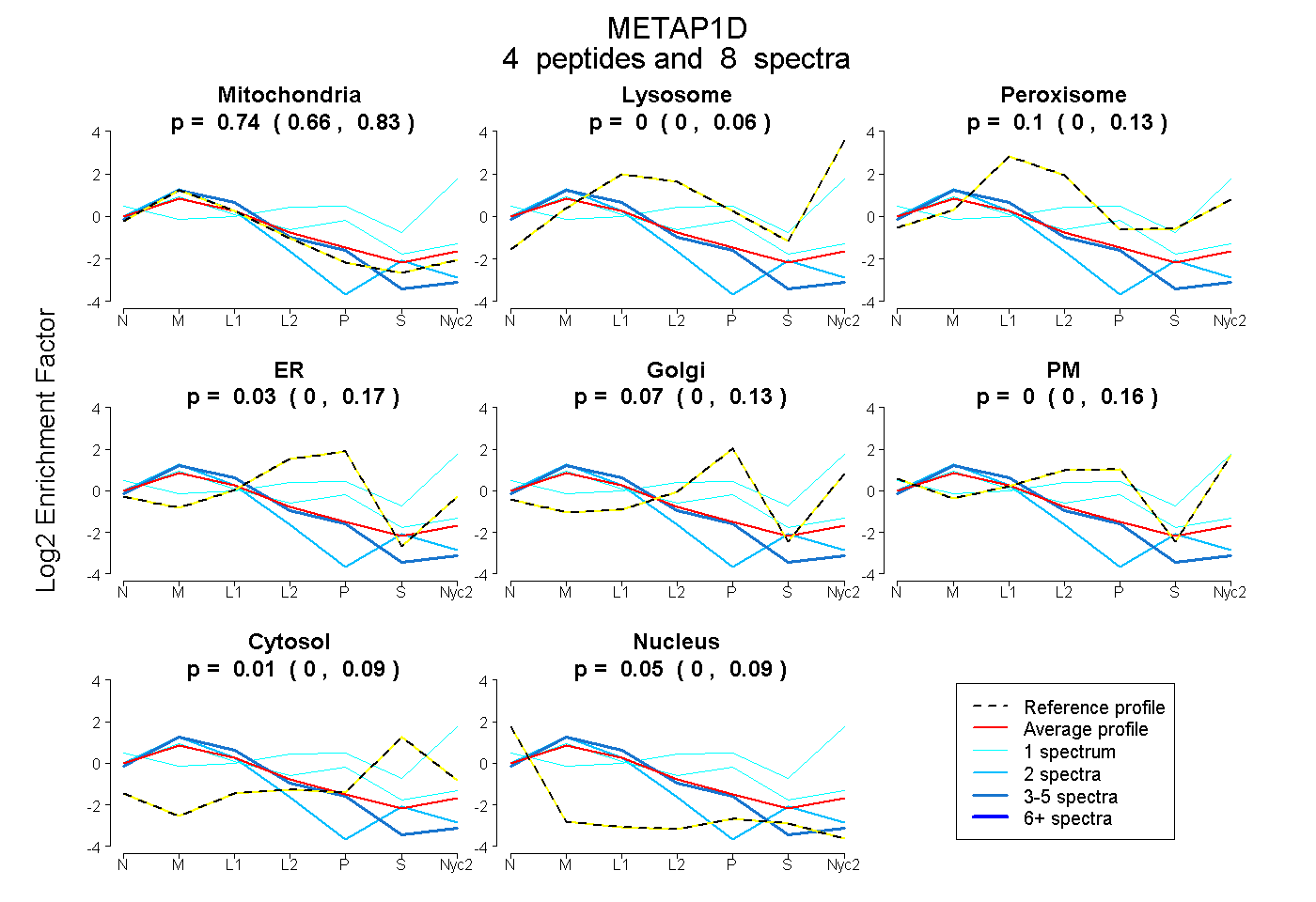
0.657 | 0.827
0.000 | 0.061
0.000 | 0.132
0.000 | 0.172
0.000 | 0.125
0.000 | 0.157
0.000 | 0.091
0.000 | 0.095
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
8 spectra |
 |
0.741 0.657 | 0.827 |
0.000 0.000 | 0.061 |
0.102 0.000 | 0.132 |
0.027 0.000 | 0.172 |
0.068 0.000 | 0.125 |
0.000 0.000 | 0.157 |
0.014 0.000 | 0.091 |
0.048 0.000 | 0.095 |
| 1 spectrum, SAQFEHTVLITPR | 0.595 | 0.000 | 0.065 | 0.064 | 0.255 | 0.000 | 0.021 | 0.000 | ||
| 4 spectra, VGMTTEEIDALVHR | 0.964 | 0.000 | 0.000 | 0.022 | 0.000 | 0.000 | 0.000 | 0.014 | ||
| 1 spectrum, MAAPIGVHLLVR | 0.000 | 0.166 | 0.000 | 0.000 | 0.000 | 0.627 | 0.208 | 0.000 | ||
| 2 spectra, LVEVAR | 0.909 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.091 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
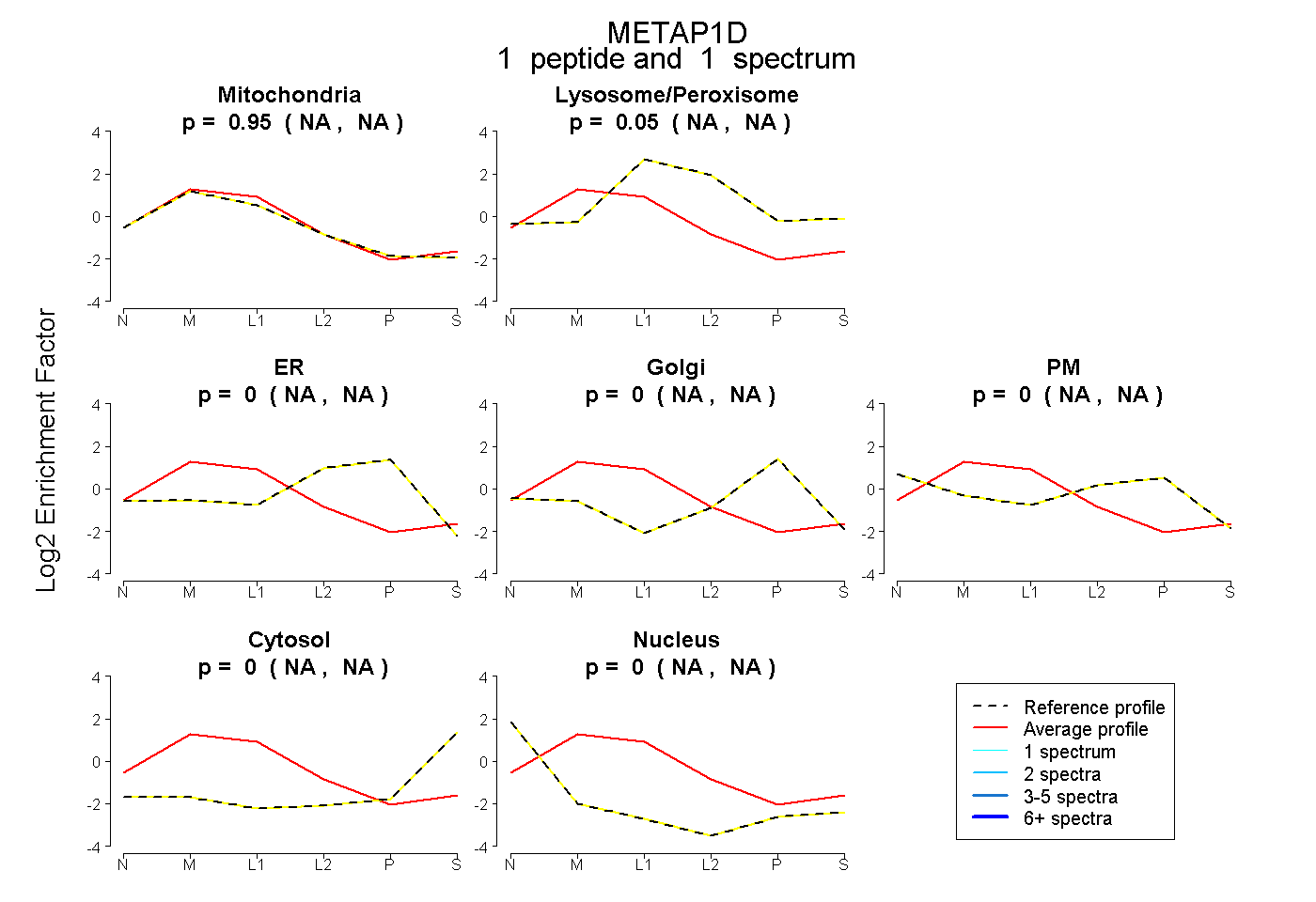 |
0.953 NA | NA |
0.047 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
30 spectra |
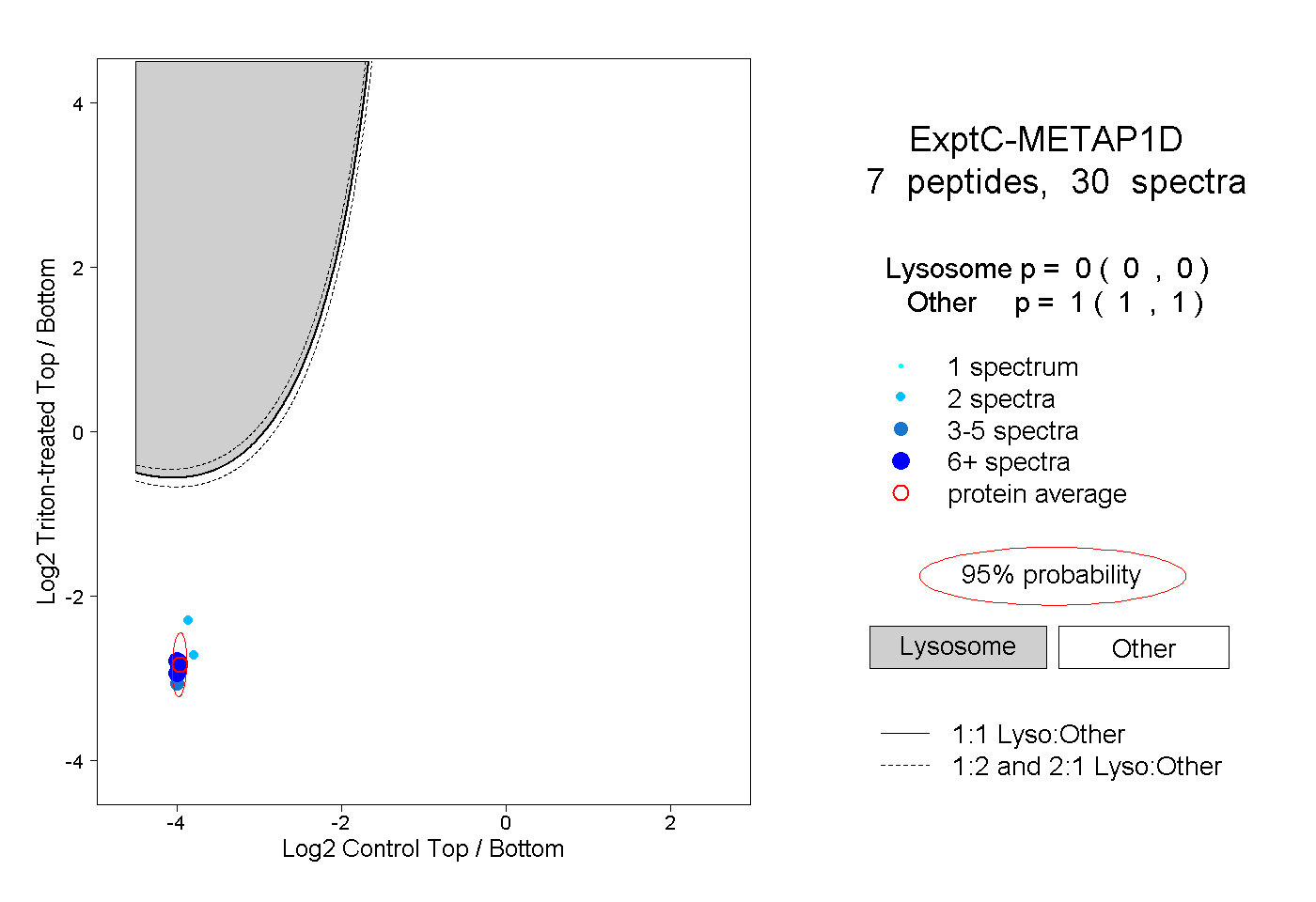 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
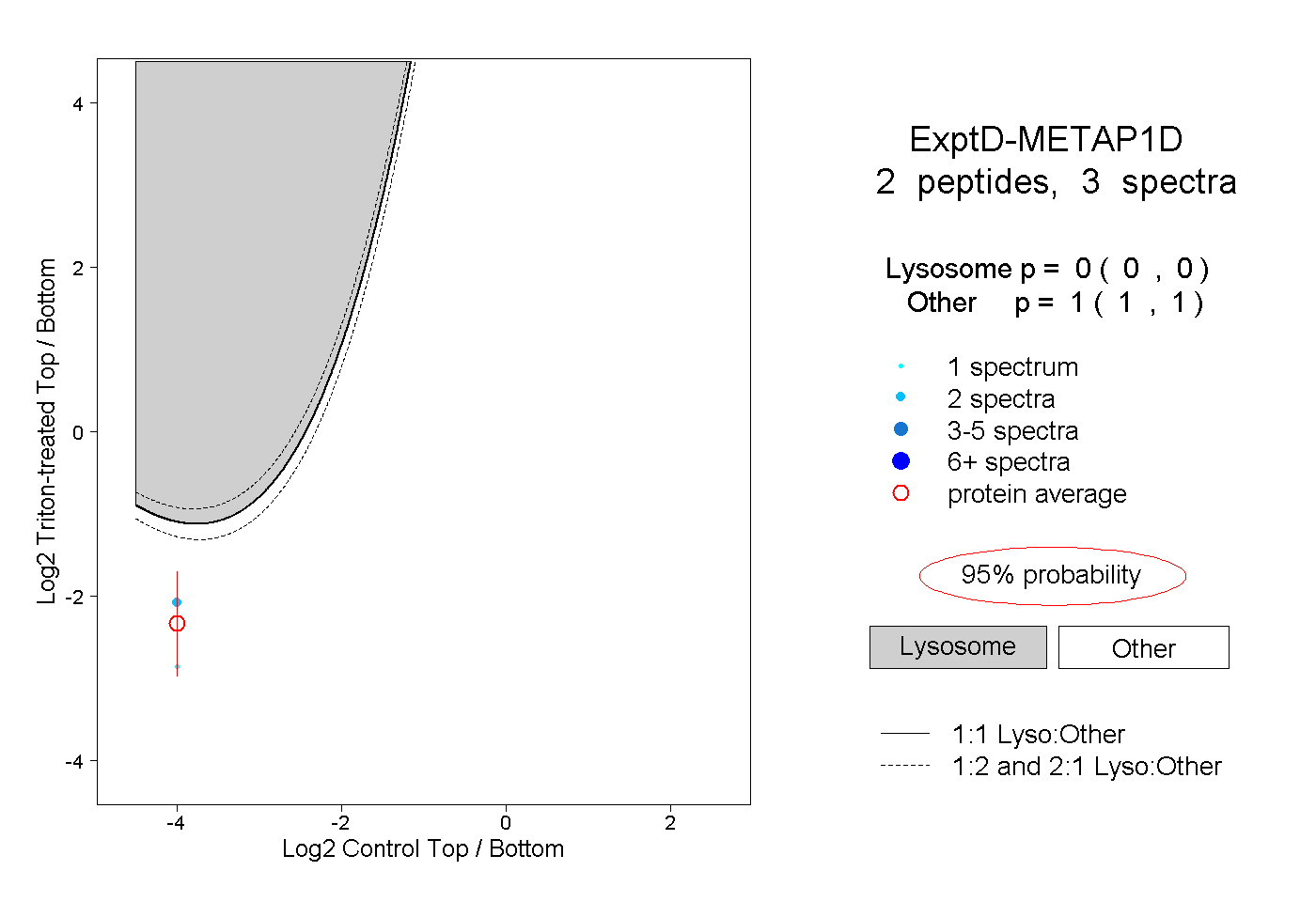 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |