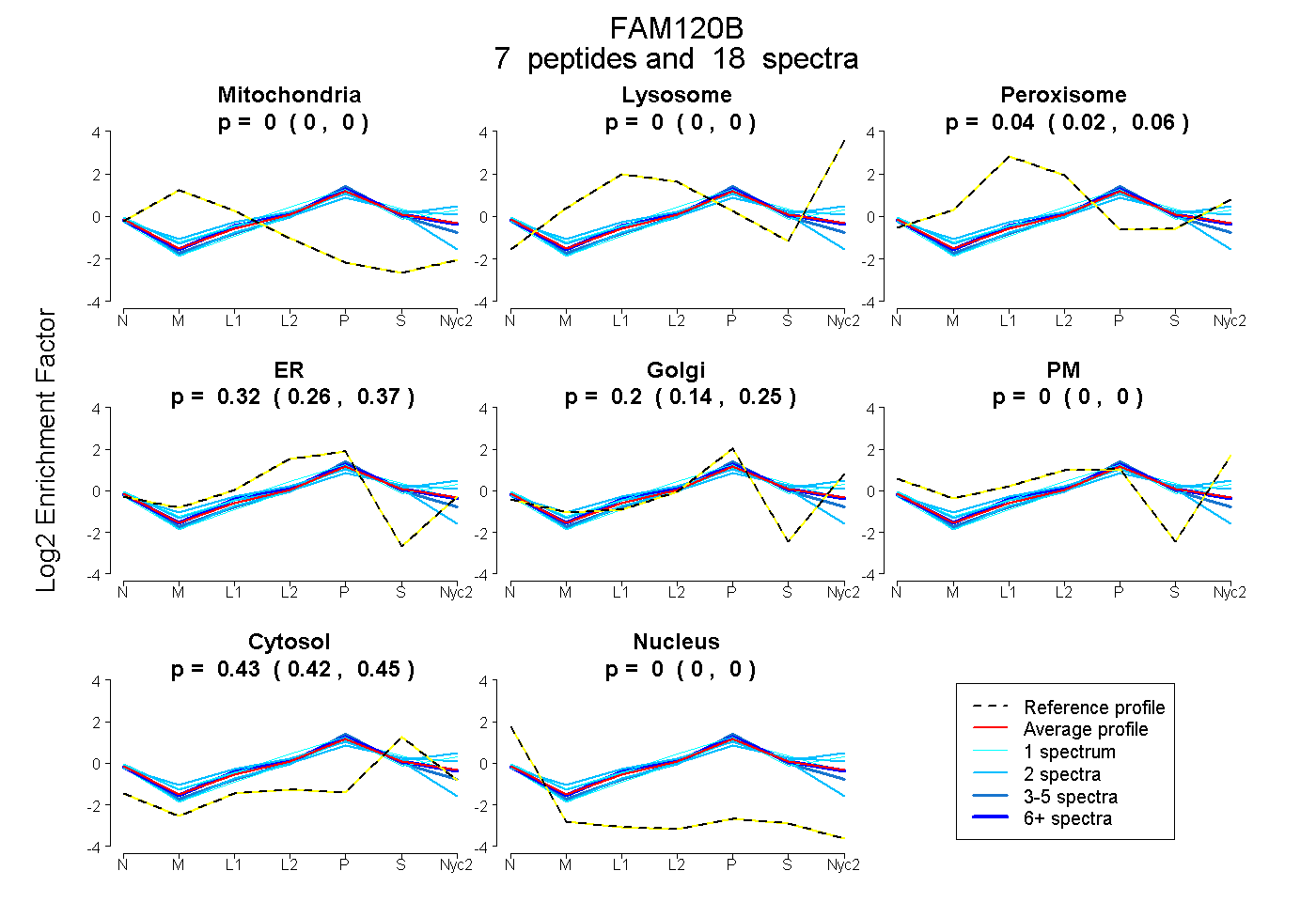
peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.025 | 0.061
0.256 | 0.375
0.143 | 0.247
0.000 | 0.000
0.416 | 0.445
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
18 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.045 0.025 | 0.061 |
0.323 0.256 | 0.375 |
0.200 0.143 | 0.247 |
0.000 0.000 | 0.000 |
0.432 0.416 | 0.445 |
0.000 0.000 | 0.000 |
| 2 spectra, QEDAMDMEPEIK | 0.000 | 0.000 | 0.118 | 0.078 | 0.238 | 0.141 | 0.424 | 0.000 | ||
| 6 spectra, IFHYIK | 0.000 | 0.000 | 0.051 | 0.343 | 0.184 | 0.000 | 0.422 | 0.000 | ||
| 2 spectra, VLHLYQGEK | 0.000 | 0.011 | 0.206 | 0.000 | 0.387 | 0.073 | 0.322 | 0.000 | ||
| 4 spectra, AVQLGSLLVR | 0.000 | 0.000 | 0.000 | 0.415 | 0.134 | 0.000 | 0.451 | 0.000 | ||
| 2 spectra, EELQSVESPLR | 0.000 | 0.000 | 0.000 | 0.487 | 0.000 | 0.000 | 0.482 | 0.031 | ||
| 1 spectrum, GVTSYLLPGQK | 0.000 | 0.000 | 0.000 | 0.320 | 0.163 | 0.000 | 0.517 | 0.000 | ||
| 1 spectrum, SWLTTFHNLK | 0.000 | 0.000 | 0.093 | 0.174 | 0.245 | 0.168 | 0.320 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
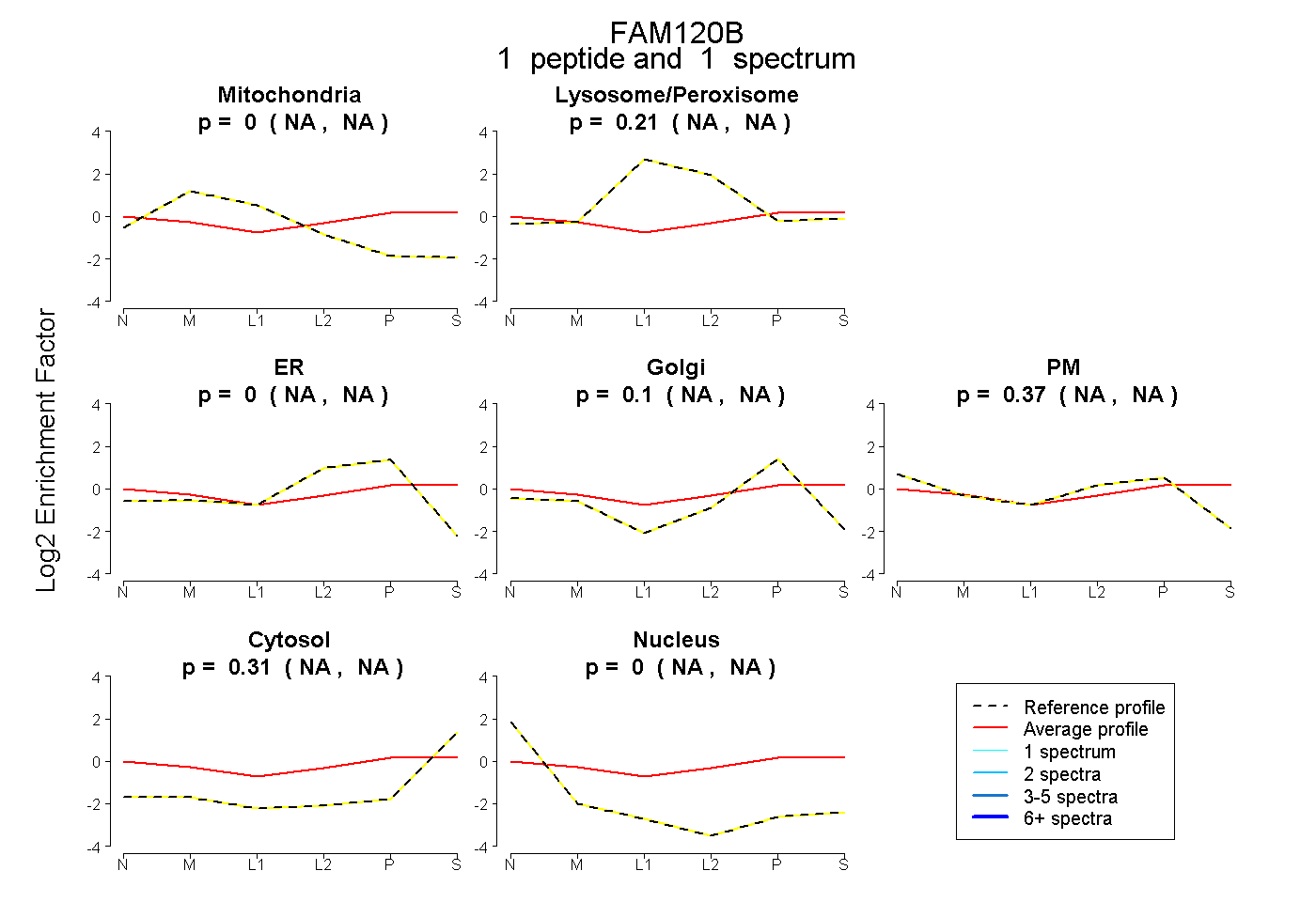 |
0.000 NA | NA |
0.212 NA | NA |
0.000 NA | NA |
0.104 NA | NA |
0.375 NA | NA |
0.310 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
13 spectra |
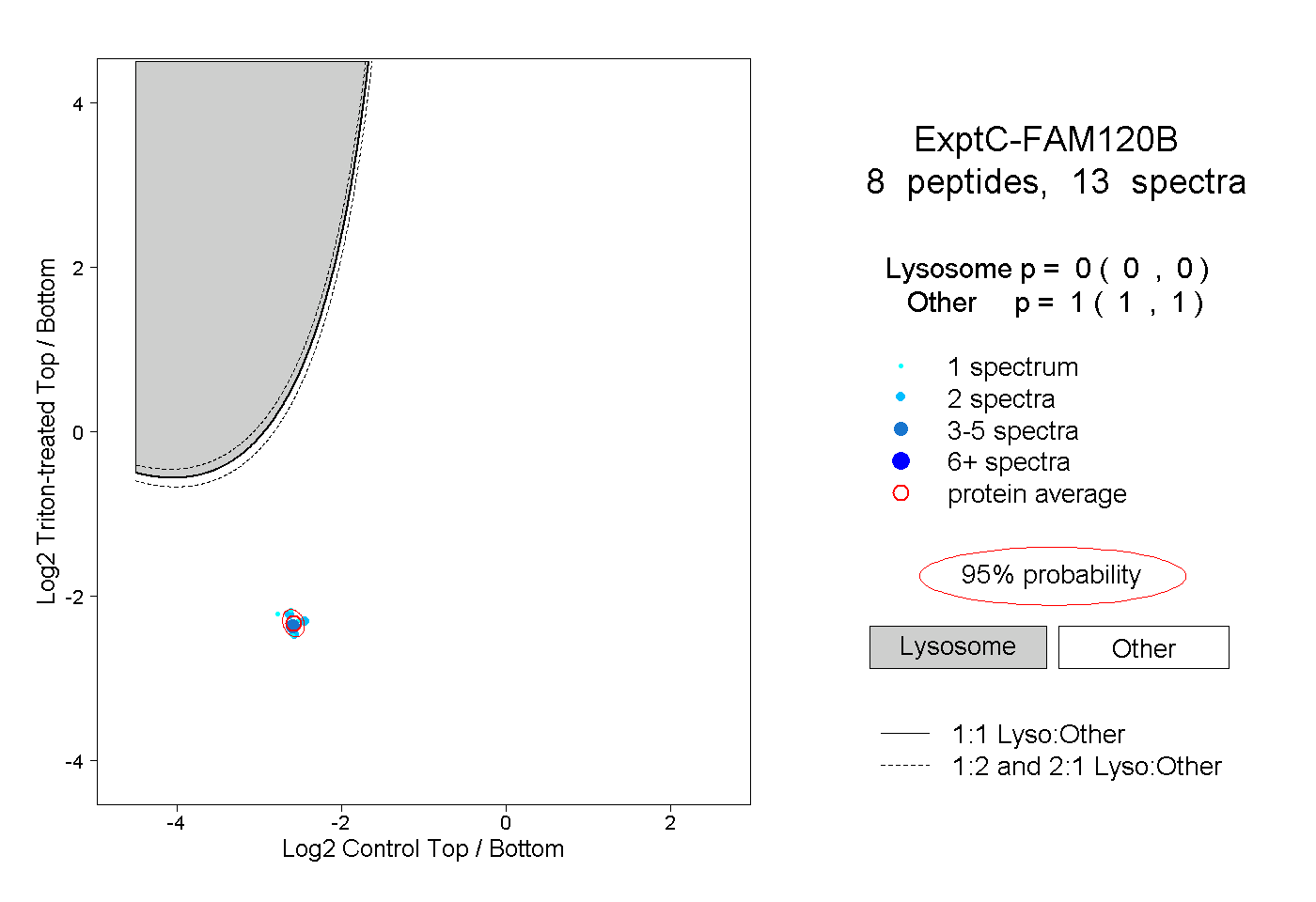 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
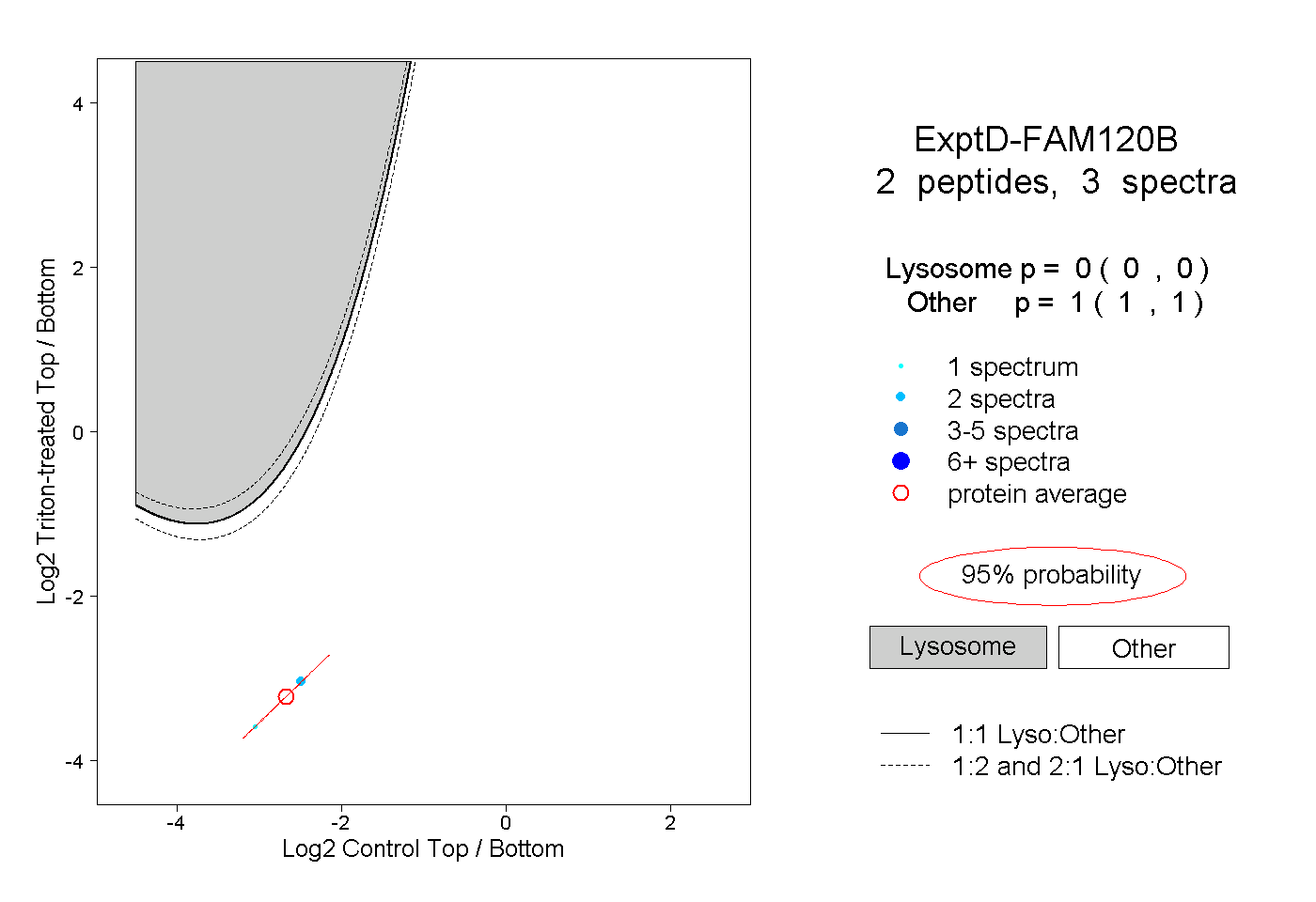 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |