peptides
spectra
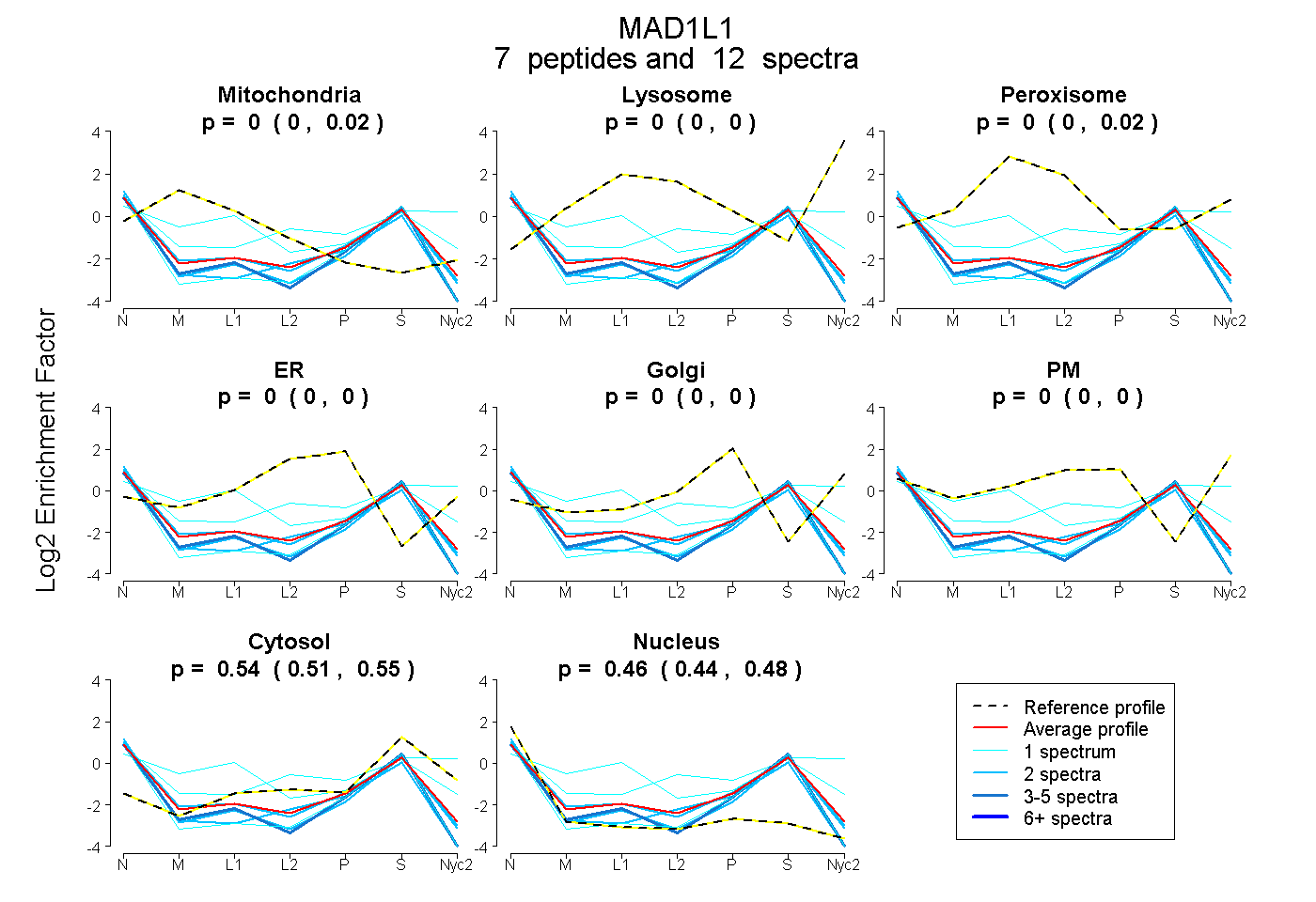
0.000 | 0.016
0.000 | 0.000
0.000 | 0.018
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.510 | 0.553
0.436 | 0.484
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
12 spectra |
 |
0.000 0.000 | 0.016 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.018 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.538 0.510 | 0.553 |
0.462 0.436 | 0.484 |
| 1 spectrum, MQEALVDLELEK | 0.148 | 0.199 | 0.108 | 0.000 | 0.000 | 0.000 | 0.402 | 0.142 | ||
| 3 spectra, MQLLETEFSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.420 | 0.580 | ||
| 2 spectra, AQQQLQDEVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.379 | 0.621 | ||
| 2 spectra, VEELEGER | 0.004 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.506 | 0.490 | ||
| 2 spectra, LTLQGDYNQSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.459 | 0.541 | ||
| 1 spectrum, QSLDAASQQLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.402 | 0.598 | ||
| 1 spectrum, ETHEALAR | 0.000 | 0.000 | 0.128 | 0.084 | 0.000 | 0.078 | 0.439 | 0.272 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
3 spectra |
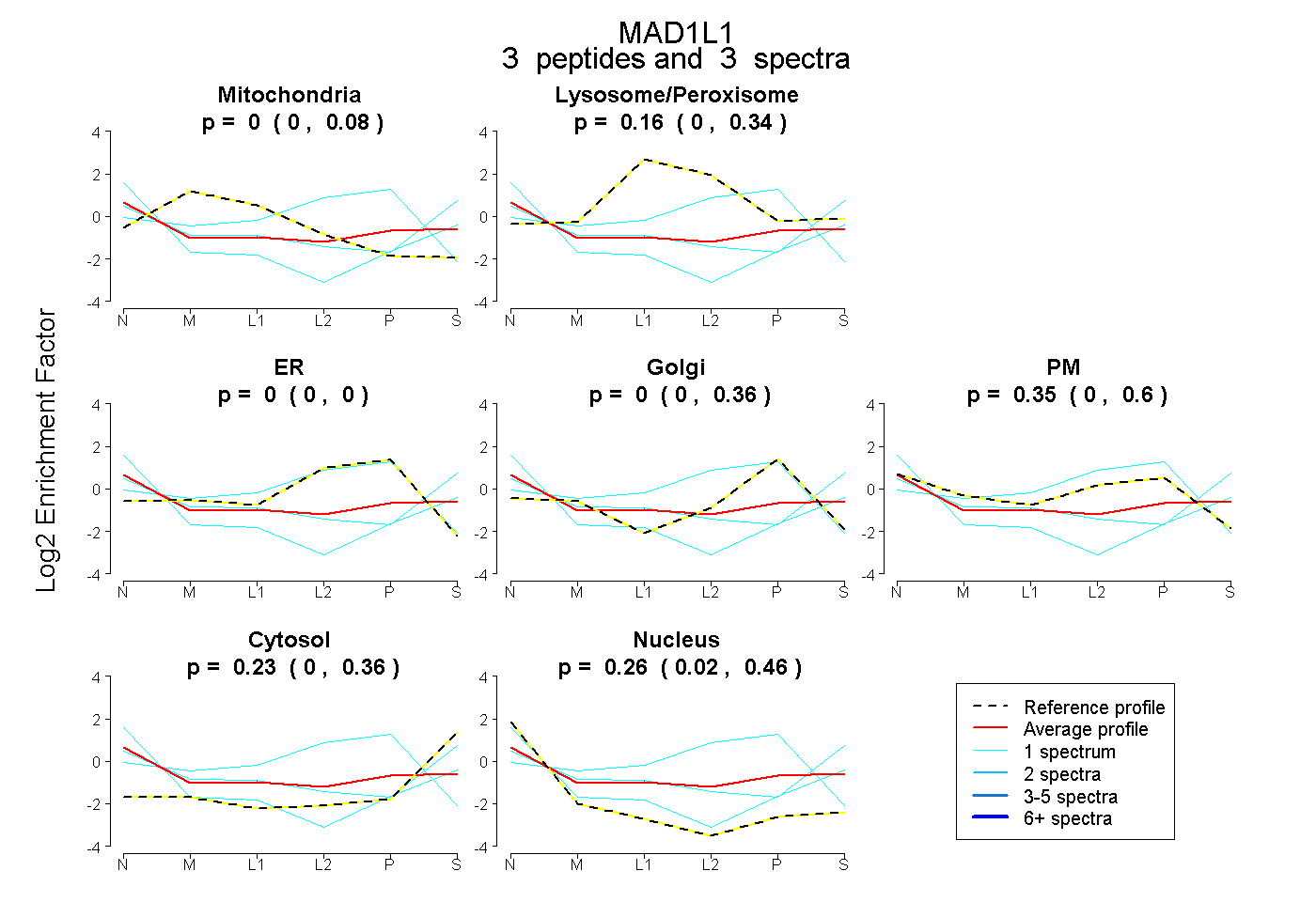 |
0.000 0.000 | 0.081 |
0.162 0.000 | 0.341 |
0.000 0.000 | 0.003 |
0.000 0.000 | 0.360 |
0.351 0.000 | 0.602 |
0.230 0.000 | 0.362 |
0.258 0.016 | 0.461 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
4 spectra |
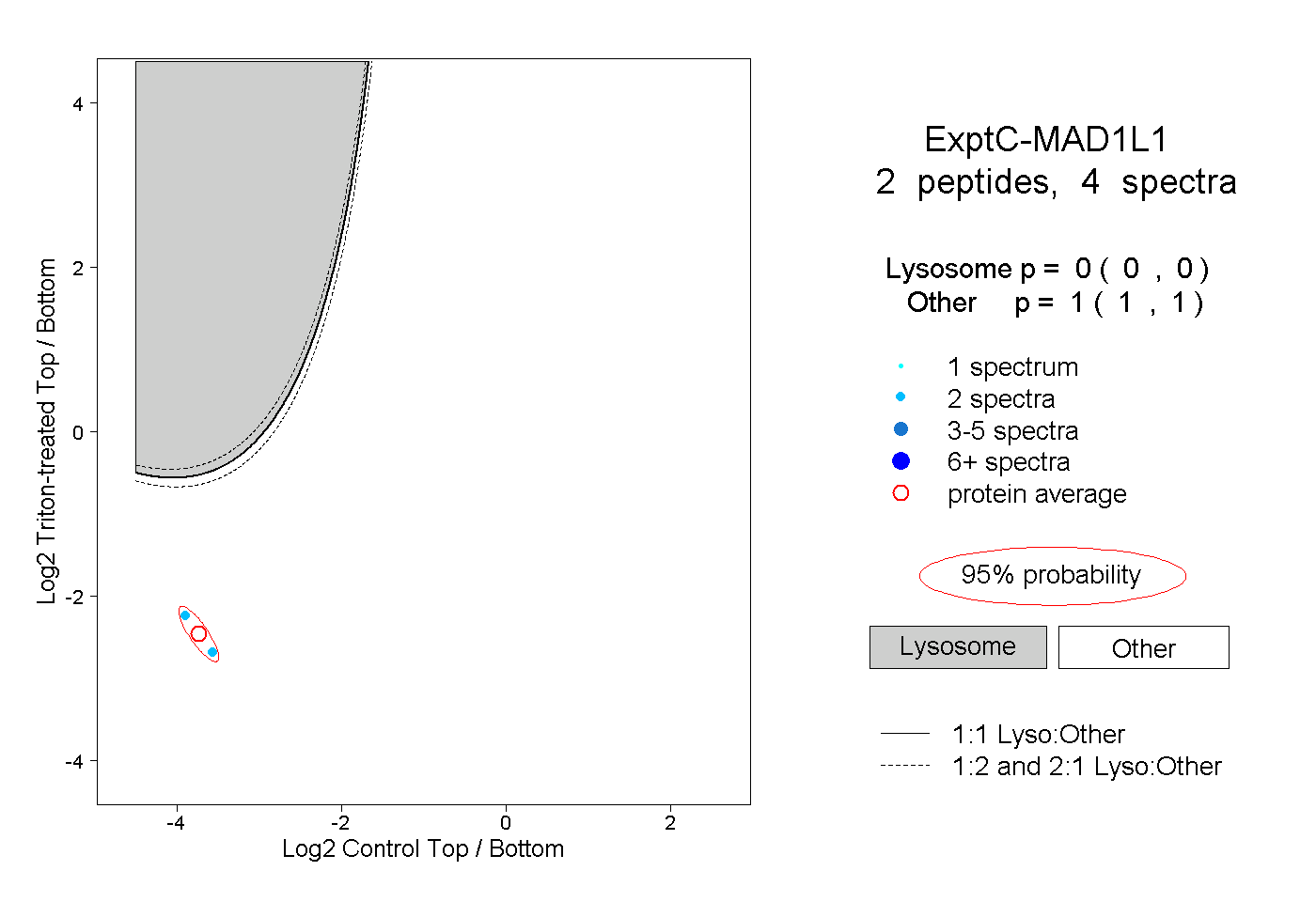 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |