peptides
spectra

0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.768 | 0.820
0.062 | 0.121
0.000 | 0.000
0.000 | 0.000
0.102 | 0.116
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
24 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.798 0.768 | 0.820 |
0.092 0.062 | 0.121 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.110 0.102 | 0.116 |
| 3 spectra, GFTTAVQCLR | 0.045 | 0.000 | 0.000 | 0.818 | 0.000 | 0.000 | 0.000 | 0.137 | ||
| 1 spectrum, LIGVTEIEK | 0.000 | 0.000 | 0.000 | 0.908 | 0.000 | 0.000 | 0.000 | 0.092 | ||
| 2 spectra, FGVLGSSK | 0.000 | 0.000 | 0.000 | 0.364 | 0.089 | 0.210 | 0.337 | 0.000 | ||
| 1 spectrum, FPLEDIPADETGAAQWLHK | 0.000 | 0.000 | 0.000 | 0.819 | 0.122 | 0.000 | 0.000 | 0.059 | ||
| 2 spectra, GSSYGNQELK | 0.000 | 0.000 | 0.000 | 0.837 | 0.058 | 0.000 | 0.000 | 0.105 | ||
| 13 spectra, YHLLPR | 0.000 | 0.000 | 0.000 | 0.791 | 0.105 | 0.000 | 0.000 | 0.103 | ||
| 2 spectra, QSGVFPGEQIKPAR | 0.000 | 0.000 | 0.000 | 0.860 | 0.057 | 0.000 | 0.000 | 0.083 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
3 spectra |
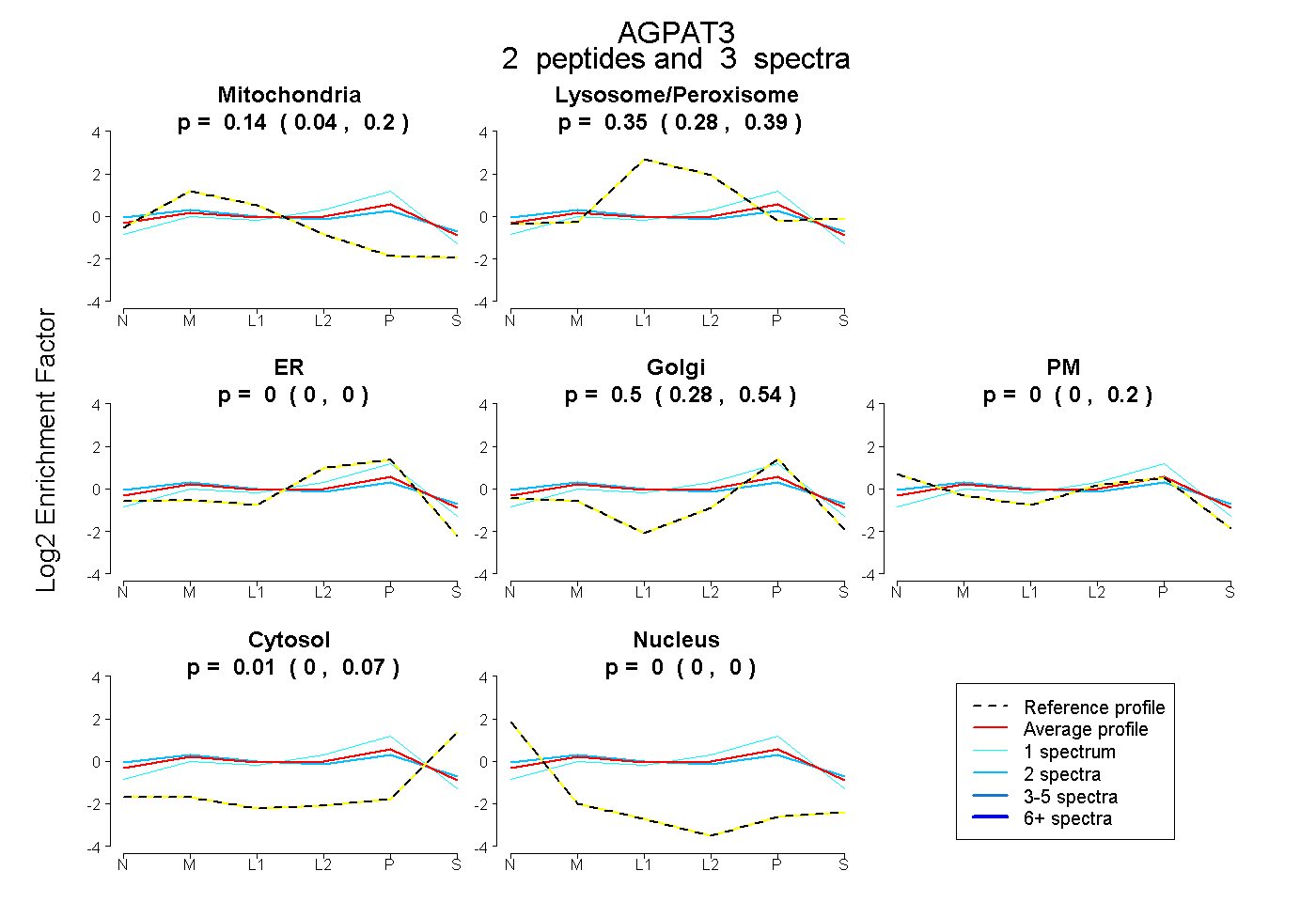 |
0.136 0.044 | 0.199 |
0.355 0.275 | 0.390 |
0.000 0.000 | 0.000 |
0.503 0.284 | 0.542 |
0.000 0.000 | 0.197 |
0.007 0.000 | 0.069 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
19 spectra |
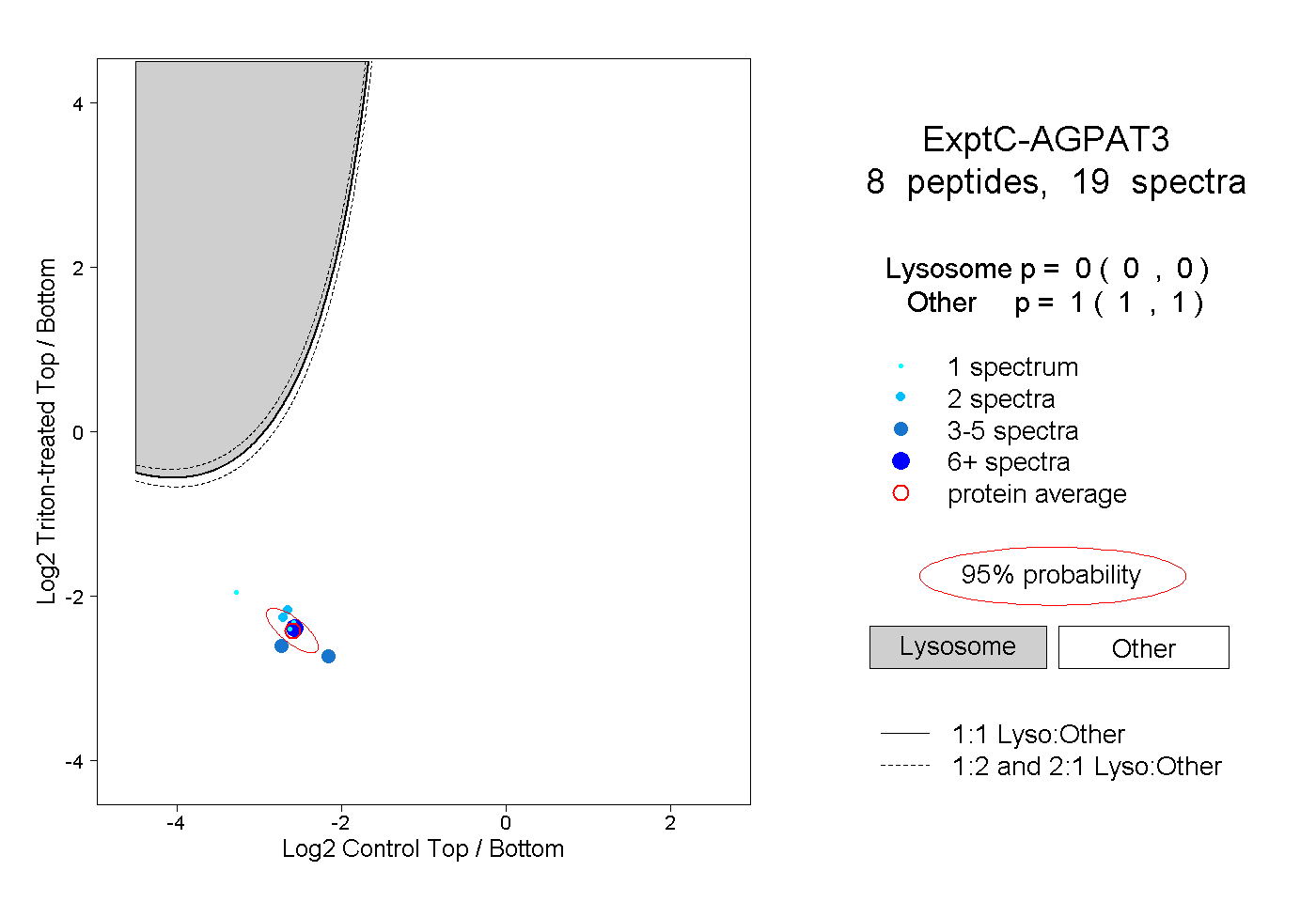 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |