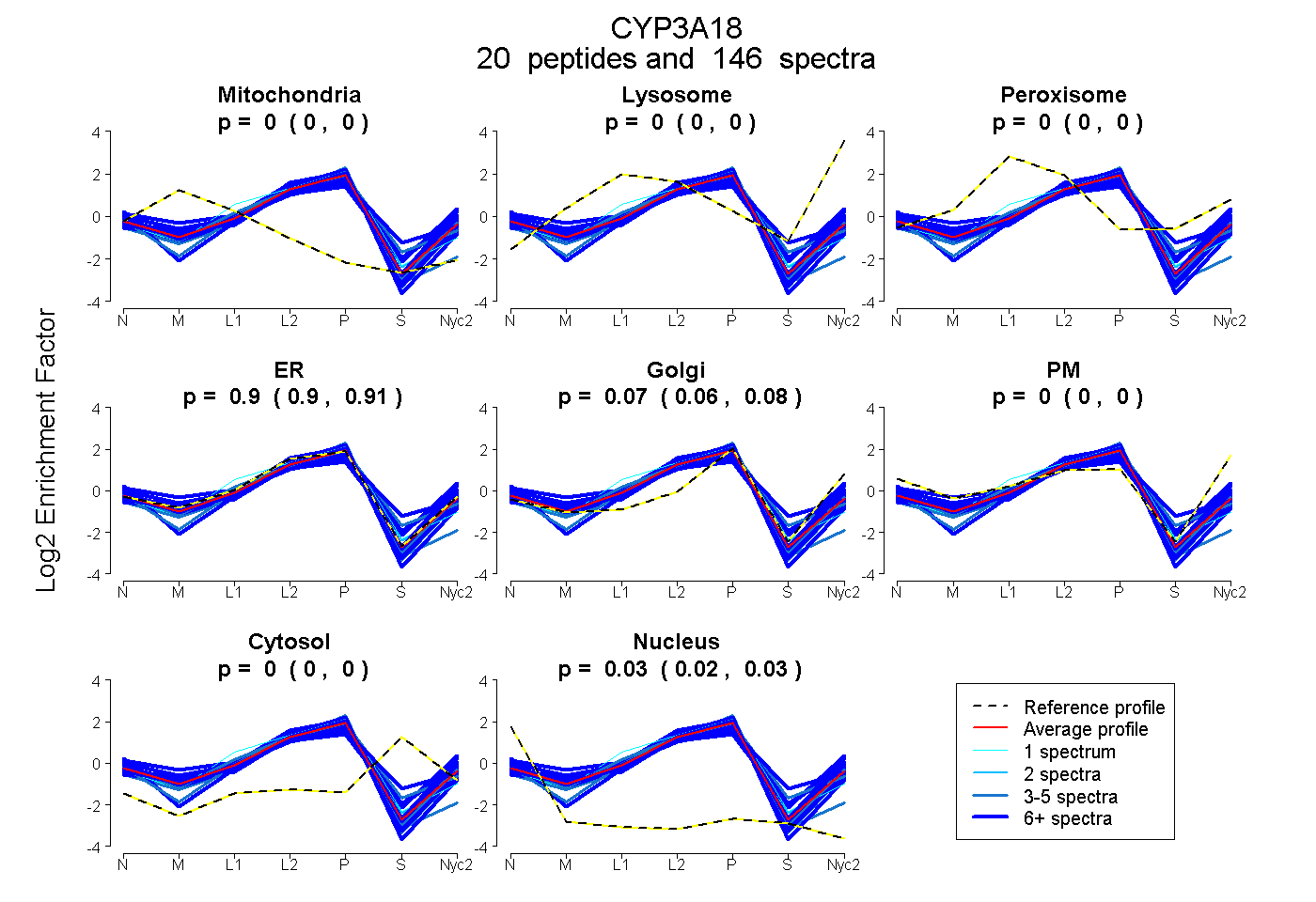
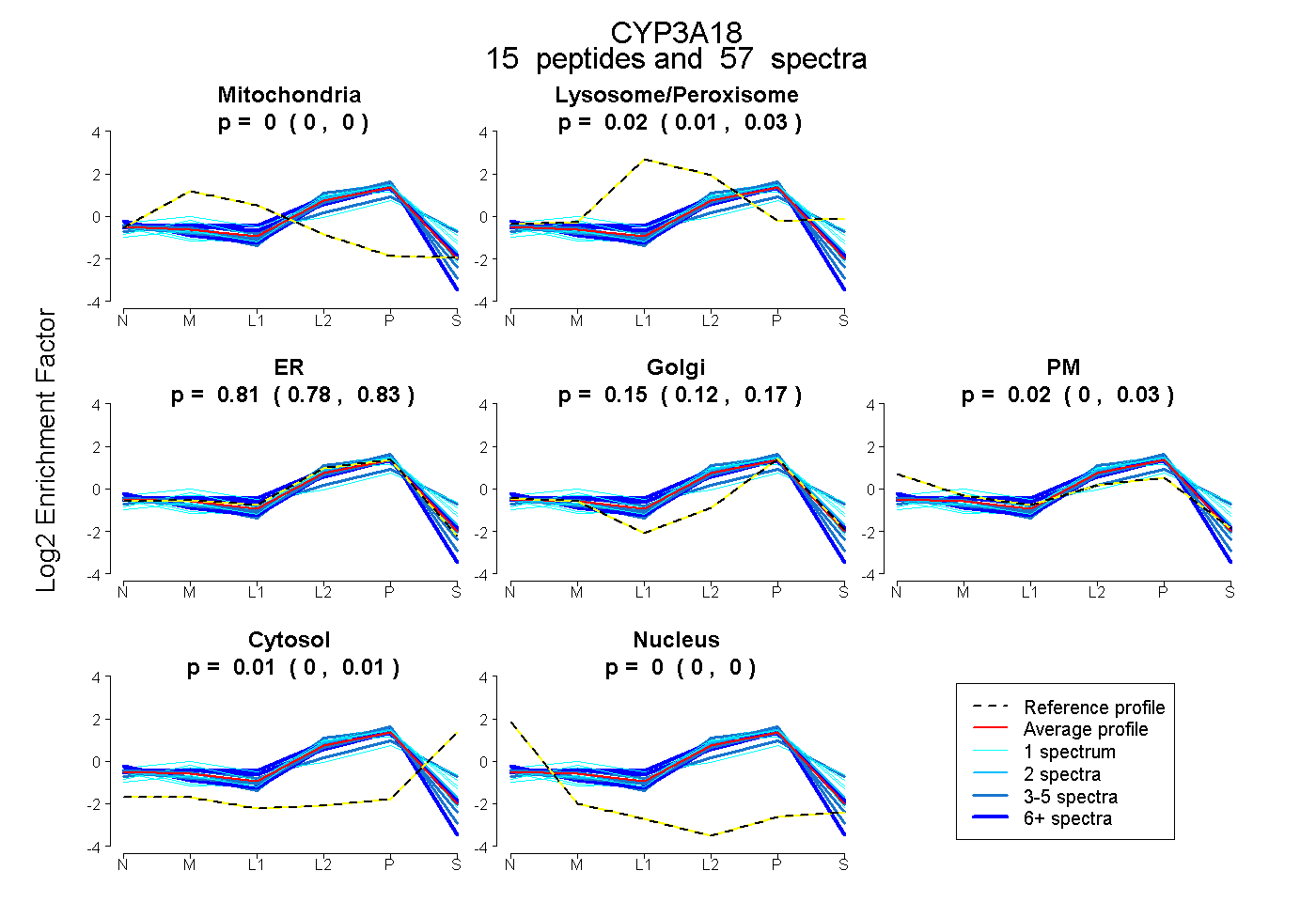
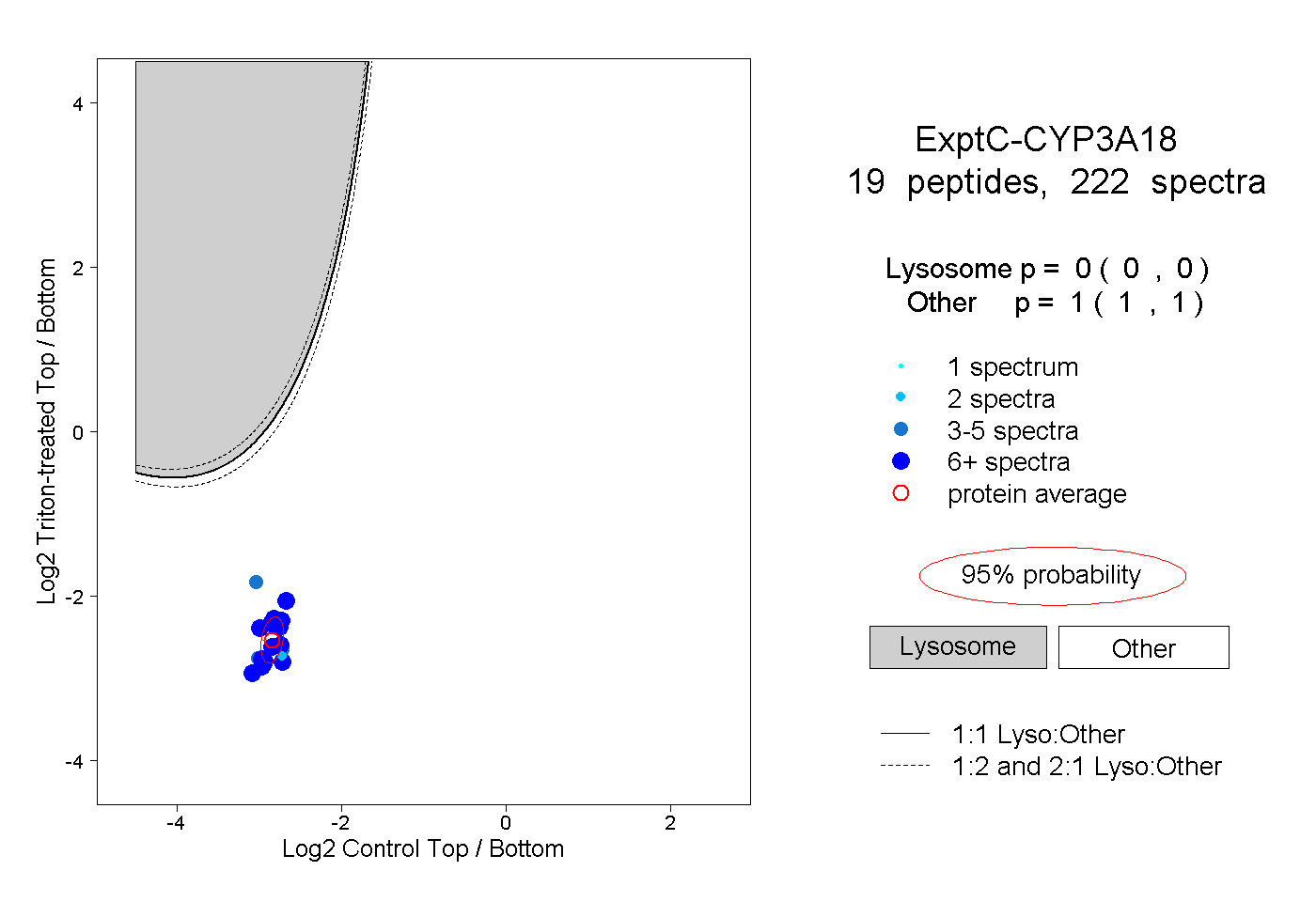
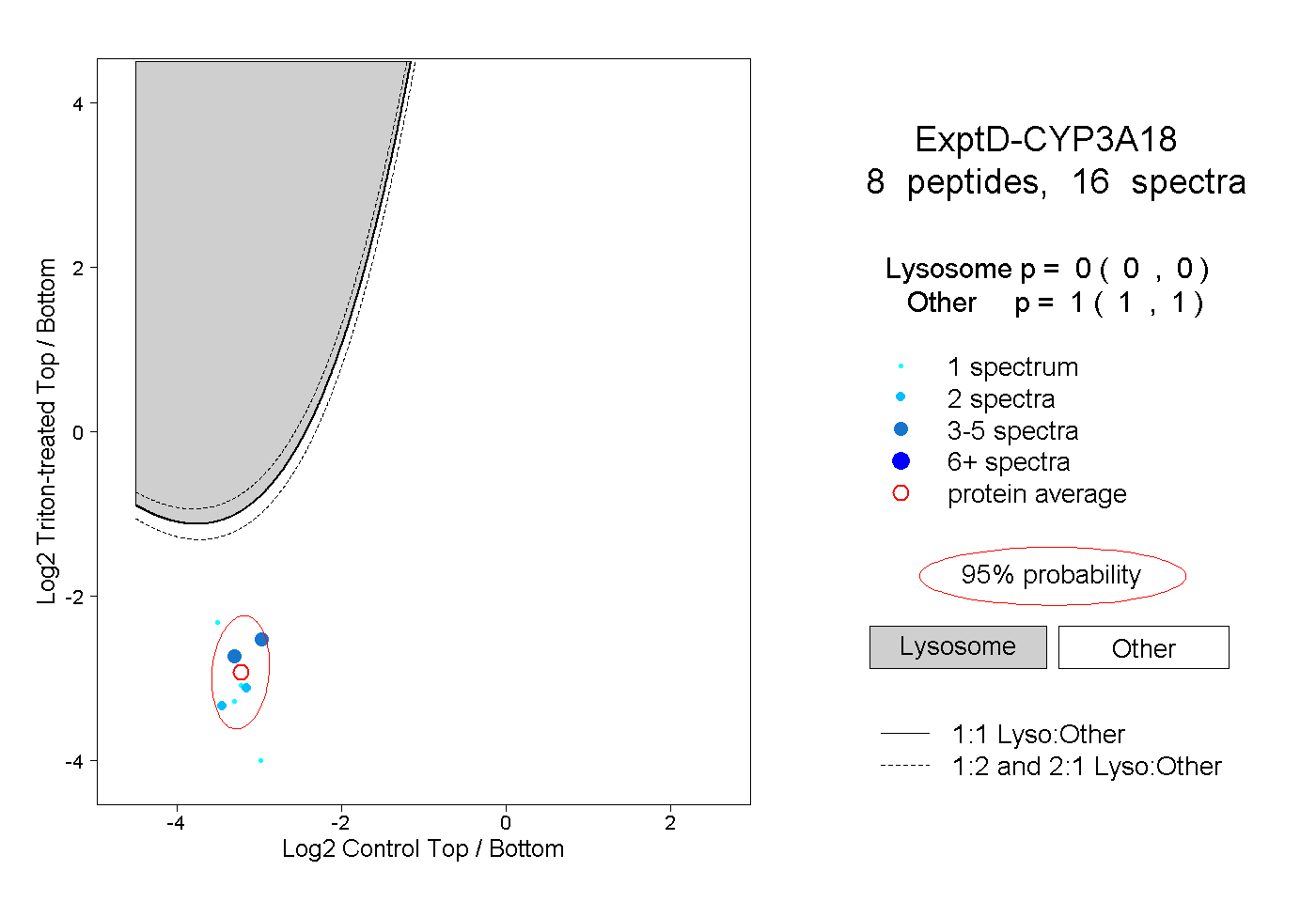
| 16 spectra, TLLSPTFTSGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, LYPIATR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, EMFPLMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, QYGDTLLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, VDFLQLMMNTQNSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, TQIPLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, NCIGMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, QSMNFFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, ECYSVFTNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, CFGPMGFMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, DVEINGVFIPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, GEPINMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, GQESQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 27 spectra, FALISMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, GSIDPYVYLPFGNGPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, LQNEIDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 29 spectra, LDSNQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, GTVVTIPIYPLHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NPEYWLEPEEFNPER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |