peptides
spectra
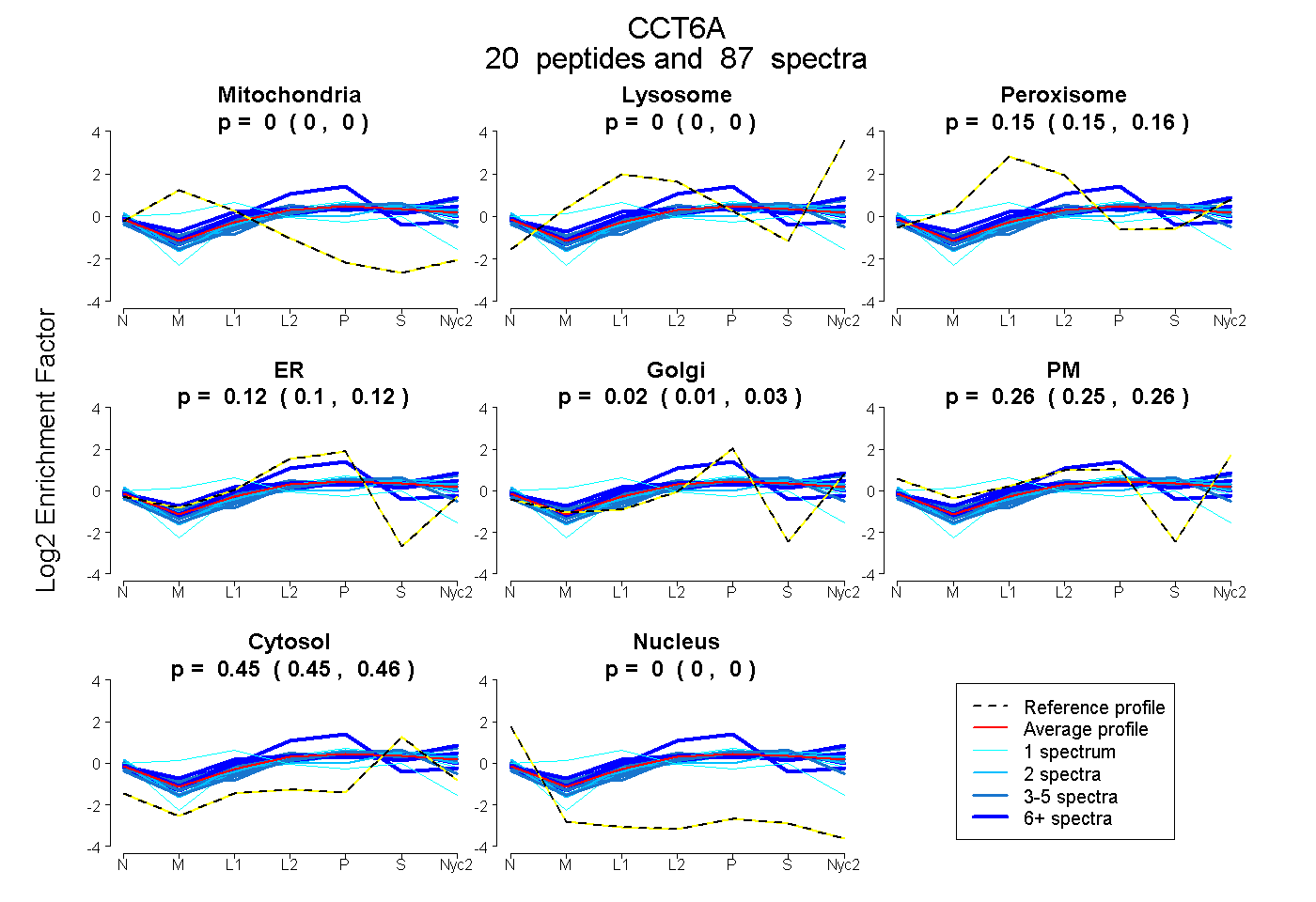
0.000 | 0.000
0.000 | 0.000
0.147 | 0.156
0.105 | 0.125
0.011 | 0.033
0.246 | 0.263
0.451 | 0.457
0.000 | 0.000
peptides
spectra
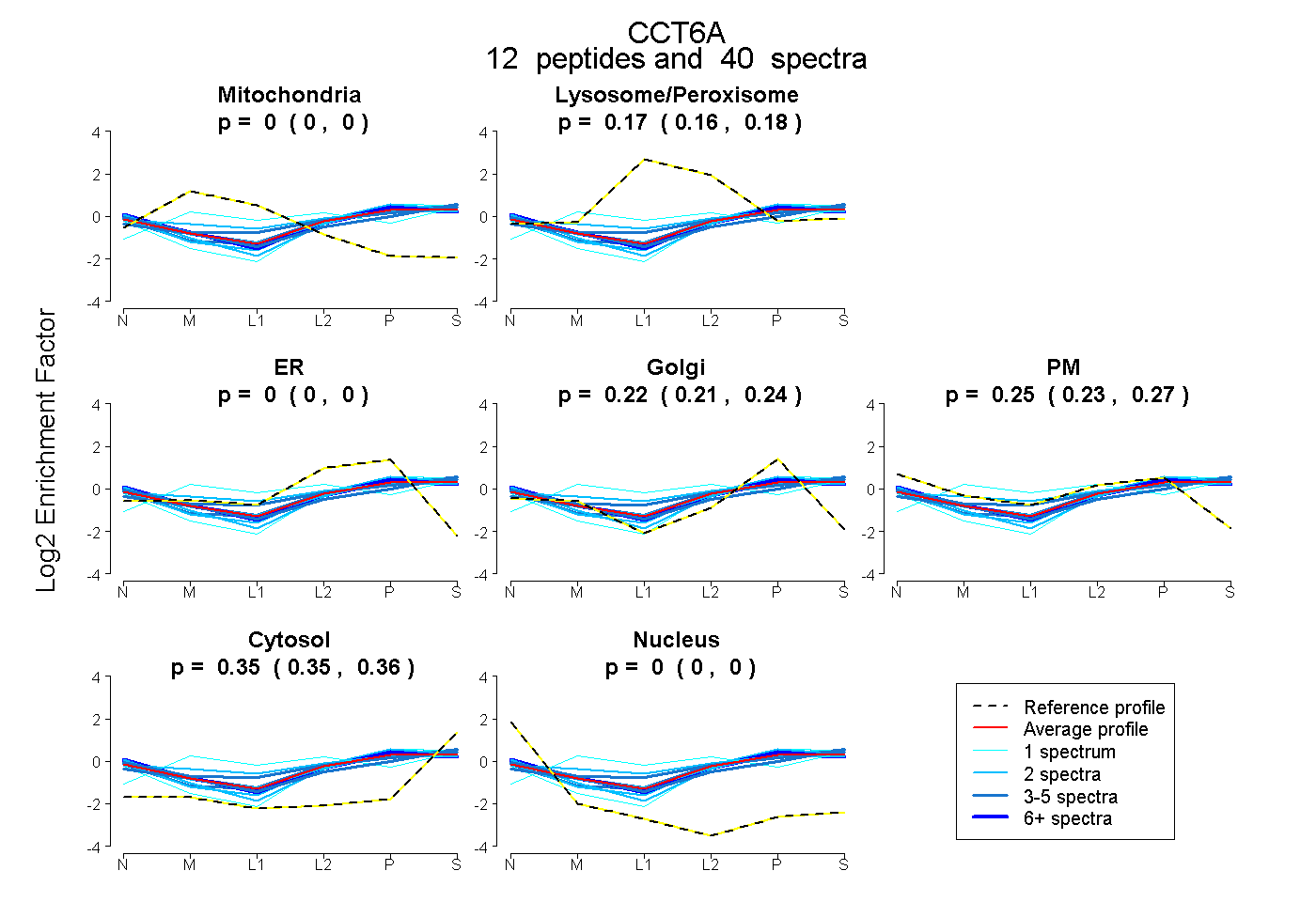
0.000 | 0.000
0.163 | 0.177
0.000 | 0.000
0.211 | 0.236
0.234 | 0.266
0.349 | 0.356
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
87 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.152 0.147 | 0.156 |
0.116 0.105 | 0.125 |
0.023 0.011 | 0.033 |
0.255 0.246 | 0.263 |
0.454 0.451 | 0.457 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
40 spectra |
 |
0.000 0.000 | 0.000 |
0.171 0.163 | 0.177 |
0.000 0.000 | 0.000 |
0.224 0.211 | 0.236 |
0.252 0.234 | 0.266 |
0.352 0.349 | 0.356 |
0.000 0.000 | 0.000 |
| 1 spectrum, IVELK | 0.074 | 0.429 | 0.000 | 0.177 | 0.000 | 0.320 | 0.000 | |||
| 1 spectrum, ETLIDVAR | 0.000 | 0.000 | 0.283 | 0.132 | 0.124 | 0.460 | 0.000 | |||
| 3 spectra, TEVNSGFFYK | 0.000 | 0.156 | 0.000 | 0.187 | 0.211 | 0.446 | 0.000 | |||
| 6 spectra, GIDPFSLDALAK | 0.000 | 0.111 | 0.000 | 0.135 | 0.413 | 0.341 | 0.000 | |||
| 3 spectra, EGIVALR | 0.000 | 0.192 | 0.000 | 0.250 | 0.179 | 0.379 | 0.000 | |||
| 2 spectra, HTLTQIK | 0.000 | 0.301 | 0.000 | 0.208 | 0.211 | 0.280 | 0.000 | |||
| 2 spectra, GLQDVLR | 0.000 | 0.036 | 0.000 | 0.224 | 0.388 | 0.352 | 0.000 | |||
| 5 spectra, ALQFLEQVK | 0.000 | 0.179 | 0.000 | 0.244 | 0.256 | 0.321 | 0.000 | |||
| 3 spectra, QADLYISEGLHPR | 0.000 | 0.243 | 0.000 | 0.100 | 0.307 | 0.350 | 0.000 | |||
| 2 spectra, IITEGFEAAK | 0.000 | 0.138 | 0.000 | 0.148 | 0.360 | 0.354 | 0.000 | |||
| 10 spectra, GLVLDHGAR | 0.000 | 0.110 | 0.000 | 0.212 | 0.348 | 0.330 | 0.000 | |||
| 2 spectra, GFVVINQK | 0.000 | 0.135 | 0.025 | 0.289 | 0.204 | 0.347 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
180 spectra |
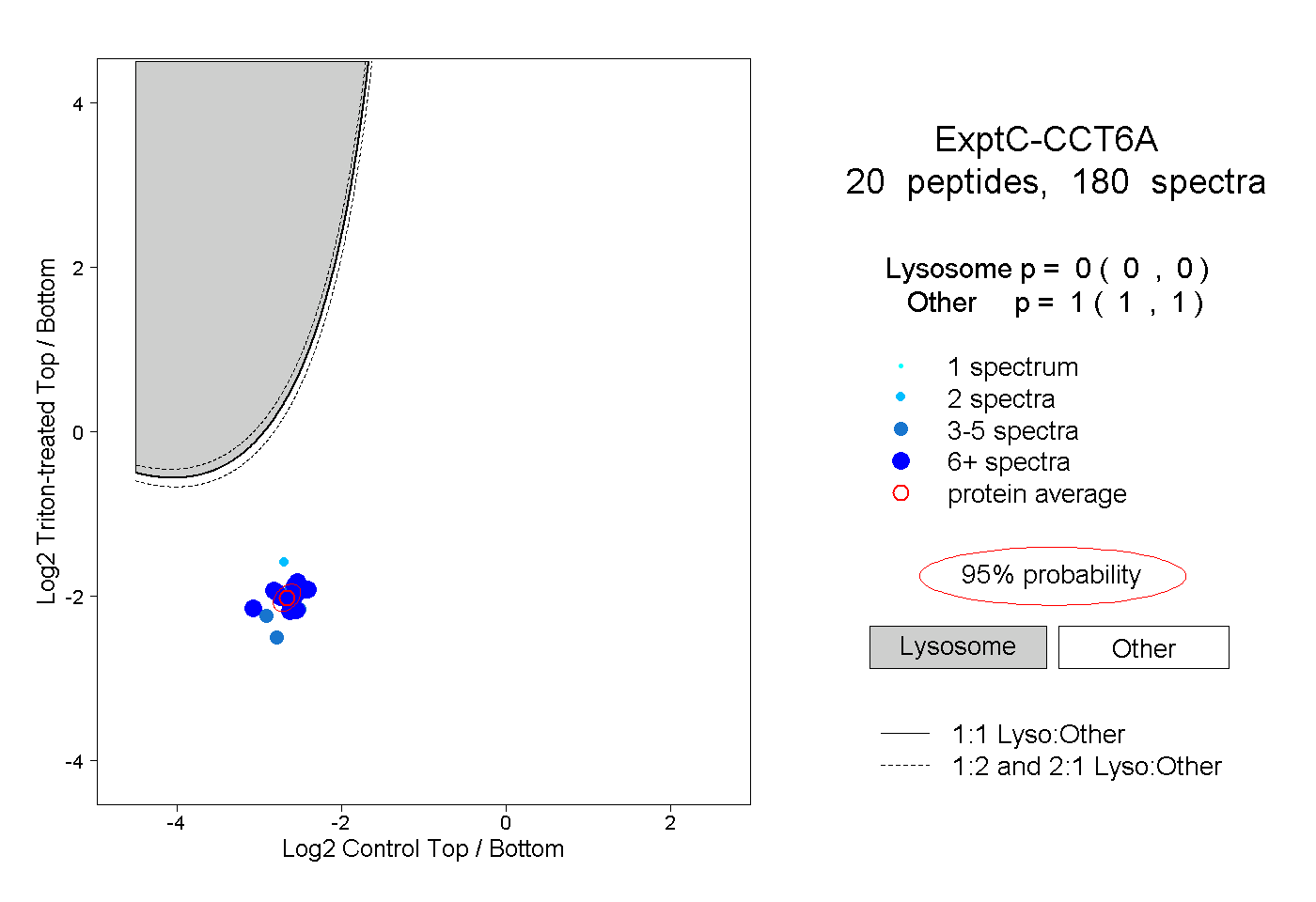 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
19 spectra |
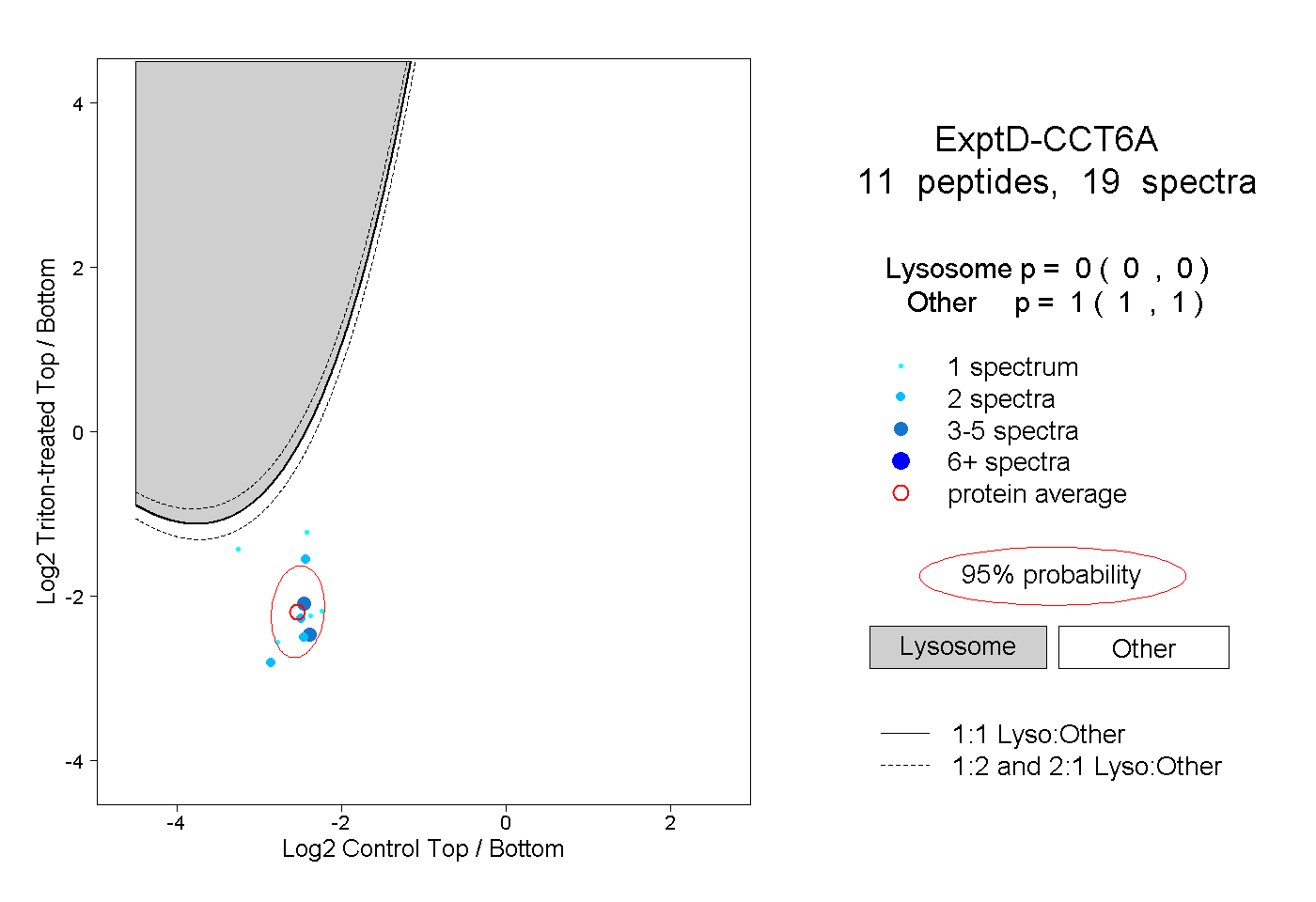 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |