peptides
spectra
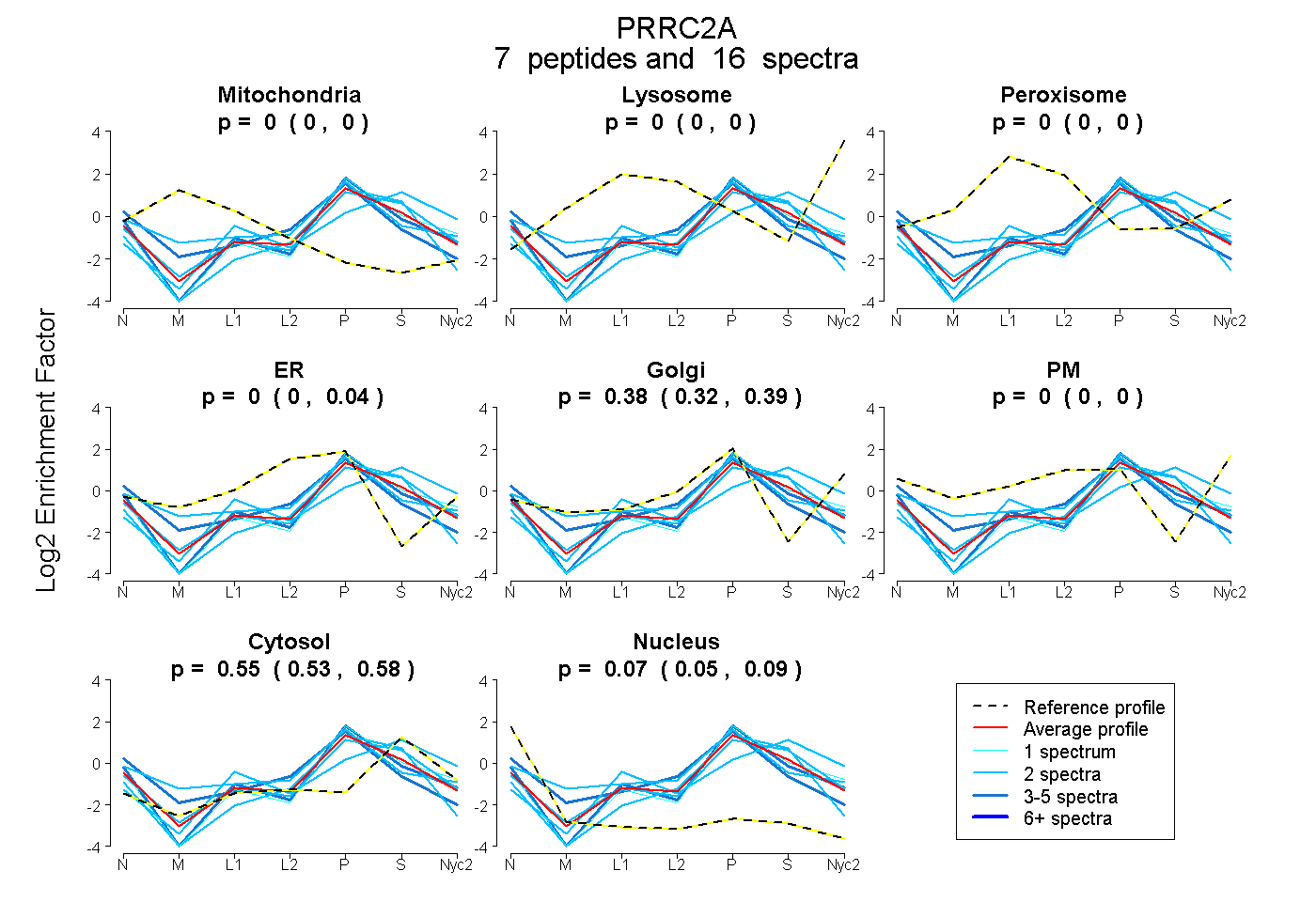
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.036
0.319 | 0.391
0.000 | 0.000
0.530 | 0.576
0.052 | 0.085
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.036 |
0.376 0.319 | 0.391 |
0.000 0.000 | 0.000 |
0.554 0.530 | 0.576 |
0.070 0.052 | 0.085 |
| 4 spectra, AQQQDKPPR | 0.000 | 0.000 | 0.000 | 0.411 | 0.095 | 0.000 | 0.303 | 0.191 | ||
| 2 spectra, SLEIQKPAVAPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.313 | 0.000 | 0.651 | 0.037 | ||
| 2 spectra, WGPRPGSCR | 0.000 | 0.000 | 0.000 | 0.156 | 0.446 | 0.000 | 0.346 | 0.051 | ||
| 1 spectrum, LISGPLSPMSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.400 | 0.000 | 0.530 | 0.070 | ||
| 2 spectra, GVPSR | 0.000 | 0.021 | 0.000 | 0.000 | 0.165 | 0.000 | 0.814 | 0.000 | ||
| 3 spectra, ETPAGGNLSPAPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.411 | 0.000 | 0.478 | 0.111 | ||
| 2 spectra, GGPPCKPPAPEDEDEAWR | 0.000 | 0.000 | 0.000 | 0.124 | 0.049 | 0.000 | 0.700 | 0.127 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
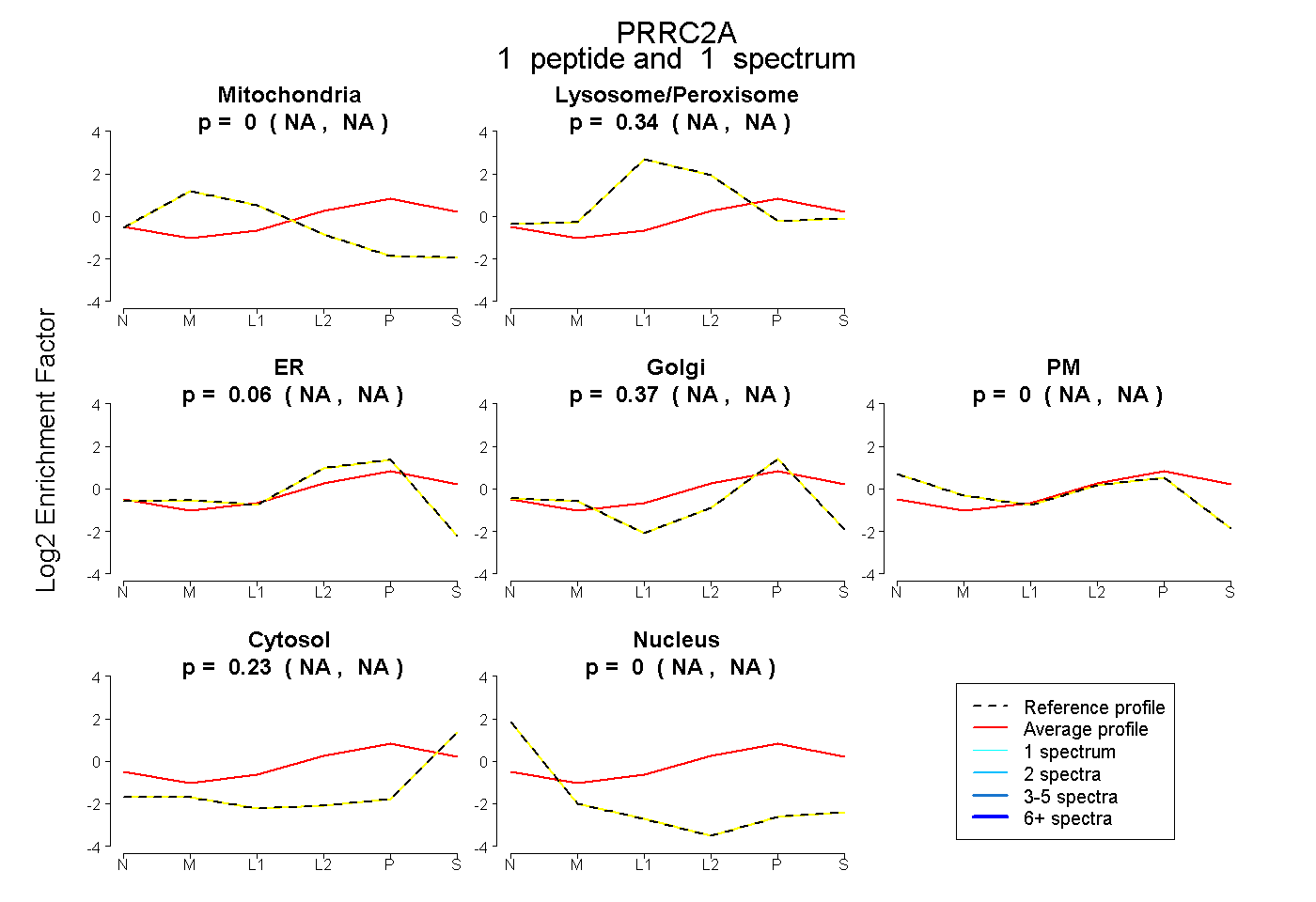 |
0.000 NA | NA |
0.341 NA | NA |
0.060 NA | NA |
0.370 NA | NA |
0.000 NA | NA |
0.229 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
3 spectra |
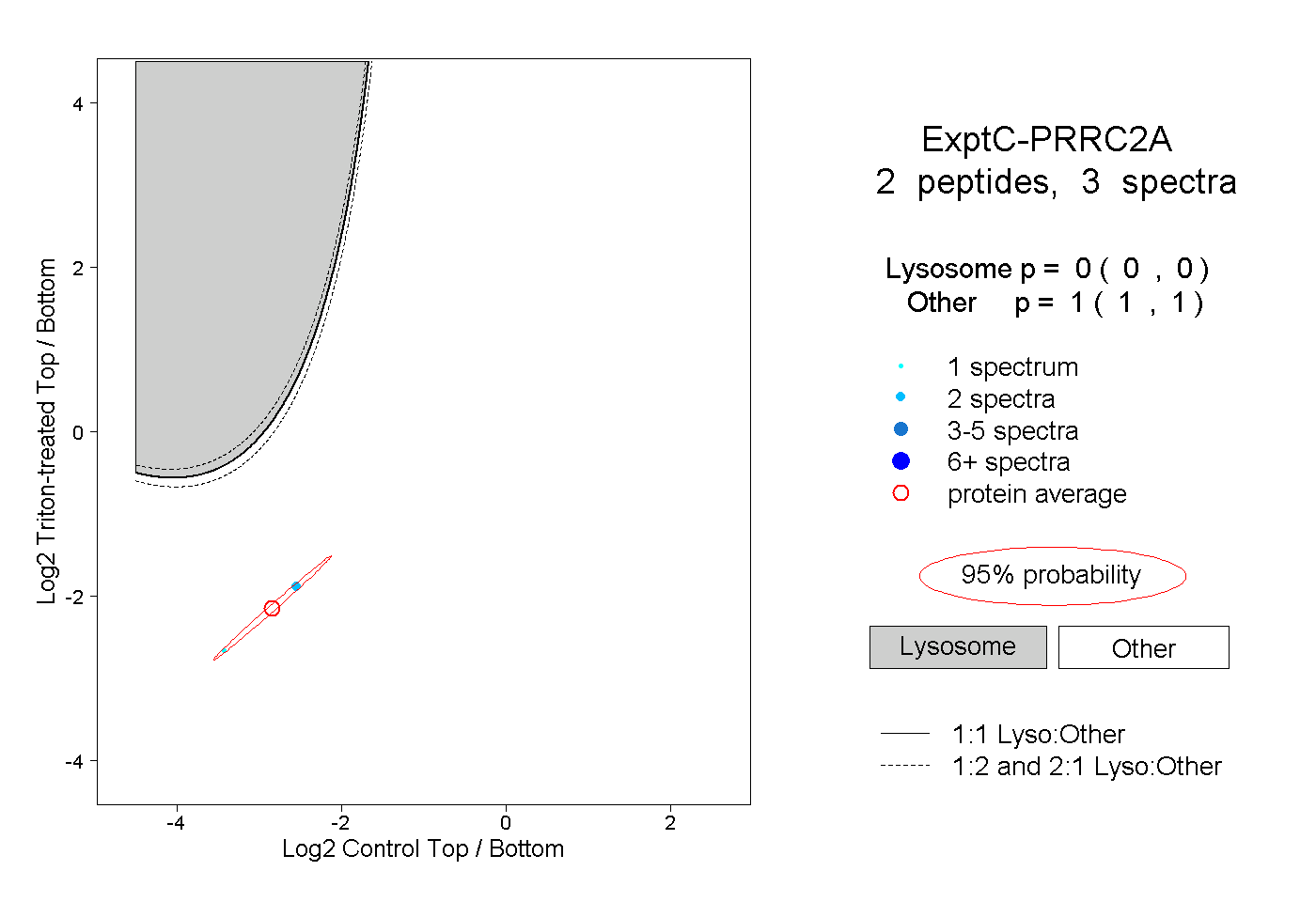 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
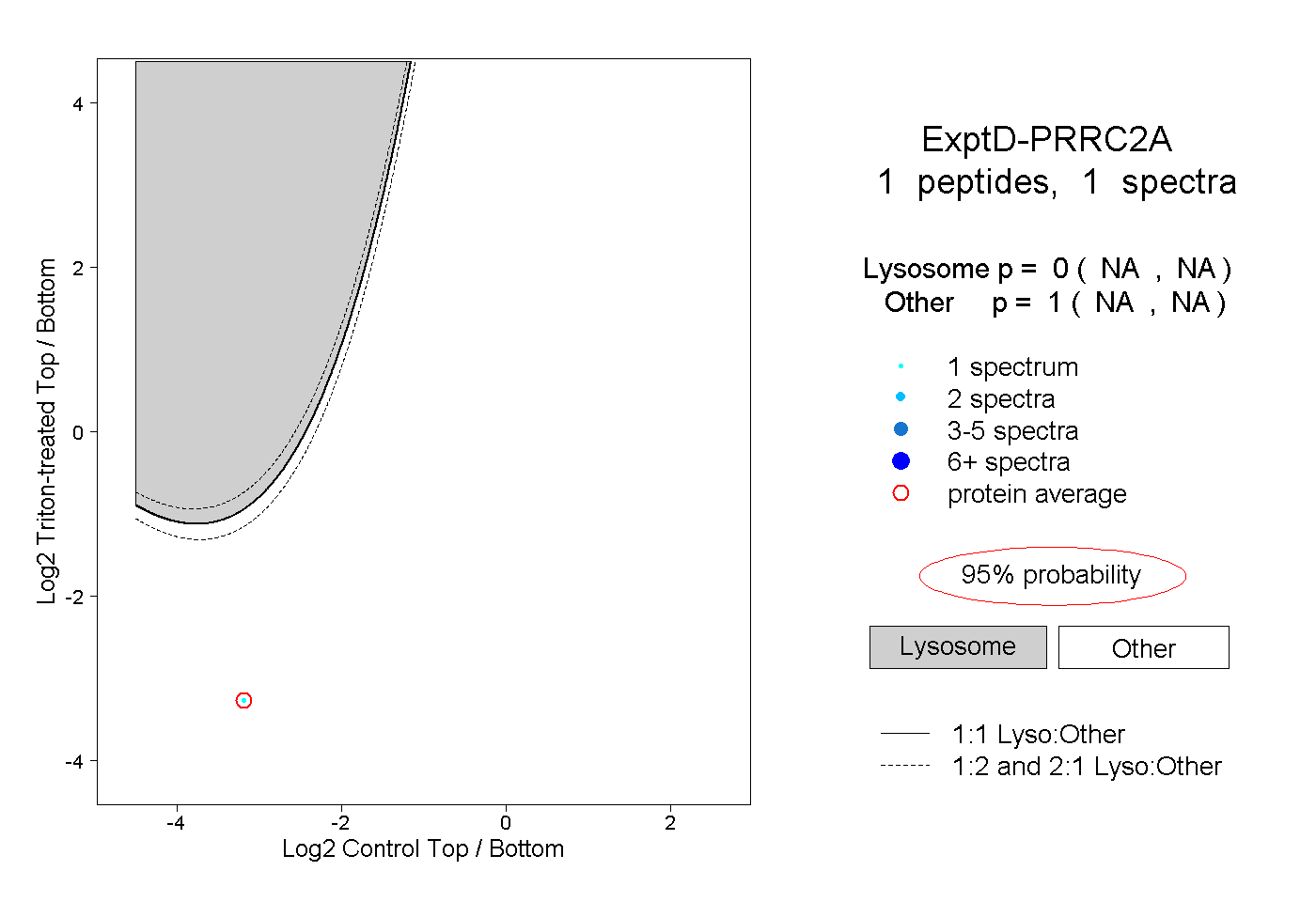 |
0.000 NA | NA |
1.000 NA | NA |