peptides
spectra
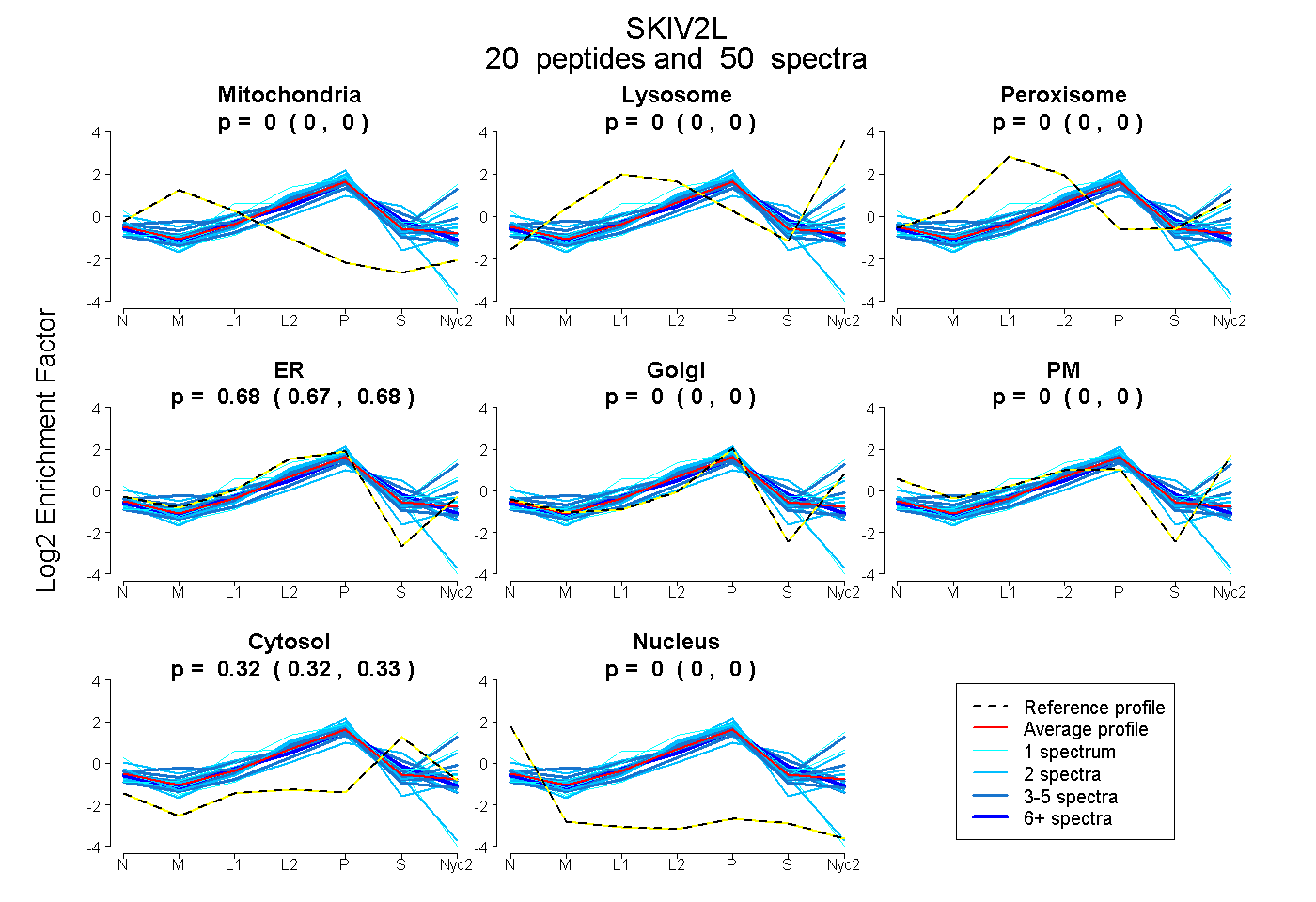
0.000 | 0.000
0.000 | 0.000
0.000 | 0.001
0.673 | 0.681
0.000 | 0.000
0.000 | 0.000
0.318 | 0.326
0.000 | 0.000
peptides
spectra
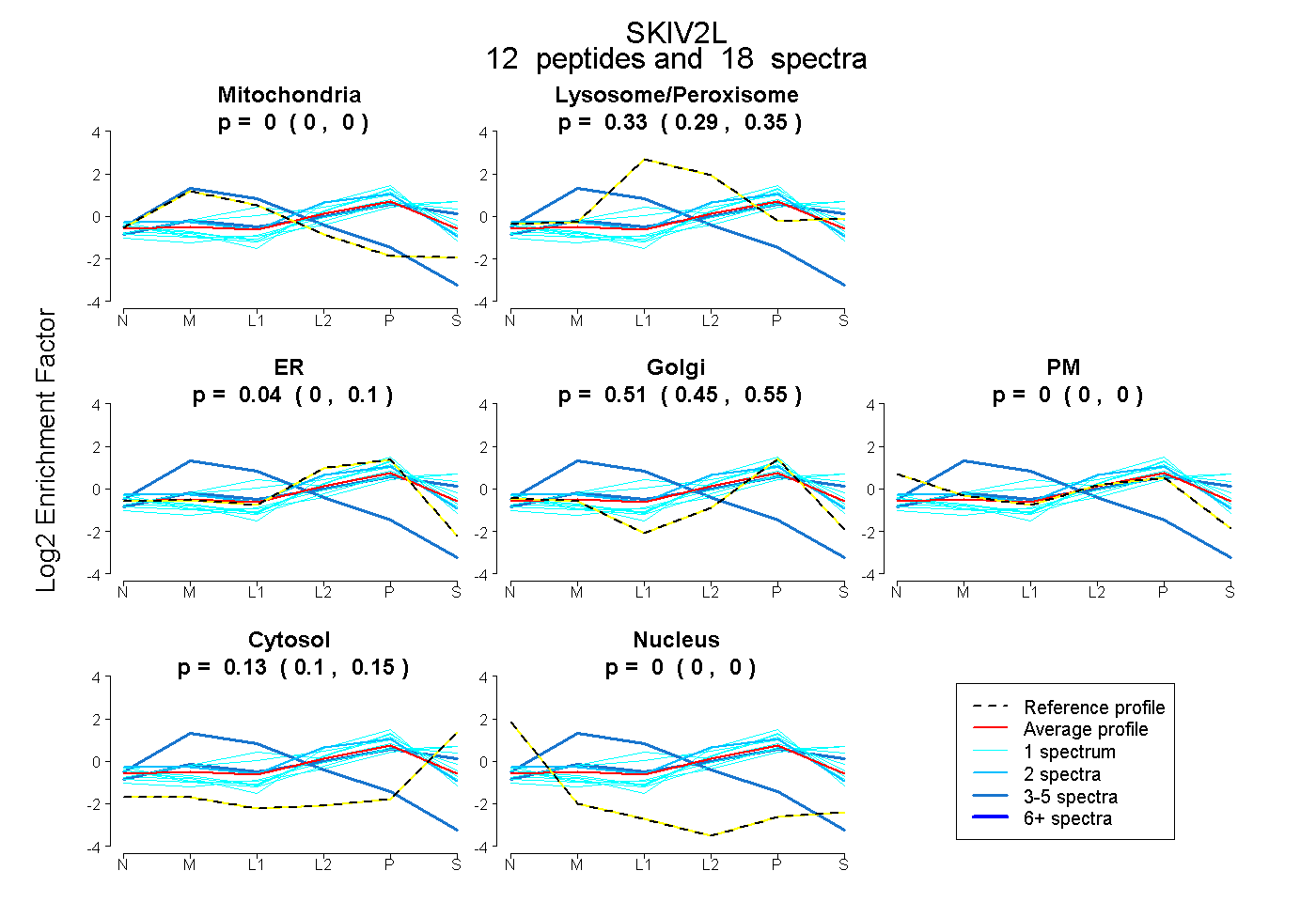
0.000 | 0.000
0.290 | 0.350
0.000 | 0.102
0.449 | 0.547
0.000 | 0.000
0.098 | 0.150
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
50 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.001 |
0.678 0.673 | 0.681 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.322 0.318 | 0.326 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
 |
0.000 0.000 | 0.000 |
0.325 0.290 | 0.350 |
0.041 0.000 | 0.102 |
0.508 0.449 | 0.547 |
0.000 0.000 | 0.000 |
0.126 0.098 | 0.150 |
0.000 0.000 | 0.000 |
| 1 spectrum, DVAVVEGGLR | 0.000 | 0.000 | 0.702 | 0.171 | 0.000 | 0.128 | 0.000 | |||
| 1 spectrum, LQPGDVAAISTK | 0.000 | 0.249 | 0.000 | 0.442 | 0.000 | 0.309 | 0.000 | |||
| 1 spectrum, LFLPEGPCEHTVAK | 0.000 | 0.159 | 0.281 | 0.482 | 0.000 | 0.077 | 0.000 | |||
| 4 spectra, LEEILR | 0.898 | 0.000 | 0.102 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VFTTLVLCDKPAVSENPR | 0.000 | 0.294 | 0.227 | 0.424 | 0.030 | 0.025 | 0.000 | |||
| 1 spectrum, GAFHTK | 0.000 | 0.285 | 0.000 | 0.318 | 0.000 | 0.397 | 0.000 | |||
| 1 spectrum, HAQTFGAK | 0.000 | 0.451 | 0.000 | 0.549 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, ISEDFSK | 0.000 | 0.235 | 0.214 | 0.130 | 0.000 | 0.421 | 0.000 | |||
| 1 spectrum, TLGYVDEAGTVK | 0.000 | 0.224 | 0.183 | 0.456 | 0.000 | 0.136 | 0.000 | |||
| 3 spectra, FLLSDQSLLLLPEYHQR | 0.000 | 0.375 | 0.000 | 0.397 | 0.000 | 0.229 | 0.000 | |||
| 1 spectrum, TVVAEYAIALAQK | 0.000 | 0.145 | 0.344 | 0.383 | 0.000 | 0.128 | 0.000 | |||
| 1 spectrum, GYYAAVEAK | 0.000 | 0.495 | 0.000 | 0.392 | 0.000 | 0.113 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
26 spectra |
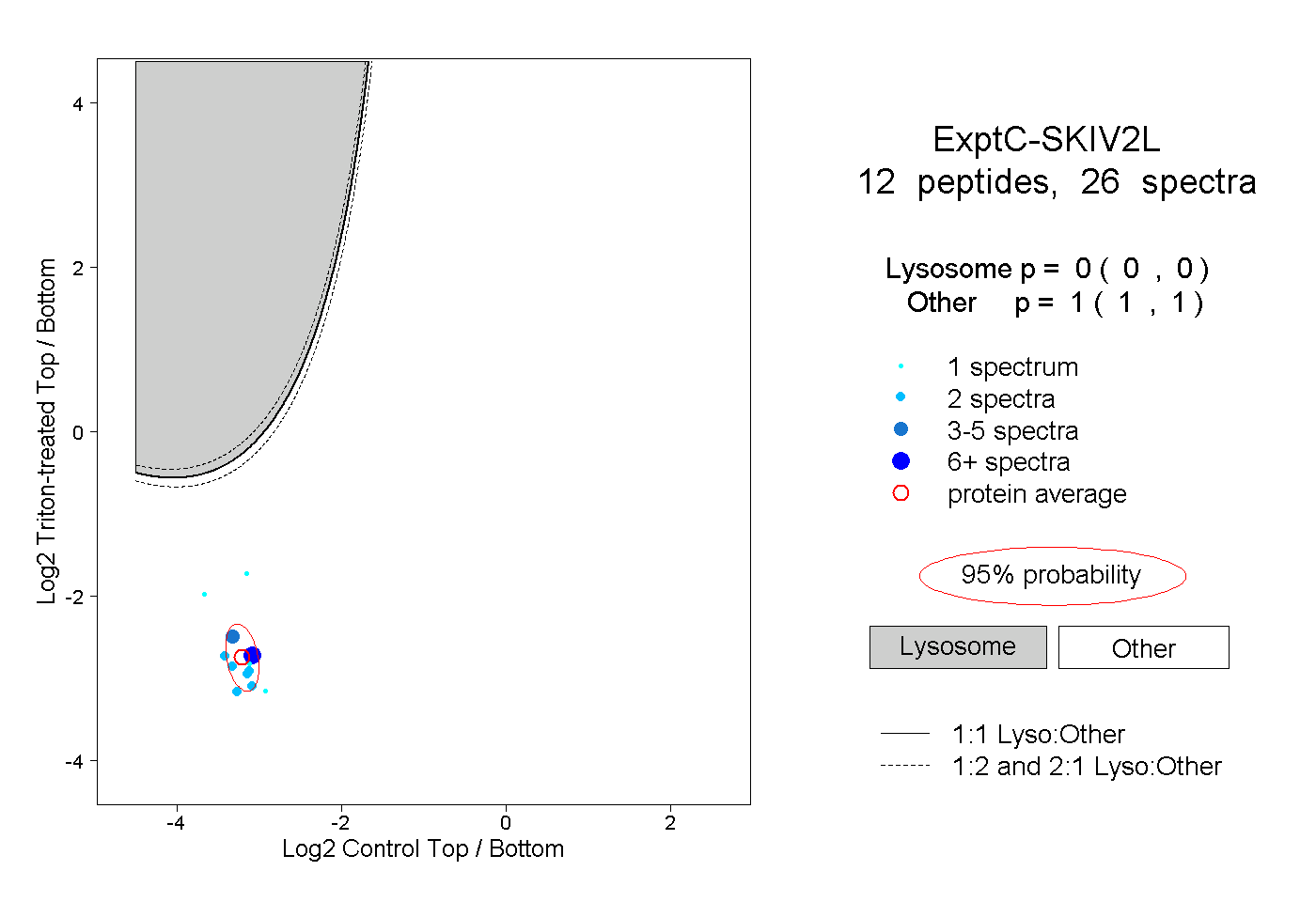 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
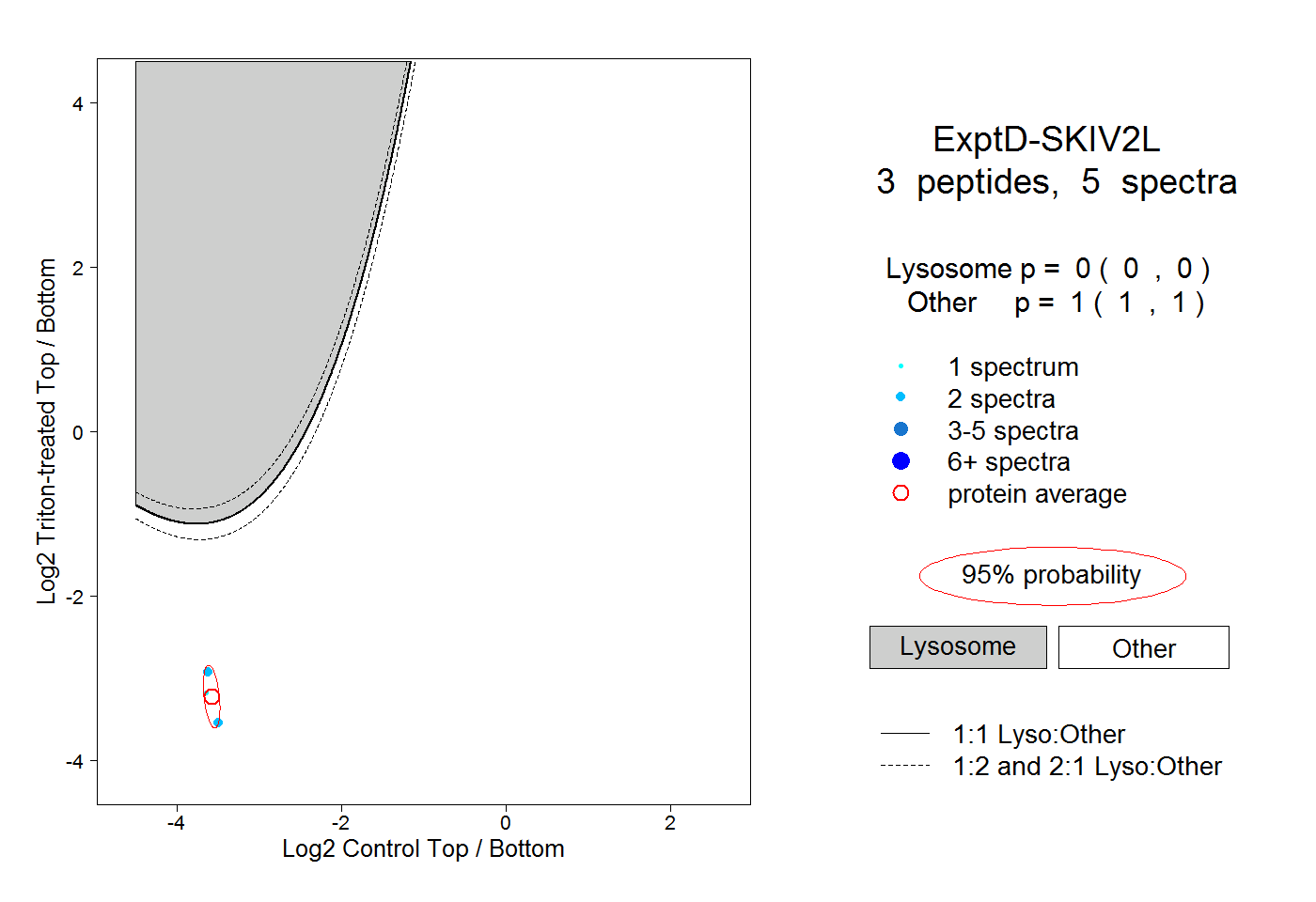 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |